Clear Sky Science · sv
Kartläggning av reglerande element i nukleotidskick via allel-specifik avläsning av tiled basredigering
Varför små DNA-förändringar kan spela roll för cancerbehandling
Cancerläkare förlitar sig i allt högre grad på smarta immunterapier som letar upp tumörceller genom att känna igen specifika markörer på deras yta. En av de bäst kända markörerna på leukemiceller är CD19, målet för kraftfulla CAR-T-cellsterapier. Ändå får vissa patienter återfall eftersom deras cancerceller tyst tappar eller dämpar denna markör och därmed undslipper behandlingen. Denna studie visar hur forskare nu kan zooma in på DNA-avsnitt som kontrollerar CD19 och ange vilka enskilda ”bokstäver” i dessa kontrollregioner som är viktiga för att CD19 ska vara synligt — och hur förändringar i bara några av dessa bokstäver kan hjälpa cancerceller att undkomma terapi. 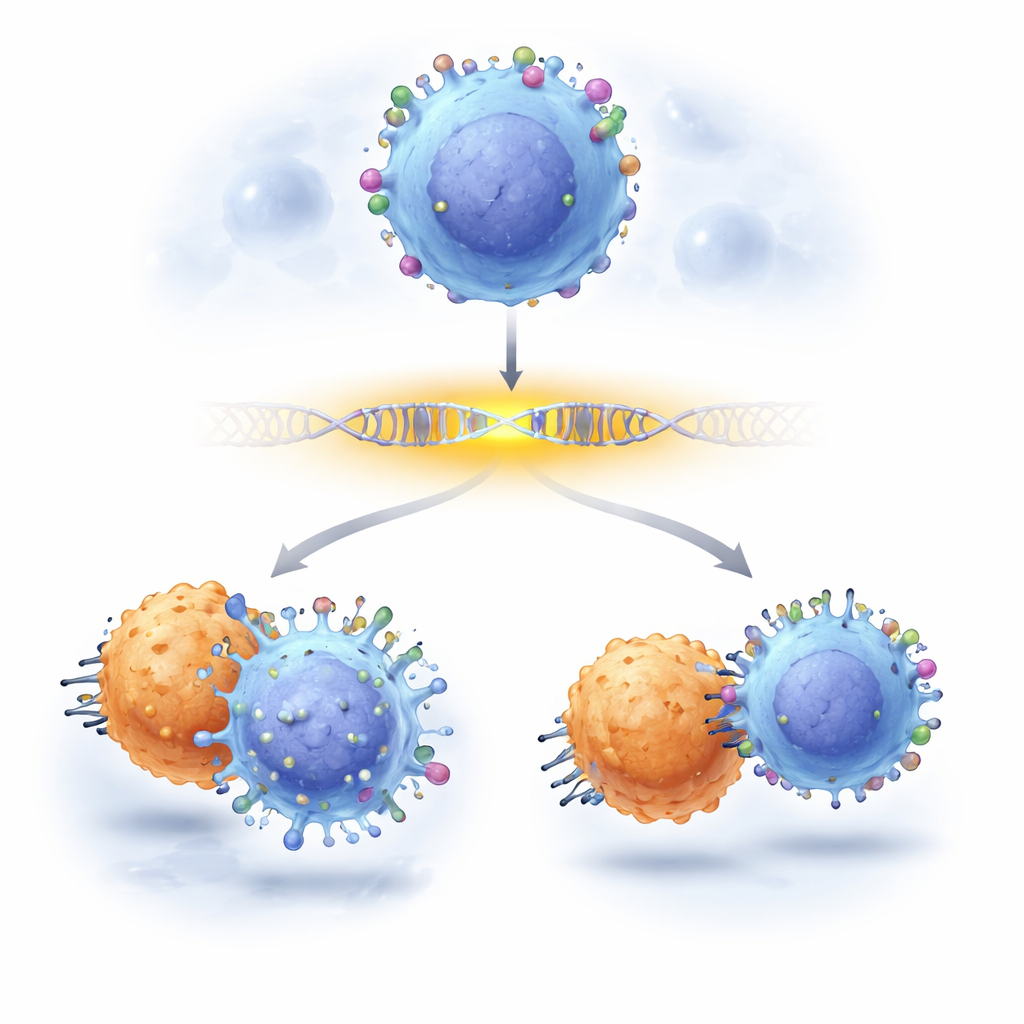
Läsa våra geners kontrollswitchar
Gener är inte bara på eller av; de styrs av närliggande DNA-switchar kallade enhancers som finjusterar hur mycket av ett visst protein en cell tillverkar. Många sjukdomsassocierade DNA-förändringar finns i dessa icke-kodande kontrollregioner snarare än i protein-kodande gener. Traditionella genetiska studier kan peka ut misstänkta regioner men har svårt att säga exakt vilka DNA-bokstäver inom dem som är avgörande eller hur de påverkar cellens beteende. För terapier som CD19 CAR-T-celler är detta gap viktigt: en subtil förändring i en kontrollswitch kan sänka CD19 tillräckligt för att cancerceller ska gömma sig, samtidigt som resten av cellens maskineri förblir intakt.
Använda molekylära pennor för att skriva om DNA en bokstav i taget
Forskarna byggde ett komplett experimentellt och beräkningsmässigt ramverk för att kartlägga dessa avgörande DNA-bokstäver med enastående precision. De fokuserade på en 346-bokstavslång enhancer precis uppströms om CD19-genen i leukemiceller. Med avancerade CRISPR-basredigerare — molekylära ”pennor” som kan byta enstaka DNA-bokstäver utan att klippa DNA:t — svepte de över denna enhancer med ett tätt bibliotek av guide-molekyler. Varje guide riktade sig mot en något annan plats, och tillsammans beströdde de miljontals celler med distinkta enkelbokstavsförändringar och små kombinationer av förändringar inom samma korta DNA-segment.
Koppla DNA-varianter till proteinnivåer i bulk
För att se hur varje redigerad DNA-version påverkade CD19 färgade teamet cellerna med en fluorescerande antikropp som lyser starkare när CD19-nivåerna är höga. De använde sedan en cellsorterare för att dela populationen i CD19-höga och CD19-låga grupper. Avgörande var att de, i stället för att bara räkna vilka guider som fanns, direkt sekvenserade den redigerade enhancer-regionen i varje grupp. Nya analysverktyg — CRISPR-Millipede och en anpassad version av DESeq2-mjukvaran — gjorde det möjligt att betrakta varje distinkta redigerade DNA-sekvens som sin egen variant och statistiskt sluta sig till vilka exakta enkelbokstavsförändringar som förskjöt celler mot lägre eller högre CD19. 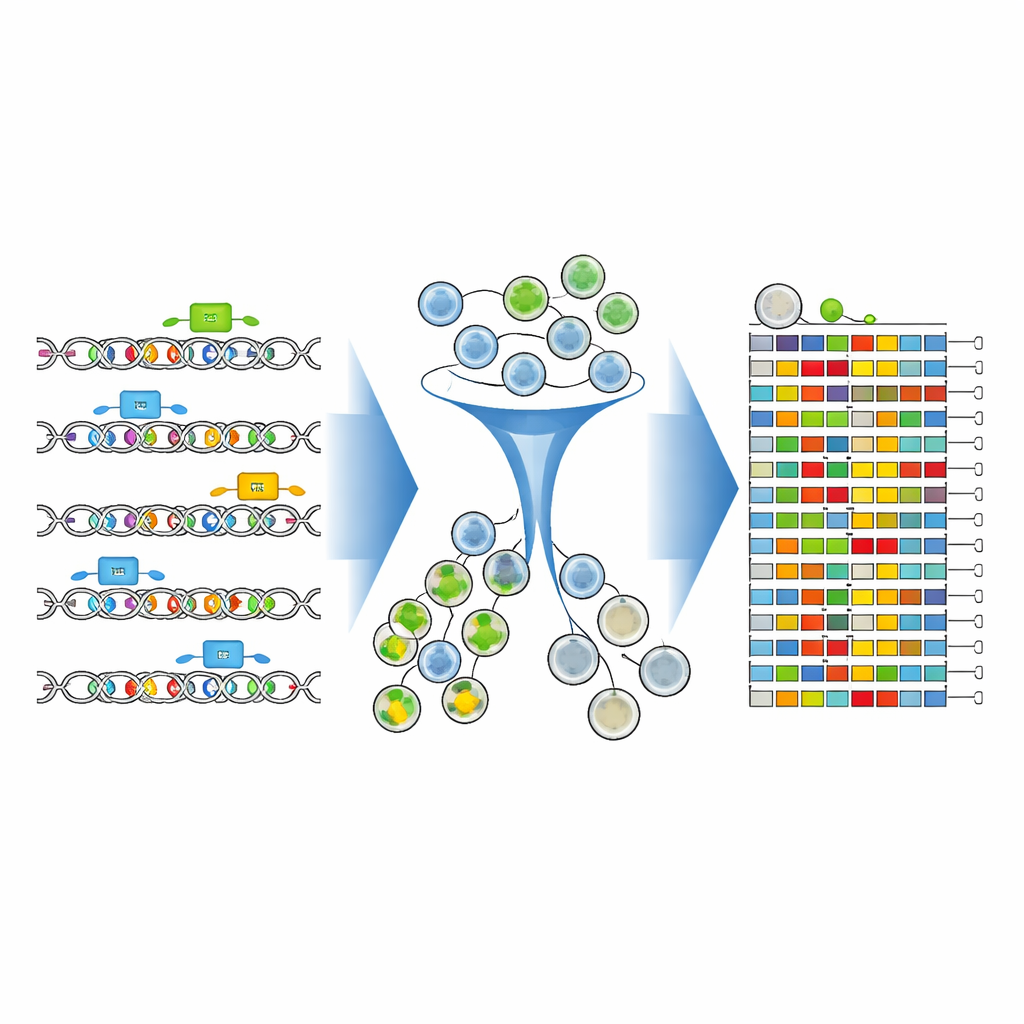
Hitta de viktiga protein-dockningsställena i enhancern
Med denna nukleotid-för-nukleotid-karta i handen överlappade forskarna sina resultat med kända bindningsmotif för transkriptionsfaktorer — proteiner som binder DNA för att skruva upp eller ner genuttryck. De fann att de mest påverkande bokstäverna klustrade inom platser som känns igen av faktorer som MYB, PAX5 och EBF1, vilka är viktiga regulatorer i B-celler. Genom att avsiktligt återskapa dessa specifika enhancer-mutationer och genom att inaktivera de motsvarande transkriptionsfaktorerna bekräftade de att skada dessa dockningsställen sänker CD19-nivåerna. De visade också att några uppenbara träffar från äldre, guide-räkningsbaserade metoder var falska positiva orsakade av den skrymmande redigerarmaskinerins närvaro på DNA snarare än av verkliga sekvensförändringar, och de konstruerade en nedbrytbar redigerare för att separera dessa effekter.
Hur små enhancerförändringar kan underminera CAR-T-terapi
Slutligen frågade teamet om dessa subtila regulatoriska justeringar faktiskt påverkar cancerbehandling. De blandade leukemiceller med och utan enhancer-mutationerna och exponerade dem för CD19 CAR-T-celler. Redigerade celler som bar särskilda enhancer-förändringar växte konsekvent ut sina oredigerade motsvarigheter under CAR-T-attack, vilket visade att måttliga reduktioner i CD19 — som drivs inte av att CD19-genen krossas utan av att dess enhancer förändras — var tillräckliga för att hjälpa cancerceller att överleva. Arbetet visar ett praktiskt, skalbart sätt att kartlägga orsak och verkan på enkelbokstavsnivå i genkontrollregioner och visar att icke-kodande varianter tyst kan styra framgång eller misslyckande för banbrytande immunterapier.
Citering: Becerra, B., Wittibschlager, S., Patel, Z.M. et al. Nucleotide-resolution mapping of regulatory elements via allelic readout of tiled base editing. Nat Commun 17, 3398 (2026). https://doi.org/10.1038/s41467-026-69918-8
Nyckelord: CRISPR-basredigering, genreglering, CD19 CAR-T-resistens, icke-kodande varianter, kartläggning av enhancer