Clear Sky Science · pt
Detecção e classificação de cromossomos com defeitos de coesão entre cromátides-irmãs usando modelos de detecção de objetos
Por que pequenas torções no DNA importam
Cada vez que uma célula se divide, ela precisa transmitir uma cópia exata de seu material genético. Para manter essas cópias juntas até o momento certo, as células dependem de uma “cola” molecular que mantém os cromossomos pareados lado a lado. Quando essa cola falha, os cromossomos podem se separar cedo demais, levando a genomas quebrados, distúrbios do desenvolvimento e câncer. O estudo descrito aqui trata de um problema muito prático: como identificar automaticamente, em imagens de microscópio, essas falhas sutis na cola, usando inteligência artificial moderna em vez de olhos humanos cansados.
Como os cromossomos permanecem juntos
Antes que uma célula se divida, cada cromossomo é copiado, de modo que existem duas fitas idênticas, conhecidas como cromátides-irmãs. Uma máquina proteica chamada coesina ajuda a manter essas irmãs pareadas até que a célula esteja pronta para separá-las. Se a coesina ou suas proteínas auxiliares falharem, as cromátides podem se afastar cedo demais. Um desses auxiliares é DDX11, uma enzima que desenrola o DNA e cujos defeitos estão ligados a uma condição humana rara chamada síndrome de Quebra de Varsóvia. Ao microscópio, células com problemas de coesão frequentemente mostram cromossomos cujas duas fitas estão estranhamente abertas ou divididas no centro, mas distinguir formas normais de anormais exige paciência e julgamento.
Por que verificações manuais não bastam
Tradicionalmente, pesquisadores espalham cromossomos em uma lâmina, coram-nos e então classificam pelo menos 50 a 100 por amostra manualmente. Cada cromossomo é julgado pelo formato e pela distância entre suas fitas-irmãs. Esse trabalho é lento, subjetivo e cansativo, o que aumenta o risco de erros e resultados inconsistentes entre cientistas. Esforços anteriores do mesmo grupo usaram aprendizado profundo para classificar imagens individuais de cromossomos, mas esses sistemas exigiam etapas separadas de software para recortar cromossomos isolados de imagens de microscopia lotadas e descartar sobreposições confusas. Esse tratamento extra das imagens ainda dependia fortemente de ajustes e limpeza manuais, impedindo uma automação verdadeiramente “apertar um botão”.
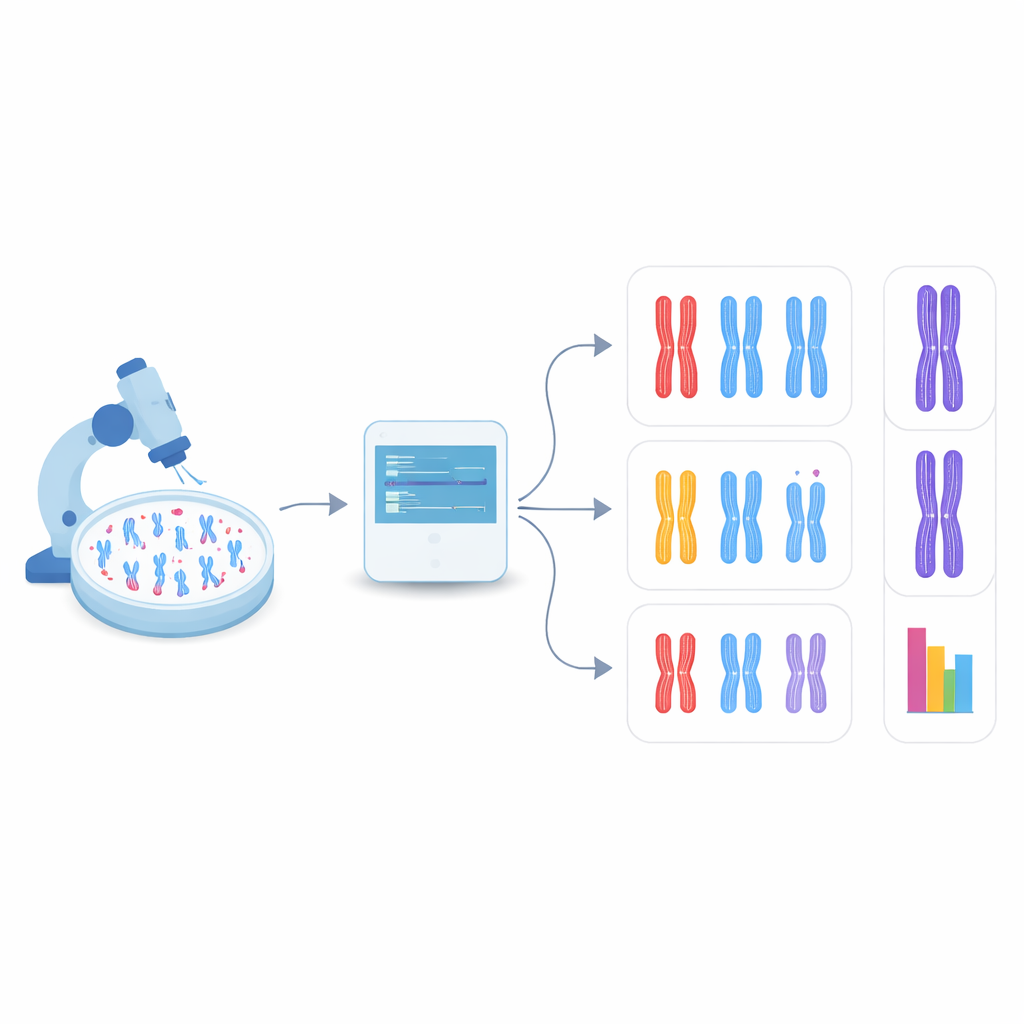
Deixar o computador localizar os cromossomos sozinho
No novo estudo, a equipe recorreu à detecção de objetos, um ramo da visão computacional que pode localizar e categorizar muitos itens dentro de uma única imagem. Eles se concentraram em uma família de modelos rápidos e amplamente usados chamados YOLO (sigla para “You Only Look Once”) junto com vários métodos concorrentes. Primeiro, criaram um sistema de teste modificando células humanas que não possuem DDX11 e, portanto, exibem fortes problemas de coesão, então prepararam imagens de microscópio desses cromossomos junto com os de células normais. Cada cromossomo visível nessas imagens foi delimitado com uma caixa e rotulado em uma das três categorias de forma: fortemente pareado, parcialmente separado ao longo dos braços, ou claramente dividido no centro. Esses rótulos feitos à mão serviram como material de ensino para os algoritmos.
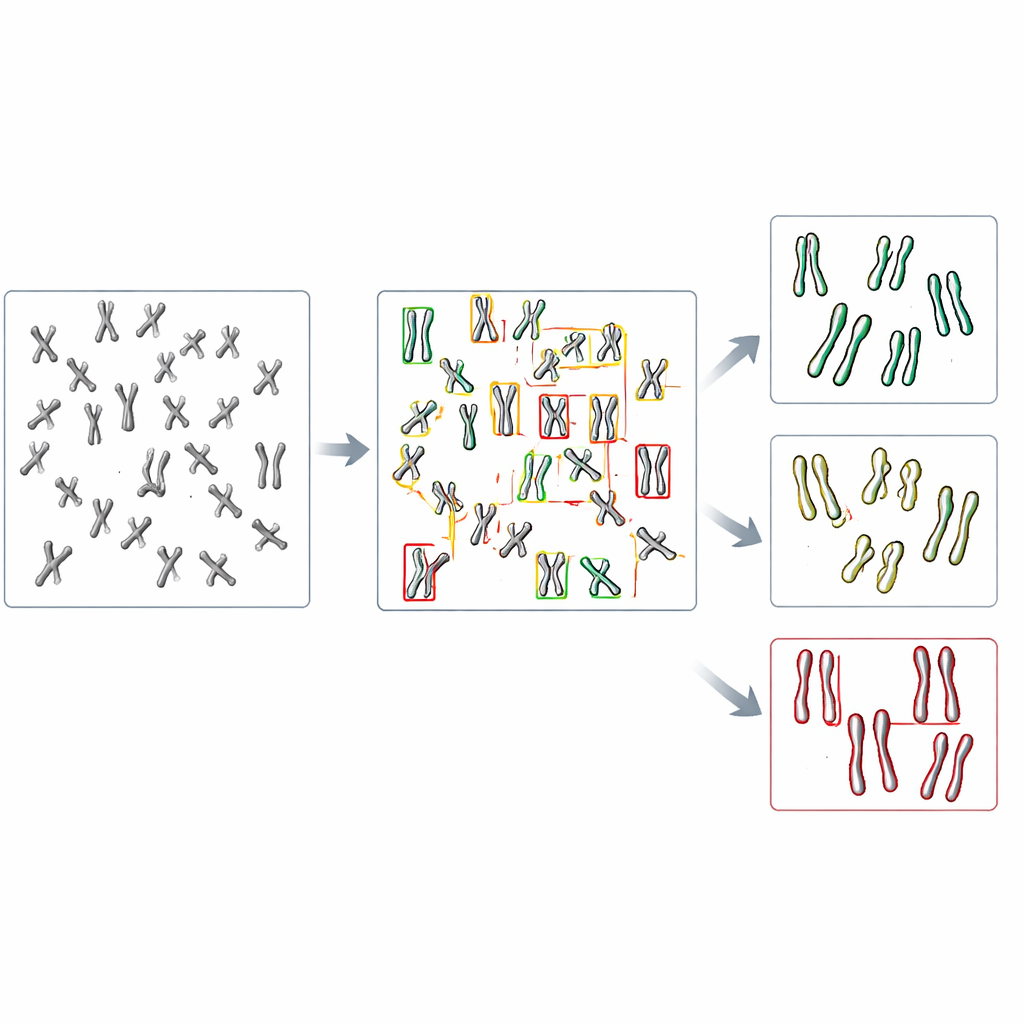
Ensinar a IA a ver diferenças sutis de forma
Os pesquisadores ajustaram vários modelos de detecção de objetos pré-treinados com pouco mais de mil cromossomos rotulados, reservando outras imagens para verificar o desempenho. Compararam quão bem cada modelo conseguia primeiro localizar cromossomos e depois atribuí-los à uma das três categorias de forma. Entre os sistemas testados, uma versão chamada YOLOv8 teve o melhor desempenho. Ela correspondeu corretamente aos rótulos humanos em quase nove de cada dez cromossomos, mesmo quando as diferenças entre categorias eram frequentemente bastante sutis. Importante: ao ser aplicada a imagens de células normais e deficientes em DDX11, a YOLOv8 reproduziu o padrão biológico chave observado por especialistas humanos: as células com defeito tinham muito menos cromossomos fortemente pareados e muitos mais com fitas-irmãs claramente separadas.
O que isso significa para trabalhos de laboratório futuros
O estudo mostra que um modelo de IA pode analisar espalhamentos integrais de cromossomos e sinalizar automaticamente defeitos de coesão sem etapas adicionais de recorte ou limpeza manual. Embora ainda haja espaço para melhorar o desempenho—especialmente para cromossomos sobrepostos e formas limítrofes— a abordagem já rivaliza com métodos anteriores que exigiam mais intervenção humana. Como os modelos foram construídos adaptando ferramentas de código aberto existentes e podem ser re-treinados com conjuntos de imagens modestos, laboratórios sem profunda expertise em computação poderiam desenvolver seus próprios sistemas personalizados. A longo prazo, estratégias semelhantes podem acelerar triagens de fármacos, ajudar a comparar muitos mutantes genéticos e se estender além da coesão para outras mudanças delicadas nos cromossomos que importam para a saúde humana.
Citação: Matsumoto, S., Sojo, M., Oshima, K. et al. Detection and classification of chromosomes with sister chromatid cohesion defects using object detection models. Sci Rep 16, 13719 (2026). https://doi.org/10.1038/s41598-026-43009-6
Palavras-chave: imagens de cromossomos, aprendizado de máquina, detecção de objetos, defeitos de coesão, YOLOv8