Clear Sky Science · ja
姉妹染色分体接着欠損を伴う染色体の検出と分類を物体検出モデルで行う研究
なぜDNAの小さな変化が重要なのか
細胞が分裂するたびに、その遺伝情報の正確なコピーを次へ渡す必要があります。これらのコピーを適切な時点まで一緒に保つために、細胞は対になった染色体を並べて保持する分子“のり”に頼っています。こののりがうまく働かないと、染色体が早期に分離し、ゲノムの破壊、発達障害、がんにつながることがあります。本研究は非常に実用的な問題に取り組んでいます。すなわち、顕微鏡画像の中でこうした微妙なのりの不具合を、人の目ではなく現代の人工知能を使って自動的に見つける方法です。
染色体はどうやって一緒にいるのか
細胞が分裂する前に、各染色体は複製され、姉妹染色分体と呼ばれる二つの同一の鎖ができます。コヒーシンというタンパク質複合体が、細胞がそれらを引き離す準備が整うまで姉妹を結びつけておく役割を果たします。コヒーシンやそれを助けるタンパク質が機能しなくなると、姉妹は早期に離れてしまいます。たとえばDDX11はDNAをほどく酵素で、その欠損はWarsaw Breakage症候群という稀な疾患に関連しています。顕微鏡では、接着に問題のある細胞は二本の鎖が中心で開いたり分かれたりしたように見えることが多いですが、正常と異常の形を判別するには忍耐と判断が必要です。
なぜ手作業のチェックだけでは不十分なのか
従来、研究者は染色体をスライドに展開して染色し、サンプルごとに少なくとも50〜100本の染色体を手作業で分類してきました。各染色体は形状や姉妹鎖の離開度合いで判断されます。この作業は遅く、主観的で疲れやすく、ミスや研究者間の結果のばらつきを招きやすいという問題があります。同じ研究グループの以前の取り組みでは、深層学習を用いて個々の染色体画像を分類していましたが、それらのシステムは混み合った顕微鏡画像から単一染色体を切り出したり、重なり合いを除外したりするために別のソフトウェア工程を必要としていました。その追加の画像処理は依然として人手での調整やクリーンアップに大きく依存しており、真の「ボタン一つで動く」自動化を阻んでいました。
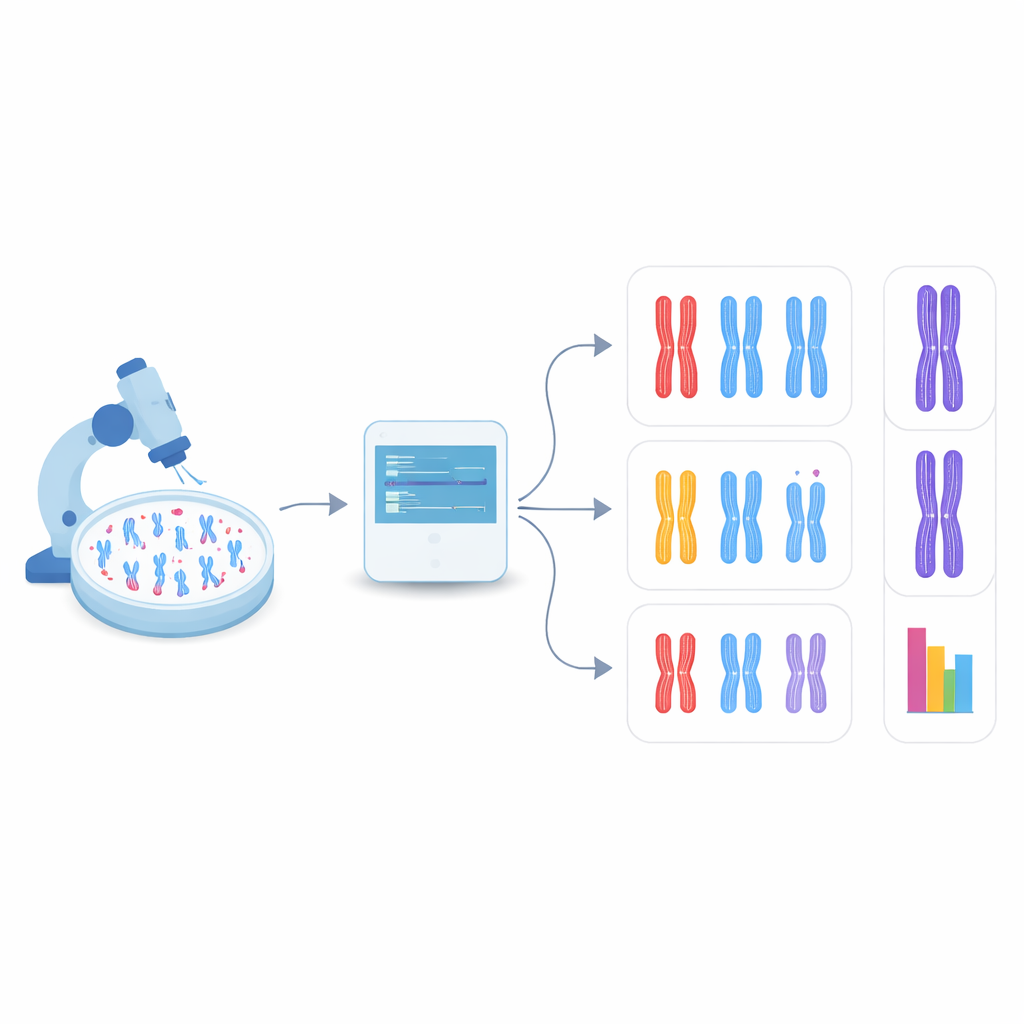
コンピュータに染色体を自分で見つけさせる
新しい研究では、物体検出という、単一画像内の多数の対象を同時に検出・分類できるコンピュータビジョンの分野に着目しました。研究者らは高速で広く使われるYOLO(You Only Look Onceの略)系のモデルと、いくつかの競合手法に注目しました。まず、DDX11を欠損させて強い接着不良を示すように改変したヒト細胞を用意し、正常細胞のものと合わせて染色体の顕微鏡画像を作成しました。これらの画像に写る各染色体にはバウンディングボックスを付け、形状を三つのカテゴリ(密に結合したもの、腕に沿って部分的に離れたもの、中心で明らかに分かれたもの)にラベリングしました。これら手作業のラベルがアルゴリズムへの学習素材となりました。
AIに微妙な形の違いを教える
研究チームは、事前学習済みの複数の物体検出モデルを約千点のラベル付き染色体で微調整し、残りの画像は性能チェック用に取っておきました。それぞれのモデルがまず染色体を検出できるか、次に三つの形カテゴリに正しく分類できるかを比較しました。テストされたシステムの中では、YOLOv8というバージョンが最も良い成績を示しました。カテゴリー間の差が非常に微妙な場合でも、ほぼ9割近くの染色体で人のラベルと一致しました。重要なのは、正常細胞とDDX11欠損細胞の画像に適用したとき、YOLOv8が人間の専門家が見る重要な生物学的パターンを再現したことです。欠陥のある細胞では密に結合した染色体が著しく少なく、明らかに分かれたものが多く観察されました。
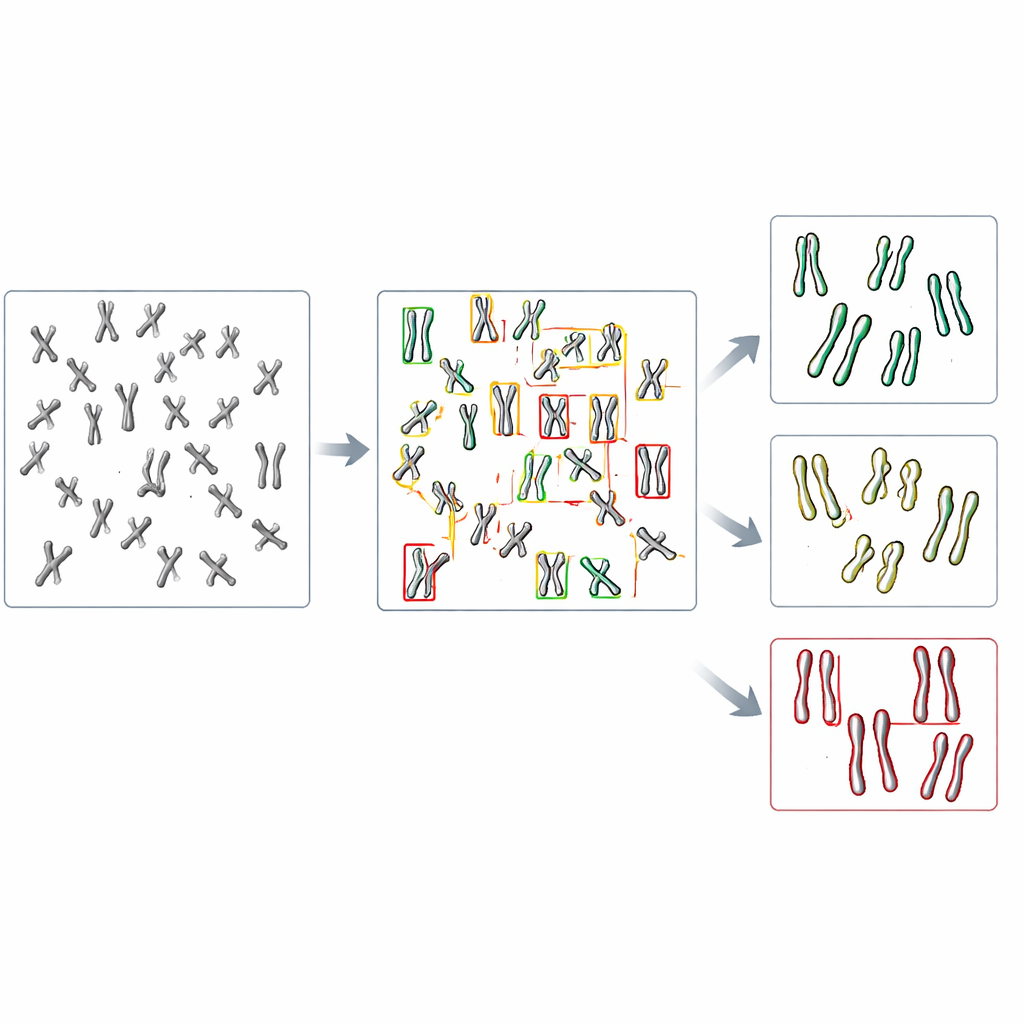
今後の実験室作業にとっての意味
この研究は、AIモデルがフルの染色体スプレッドをスキャンして、追加の切り出し工程や手動でのクリーンアップなしに接着欠損を自動で検出できることを示しています。重なり合った染色体や境界的な形状では改善の余地がありますが、このアプローチは既存の人手介入を多く必要とした従来手法に匹敵する成果を既に示しています。モデルは既存のオープンソースツールを適応して構築され、比較的少数の画像セットで再学習できるため、深い計算機専門知識を持たない研究室でも独自のシステムを作れる可能性があります。長期的には、同様の戦略が薬剤スクリーニングの高速化、多数の遺伝子変異体の比較、さらには接着以外の微妙な染色体変化の検出にも役立ち、人の健康に関わるさまざまな課題の解決に寄与するでしょう。
引用: Matsumoto, S., Sojo, M., Oshima, K. et al. Detection and classification of chromosomes with sister chromatid cohesion defects using object detection models. Sci Rep 16, 13719 (2026). https://doi.org/10.1038/s41598-026-43009-6
キーワード: 染色体イメージング, 機械学習, 物体検出, 接着欠損, YOLOv8