Clear Sky Science · zh
基于泛基因组设计的菌株特异性引物实现对人体微生物干预试验中细菌的精确监测
为什么追踪“有益”细菌很重要
我们常听到的许多细菌是麻烦制造者,但也有一些是默默的帮手,它们把牛奶变成酸奶、保护我们的皮肤,甚至可能缓解气道炎症。这些“有益细菌”以益生菌或更严格监管的活体生物治疗产品形式出售,正被用于皮肤问题、过敏、肠道疾病等的人体试验。然而,一个基础性的问题却出奇地难以回答:当我们给人特定的细菌菌株时,是否能确凿证明就是这个精确的菌株在体内存活并定植,而不是其近亲?本研究提出了一种利用日益增长的基因组数据来高精度追踪个体菌株的新方法。
从混合微生物到单个菌株
益生菌产品很少只是泛泛地包含“细菌”;它们包含精心挑选的菌株,比如特定版本的Lacticaseibacillus rhamnosus GG或Lactiplantibacillus plantarum WCFS1。这些密切相关的菌株在与免疫系统的相互作用或在皮肤与咽喉组织的粘附能力上可能存在差异,因此研究人员和监管者希望确切知道处理后哪种菌株存在。传统方法,如在选择性培养基上培养细菌,只能告诉我们广义群体——例如乳酸菌总量——且在有益菌株数量被其他细菌压倒时常常失效。更高端的方案,如给菌株打上荧光标签或DNA条形码,会将其变为转基因生物,这在食品或人体治疗中通常不可接受。挑战在于在不改变菌株本身的前提下区分几乎相同的菌株。
在泛基因组中挖掘独特的遗传指纹
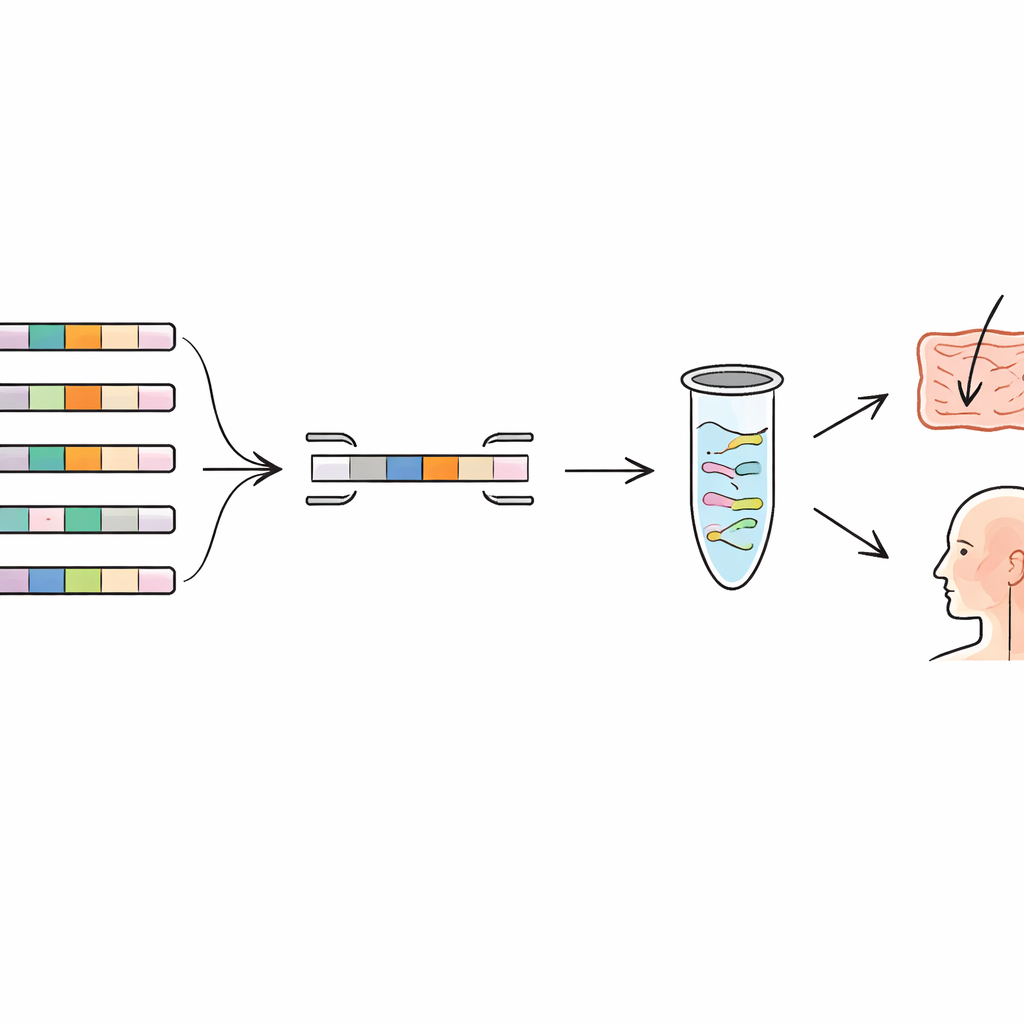
作者们转向“泛基因组”概念,即同一物种多个基因组中基因的全部集合。有些基因是所有成员共有的(核心基因组),而另一些仅在某些菌株中存在(可变部分)。通过比较若干乳酸菌物种和一种常见口腔细菌的数百个基因组,他们寻找那些只出现在单一菌株、而在任何已知近缘中均未出现的基因。这些罕见基因就像遗传指纹。团队构建了一个生物信息学流水线,自动组装泛基因组、去除高度相似的重复基因组,并标记菌株特异性基因。随后他们又将这些候选基因与更广泛的基因组数据库进行交叉验证,以确保没有隐藏在其他物种中的相似序列。
设计精确的分子“条形码扫描器”
一旦识别出菌株特异性基因,下一步就是围绕这些基因构建高特异性的分子检测工具。研究人员设计了短小的DNA片段,称为引物,仅能与这些独特基因结合。在称为定量PCR(qPCR)的技术中,这些引物就像条形码扫描器,只复制并检测目标菌株的DNA。团队为六个跨不同物种的菌株创建并优化了引物集,包含常用益生菌和从人体分离出的潜在新候选菌株。在实验室中,他们不仅在目标菌株上测试每组引物,还在同一物种的数个近缘菌株上进行检测。结果显示只有目标菌株产生强烈扩增,而其他菌株的信号极微,证实了所选遗传指纹确实具有独特性。
在皮肤和呼吸道上追踪益生菌
为检验该方法在人群中的可行性,作者将这些引物应用于三项安慰剂对照的人体干预试验样本。在一项研究中,志愿者使用含有两种益生菌菌株的面霜;在其他研究中,人们接受了益生菌咽喉喷雾或咀嚼片。使用新的qPCR检测,科学家能够可靠地在受试者的皮肤和上呼吸道中检测到添加的菌株,而在安慰剂组几乎未见到这些菌株。他们还观察到使用期间信号上升、停止后信号衰减的模式,清晰地呈现了短暂定植的过程。在少数情况下,对照组出现低水平信号,这提醒研究人员需考虑自然背景菌群以及在细菌数量较低的部位非常微量污染的风险。
这对未来微生物组疗法意味着什么
通俗地说,这项工作展示了如何在不对细菌进行基因改造的情况下建立非常灵敏的“菌株雷达”。通过利用大规模基因组比较揭示的细微遗传差异,科学家可以设计出在众多近似菌株中识别出单一益生菌菌株的qPCR检测方法。这使得回答一些实际问题变得更容易:该菌株能否度过产品的货架期?它是否到达目标部位?它停留了多长时间,浓度如何?由于该方法透明、成本低且可扩展到其他物种,它有望成为设计和测试下一代益生菌与活体生物治疗产品的标准工具,为快速发展的基于微生物组的干预领域带来更多严谨性与安全性。
引用: Eilers, T., Delanghe, L., De Boeck, I. et al. Pangenome-based design of strain-specific primers enables precise monitoring of bacteria in human microbiome intervention trials. Sci Rep 16, 11274 (2026). https://doi.org/10.1038/s41598-026-41449-8
关键词: 益生菌, 微生物组, 菌株追踪, qPCR, 泛基因组分析