Clear Sky Science · de
Pangenombasierte Gestaltung stammspezifischer Primer ermöglicht präzises Monitoring von Bakterien in Human‑Mikrobiom‑Interventionsstudien
Warum die Verfolgung nützlicher Keime wichtig ist
Viele der Bakterien, von denen wir hören, sind Problemverursacher, aber einige sind stille Helfer, die Milch zu Joghurt verwandeln, unsere Haut schützen und möglicherweise Entzündungen in den Atemwegen dämpfen. Diese „guten Bakterien“ werden als Probiotika oder als streng regulierte lebende biotherapeutische Produkte verkauft und werden inzwischen in Humanstudien zu Hautproblemen, Allergien, Darmbeschwerden und mehr getestet. Eine grundlegende Frage ist jedoch überraschend schwer zu beantworten: Wenn wir Menschen einen bestimmten Bakterienstamm verabreichen, können wir dann tatsächlich nachweisen, dass genau dieser Stamm im Körper überlebt und sich ansiedelt — und nicht nur enge Verwandte? Diese Studie stellt einen neuen Weg vor, individuelle Bakterienstämme mit hoher Präzision zu verfolgen, indem die wachsende Menge verfügbarer Genomdaten genutzt wird.
Von gemischten Mikroben zu einzelnen Stämmen
Probiotische Produkte enthalten selten einfach nur „Bakterien“ im Allgemeinen; sie enthalten gezielt ausgewählte Stämme, etwa eine bestimmte Variante von Lacticaseibacillus rhamnosus GG oder Lactiplantibacillus plantarum WCFS1. Diese eng verwandten Stämme können sich darin unterscheiden, wie sie mit unserem Immunsystem interagieren oder wie gut sie an Haut‑ oder Rachengewebe haften, weshalb Forschende und Aufsichtsbehörden genau wissen wollen, welcher Stamm nach einer Behandlung vorhanden ist. Traditionelle Methoden, wie das Anzüchten von Bakterien auf selektiven Nährmedien, liefern nur Informationen über breite Gruppen — etwa die Gesamtzahl der Milchsäurebakterien — und versagen oft, wenn hilfreiche Stämme von anderen überwuchert werden. Hightech‑Lösungen, etwa das Markieren von Stämmen mit Fluoreszenzmarkern oder DNA‑Barcodes, würden die Organismen genetisch verändern und wären für Lebensmittel oder Therapien beim Menschen häufig nicht akzeptabel. Die Herausforderung besteht darin, fast identische Stämme zu unterscheiden, ohne sie zu verändern.
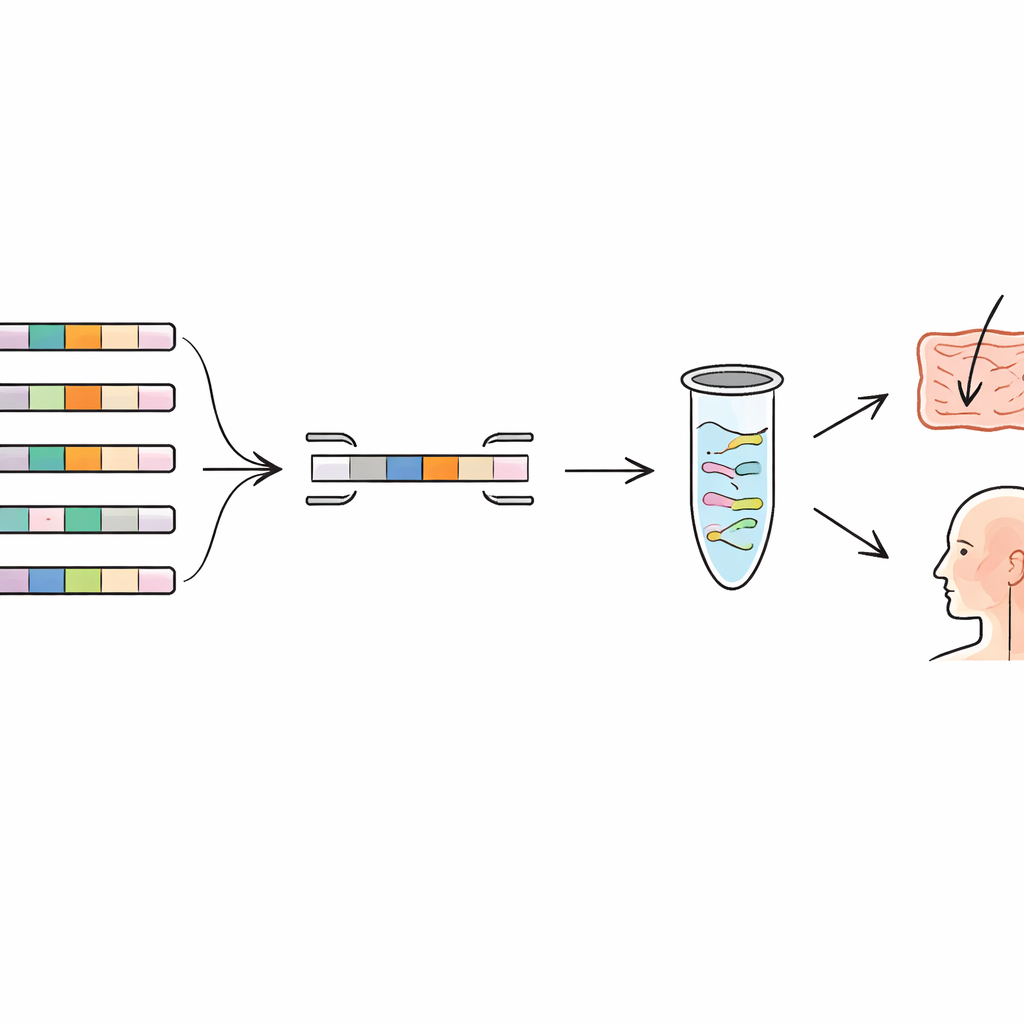
Das Pangenom nach einzigartigen genetischen Fingerabdrücken durchsuchen
Die Autorinnen und Autoren griffen auf das Konzept des „Pangenoms“ zurück, der Gesamtheit aller Gene, die in vielen Genomen derselben Spezies vorkommen. Einige Gene werden von allen Mitgliedern geteilt (das Core‑Genom), andere kommen nur in bestimmten Stämmen vor (der akzessorische Anteil). Durch den Vergleich von Hunderten von Genomen mehrerer Spezies der Milchsäurebakterien und eines häufigen Mundbakteriums suchten sie nach Genen, die nur in einem Stamm und in keinem anderen bekannten Verwandten vorkommen. Diese seltenen Gene wirken wie genetische Fingerabdrücke. Das Team baute eine Bioinformatik‑Pipeline, die automatisch das Pangenom zusammenstellt, nahezu identische Doppelungen entfernt und stamm‑einzigartige Gene markiert. Diese Kandidaten wurden anschließend gegen umfangreichere Genom‑Datenbanken geprüft, um sicherzustellen, dass ähnliche Sequenzen nicht bei anderen Arten versteckt sind.
Präzise molekulare „Barcode‑Scanner“ entwerfen
Sobald stamm‑einzigartige Gene identifiziert waren, bestand der nächste Schritt darin, hochspezifische molekulare Tests darum herum zu entwickeln. Die Forschenden entwarfen kurze DNA‑Abschnitte, sogenannte Primer, die nur an diese einzigartigen Gene binden. In einer Technik, die als quantitative PCR (qPCR) bekannt ist, wirken diese Primer wie Barcode‑Scanner, die nur DNA des Zielstamms vervielfältigen und nachweisen. Das Team entwickelte und optimierte Primer für sechs Stämme aus verschiedenen Arten, darunter weit verbreitete Probiotika und neue Kandidaten, die aus dem menschlichen Körper isoliert wurden. Im Labor testeten sie jedes Primerset nicht nur an seinem vorgesehenen Stamm, sondern auch an mehreren eng verwandten Stämmen derselben Art. Die Tests zeigten starke Amplifikation nur für den Zielstamm und minimale Signale bei den anderen, was bestätigte, dass die gewählten genetischen Fingerabdrücke tatsächlich unterscheidbar waren.
Probiotika auf der Haut und in den Atemwegen verfolgen
Um zu prüfen, ob der Ansatz bei Menschen funktioniert, wendeten die Autorinnen und Autoren ihre Primer auf Proben aus drei placebokontrollierten Human‑Interventionsstudien an. In einer Studie verwendeten Freiwillige eine Gesichtscreme mit zwei probiotischen Stämmen; in anderen erhielten Personen ein probiotisches Rachenspray oder ein lutschbares Tablettenpräparat. Mit den neuen qPCR‑Tests konnten die Wissenschaftlerinnen und Wissenschaftler die zugesetzten Stämme zuverlässig auf der Haut und in den oberen Atemwegen der behandelten Teilnehmenden nachweisen, während sie in den Placebo‑Gruppen so gut wie nie auftauchten. Sie beobachteten außerdem, wie das Signal während der Anwendung anstieg und nach Absetzen der Behandlung wieder abnahm, was ein klares Bild temporärer Besiedlung ergab. In wenigen Fällen traten in den Kontrollen sehr schwache Signale auf, was die Forschenden daran erinnert, natürliche Hintergrundbakterien und das Risiko minimaler Kontamination — besonders an Körperstellen mit niedrigen Bakterienzahlen — zu berücksichtigen.
Was das für künftige Mikrobiom‑Therapien bedeutet
Alltagsverständlich zeigt diese Arbeit, wie sich ein sehr scharfes „Stamm‑Radar“ bauen lässt, ohne die Bakterien selbst genetisch zu verändern. Indem subtile genetische Unterschiede genutzt werden, die durch groß angelegte Genomvergleiche ans Licht kommen, können Forschende qPCR‑Tests entwickeln, die einen Probiotika‑Stamm aus einer Menge nahezu identischer Verwandter herausfiltern. Das erleichtert es erheblich, praktische Fragen zu beantworten: Überlebte der Stamm die Lagerung des Produkts? Erreichte er die Zielregion im Körper? Wie lange blieb er dort und in welcher Menge? Da die Methode transparent, kostengünstig und auf andere Arten anpassbar ist, kann sie zu einem Standardwerkzeug bei der Entwicklung und Prüfung der nächsten Generation von Probiotika und lebenden Biotherapeutika werden und so mehr Strenge und Sicherheit in das schnell wachsende Feld mikrobiombasierter Interventionen bringen.
Zitation: Eilers, T., Delanghe, L., De Boeck, I. et al. Pangenome-based design of strain-specific primers enables precise monitoring of bacteria in human microbiome intervention trials. Sci Rep 16, 11274 (2026). https://doi.org/10.1038/s41598-026-41449-8
Schlüsselwörter: Probiotika, Mikrobiom, Stammverfolgung, qPCR, Pangenom‑Analyse