Clear Sky Science · pt
Design baseado em pangenoma de primers específicos por linhagem permite monitoramento preciso de bactérias em ensaios de intervenção no microbioma humano
Por que rastrear microrganismos benéficos importa
Muitas das bactérias de que ouvimos falar são problemáticas, mas algumas são auxiliares discretos que transformam leite em iogurte, protegem nossa pele e podem até reduzir inflamação nas vias aéreas. Essas “boas bactérias” são comercializadas como probióticos ou como produtos bioterapêuticos vivos mais estritamente regulados, e agora estão sendo testadas em ensaios humanos para problemas de pele, alergias, distúrbios intestinais e mais. Ainda assim, uma pergunta básica é surpreendentemente difícil de responder: quando administramos a uma pessoa uma linhagem bacteriana específica, podemos realmente provar que exatamente essa linhagem sobreviveu e se estabeleceu no corpo, em vez de apenas seus parentes próximos? Este estudo apresenta uma nova maneira de rastrear linhagens bacterianas individuais com alta precisão, usando a crescente disponibilidade de dados genômicos.
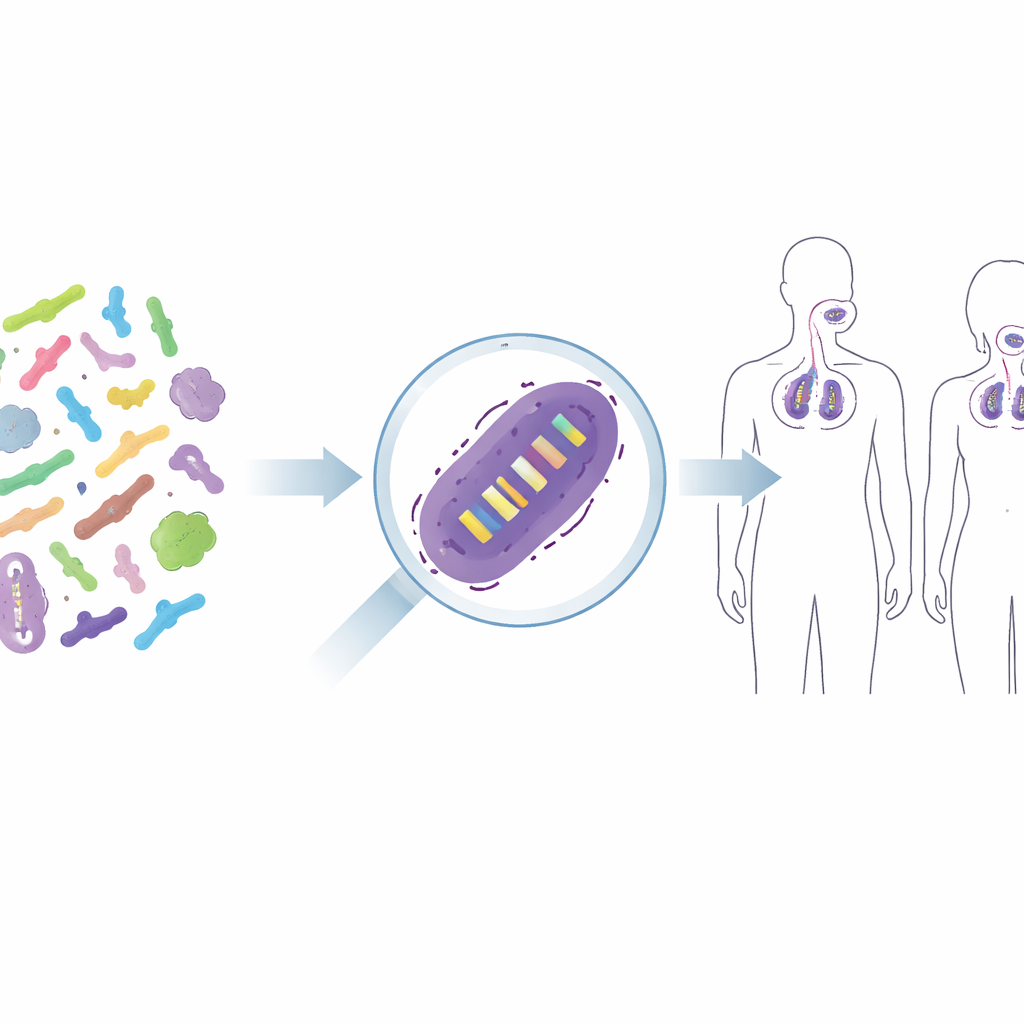
De micróbios mistos a linhagens individuais
Produtos probióticos raramente contêm apenas “bactérias” de forma abstrata; eles contêm linhagens escolhidas cuidadosamente, como uma versão particular de Lacticaseibacillus rhamnosus GG ou Lactiplantibacillus plantarum WCFS1. Essas linhagens intimamente relacionadas podem diferir na forma como interagem com nosso sistema imunológico ou na capacidade de aderir à pele ou à mucosa da garganta, por isso pesquisadores e reguladores querem saber exatamente qual linhagem está presente após o tratamento. Métodos tradicionais, como cultivar bactérias em meios seletivos, informam apenas sobre grupos amplos — como o total de bactérias láticas — e frequentemente falham quando as linhagens úteis estão em menor número que outras. Soluções mais sofisticadas, como marcar linhagens com proteínas fluorescentes ou códigos de barras de DNA, transformariam-nas em organismos geneticamente modificados, o que costuma ser inaceitável para alimentos ou terapias humanas. O desafio é distinguir linhagens quase idênticas sem alterá‑las.
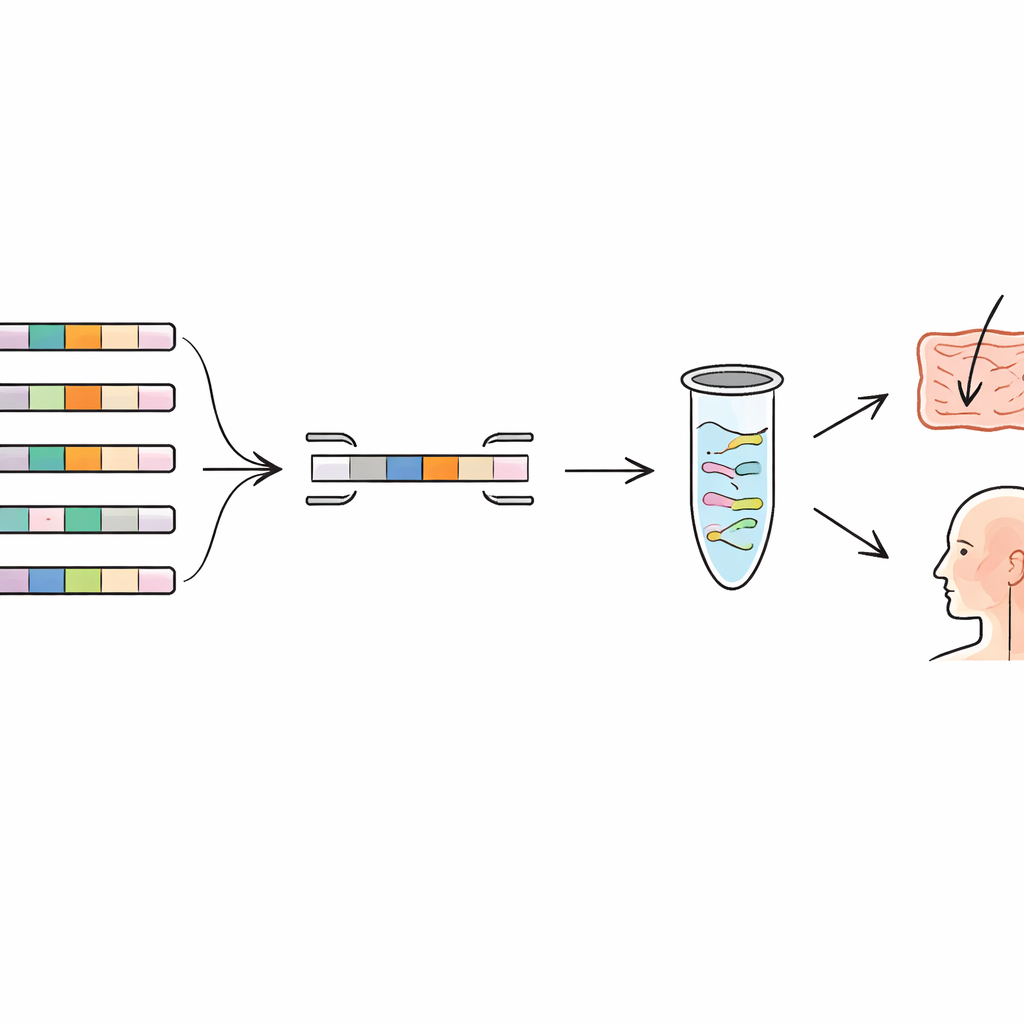
Minerando o pangenoma por impressões genéticas únicas
Os autores recorreram ao conceito de “pangenoma”, a coleção completa de genes encontrada entre muitos genomas da mesma espécie. Alguns genes são compartilhados por todos os membros (o núcleo), enquanto outros estão presentes apenas em certas linhagens (a parte acessória). Comparando centenas de genomas de várias espécies de bactérias láticas e de uma bactéria comum da boca, eles buscaram genes que aparecem em apenas uma linhagem e não em qualquer outro parente conhecido. Esses genes raros atuam como impressões genéticas. A equipe construiu um pipeline bioinformático que monta automaticamente o pangenoma, remove genomas quase idênticos duplicados e sinaliza genes exclusivos de linhagem. Em seguida, verificaram esses candidatos contra bancos de dados genômicos mais amplos para garantir que sequências semelhantes não estivessem escondidas em outras espécies.
Projetando “leitores de código de barras” moleculares precisos
Uma vez identificados os genes exclusivos de cada linhagem, o próximo passo foi construir testes moleculares altamente específicos em torno deles. Os pesquisadores desenharam pequenos trechos de DNA, chamados primers, que se ligam apenas a esses genes únicos. Em uma técnica conhecida como reação em cadeia da polimerase quantitativa (qPCR), esses primers funcionam como leitores de código de barras, copiando e detectando apenas o DNA da linhagem alvo. A equipe criou e otimizou conjuntos de primers para seis linhagens de diferentes espécies, incluindo probióticos amplamente usados e novos candidatos isolados do corpo humano. No laboratório, testaram cada conjunto de primers não apenas na linhagem pretendida, mas também em várias linhagens intimamente relacionadas da mesma espécie. Os testes mostraram forte amplificação apenas para a linhagem alvo, com sinal mínimo nas outras, confirmando que as impressões genéticas escolhidas eram realmente distintivas.
Acompanhando probióticos na pele e nas vias aéreas
Para saber se essa abordagem funciona em pessoas reais, os autores aplicaram seus primers em amostras de três ensaios de intervenção humana controlados por placebo. Em um estudo, voluntários usaram um creme facial contendo duas linhagens probióticas; em outros, pessoas receberam um spray faríngeo probiótico ou um comprimido mastigável. Usando os novos testes de qPCR, os cientistas puderam detectar de forma confiável as linhagens adicionadas na pele e no trato respiratório superior dos participantes tratados, enquanto quase nunca as encontravam nos grupos placebo. Também observaram como o sinal aumentou durante o uso e diminuiu após a suspensão do tratamento, fornecendo um retrato claro de colonização temporária. Em alguns casos surgiram sinais de baixo nível nos controles, lembrando os pesquisadores de considerar bactérias de fundo naturais e o risco de contaminação muito pequena, especialmente em locais do corpo com baixas quantidades bacterianas.
O que isso significa para futuras terapias do microbioma
Em termos práticos, este trabalho mostra como construir um “radar de linhagem” muito acurado sem manipular geneticamente as próprias bactérias. Ao explorar diferenças genéticas sutis reveladas por comparações genômicas em larga escala, cientistas podem desenvolver testes de qPCR que distinguem uma linhagem probiótica em meio a um grupo de quase idênticas. Isso facilita responder a perguntas práticas: a linhagem sobreviveu à vida de prateleira do produto? Alcançou o local alvo no corpo? Quanto tempo permaneceu e em que níveis? Por ser um método transparente, de baixo custo e adaptável a outras espécies, ele pode se tornar uma ferramenta padrão para projetar e testar probióticos de próxima geração e bioterapêuticos vivos, trazendo mais rigor e segurança ao campo em rápido crescimento das intervenções baseadas no microbioma.
Citação: Eilers, T., Delanghe, L., De Boeck, I. et al. Pangenome-based design of strain-specific primers enables precise monitoring of bacteria in human microbiome intervention trials. Sci Rep 16, 11274 (2026). https://doi.org/10.1038/s41598-026-41449-8
Palavras-chave: probióticos, microbioma, rastreamento de linhagem, qPCR, análise de pangenoma