Clear Sky Science · it
Progettazione di primer specifici per ceppi basata sul pangenoma consente il monitoraggio preciso dei batteri negli studi di intervento sul microbioma umano
Perché è importante tracciare i germi utili
Molti dei batteri di cui sentiamo parlare sono fonte di problemi, ma alcuni sono aiutanti discreti che trasformano il latte in yogurt, proteggono la nostra pelle e possono persino ridurre l’infiammazione delle vie aeree. Questi “batteri buoni” vengono venduti come probiotici o come prodotti bioterapeutici vivi soggetti a normative più rigide, e oggi vengono testati in studi umani per problemi della pelle, allergie, disturbi intestinali e altro. Tuttavia una domanda di base è sorprendentemente difficile da rispondere: quando somministriamo a una persona un ceppo batterico specifico, possiamo davvero dimostrare che quel preciso ceppo sopravvive e si insedia nell’organismo, e non solo i suoi parenti stretti? Questo studio presenta un nuovo modo per monitorare singoli ceppi batterici con elevata precisione, sfruttando la crescente disponibilità di dati genomici.
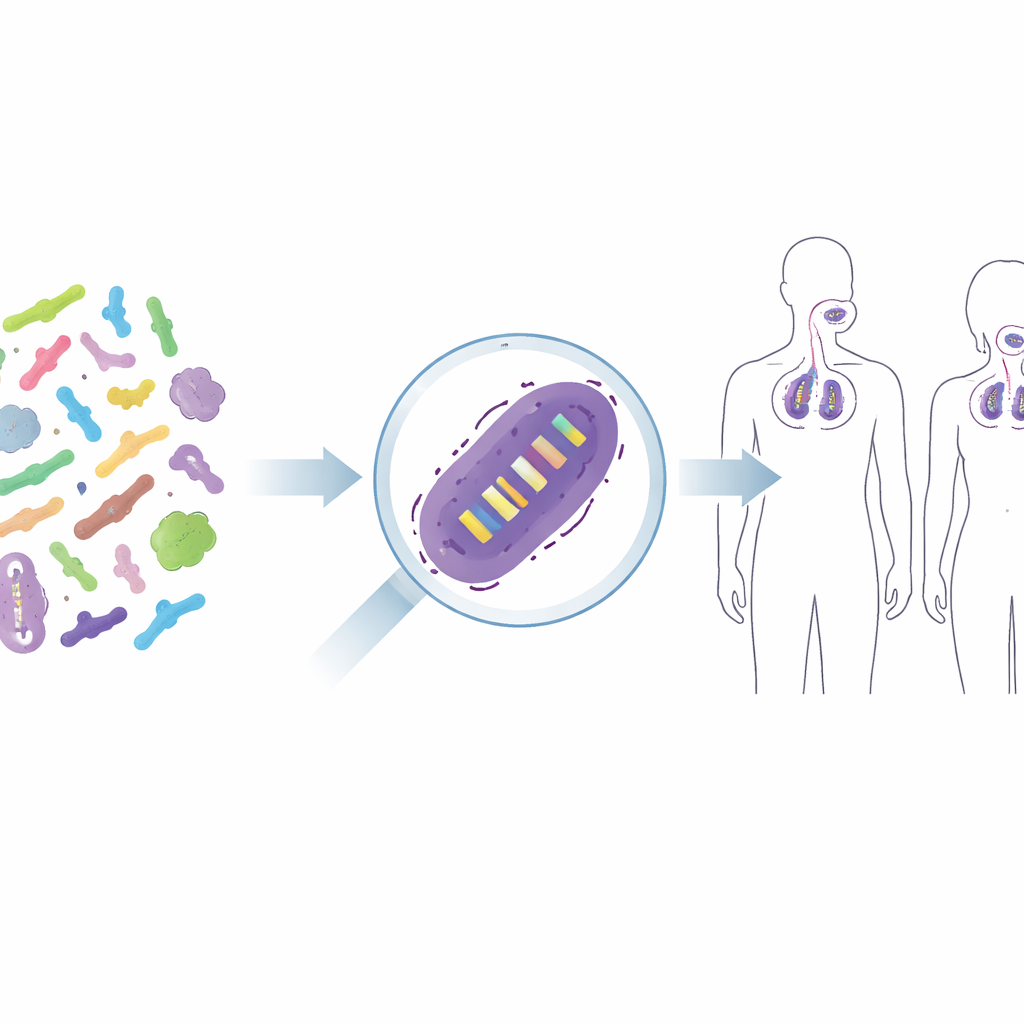
Da microbi misti a ceppi individuali
I prodotti probiotici raramente contengono semplicemente “batteri” in senso astratto; contengono ceppi scelti con cura, come una specifica versione di Lacticaseibacillus rhamnosus GG o di Lactiplantibacillus plantarum WCFS1. Questi ceppi strettamente correlati possono differire nel modo in cui interagiscono con il nostro sistema immunitario o nella loro capacità di aderire alla pelle o alle mucose della gola, perciò ricercatori e regolatori vogliono sapere esattamente quale ceppo è presente dopo il trattamento. I metodi tradizionali, come la coltura su terreni selettivi, informano solo su gruppi ampi—per esempio il totale dei batteri lattici—e spesso falliscono quando i ceppi utili sono numericamente sopraffatti da altri. Soluzioni più tecnologiche, come marchiare i ceppi con marker fluorescenti o codici a barre DNA, li trasformerebbero in organismi geneticamente modificati, cosa spesso non accettabile per alimenti o terapie umane. La sfida è distinguere ceppi quasi identici senza alterarli.
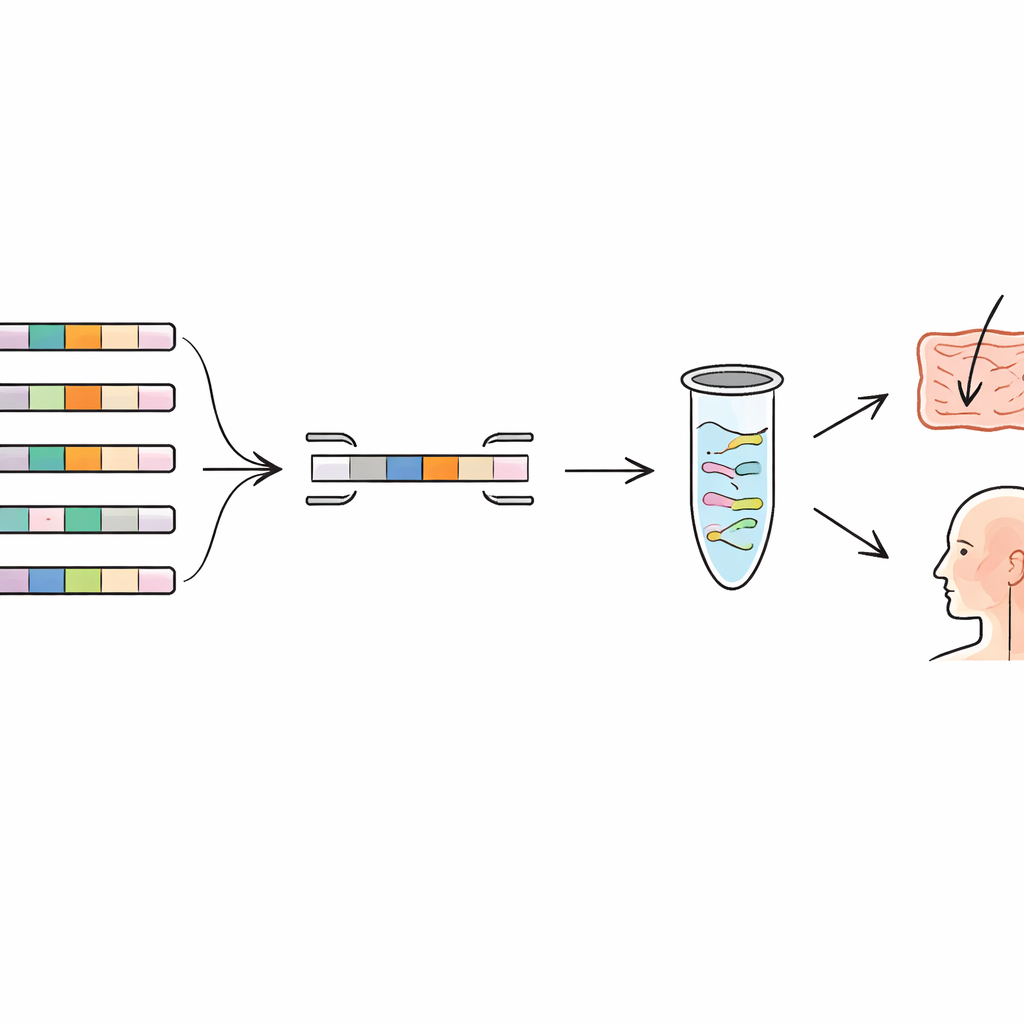
Analizzare il pangenoma per trovare impronte genetiche uniche
Gli autori si sono rivolti al concetto di “pangenoma”, la collezione completa di geni trovata attraverso molti genomi della stessa specie. Alcuni geni sono condivisi da tutti i membri (il core), mentre altri sono presenti solo in certi ceppi (la parte accessoria). Confrontando centinaia di genomi per diverse specie di batteri lattici e un comune batterio orale, hanno cercato geni che compaiono in un solo ceppo e non in nessun altro parente noto. Questi geni rari agiscono come impronte genetiche. Il team ha costruito una pipeline bioinformatica che compone automaticamente il pangenoma, rimuove genomi quasi identici duplicati e segnala i geni unici per ceppo. Ha quindi ricontrollato questi candidati contro banche genomiche più ampie per assicurarsi che sequenze simili non fossero nascoste in altre specie.
Progettare precisi “scanner” molecolari a codici a barre
Una volta identificati i geni unici per ceppo, il passo successivo è stato costruire test molecolari altamente specifici intorno a essi. I ricercatori hanno progettato brevi frammenti di DNA, chiamati primer, che si legano solo a questi geni unici. In una tecnica nota come PCR quantitativa (qPCR), questi primer funzionano come scanner di codici a barre, copiando e rilevando soltanto il DNA del ceppo target. Il team ha creato e ottimizzato primer per sei ceppi appartenenti a specie diverse, includendo probiotici di largo uso e nuovi candidati isolati dall’organismo umano. In laboratorio hanno testato ogni set di primer non solo sul ceppo previsto ma anche su diversi ceppi strettamente correlati della stessa specie. I test hanno mostrato una forte amplificazione solo per il ceppo target, con segnali minimi dagli altri, confermando che le impronte genetiche scelte erano davvero distintive.
Seguire i probiotici sulla pelle e nelle vie aeree
Per verificare se questo approccio funziona nelle persone reali, gli autori hanno applicato i loro primer a campioni provenienti da tre studi di intervento umano controllati con placebo. In uno studio i volontari hanno usato una crema per il viso contenente due ceppi probiotici; in altri, le persone hanno ricevuto uno spray per la gola probiotico o una compressa masticabile. Utilizzando i nuovi test qPCR, gli scienziati sono riusciti a rilevare in modo affidabile i ceppi aggiunti sulla pelle e nell’alto tratto respiratorio dei partecipanti trattati, mentre quasi mai li hanno riscontrati nei gruppi placebo. Hanno anche osservato come il segnale aumentava durante l’uso e diminuiva dopo la sospensione del trattamento, fornendo un quadro chiaro di una colonizzazione temporanea. In alcuni casi sono comparsi segnali a basso livello nei controlli, ricordando ai ricercatori di considerare i batteri di fondo naturali e il rischio di contaminazioni molto deboli, specialmente in siti corporei con numeri batterici bassi.
Che cosa significa per le future terapie microbiome‑based
In termini pratici, questo lavoro mostra come costruire un “radar di ceppo” molto preciso senza manipolare geneticamente i batteri. Sfruttando differenze genetiche sottili scoperte tramite confronti genomici su larga scala, gli scienziati possono creare test qPCR che distinguono un ceppo probiotico da una folla di sosia molto simili. Ciò rende molto più semplice rispondere a domande pratiche: il ceppo ha resistito allo stoccaggio del prodotto? Ha raggiunto il sito corporeo target? Quanto tempo è rimasto e a quali livelli? Poiché il metodo è trasparente, economico e adattabile ad altre specie, può diventare uno strumento standard per progettare e testare probiotici di nuova generazione e bioterapeutici vivi, portando maggiore rigore e sicurezza al campo in rapida crescita degli interventi basati sul microbioma.
Citazione: Eilers, T., Delanghe, L., De Boeck, I. et al. Pangenome-based design of strain-specific primers enables precise monitoring of bacteria in human microbiome intervention trials. Sci Rep 16, 11274 (2026). https://doi.org/10.1038/s41598-026-41449-8
Parole chiave: probiotici, microbioma, tracciamento di ceppi, qPCR, analisi del pangenoma