Clear Sky Science · nl
Pangenoom-gebaseerd ontwerp van soortspecifieke primers maakt nauwkeurige monitoring van bacteriën in interventiestudies bij mensen mogelijk
Waarom het volgen van nuttige microben belangrijk is
Veel van de bacteriën waar we over horen zijn lastpakken, maar sommige zijn stille helpers die melk in yoghurt veranderen, onze huid beschermen en mogelijk zelfs ontsteking in de luchtwegen verminderen. Deze “goede bacteriën” worden verkocht als probiotica of als strikter gereguleerde levende biotherapeutische producten en worden nu in humane onderzoeken getest voor huidproblemen, allergieën, darmklachten en meer. Toch is een eenvoudige vraag verrassend moeilijk te beantwoorden: wanneer we mensen een specifiek bacteriestam toedienen, kunnen we dan aantonen dat precies die stam overleeft en zich vestigt in het lichaam, en niet slechts nauw verwante verwanten? Deze studie presenteert een nieuwe manier om individuele bacteriestammen met hoge precisie te volgen, door gebruik te maken van de groeiende hoeveelheid genoomgegevens.
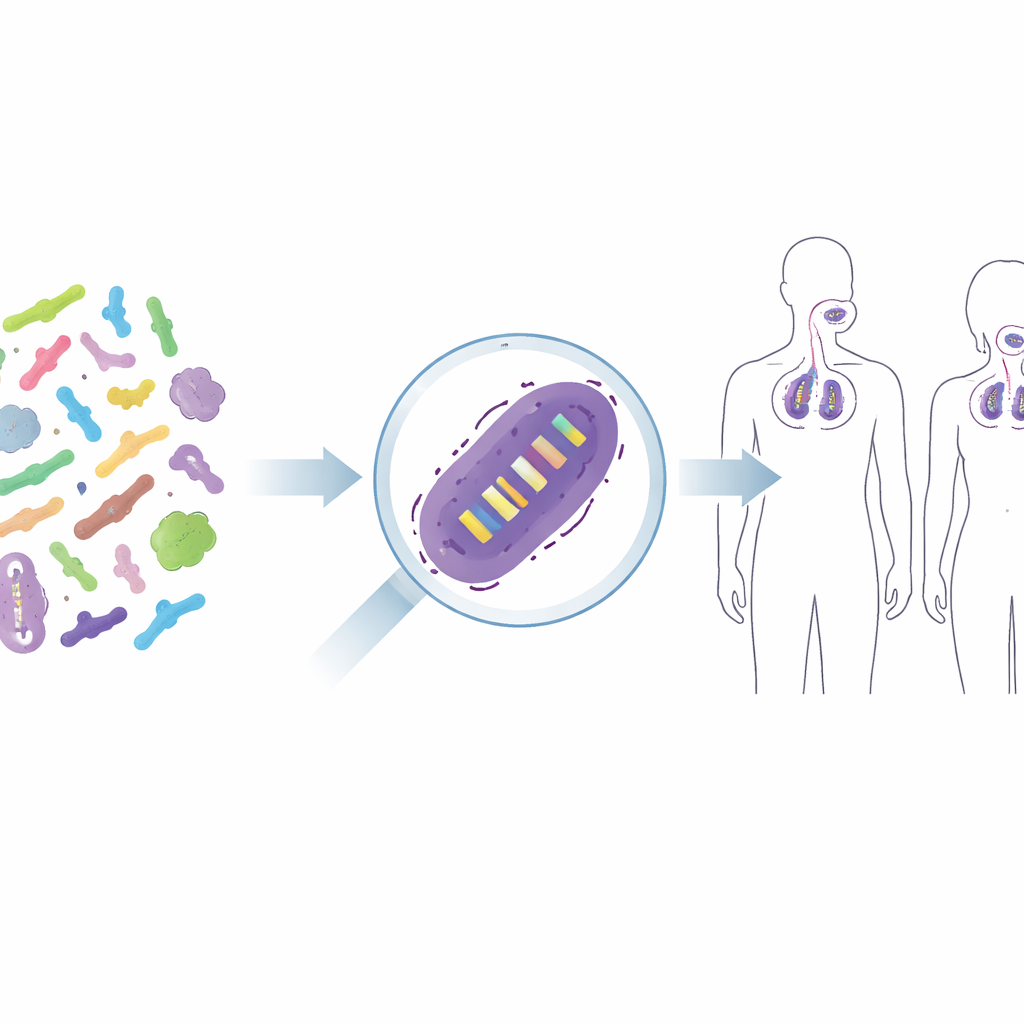
Van gemengde microben naar individuele stammen
Probiotische producten bevatten zelden slechts “bacteriën” in het abstract; ze bevatten zorgvuldig gekozen stammen, zoals een specifieke variant van Lacticaseibacillus rhamnosus GG of Lactiplantibacillus plantarum WCFS1. Deze nauw verwante stammen kunnen verschillen in hoe ze met ons immuunsysteem omgaan of hoe goed ze hechten aan huid- of keelslijmvlies, dus onderzoekers en toezichthouders willen precies weten welke stam aanwezig is na behandeling. Traditionele methoden, zoals het kweken van bacteriën op selectief medium, vertellen ons alleen over brede groepen—zoals totale melkzuurbacteriën—en falen vaak wanneer nuttige stammen in aantal worden overtroffen door andere. Meer geavanceerde oplossingen, zoals het taggen van stammen met fluorescerende markers of DNA-barcodes, zouden ze genetisch gemodificeerde organismen maken, wat vaak niet acceptabel is voor voedingsmiddelen of humane therapieën. De uitdaging is om vrijwel identieke stammen te onderscheiden zonder ze te wijzigen.
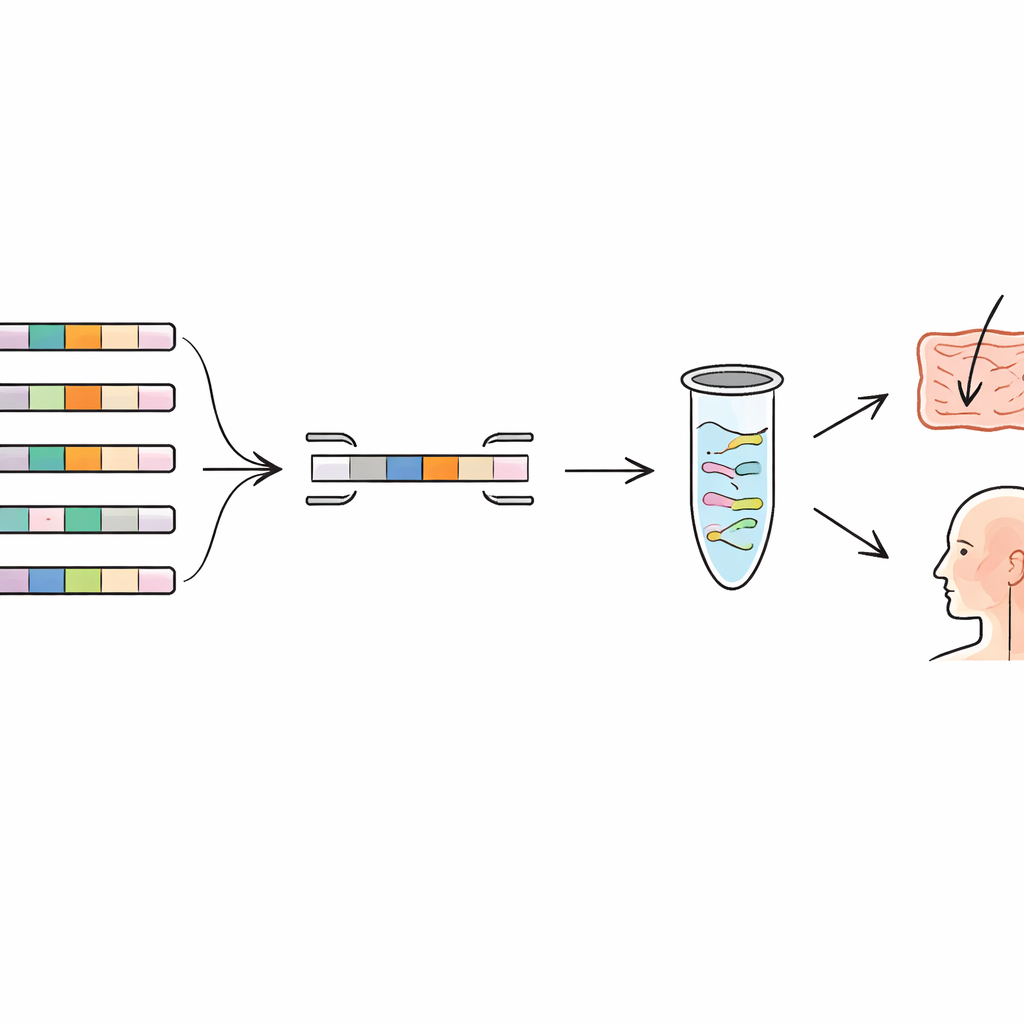
Het pangenoom afzoeken naar unieke genetische vingerafdrukken
De auteurs grepen naar het concept van een “pangenoom”, de volledige verzameling genen die voorkomt in veel genomen van dezelfde soort. Sommige genen worden door alle leden gedeeld (het core-genoom), terwijl andere alleen in bepaalde stammen voorkomen (het accessoirespect). Door honderden genomen van meerdere soorten melkzuurbacteriën en een veelvoorkomende mondbacterie te vergelijken, zochten ze naar genen die slechts in één stam voorkomen en in geen enkele andere bekende verwant. Deze zeldzame genen fungeren als genetische vingerafdrukken. Het team bouwde een bioinformatica‑pipeline die automatisch het pangenoom samenstelt, vrijwel identieke dubbele genomen verwijdert en stam‑unieke genen markeert. Ze controleerden deze kandidaten vervolgens opnieuw tegen bredere genoomdatabases om zeker te zijn dat vergelijkbare sequenties niet in andere soorten verborgen zaten.
Ontwerpen van precieze moleculaire “barcodelezers”
Zodra stam‑unieke genen waren geïdentificeerd, bestond de volgende stap uit het opzetten van zeer specifieke moleculaire tests rondom deze genen. De onderzoekers ontwierpen korte DNA‑stukjes, primers genoemd, die alleen binden aan deze unieke genen. In een techniek die kwantitatieve PCR (qPCR) heet, werken deze primers als barcodelezers, doordat ze alleen DNA van de doelstam kopiëren en detecteren. Het team maakte en optimaliseerde primersets voor zes stammen uit verschillende soorten, waaronder veelgebruikte probiotica en nieuwe kandidaten die uit het menselijk lichaam waren geïsoleerd. In het laboratorium testten ze elke primerset niet alleen op de bedoelde stam maar ook op meerdere nauwe verwanten uit dezelfde soort. De tests toonden sterke amplificatie alleen voor de doelstam, met minimale signalen van de anderen, wat bevestigt dat de gekozen genetische vingerafdrukken daadwerkelijk onderscheidend waren.
Het volgen van probiotica op de huid en in de luchtwegen
Om te zien of deze aanpak werkt bij echte mensen, pasten de auteurs hun primers toe op monsters van drie placebogecontroleerde humane interventiestudies. In één onderzoek gebruikten proefpersonen een gezichtscrème met twee probiotische stammen; in andere studies kregen mensen een probiotische keelspray of een kauwtablet. Met de nieuwe qPCR‑testen konden de wetenschappers de toegevoegde stammen betrouwbaar detecteren op de huid en in de bovenste luchtweg van behandelde deelnemers, terwijl ze ze bijna nooit in placebogroepen aantroffen. Ze observeerden ook hoe het signaal tijdens gebruik toenam en na het stoppen van de behandeling afnam, wat een duidelijk beeld gaf van tijdelijke kolonisatie. In enkele gevallen verschenen er lage signalen in controles, wat onderzoekers eraan herinnert rekening te houden met natuurlijke achtergrondbacteriën en het risico op zeer kleine contaminatie, vooral op lichaamsplaatsen met weinig bacteriën.
Wat dit betekent voor toekomstige microbioomtherapieën
In gewone bewoordingen laat dit werk zien hoe je een zeer scherpe “stamradar” bouwt zonder genetisch te sleutelen aan de bacteriën zelf. Door subtiele genetische verschillen te benutten die aan het licht komen bij grootschalige genoomvergelijkingen, kunnen wetenschappers qPCR‑testen maken die één probiotische stam uit een menigte zeer gelijkende soorten halen. Dit maakt het veel eenvoudiger om praktische vragen te beantwoorden: heeft de stam de houdbaarheid van het product doorstaan? Bereikte hij de doelplaats in het lichaam? Hoe lang bleef hij en in welke aantallen? Omdat de methode transparant, goedkoop en aanpasbaar aan andere soorten is, kan het een standaardinstrument worden voor het ontwerpen en testen van de volgende generatie probiotica en levende biotherapeutica, en meer strengheid en veiligheid brengen in het snelgroeiende veld van op het microbioom gebaseerde interventies.
Bronvermelding: Eilers, T., Delanghe, L., De Boeck, I. et al. Pangenome-based design of strain-specific primers enables precise monitoring of bacteria in human microbiome intervention trials. Sci Rep 16, 11274 (2026). https://doi.org/10.1038/s41598-026-41449-8
Trefwoorden: probiotica, microbioom, strainsporing, qPCR, pangenoomanalyse