Clear Sky Science · zh
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : 荧光显微镜数据的语义解混
以更少的光看到更多
现代显微镜让科学家能够观察活细胞的动态,但每一张图像都有代价。每次照明都可能损伤脆弱的细胞,而使用许多不同的荧光标记很快会遇到物理极限。本文介绍了 MicroSplit —— 一种计算方法,允许研究者在一次更简单的拍摄中记录多个细胞结构的信号,然后在计算机上将它们分离,从而减轻显微镜和样本的负担。
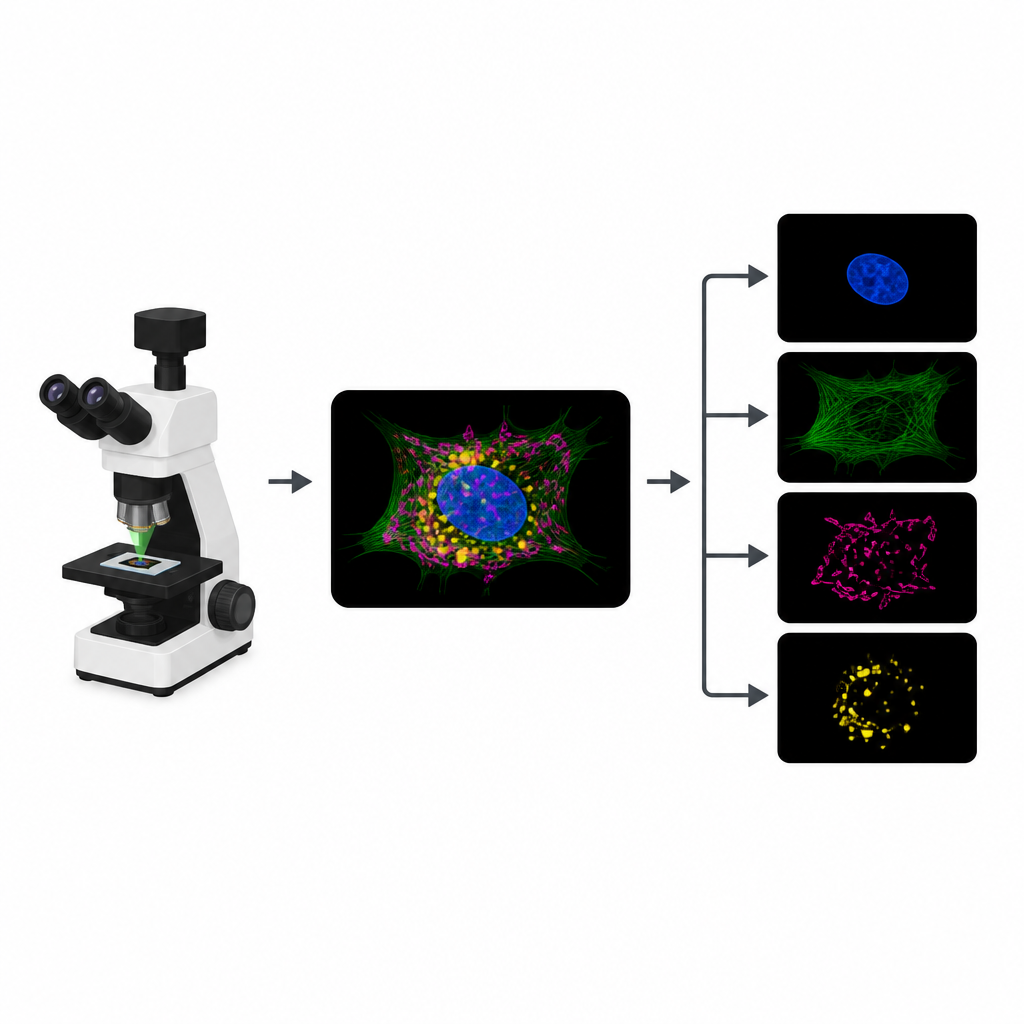
为什么荧光成像会遇到瓶颈
为了跟踪细胞的不同部分,生物学家会把不同的荧光染料标记到诸如细胞核、细胞骨架或能量工厂等结构上。在典型实验中,显微镜为每种染料记录单独的图像通道。然而,染料通常对相似波长的光有响应,因此它们的信号会相互重叠。这种重叠限制了可同时追踪的结构数量。此外,每增加一个通道就需要一次额外的照明,这消耗有限的“光子预算”,可能导致动态图像速度变慢、细节模糊或损伤活体样品。
把一张拥挤的图片变成多张清晰图像
MicroSplit 通过改变信息的采集和处理方式来应对这一权衡。研究者可以按常规对多个结构进行标记,但将它们一起记录在单个荧光通道中,而不是拍摄多个单独通道。然后将这张拥挤的图像送入已训练好的深度学习模型,该模型学会对所见模式进行“解混”。网络输出若干经清理的图像,每张图像突出不同的结构,就像从一开始就在各自通道中成像一样。
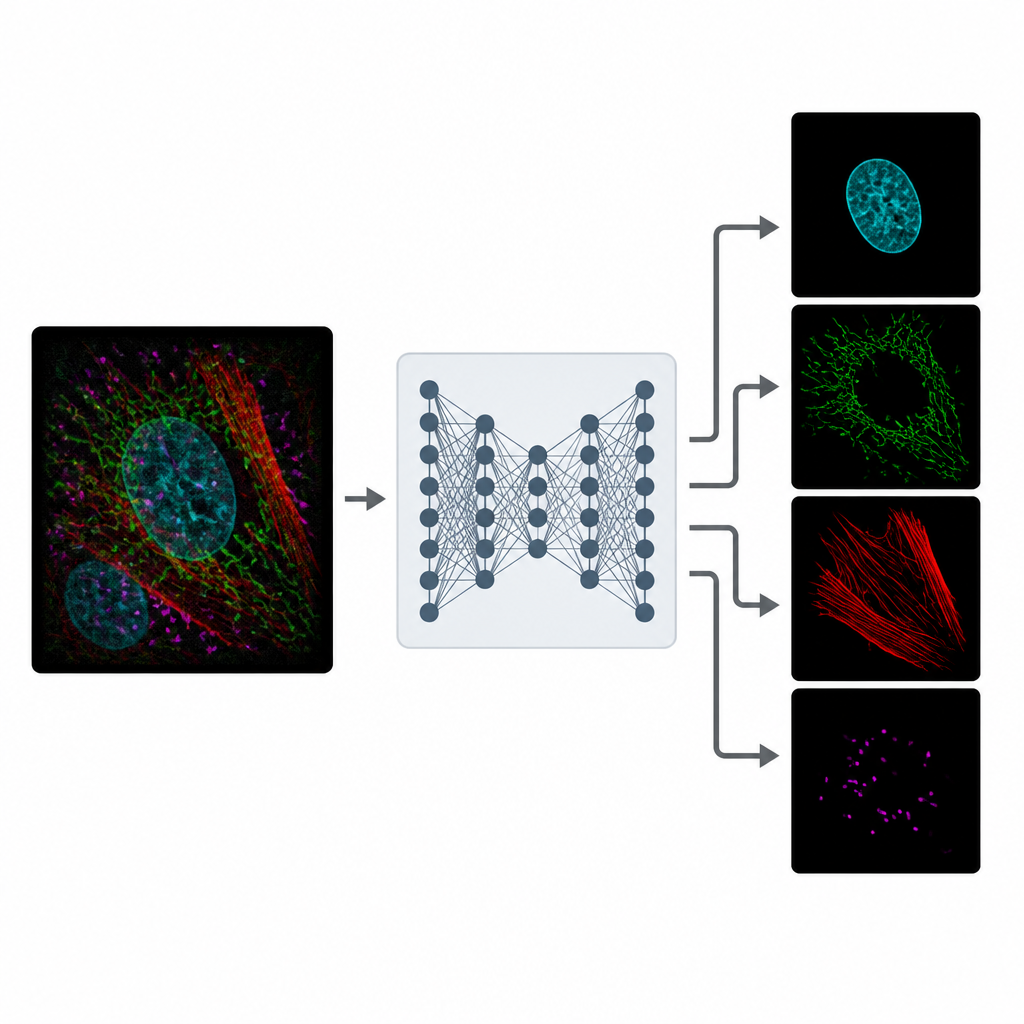
从嘈杂的现实中学习
训练 MicroSplit 并不需要完美的参考图像。作者展示了模型可以从普通的、带噪的显微镜数据中学习,而这些数据更容易获得。在训练过程中,系统会使用包含独立通道及其叠加组合的实例。模型同时学习两件事:如何分离重叠结构以及如何去噪。使用一种能够采样多种合理解的特定神经网络类型,MicroSplit 还可以估计自身预测的不确定性,标记出应谨慎处理或由专家复核的区域。
跨数据集与多种用途的适用性
研究者在十个不同的显微镜数据集上测试了 MicroSplit,涵盖二维与三维数据,并涉及最多四个重叠的细胞结构。在 30 个主要任务中,分离后的图像足够准确,可支持常规的下游分析,如分割细胞部位。在严谨的对比测试中,分析人员对 MicroSplit 输出与传统多通道图像的分割结果表现出同等一致性。该方法也可以反向用于去除不需要的特征:通过教会 MicroSplit 区分真实信号与反复出现的斑点或污迹,模型能在保留真实结构的同时减去这些成像伪影。
认清其局限
MicroSplit 不是万能的,作者也坦率地探讨了其困难情形。当原始图像极度嘈杂、某一结构远暗于另一结构,或两种结构外观几乎相同时,性能会下降。在这些情况下,模型往往会平滑掉非常细微的细节,而不是凭空生成虚假的锐利特征。尽管如此,即便在短曝光时间下,MicroSplit 通常也能提供足够用于定量工作的分离图像,同时使用的光子远少于传统方法。
对未来成像的意义
对非专业读者来说,核心信息是:MicroSplit 通过把部分工作从硬件转移到软件,使显微镜在更短时间、用更少光照条件下“看到”更多结构。研究者不再受限于显微镜在光学上能区分多少颜色,而可以将信号合并到单个通道,让 MicroSplit 来做分拣。这释放了光子,可以更快地拍摄动态图、以更温和的方式捕捉微弱结构,或加入此前不切实际的额外标记。作者通过公开代码、数据和训练模型,旨在使这种计算多重化成为生物成像的常规工具。
引用: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
关键词: 荧光显微镜, 深度学习, 图像解混, 计算多重化, 生物图像分析