Clear Sky Science · pt
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : unmixing semântico de dados de microscopia fluorescente
Ver Mais com Menos Luz
Microscópios modernos permitem que cientistas observem células vivas em ação, mas cada imagem tem um custo. Cada lampejo de luz pode danificar células delicadas, e usar muitas etiquetas fluorescentes diferentes rapidamente encontra limites físicos. Este trabalho apresenta o MicroSplit, um artifício computacional que permite aos pesquisadores capturar várias estruturas celulares em uma única imagem mais simples e depois separá-las no computador, aliviando a carga tanto sobre o microscópio quanto sobre as próprias células.
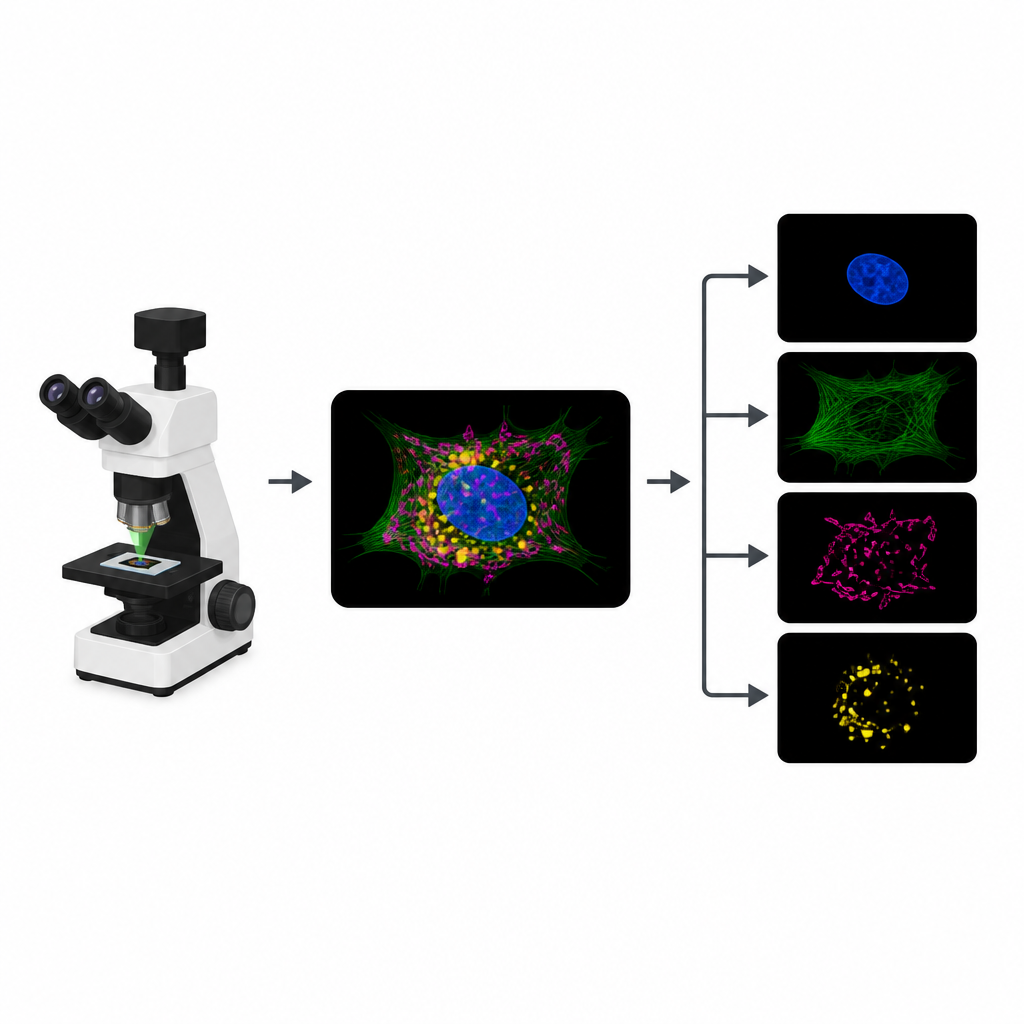
Por que Células Brilhantes Batem em um Limite
Para acompanhar diferentes partes de uma célula, biólogos fixam corantes fluorescentes distintos em estruturas como o núcleo, o citoesqueleto ou as usinas de energia. Em um experimento típico, o microscópio registra um canal de imagem separado para cada corante. No entanto, os corantes frequentemente respondem a cores de luz semelhantes, de modo que seus sinais se sobrepõem. Essa sobreposição limita quantas estruturas podem ser monitoradas ao mesmo tempo. Além disso, cada canal extra significa mais rodadas de iluminação, o que consome um “orçamento de fótons” limitado e pode tornar filmes mais lentos, borrar detalhes ou prejudicar amostras vivas.
Transformando Uma Imagem Lotada em Várias Claras
O MicroSplit enfrenta esse trade-off mudando como a informação é coletada e processada. Em vez de tirar várias fotos separadas, os cientistas podem marcar múltiplas estruturas normalmente, mas registrá‑las juntas em um único canal fluorescente. Essa imagem única e congestionada é então alimentada em um modelo de aprendizado profundo treinado para “desmezclar” os padrões que enxerga. A rede produz várias imagens limpas, cada uma destacando uma estrutura diferente, como se tivesse sido capturada em seu próprio canal desde o início.
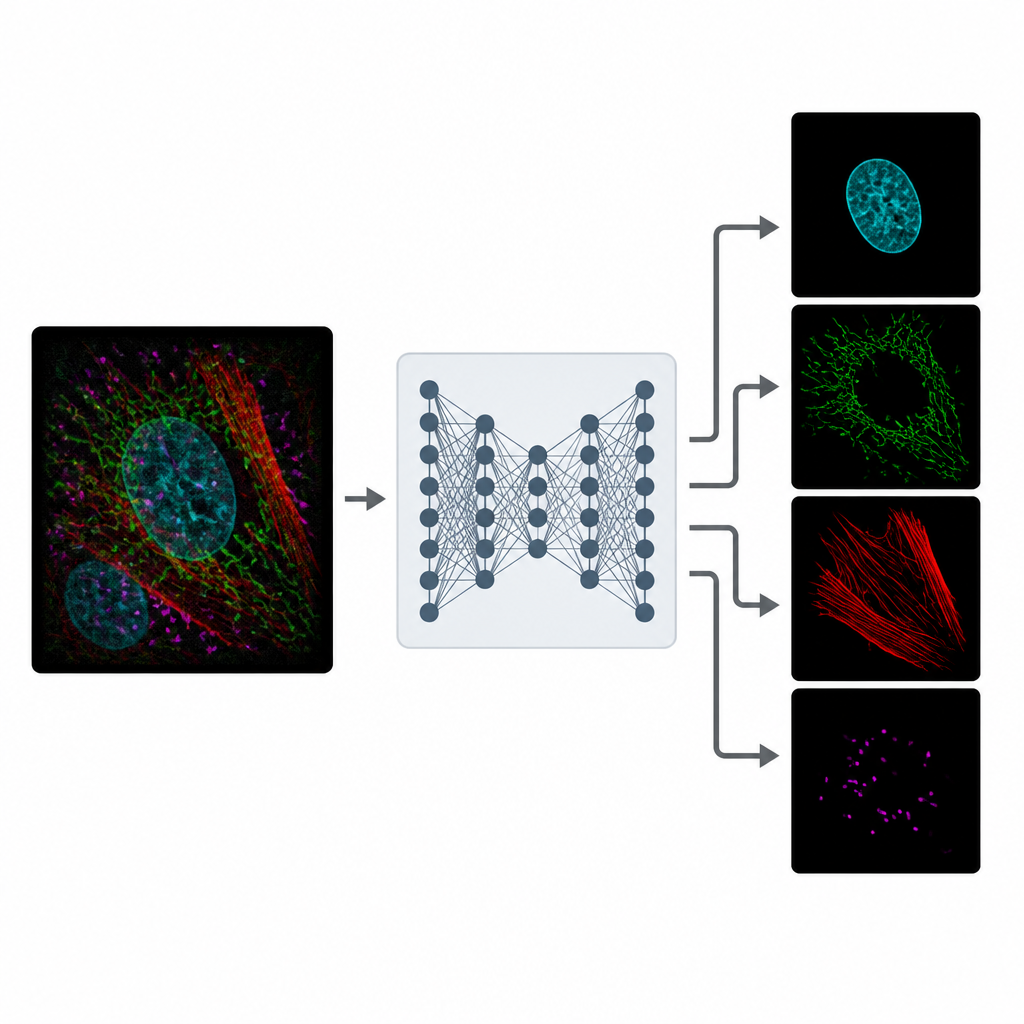
Aprendendo a Partir da Realidade Ruidosa
Treinar o MicroSplit não requer imagens de referência impecáveis. Os autores mostram que o modelo pode aprender a partir de dados de microscopia comuns e ruidosos, que são muito mais fáceis de obter. Durante o treinamento, o sistema recebe exemplos em que canais separados e sua combinação somada estão disponíveis. Ele aprende duas coisas ao mesmo tempo: como separar estruturas sobrepostas e como remover ruído. Usando um tipo especial de rede neural que amostra muitas soluções plausíveis, o MicroSplit também pode estimar onde suas próprias previsões são incertas, sinalizando regiões que devem ser tratadas com cautela ou verificadas por um especialista.
Funciona em Diferentes Conjuntos de Dados e Usos
Os pesquisadores testaram o MicroSplit em dez conjuntos de dados diferentes de microscopia, abrangendo duas e três dimensões e envolvendo até quatro estruturas celulares sobrepostas. Em 30 tarefas principais, as imagens separadas foram precisas o suficiente para suportar análises posteriores padrão, como a segmentação de partes celulares. Em testes cuidadosos, analistas humanos produziram segmentações igualmente consistentes em saídas do MicroSplit e em imagens multicanais convencionais. O método também pode ser invertido para remover características indesejadas: ao ensinar o MicroSplit a distinguir sinal verdadeiro de manchas recorrentes, o modelo pode subtrair esses artefatos de imagem preservando as estruturas reais.
Conhecendo os Limites
O MicroSplit não é magia, e os autores exploram abertamente quando ele tem dificuldades. O desempenho cai se as imagens originais forem extremamente ruidosas, se uma estrutura for muito mais fraca que outra ou se duas estruturas parecerem quase idênticas. Nesses casos, o modelo tende a suavizar detalhes muito finos em vez de inventar nitidez falsa. Ainda assim, mesmo com tempos de exposição curtos, o MicroSplit frequentemente fornece imagens separadas boas o suficiente para trabalhos quantitativos, usando muito menos fótons do que abordagens tradicionais.
O Que Isso Significa para a Imagem do Futuro
Para não especialistas, a mensagem principal é que o MicroSplit permite que microscópios “vejam” mais estruturas em menos tempo e com menos luz ao deslocar parte do trabalho do hardware para o software. Em vez de ficar limitado por quantas cores um microscópio pode separar opticamente, os pesquisadores podem combinar sinais em um canal e deixar o MicroSplit fazer a triagem. Isso libera luz para tornar filmes mais rápidos, capturar estruturas tênues de forma mais suave ou adicionar etiquetas extras que antes eram impraticáveis. Ao tornar o código, os dados e os modelos treinados abertamente disponíveis, os autores objetivam tornar esse tipo de multiplexagem computacional uma parte rotineira da imagem biológica.
Citação: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
Palavras-chave: microscopia de fluorescência, aprendizado profundo, separação de imagens, multiplexagem computacional, análise de bioimagens