Clear Sky Science · fr
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : démélange sémantique des données de microscopie à fluorescence
Voir plus avec moins de lumière
Les microscopes modernes permettent aux scientifiques d'observer des cellules vivantes en action, mais chaque image a un coût. Chaque éclair peut endommager des cellules délicates, et l'utilisation de nombreuses sondes fluorescentes se heurte rapidement à des limites physiques. Cet article présente MicroSplit, une astuce computationnelle qui permet aux chercheurs de capturer plusieurs structures cellulaires dans une seule image plus simple, puis de les séparer ensuite sur ordinateur, soulageant à la fois l'instrument et les échantillons.
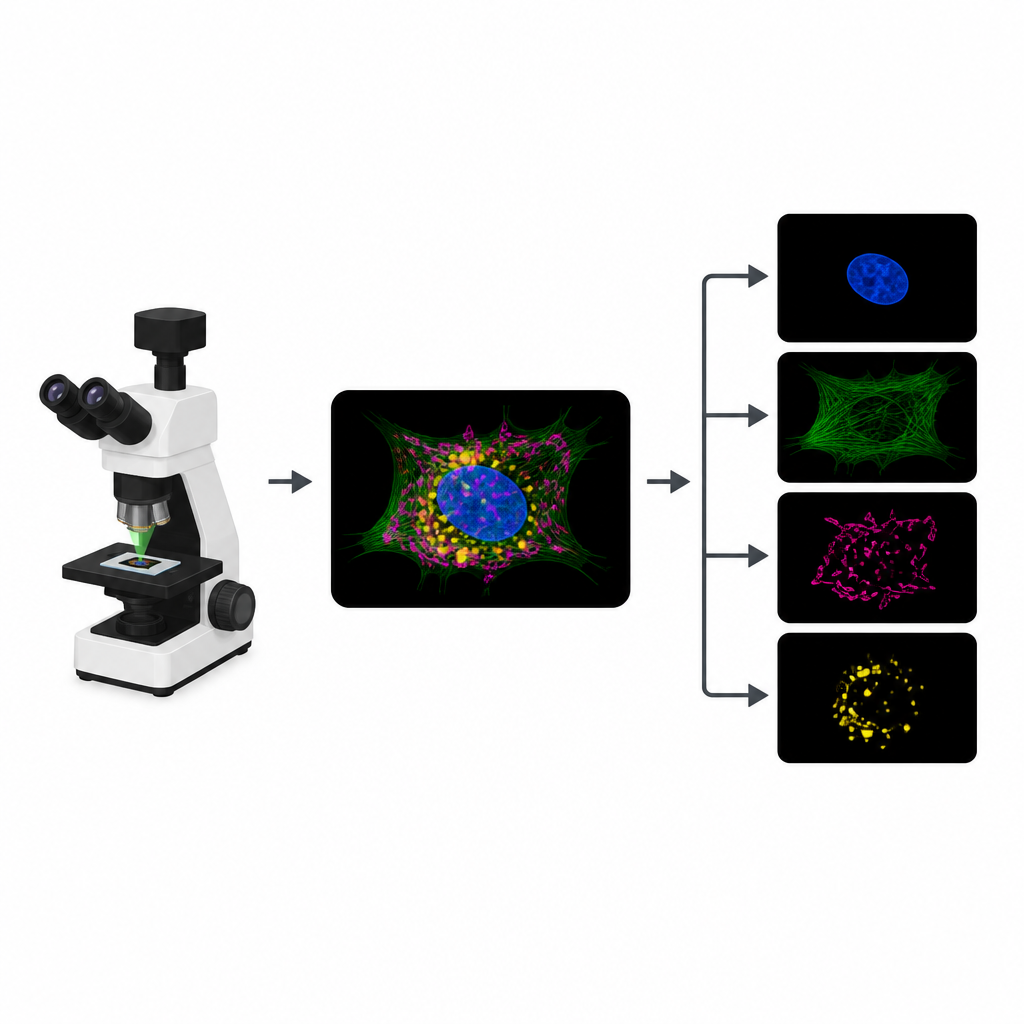
Pourquoi la fluorescence atteint ses limites
Pour suivre différentes parties d'une cellule, les biologistes fixent des colorants fluorescents distincts sur des structures comme le noyau, le cytosquelette ou les centrales énergétiques. Dans une expérience typique, le microscope enregistre un canal d'image distinct pour chaque colorant. Cependant, les colorants réagissent souvent à des longueurs d'onde proches, de sorte que leurs signaux se chevauchent. Ce chevauchement limite le nombre de structures pouvant être suivies simultanément. De plus, chaque canal supplémentaire implique une nouvelle phase d'illumination, qui consomme un « budget de photons » limité et peut ralentir les films, flouter les détails ou endommager les échantillons vivants.
Transformer une image encombrée en plusieurs images nettes
MicroSplit résout ce compromis en modifiant la façon dont l'information est collectée et traitée. Plutôt que de prendre plusieurs clichés séparés, les chercheurs peuvent marquer plusieurs structures comme d'habitude mais les enregistrer ensemble dans un seul canal fluorescent. Cette image unique et encombrée est ensuite fournie à un modèle d'apprentissage profond entraîné à « démêler » les motifs qu'il observe. Le réseau produit plusieurs images nettoyées, chacune mettant en valeur une structure différente comme si elle avait été imagée dans son propre canal dès le départ.
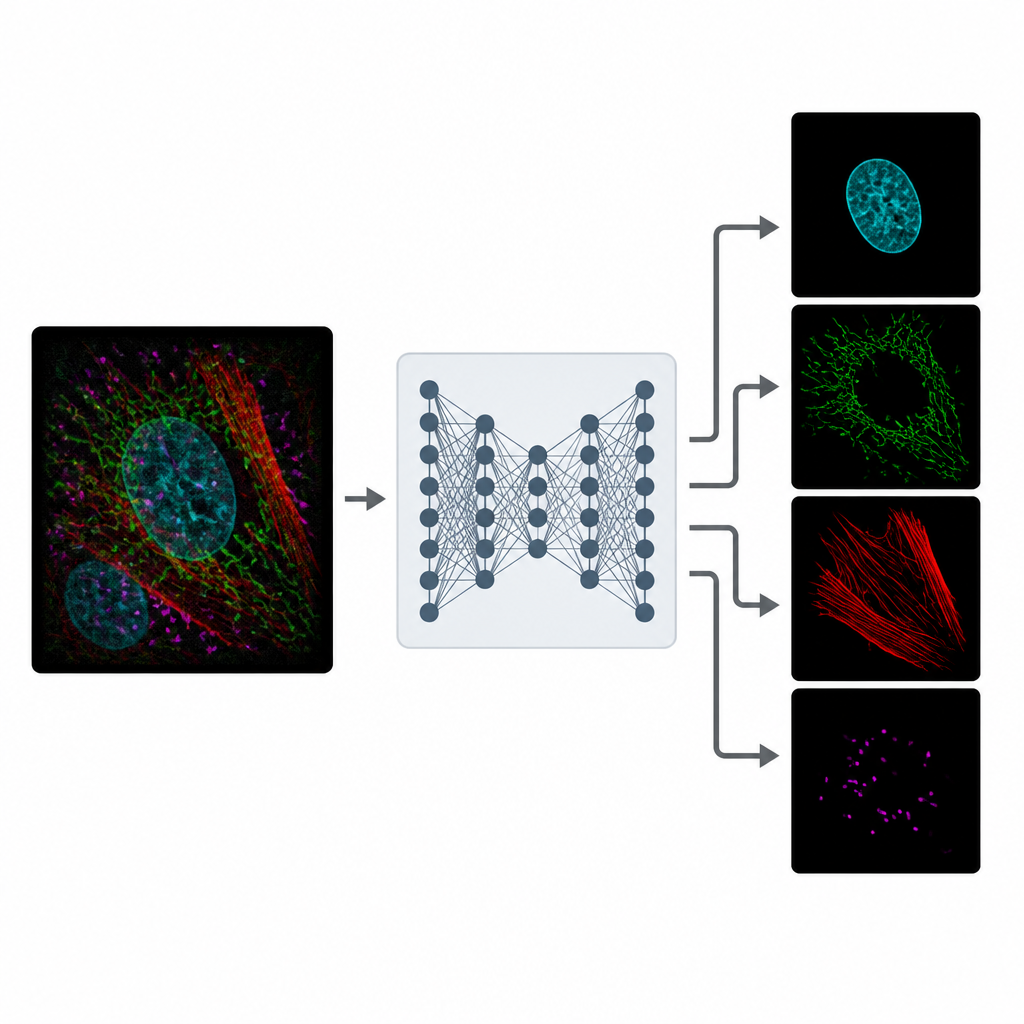
Apprendre à partir d'une réalité bruitée
L'entraînement de MicroSplit ne nécessite pas d'images de référence impeccables. Les auteurs montrent que le modèle peut apprendre à partir de données de microscope ordinaires et bruitées, beaucoup plus faciles à obtenir. Pendant l'entraînement, le système reçoit des exemples où les canaux séparés et leur somme combinée sont disponibles. Il apprend deux choses à la fois : comment séparer les structures qui se chevauchent et comment supprimer le bruit. En utilisant un type spécial de réseau neuronal qui échantillonne de nombreuses solutions plausibles, MicroSplit peut aussi estimer l'incertitude de ses propres prédictions, signalant des régions à traiter avec prudence ou à vérifier par un expert.
Fonctionne sur plusieurs jeux de données et usages
Les chercheurs ont testé MicroSplit sur dix jeux de données de microscopie différents, en deux et trois dimensions et impliquant jusqu'à quatre structures cellulaires se chevauchant. Sur 30 tâches principales, les images séparées étaient suffisamment précises pour soutenir des analyses en aval standard telles que la segmentation des parties cellulaires. Dans des tests rigoureux, des analystes humains ont produit des segmentations aussi cohérentes sur les sorties de MicroSplit que sur des images multicanaux conventionnelles. La méthode peut aussi être renversée pour supprimer des artefacts indésirables : en apprenant à MicroSplit à distinguer le vrai signal des taches récurrentes ou des marbrures, le modèle peut soustraire ces artefacts d'imagerie tout en préservant les structures réelles.
Connaître les limites
MicroSplit n'est pas magique, et les auteurs explorent ouvertement ses faiblesses. Les performances diminuent si les images initiales sont extrêmement bruitées, si une structure est beaucoup plus faible qu'une autre, ou si deux structures se ressemblent presque complètement. Dans de tels cas, le modèle a tendance à lisser les très fins détails plutôt qu'à inventer une netteté artificielle. Néanmoins, même avec des temps d'exposition courts, MicroSplit fournit souvent des images séparées suffisamment bonnes pour des analyses quantitatives, tout en utilisant beaucoup moins de photons que les approches classiques.
Ce que cela signifie pour l'imagerie future
Pour les non-spécialistes, le message clé est que MicroSplit permet aux microscopes de « voir » plus de structures en moins de temps et avec moins de lumière en transférant une partie du travail du matériel vers le logiciel. Plutôt que d'être limité par le nombre de couleurs qu'un microscope peut séparer optiquement, les chercheurs peuvent combiner les signaux dans un seul canal et laisser MicroSplit effectuer le tri. Cela libère de la lumière pour accélérer les films, capturer des structures faibles plus en douceur ou ajouter des marquages supplémentaires auparavant impraticables. En publiant le code, les données et les modèles entraînés en accès ouvert, les auteurs visent à faire de ce type de multiplexage computationnel une pratique courante de l'imagerie biologique.
Citation: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
Mots-clés: microscopie à fluorescence, apprentissage profond, démélange d'images, multiplexage computationnel, analyse d'images biologiques