Clear Sky Science · ja
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : 蛍光顕微鏡データの意味的分離
より少ない光でより多くを観る
現代の顕微鏡は生きた細胞の動きを観察することを可能にしますが、各画像取得には代償があります。光の閃光は繊細な細胞を損なう可能性があり、複数の蛍光標識を使うとすぐに物理的な限界に達します。本稿はMicroSplitを紹介します。これは研究者が複数の細胞構造を単一の簡素な画像で取得し、後でコンピュータ上で分離できるようにする計算的手法であり、顕微鏡と試料の両方への負担を軽くします。
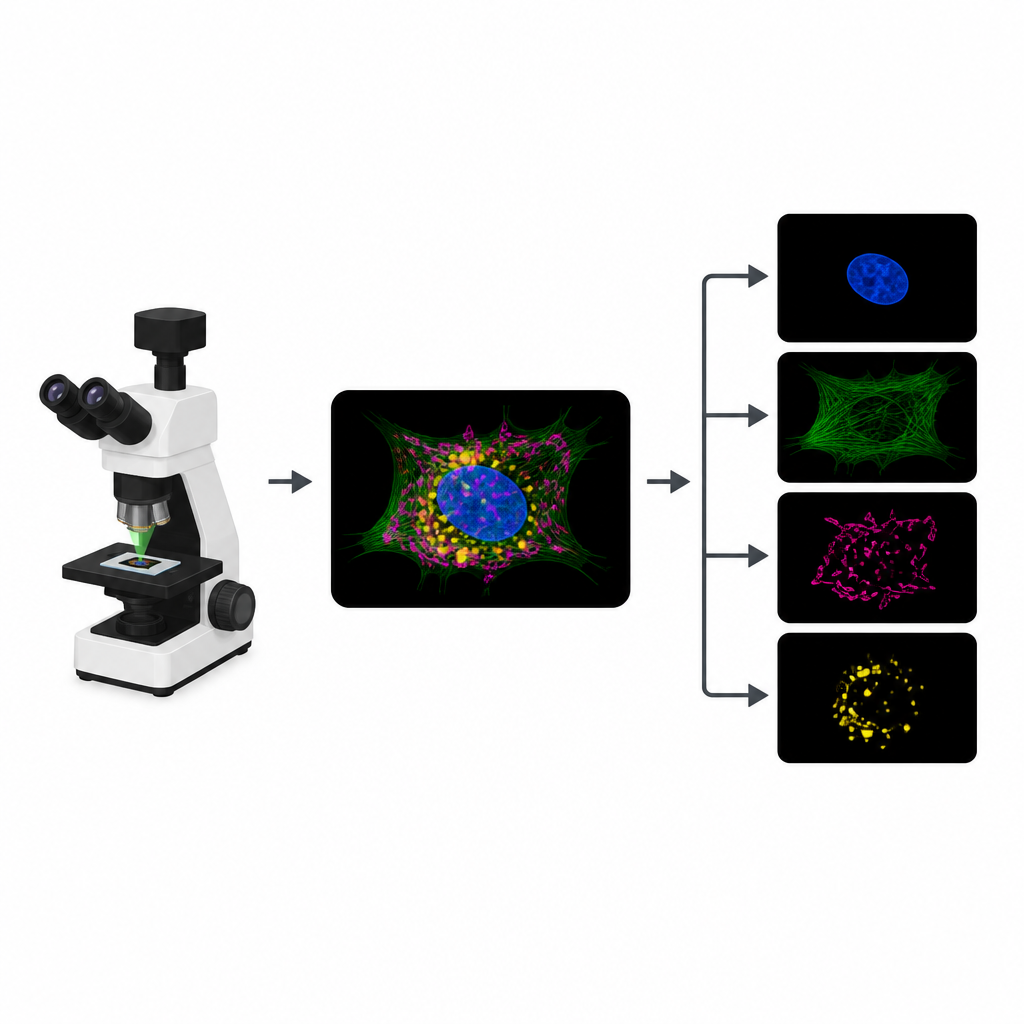
なぜ発光する細胞は壁にぶつかるのか
細胞の異なる部分を追跡するために、生物学者は核や細胞骨格、エネルギー生成器官などの構造にそれぞれ異なる蛍光色素を結合します。典型的な実験では、顕微鏡は色素ごとに別々のイメージチャネルを記録します。しかし多くの色素は似た波長帯に反応するため、その信号は重なり合います。その重なりが同時に追跡できる構造数を制限します。加えて、チャネルを増やすごとに照明が一回増え、限られた“光子予算”を消費し、動画像が遅くなったり解像が低下したり、生きた試料を傷めたりします。
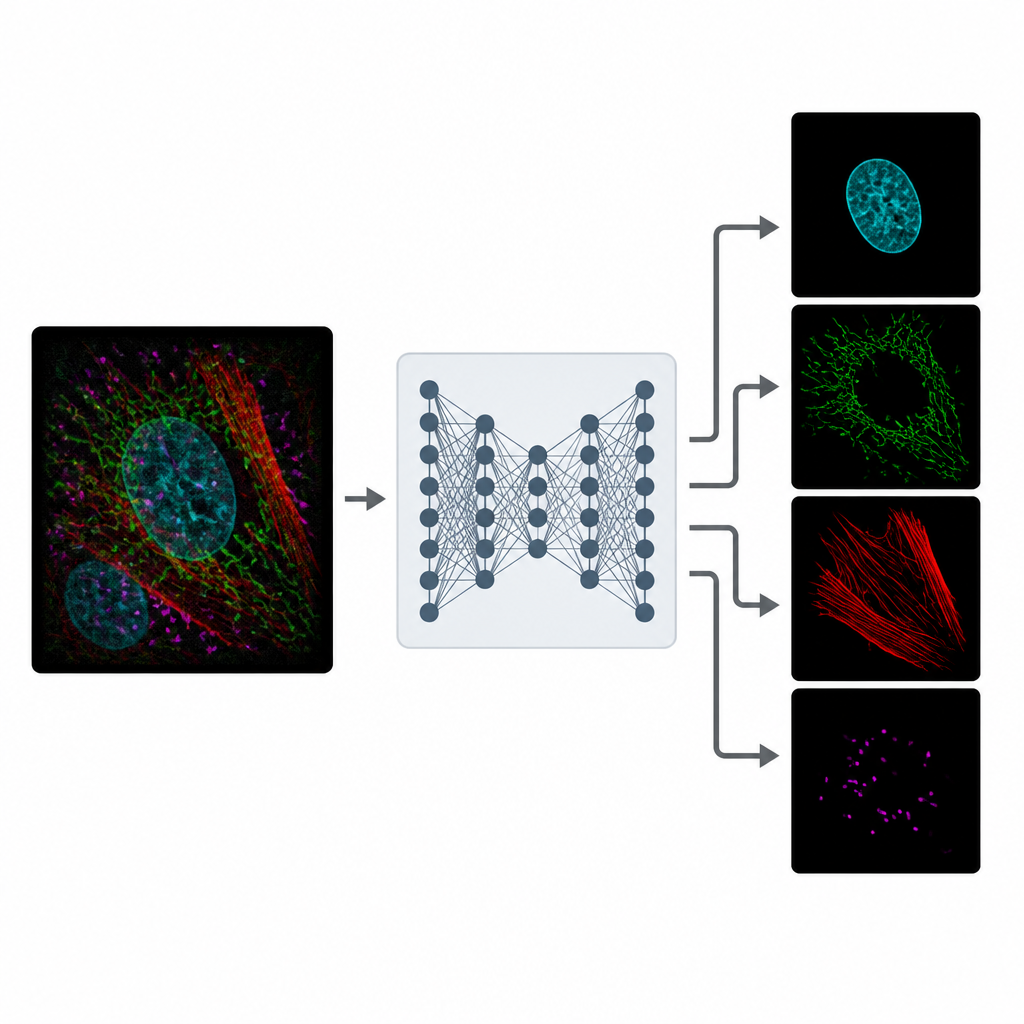
ひとつの混雑した画像を複数の鮮明な画像に変える
MicroSplitは情報の取得と処理のやり方を変えることでこのトレードオフに対処します。複数の別撮りを行う代わりに、研究者は通常通り複数の構造にラベルを付けつつ、それらを単一の蛍光チャネルにまとめて記録できます。この一枚の混在した画像を深層学習モデルに入力すると、モデルは観られるパターンを“アンミックス”するよう学習しています。ネットワークは複数のクリーンな画像を出力し、それぞれがまるで最初から別チャネルで撮影されたかのように異なる構造を強調します。
ノイズを含む現実から学ぶ
MicroSplitの訓練には完璧な参照画像は必要ありません。著者らは、モデルが通常のノイズを含む顕微鏡データから学習できることを示しています。これらは入手がずっと容易です。訓練中、システムには別々のチャネルとそれらを合成したものが与えられます。モデルは重なり合う構造を分離する方法とノイズを除去する方法を同時に学びます。多様な妥当な解をサンプリングできる特殊なネットワークを用いることで、MicroSplitは自身の予測が不確かである領域の推定も行い、注意や専門家による確認が必要な箇所を示せます。
データセットや用途を超えて働く
研究者たちはMicroSplitを10種類の異なる顕微鏡データセットで評価し、2次元・3次元を含み最大4つの重なり合う細胞構造を扱いました。30の主要課題において、分離された画像は細胞部分のセグメンテーションなど標準的な下流解析を支えるのに十分な正確さを示しました。入念なテストでは、人間の解析者はMicroSplit出力と従来のマルチチャネル画像のいずれでも同等に一貫したセグメンテーションを行いました。この手法は逆に不要な特徴を取り除く用途にも転用可能です。MicroSplitに繰り返し現れる斑点やムラを真の信号と区別させることで、実際の構造を保持しつつこれらの撮影アーチファクトを差し引けます。
限界を知る
MicroSplitは魔法ではなく、著者らは失敗しやすい状況を率直に提示しています。元画像が極端にノイズが多い場合、ある構造が他よりはるかに暗い場合、あるいは二つの構造の見た目がほとんど同じ場合には性能が低下します。そのような場合、モデルは誤って鋭い細部を創り出すよりも非常に細かいディテールを平滑化してしまう傾向があります。それでも短い露光時間でも、MicroSplitは従来法より遥かに少ない光子で定量的な作業に十分な分離画像をしばしば提供します。
今後のイメージングに意味すること
専門外の人にとっての要点は、MicroSplitがハードウェアからソフトウェアへ役割を移すことで、顕微鏡がより少ない時間と光で多くの構造を“見る”ことを可能にするということです。顕微鏡が光学的に区別できる色数に制約される代わりに、研究者は信号を一つのチャネルにまとめ、MicroSplitに仕分けさせることができます。これにより光を節約して動画を高速化したり、暗い構造をやさしく捉えたり、従来は実用的でなかった追加ラベルを使ったりする余地が生まれます。コード、データ、学習済みモデルを公開することで、著者らはこの種の計算的多重化を生物画像計測の標準的な手法にしたいと考えています。
引用: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
キーワード: 蛍光顕微鏡法, 深層学習, 画像分離, 計算的多重化, バイオ画像解析