Clear Sky Science · es
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : separación semántica de datos de microscopía fluorescente
Ver más con menos luz
Los microscopios modernos permiten a los científicos observar células vivas en acción, pero cada imagen tiene un coste. Cada destello de luz puede dañar células delicadas, y usar muchas etiquetas fluorescentes distintas choca rápidamente con límites físicos. Este artículo presenta MicroSplit, un truco computacional que permite a los investigadores capturar varias estructuras celulares en una sola imagen más sencilla y luego separarlas en el ordenador, reduciendo la carga tanto sobre el microscopio como sobre las propias células.
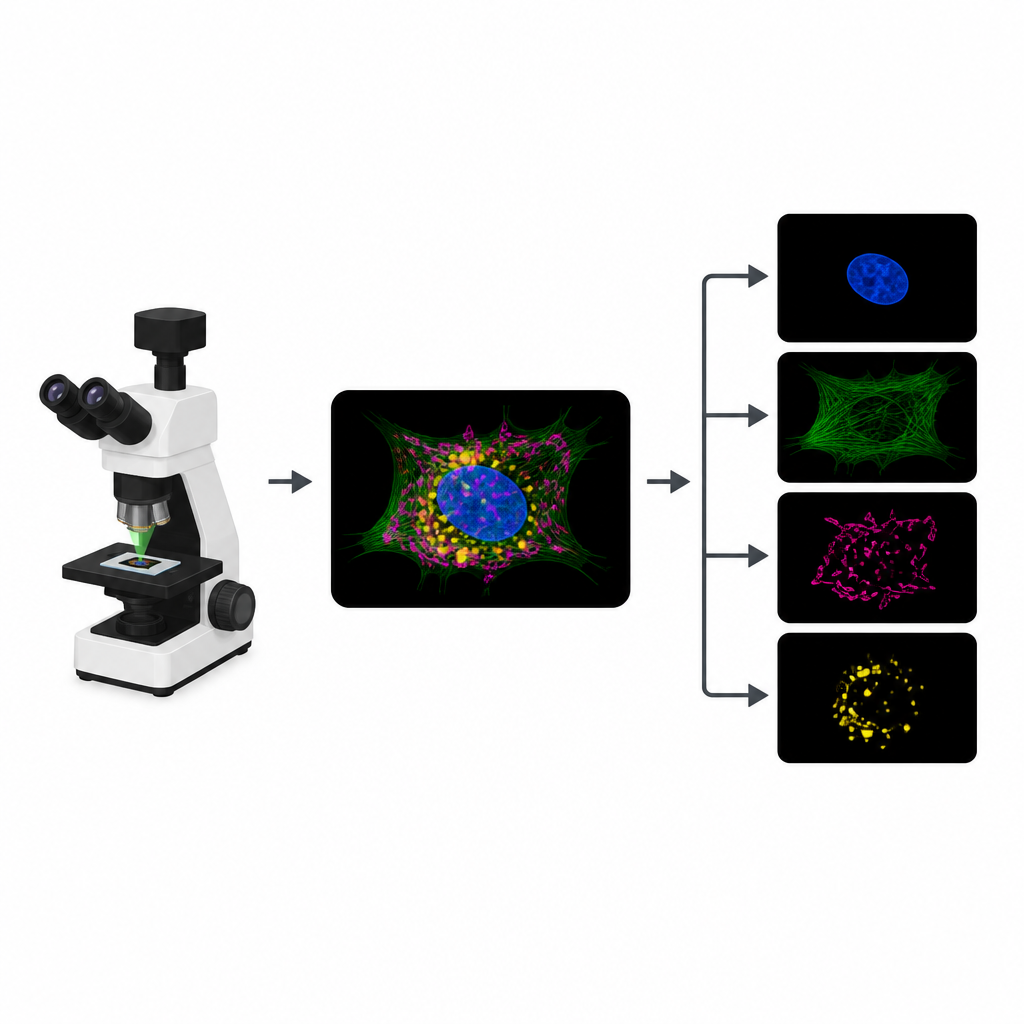
Por qué las células fluorescentes se topan con un límite
Para rastrear distintas partes de una célula, los biólogos fijan tintes fluorescentes distintos a estructuras como el núcleo, el citoesqueleto o las fábricas de energía. En un experimento típico, el microscopio registra un canal de imagen separado por cada tinte. Sin embargo, los tintes a menudo responden a colores de luz similares, por lo que sus señales se solapan. Ese solapamiento limita cuántas estructuras se pueden seguir a la vez. Además, cada canal extra implica otra ronda de iluminación, lo que consume el limitado “presupuesto de fotones” y puede ralentizar las películas, difuminar detalles o dañar las muestras vivas.
Convertir una imagen saturada en muchas limpias
MicroSplit aborda este compromiso cambiando cómo se recoge y procesa la información. En lugar de tomar varias imágenes separadas, los científicos pueden marcar múltiples estructuras como de costumbre pero registrarlas juntas en un único canal fluorescente. Esta imagen única y abarrotada se introduce en un modelo de aprendizaje profundo que ha sido entrenado para “desmezclar” los patrones que observa. La red produce varias imágenes limpiadas, cada una resaltando una estructura diferente como si se hubiera capturado en su propio canal desde el principio.
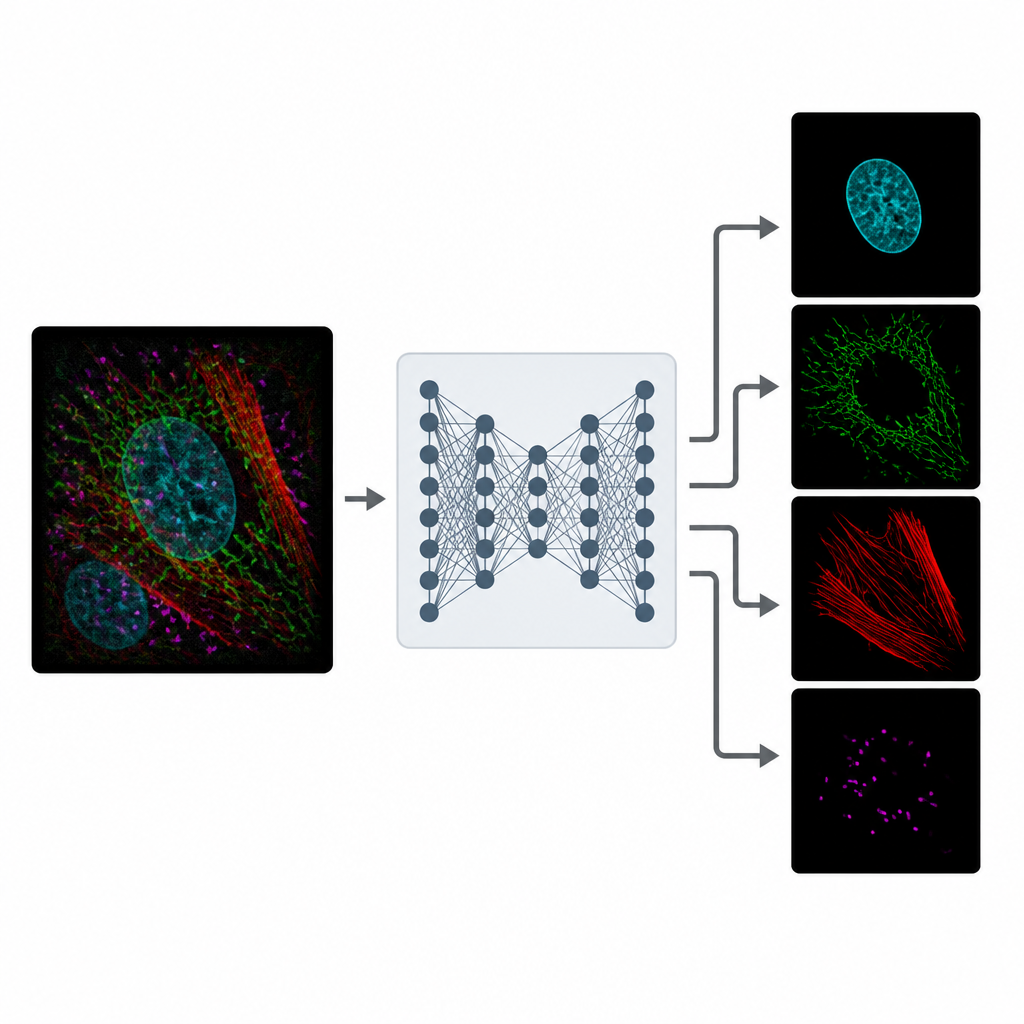
Aprender a partir de la realidad ruidosa
Entrenar a MicroSplit no requiere imágenes de referencia impecables. Los autores muestran que el modelo puede aprender a partir de datos microscópicos ordinarios y ruidosos, que son mucho más fáciles de obtener. Durante el entrenamiento, el sistema recibe ejemplos donde están disponibles los canales separados y su combinación sumada. Aprende dos cosas a la vez: cómo separar estructuras solapadas y cómo eliminar el ruido. Usando un tipo especial de red neuronal que muestrea muchas soluciones plausibles, MicroSplit también puede estimar dónde sus propias predicciones son inciertas, señalando regiones que deberían tratarse con cautela o revisarse por un experto.
Funcionando a través de conjuntos de datos y usos
Los investigadores probaron MicroSplit en diez conjuntos de datos microscópicos diferentes, abarcando dos y tres dimensiones e implicando hasta cuatro estructuras celulares solapadas. En 30 tareas principales, las imágenes separadas fueron lo bastante precisas como para soportar análisis posteriores estándar, como la segmentación de partes celulares. En pruebas cuidadosas, analistas humanos produjeron segmentaciones igualmente consistentes sobre las salidas de MicroSplit y sobre imágenes multicanal convencionales. El método también puede invertirse para eliminar características no deseadas: enseñando a MicroSplit a distinguir señal verdadera de motas recurrentes o manchas, el modelo puede restar esos artefactos de imagen preservando las estructuras reales.
Conocer los límites
MicroSplit no es mágico, y los autores exploran abiertamente cuándo tiene dificultades. El rendimiento cae si las imágenes originales son extremadamente ruidosas, si una estructura es mucho más tenue que otra, o si dos estructuras se parecen casi idénticas. En tales casos, el modelo tiende a suavizar detalles muy finos en vez de inventar nitidez falsa. No obstante, incluso con tiempos de exposición cortos, MicroSplit a menudo produce imágenes separadas lo suficientemente buenas para trabajos cuantitativos, usando muchos menos fotones que los enfoques tradicionales.
Qué significa esto para la imagen futura
Para quienes no son especialistas, el mensaje clave es que MicroSplit permite a los microscopios “ver” más estructuras en menos tiempo y con menos luz al trasladar parte del trabajo del hardware al software. En lugar de estar limitados por cuántos colores puede separar ópticamente un microscopio, los investigadores pueden combinar señales en un canal y dejar que MicroSplit haga la clasificación. Esto libera luz para hacer películas más rápidas, captar estructuras tenues con más suavidad o añadir etiquetas extra que antes eran poco prácticas. Al publicar el código, los datos y los modelos entrenados de forma abierta, los autores quieren que este tipo de multiplexación computacional se convierta en una práctica habitual en la imagen biológica.
Cita: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
Palabras clave: microscopía de fluorescencia, aprendizaje profundo, separación de imágenes, multiplexación computacional, análisis de bioimágenes