Clear Sky Science · pl
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : semantyczne rozdzielanie danych z mikroskopii fluorescencyjnej
Widzieć więcej przy mniejszym świetle
Nowoczesne mikroskopy pozwalają naukowcom obserwować żywe komórki w działaniu, ale każdy obraz ma swoją cenę. Każde błyskanie światła może uszkodzić delikatne komórki, a użycie wielu różnych znaczników fluorescencyjnych szybko napotyka ograniczenia fizyczne. W artykule przedstawiono MicroSplit — sztuczkę obliczeniową, która pozwala badaczom zarejestrować kilka struktur komórkowych na jednym, prostszym obrazie, a następnie rozdzielić je w komputerze, zmniejszając obciążenie zarówno mikroskopu, jak i samych komórek.
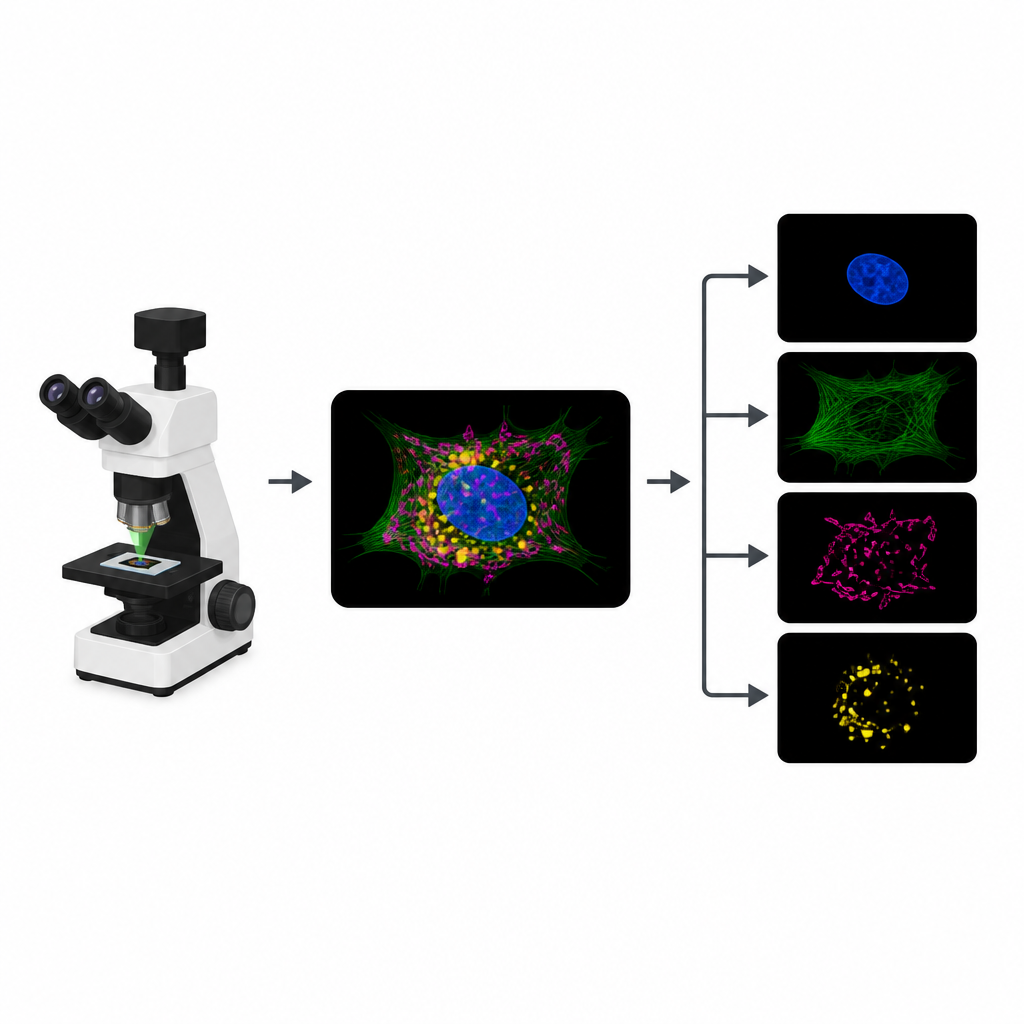
Dlaczego świecące komórki napotykają ścianę
Aby śledzić różne części komórki, biolodzy przyłączają odrębne barwniki fluorescencyjne do struktur takich jak jądro, cytoszkielet czy organelle energetyczne. W typowym eksperymencie mikroskop rejestruje osobny kanał obrazu dla każdego barwnika. Jednak barwniki często reagują na podobne kolory światła, więc ich sygnały się nakładają. To nakładanie ogranicza liczbę struktur, które można jednocześnie śledzić. Dodatkowo każdy dodatkowy kanał oznacza kolejną rundę naświetlania, która zużywa ograniczony „budżet fotonów” i może spowalniać nagrania, rozmywać detale lub szkodzić żywym próbkom.
Przekształcanie jednego zatłoczonego obrazu w wiele przejrzystych
MicroSplit rozwiązuje ten kompromis, zmieniając sposób zbierania i przetwarzania informacji. Zamiast robić kilka odrębnych zdjęć, naukowcy mogą oznaczyć wiele struktur jak zwykle, ale zarejestrować je razem w jednym kanale fluorescencyjnym. Ten pojedynczy, zatłoczony obraz jest następnie podawany do modelu głębokiego uczenia, który został wytrenowany, by „rozmieszać” widziane wzory. Sieć zwraca kilka oczyszczonych obrazów, z których każdy uwypukla inną strukturę, tak jakby została ona sfotografowana w swoim własnym kanale od samego początku.
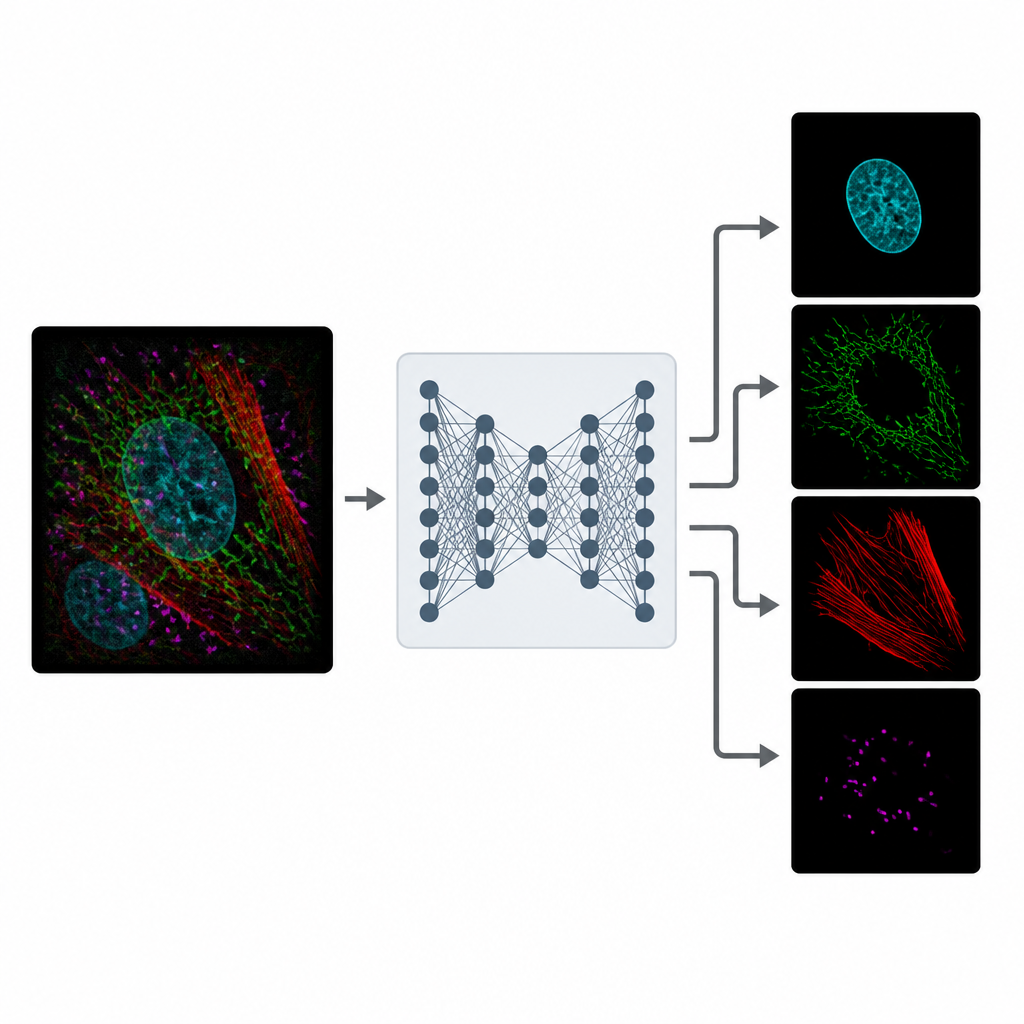
Uczenie się z hałaśliwej rzeczywistości
Trenowanie MicroSplit nie wymaga idealnych obrazów referencyjnych. Autorzy pokazują, że model może uczyć się na zwykłych, zaszumionych danych mikroskopowych, które są znacznie łatwiejsze do pozyskania. Podczas treningu system otrzymuje przykłady, w których dostępne są osobne kanały i ich suma. Uczy się dwóch rzeczy jednocześnie: jak rozdzielać nakładające się struktury i jak redukować szum. Przy użyciu specjalnego typu sieci neuronowej, która próbuje wielu prawdopodobnych rozwiązań, MicroSplit może także oszacować, gdzie jego predykcje są niepewne, wskazując obszary, które warto traktować z ostrożnością lub sprawdzić przez eksperta.
Praca w różnych zbiorach danych i zastosowaniach
Naukowcy przetestowali MicroSplit na dziesięciu różnych zbiorach mikroskopowych, obejmujących wymiary 2D i 3D oraz do czterech nakładających się struktur komórkowych. W 30 głównych zadaniach rozdzielone obrazy były wystarczająco dokładne, by wspierać standardowe analizy dalsze, takie jak segmentacja części komórek. W starannych testach analitycy ludzie uzyskali równie spójne segmentacje na wynikach MicroSplit i na konwencjonalnych obrazach wielokanałowych. Metodę można też wykorzystać odwrotnie, do usuwania niepożądanych elementów: ucząc MicroSplit rozróżniania prawdziwego sygnału od powtarzających się plamek czy skaz, model może odfiltrować te artefakty obrazowania, zachowując prawdziwe struktury.
Znajomość ograniczeń
MicroSplit nie jest magią, a autorzy otwarcie omawiają, kiedy ma problemy. Wydajność spada, jeśli oryginalne obrazy są ekstremalnie zaszumione, jeśli jedna struktura jest znacznie słabsza od innej lub jeśli dwie struktury wyglądają niemal identycznie. W takich przypadkach model ma tendencję do wygładzania bardzo drobnych detali zamiast tworzenia fałszywej ostrości. Niemniej jednak, nawet przy krótkich czasach ekspozycji, MicroSplit często dostarcza rozdzielone obrazy wystarczające do pracy ilościowej, przy użyciu znacznie mniejszej liczby fotonów niż tradycyjne podejścia.
Co to oznacza dla przyszłych obrazowań
Dla osób spoza specjalizacji kluczowy wniosek jest taki, że MicroSplit pozwala mikroskopom „widzieć” więcej struktur w krótszym czasie i przy mniejszym świetle, przesuwając część zadania z sprzętu do oprogramowania. Zamiast być ograniczonym przez liczbę kolorów, które mikroskop może optycznie rozdzielić, badacze mogą łączyć sygnały w jednym kanale i pozwolić MicroSplit je uporządkować. To uwalnia światło, pozwalając szybciej rejestrować filmy, delikatniej uchwycić słabe struktury lub dodać dodatkowe znaczniki, które wcześniej były niepraktyczne. Publikując kod, dane i wytrenowane modele otwarcie, autorzy dążą do tego, by tego rodzaju obliczeniowe multipleksowanie stało się rutynową częścią obrazowania biologicznego.
Cytowanie: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
Słowa kluczowe: mikroskopia fluorescencyjna, głębokie uczenie, rozdzielanie obrazów, obliczeniowe multipleksowanie, analiza bioobrazów