Clear Sky Science · nl
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : semantische ontmenging van fluorescentiemicroscopiegegevens
Meer zien met minder licht
Moderne microscopen laten wetenschappers levende cellen in actie observeren, maar elke opname heeft een prijs. Iedere lichtflits kan fragiele cellen beschadigen, en het gebruik van veel verschillende fluorescerende labels stuit snel op fysieke grenzen. Dit artikel introduceert MicroSplit, een computationele truc waarmee onderzoekers meerdere celstructuren in één enkele, eenvoudigere opname kunnen vastleggen en ze later op de computer kunnen scheiden, waardoor zowel de microscoop als de cellen minder belast worden.
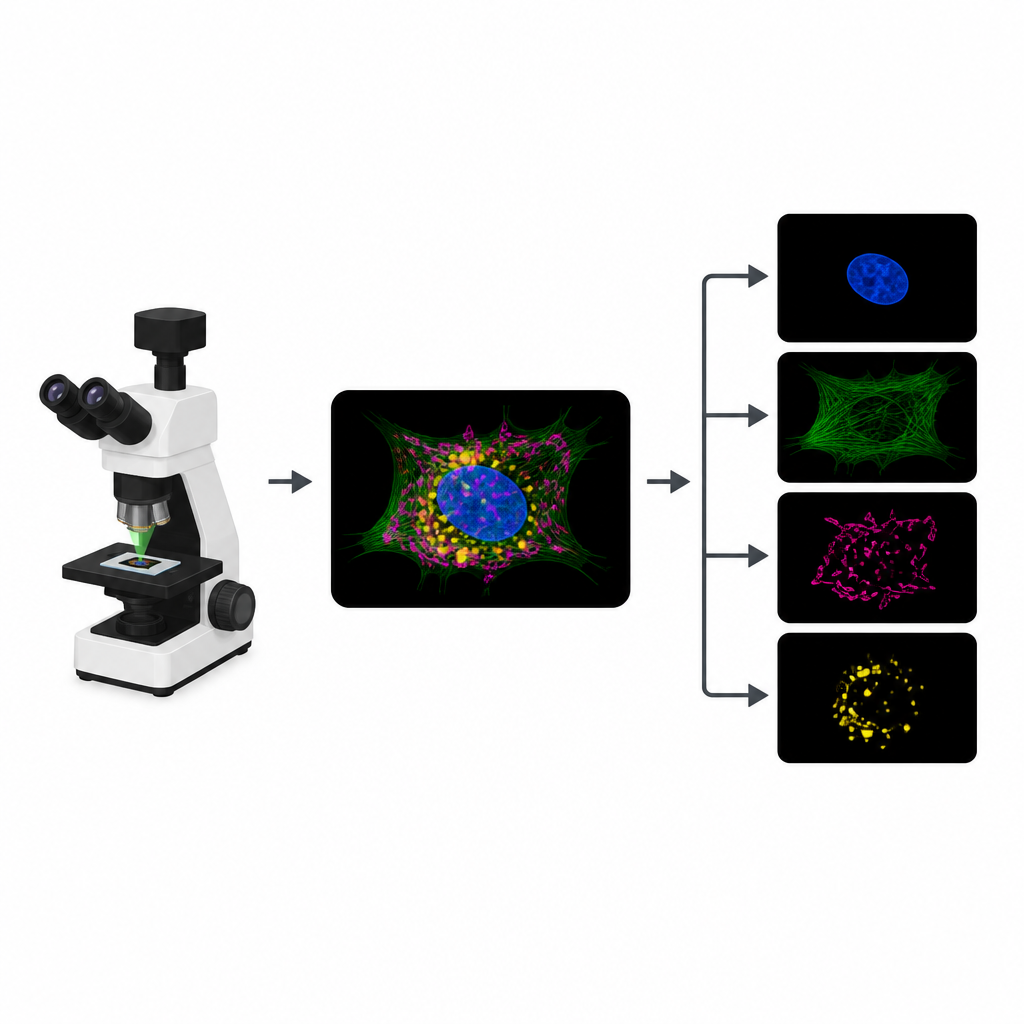
Waarom gloeiende cellen op grenzen stuiten
Om verschillende delen van een cel te volgen, koppelen biologen specifieke fluorescentiedragers aan structuren zoals de kern, het cytoskelet of de energiecentrales. In een gewoon experiment registreert de microscoop voor elke kleurstof een apart afbeeldingskanaal. De kleurstoffen reageren echter vaak op vergelijkbare lichtkleuren, waardoor hun signalen overlappen. Die overlap beperkt hoeveel structuren tegelijk gevolgd kunnen worden. Bovendien betekent elk extra kanaal een extra belichtingsronde, wat het beperkte "fotonenbudget" aantast en films kan vertragen, details kan vervagen of levende monsters kan beschadigen.
Van één drukke afbeelding naar meerdere heldere
MicroSplit pakt deze afweging aan door te veranderen hoe informatie wordt verzameld en verwerkt. In plaats van meerdere aparte opnames kunnen onderzoekers verschillende structuren zoals gebruikelijk labelen maar ze samen opnemen in één enkel fluorescentiekanaal. Deze ene, drukke afbeelding wordt vervolgens ingevoerd in een deep learning-model dat getraind is om de patronen te "ontmengen" die het ziet. Het netwerk levert meerdere opgeschoonde beelden op, elk gericht op een andere structuur alsof die vanaf het begin in zijn eigen kanaal was vastgelegd.
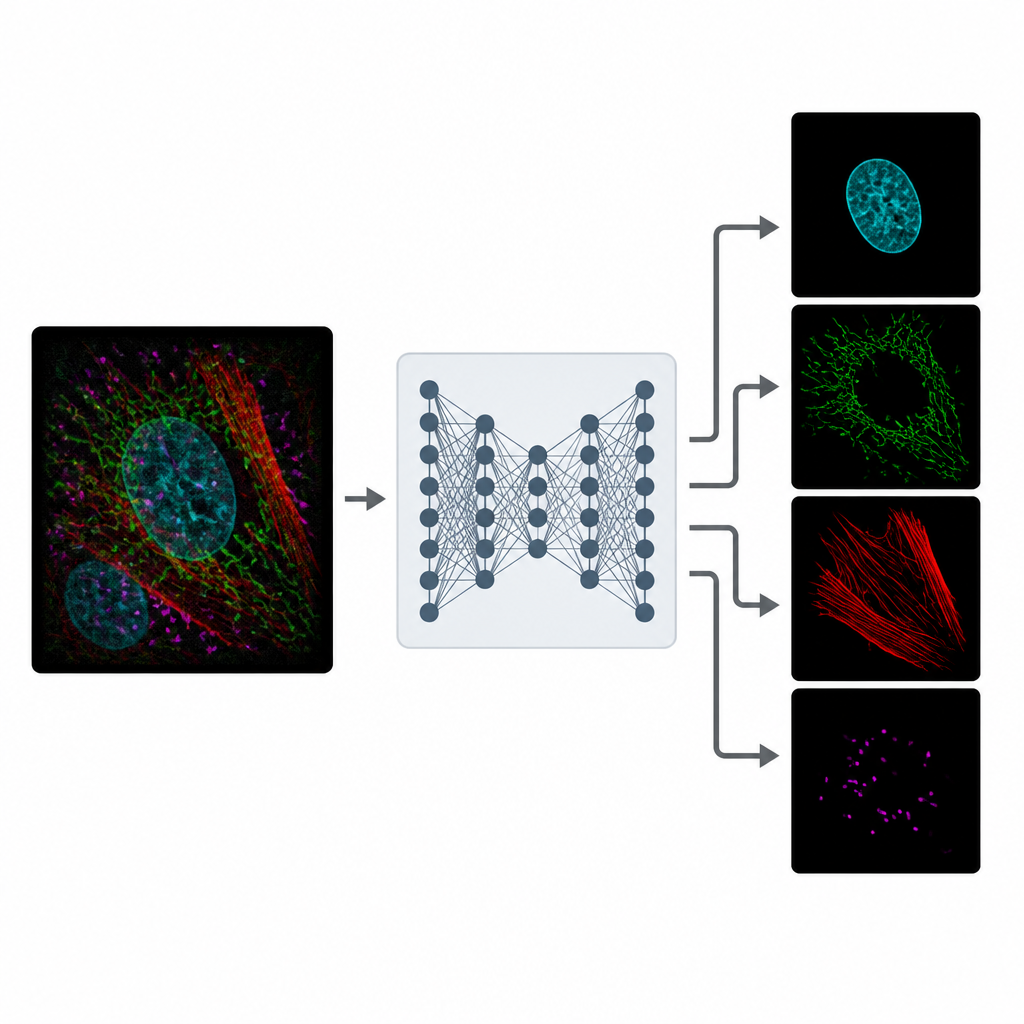
Leren van luidruchtige realiteit
Het trainen van MicroSplit vereist geen vlekkeloze referentieafbeeldingen. De auteurs tonen aan dat het model kan leren van gewone, rumoerige microscoopdata, die veel makkelijker te verkrijgen zijn. Tijdens het trainen krijgt het systeem voorbeelden waarbij afzonderlijke kanalen en hun opgetelde combinatie beschikbaar zijn. Het leert twee dingen tegelijk: hoe overlappende structuren te scheiden en hoe ruis te verwijderen. Met een speciaal type neuraal netwerk dat veel plausibele oplossingen kan bemonsteren, kan MicroSplit ook inschatten waar zijn eigen voorspellingen onzeker zijn en zo gebieden markeren die met voorzichtigheid behandeld of door een expert gecontroleerd moeten worden.
Werkt over datasets en toepassingen heen
De onderzoekers testten MicroSplit op tien verschillende microscopiedatasets, variërend van twee- tot driedimensionaal en met maximaal vier overlappende celstructuren. Over 30 hoofdtaken waren de gescheiden beelden nauwkeurig genoeg om standaard vervolganalyses zoals segmentatie van celonderdelen te ondersteunen. In zorgvuldige tests produceerden menselijke analisten even consistente segmentaties op MicroSplit-uitvoer als op conventionele multikanaalbeelden. De methode kan ook omgekeerd worden gebruikt om ongewenste kenmerken te verwijderen: door MicroSplit te leren het echte signaal te onderscheiden van terugkerende vlekjes of vlekken, kan het model deze beeldartefacten wegsubtracten terwijl echte structuren behouden blijven.
De grenzen kennen
MicroSplit is geen tovermiddel, en de auteurs onderzoeken openlijk wanneer het moeite heeft. De prestatie neemt af als de oorspronkelijke beelden extreem lawaaierig zijn, als de ene structuur veel zwakker is dan de andere, of als twee structuren bijna identiek lijken. In zulke gevallen neigt het model ernaar zeer fijne details te versoepelen in plaats van valse scherpte te verzinnen. Desondanks levert MicroSplit, zelfs bij korte belichtingstijden, vaak gescheiden beelden die goed genoeg zijn voor kwantitatief werk, terwijl het veel minder fotonen gebruikt dan traditionele benaderingen.
Wat dit betekent voor toekomstige beeldvorming
Voor niet-specialisten is de kernboodschap dat MicroSplit microscopen in staat stelt meer structuren in minder tijd en met minder licht te "zien" door een deel van het werk van hardware naar software te verplaatsen. In plaats van beperkt te zijn door hoeveel kleuren een microscoop optisch kan scheiden, kunnen onderzoekers signalen in één kanaal combineren en MicroSplit het sorteerwerk laten doen. Dit maakt licht vrij om films sneller te maken, zwakke structuren zachter vast te leggen of extra labels toe te voegen die eerder onpraktisch waren. Door de code, data en getrainde modellen openlijk vrij te geven, streven de auteurs ernaar dit soort computationele multiplexing tot een routinemethode in biologische beeldvorming te maken.
Bronvermelding: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
Trefwoorden: fluorescentiemicroscopie, deep learning, beeldontmenging, computationale multiplexing, bioimage-analyse