Clear Sky Science · it
$${\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}$$ : separazione semantica dei dati di microscopia fluorescente
Vedere di più con meno luce
I microscopi moderni permettono agli scienziati di osservare le cellule vive in azione, ma ogni immagine ha un costo. Ogni lampo di luce può danneggiare cellule delicate, e l’uso di molti marcatori fluorescenti incontra rapidamente limiti fisici. Questo articolo presenta MicroSplit, un espediente computazionale che consente ai ricercatori di acquisire più strutture cellulari in una singola immagine più semplice e poi separarle al computer, riducendo la pressione sia sul microscopio sia sulle cellule stesse.
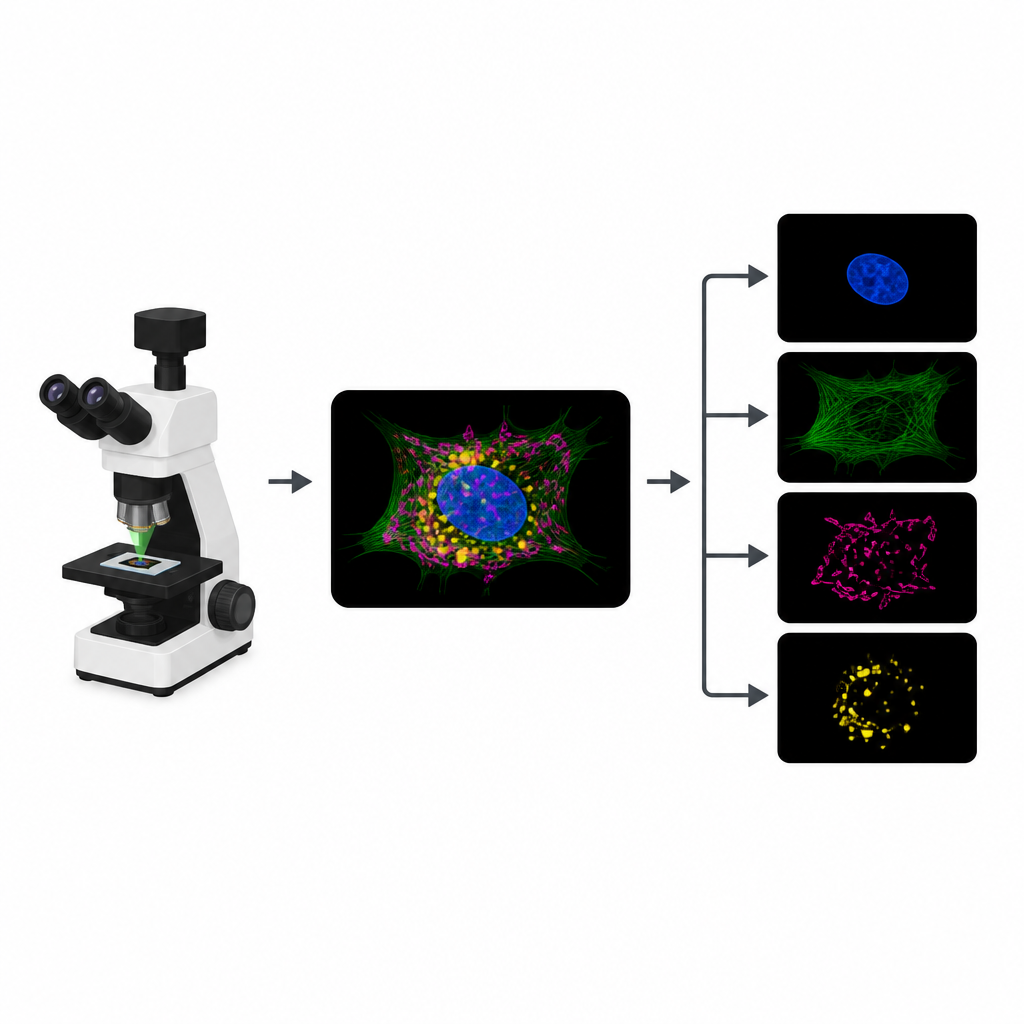
Perché le cellule fluorescenti incontrano un limite
Per tracciare parti diverse di una cellula, i biologi legano coloranti fluorescenti distinti a strutture come il nucleo, il citoscheletro o le centrali energetiche. In un esperimento tipico, il microscopio registra un canale immagine separato per ciascun colorante. Tuttavia, i coloranti spesso rispondono a gamme di luce simili, perciò i loro segnali si sovrappongono. Questa sovrapposizione limita il numero di strutture che si possono seguire contemporaneamente. Inoltre, ogni canale aggiuntivo richiede un’ulteriore illuminazione, che consuma un limitato “budget di fotoni” e può rallentare le riprese, sfocare i dettagli o danneggiare i campioni viventi.
Trasformare un’immagine affollata in molte immagini chiare
MicroSplit affronta questo compromesso cambiando il modo in cui l’informazione viene raccolta e processata. Invece di scattare più immagini separate, gli scienziati possono marcare più strutture come al solito ma registrarne i segnali insieme in un unico canale fluorescente. Questa singola immagine affollata viene poi fornita a un modello di deep learning addestrato a “separare” i pattern che osserva. La rete restituisce diverse immagini ripulite, ognuna delle quali evidenzia una struttura diversa come se fosse stata acquisita nel proprio canale fin dall’inizio.
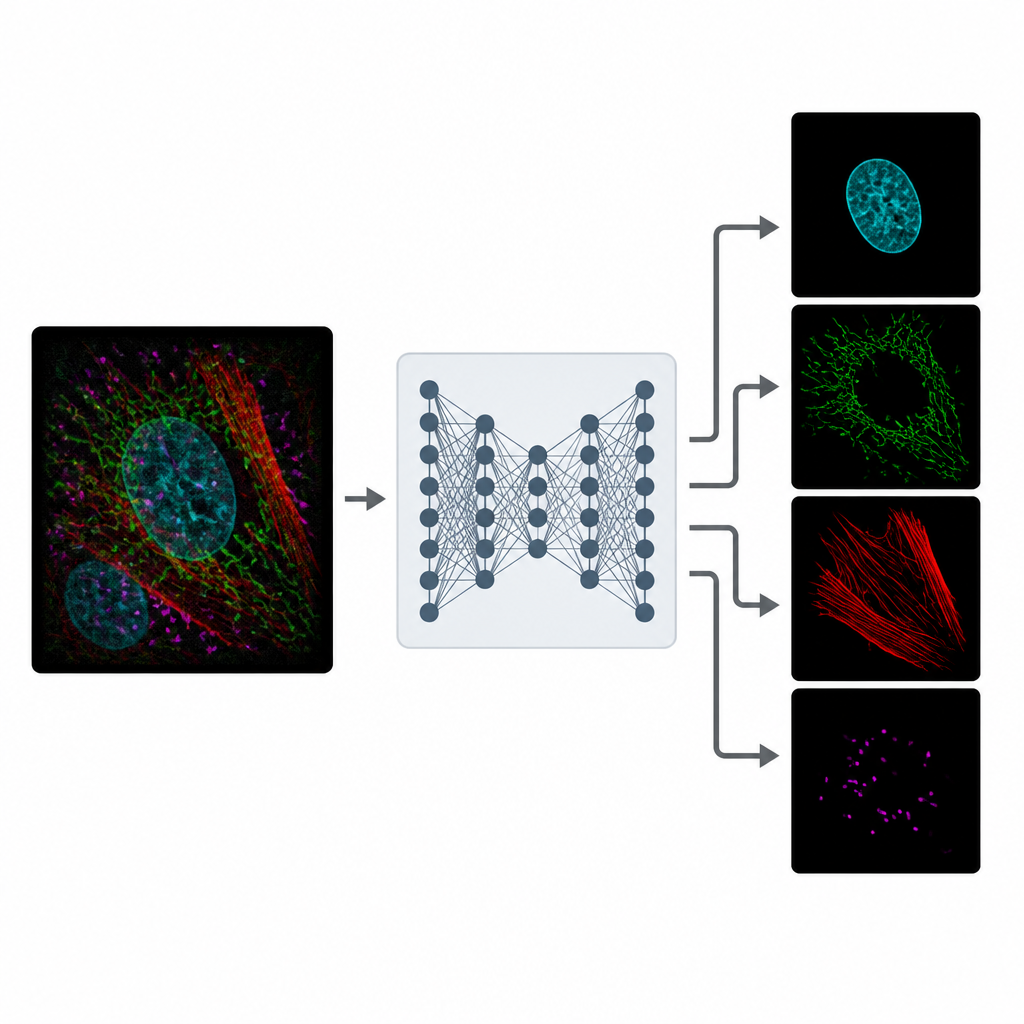
Apprendere dalla realtà rumorosa
L’addestramento di MicroSplit non richiede immagini di riferimento perfette. Gli autori dimostrano che il modello può imparare da dati microscopici ordinari e rumorosi, molto più facili da ottenere. Durante l’addestramento, al sistema vengono mostrati esempi in cui sono disponibili i canali separati e la loro somma combinata. Impara due cose contemporaneamente: come separare strutture sovrapposte e come rimuovere il rumore. Usando un tipo speciale di rete neurale che campiona molte soluzioni plausibili, MicroSplit può anche stimare dove le proprie predizioni sono incerte, segnalando regioni che dovrebbero essere trattate con cautela o verificate da un esperto.
Funzionare su dataset e usi diversi
I ricercatori hanno testato MicroSplit su dieci diversi dataset di microscopia, coprendo dimensioni bidimensionali e tridimensionali e coinvolgendo fino a quattro strutture cellulari sovrapposte. Su 30 compiti principali, le immagini separate erano sufficientemente accurate da supportare analisi successive standard come la segmentazione delle parti cellulari. In test accurati, gli analisti umani hanno prodotto segmentazioni altrettanto coerenti su output di MicroSplit e su immagini multicanale convenzionali. Il metodo può anche essere invertito per rimuovere caratteristiche indesiderate: insegnando a MicroSplit a distinguere il segnale reale da macchie ricorrenti o difetti, il modello può sottrarre questi artefatti di imaging preservando le strutture reali.
Conoscere i limiti
MicroSplit non è magia, e gli autori esplorano apertamente quando incontra difficoltà. Le prestazioni calano se le immagini originali sono estremamente rumorose, se una struttura è molto più debole di un’altra o se due strutture appaiono quasi identiche. In tali casi, il modello tende a levigare dettagli finissimi piuttosto che inventare nettezza falsa. Ciononostante, anche con tempi di esposizione brevi, MicroSplit spesso fornisce immagini separate abbastanza valide per lavori quantitativi, usando molti meno fotoni rispetto agli approcci tradizionali.
Cosa significa per l’imaging futuro
Per il pubblico non specialista, il messaggio chiave è che MicroSplit permette ai microscopi di “vedere” più strutture in meno tempo e con meno luce spostando parte del lavoro dall’hardware al software. Invece di essere limitati da quante “colori” un microscopio può separare otticamente, i ricercatori possono combinare i segnali in un singolo canale e lasciare che MicroSplit faccia l’ordinamento. Questo libera luce per accelerare le riprese, catturare strutture deboli in modo più delicato o aggiungere etichette extra prima impraticabili. Rilasciando codice, dati e modelli addestrati in modo aperto, gli autori mirano a rendere questo tipo di multiplex computazionale una pratica di routine nell’imaging biologico.
Citazione: Ashesh, A., Carrara, F., Zubarev, I. et al. \({\bf{Micro}}{{\mathbb{S}}}{\bf{plit}}\): semantic unmixing of fluorescent microscopy data. Nat Methods 23, 1047–1057 (2026). https://doi.org/10.1038/s41592-026-03082-1
Parole chiave: microscopia a fluorescenza, deep learning, separazione delle immagini, multiplex computazionale, analisi di bioimmagini