Clear Sky Science · zh
XA-Novo:用于单克隆抗体和抗体混合物的高通量质谱去新测序技术
为何解读抗体至关重要
抗体是识别病毒、细菌甚至癌细胞的微小Y形蛋白,具有惊人的特异性。要将它们转化为强效药物或诊断工具,科学家需要其精确的氨基酸“拼写”——也就是序列。但读取该序列通常耗时、昂贵,且现有基于DNA的方法有时无法做到。这项研究介绍了XA-Novo,一种直接从蛋白质本身读取抗体序列的新技术,借助质谱和智能算法实现更快、更准确的测序,甚至可应对复杂的抗体混合物。
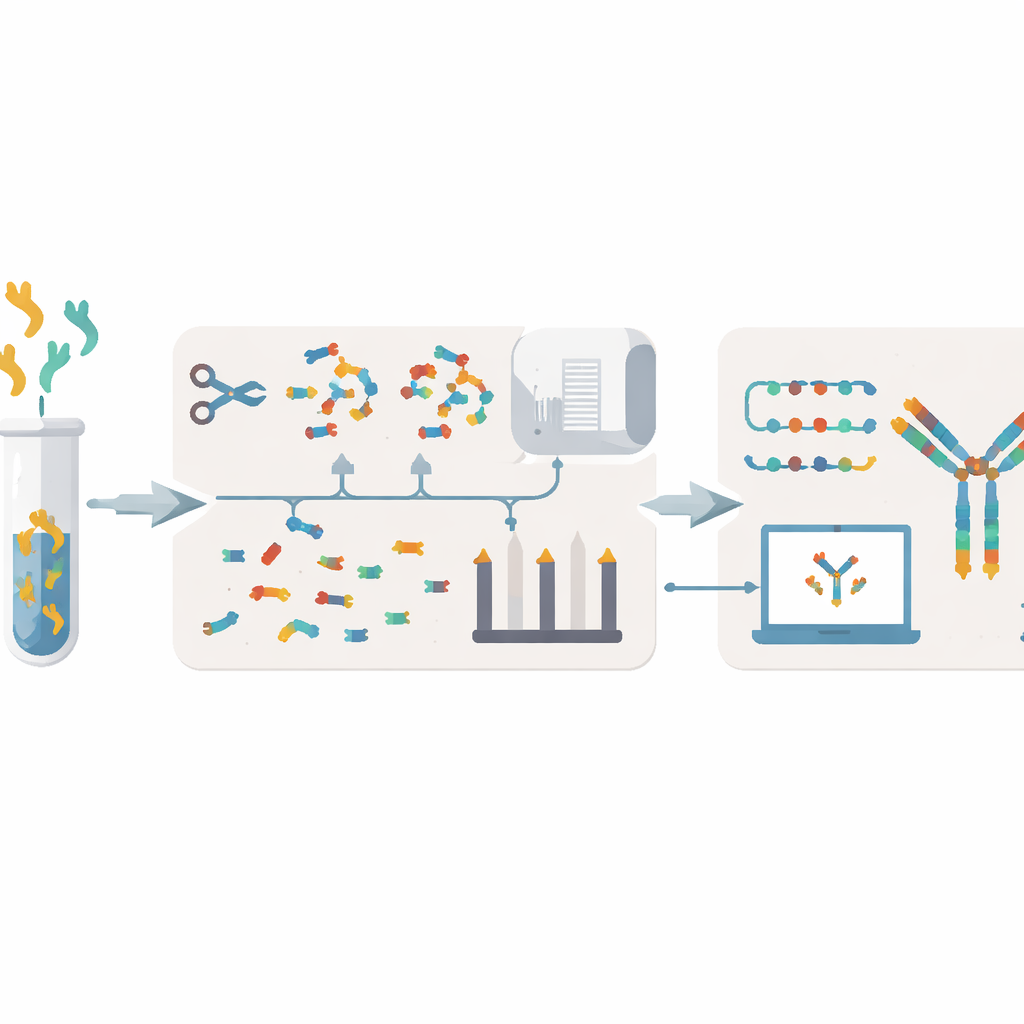
当前读取抗体“配方”的障碍
传统的抗体解码方法通常从产生抗体的细胞入手。研究人员培养杂交瘤细胞或分离B细胞,提取其遗传物质,然后对DNA或RNA进行测序。这些方法可能需要数周到数月,依赖可能脆弱或易丢失的活细胞,有时仍会留下空白或错误。它们也难以说明血液或粘液中游离抗体与产生它们的B细胞群体之间的真实关系。另一种替代方法是在蛋白水平上工作,将抗体切割成小片段并用质谱分析。然而现有的质谱方法往往需要大量样本、通量低,并且在多种相似抗体同时存在时容易错误组装序列。
从蛋白质起步的新流程
XA-Novo通过将改良的化学方法、先进的质谱技术和现代机器学习结合到一个简化的工作流程中来解决这些问题。首先,抗体通过“单管多酶梯度消化”策略被温和但彻底地切割成具有重叠的肽段,五种不同的酶按时间错开作用。这增加了片段的多样性和重叠度,同时不浪费宝贵样本。接着,这些片段在两种互补的碎片化模式下用高分辨率质谱分析,生成丰富的光谱信息,捕捉每个肽段如何断裂的细节。
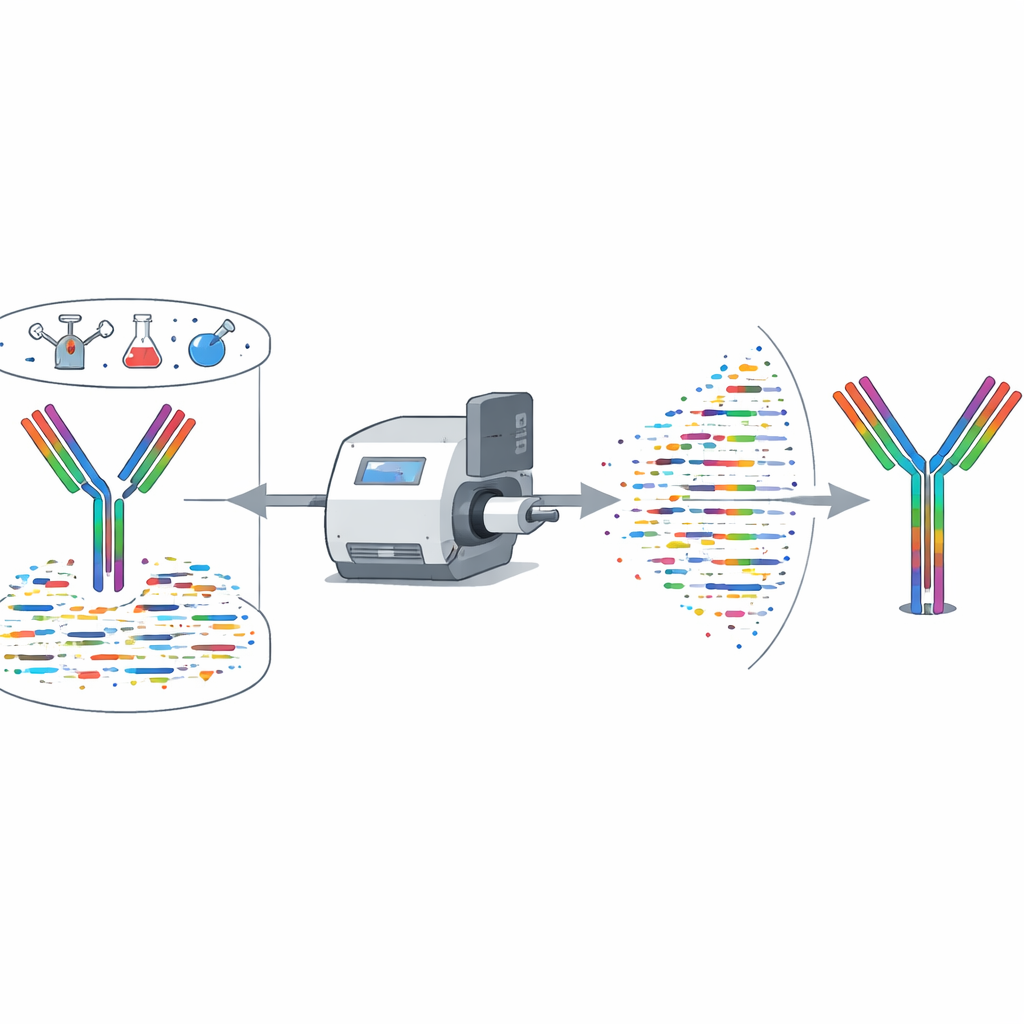
深度学习与智能组装
在采集光谱后,XA-Novo使用名为Casanovo的深度学习模型将复杂的质量峰模式翻译为预测的肽序列,类似语言模型在语言之间翻译。得到的众多短“读段”随后传递给一个名为Fusion的新组装器。Fusion采用beam-search(束搜索)策略并利用已知抗体模板的信息,将重叠肽段拼接为完整的重链和轻链。它被设计用来处理常见难点——例如质量几乎相同的氨基酸和抗体用于结合的变化最多的互补决定区(CDR)——同时避免会破坏功能的缺口、插入和错序段。
方法的实测验证
作者对来自人和小鼠且已知序列的抗体(包括数种中和SARS-CoV-2的抗体)对XA-Novo进行了严格基准测试。与商业工具和公开算法相比,XA-Novo在序列覆盖率和准确性方面始终表现更优,在关键结合区域实现了完整且无错误的重构。即使从仅50微克抗体起始,也能可靠工作。研究团队随后处理了六种未经公开的治疗性抗体。XA-Novo解码了它们的重链和轻链序列,这些序列随后被克隆并表达,所得抗体在小鼠体内进行了测试。体内实验显示,经重构的抗体在减少目标免疫细胞或巨噬细胞方面与原始商业版本同样有效,证实了解码序列在功能上是正确的。
一次处理抗体混合物
许多真实样本包含抗体混合物,而不是单一纯品。XA-Novo在同时含有两种或三种COVID-19中和抗体的混合样本(包含人源和小鼠抗体)上接受了挑战。系统以至少99.54%的准确覆盖率(通常为100%)恢复了每个组分的序列,包括变化最大的结合环。这一性能优于通常仅限于单一抗体的现有组装器。作者还构建了网页界面,研究者可以上传质谱数据并获取重构的抗体序列和覆盖图,而无需专用硬件或复杂设置。
对未来抗体药物的意义
XA-Novo表明,现在可以直接从蛋白样本中读出完整、高度准确的抗体序列,即便在混合物中也能做到,所需样本量适中且工作流程基本自动化。对非专业人士而言,这意味着在实验室或临床发现的有前景抗体可以更快地被逆向工程、可靠地复制并被改造出更佳版本。通过使抗体测序更快、更易扩展且不那么依赖脆弱的细胞系,XA-Novo有望加速基础免疫学研究,帮助追踪像COVID-19这样的感染的免疫反应,并推动基于抗体的疗法的开发与优化。
引用: Xiong, Y., Jiang, W., Xiao, J. et al. XA-Novo: high-throughput mass spectrometry-based de novo sequencing technology for monoclonal antibodies and antibody mixtures. Nat Commun 17, 3391 (2026). https://doi.org/10.1038/s41467-026-70496-y
关键词: 抗体测序, 质谱, 单克隆抗体, COVID-19中和抗体, 蛋白质工程