Clear Sky Science · pt
XA-Novo: tecnologia de sequenciamento de novo baseada em espectrometria de massas de alto rendimento para anticorpos monoclonais e misturas de anticorpos
Por que decodificar anticorpos importa
Anticorpos são pequenas proteínas em forma de Y que reconhecem vírus, bactérias e até células cancerígenas com notável precisão. Para transformá‑los em medicamentos poderosos ou ferramentas de diagnóstico, os cientistas precisam da “ortografia” exata de aminoácidos — sua sequência. Mas ler essa sequência costuma ser lento, caro e às vezes impossível com os métodos atuais baseados em DNA. Este estudo apresenta o XA‑Novo, uma nova tecnologia que lê sequências de anticorpos diretamente nas proteínas, utilizando espectrometria de massas e algoritmos inteligentes para fazer o trabalho mais rápido, com maior precisão e mesmo em misturas complexas de anticorpos.
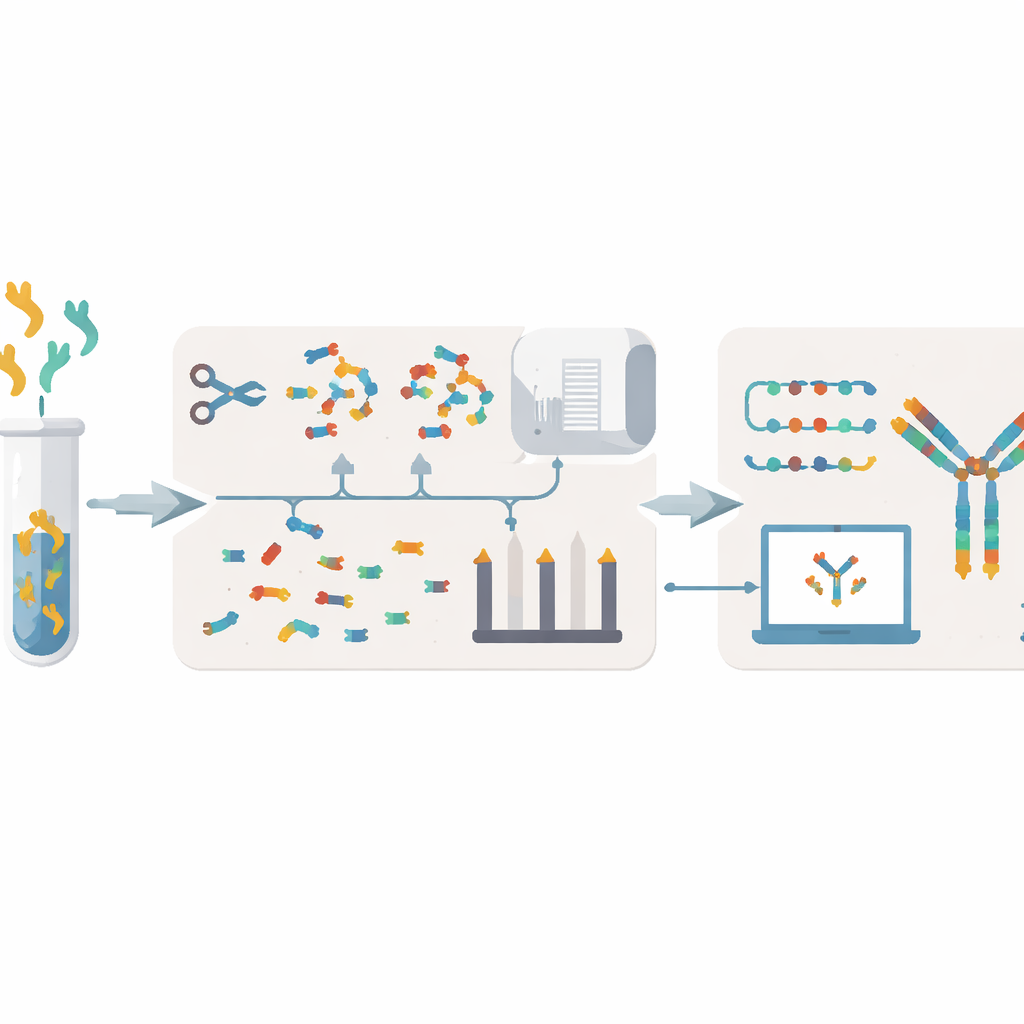
Obstáculos atuais para ler as receitas de anticorpos
As formas tradicionais de decodificar anticorpos geralmente começam pelas células que os produzem. Pesquisadores cultivam células híbridas ou isolam células B, extraem seu material genético e então sequenciam o DNA ou RNA. Essas abordagens podem levar semanas a meses, exigem células vivas que podem ser frágeis ou perdidas, e às vezes ainda deixam lacunas ou erros. Elas também têm dificuldade em relacionar com precisão os anticorpos presentes no sangue ou muco à população de células B que os produziu. Uma alternativa é trabalhar ao nível da proteína, quebrando os anticorpos em pequenos pedaços e analisando‑os por espectrometria de massas. No entanto, os métodos atuais de espectrometria frequentemente exigem grandes quantidades de amostra, têm baixo rendimento e podem montar sequências de forma incorreta, especialmente quando muitas proteínas semelhantes estão presentes juntas.
Um novo fluxo de trabalho que parte das proteínas
O XA‑Novo enfrenta essas questões ao combinar química aprimorada, espectrometria de massas avançada e aprendizado de máquina moderno em um fluxo de trabalho integrado. Primeiro, os anticorpos são suavemente, mas de forma abrangente, fragmentados em peptídeos sobrepostos usando uma estratégia de “digestão em gradiente multienzimática em um único recipiente”, na qual cinco enzimas diferentes atuam em tempos escalonados. Isso aumenta a diversidade e a sobreposição de fragmentos sem desperdiçar amostra preciosa. Em seguida, esses fragmentos são analisados por espectrometria de massas de alta resolução sob dois modos complementares de fragmentação, gerando informação espectral rica que captura como cada peptídeo se rompe.
Aprendizado profundo e montagem inteligente
Uma vez coletados os espectros, o XA‑Novo usa um modelo de aprendizado profundo chamado Casanovo para traduzir os padrões complexos de picos de massa em previsões de sequências peptídicas, de forma análoga a um modelo de linguagem traduzindo entre idiomas. Essas muitas leituras curtas são então passadas a um novo montador chamado Fusion. O Fusion utiliza uma estratégia de busca em feixe e informações de moldes de anticorpos conhecidos para costurar peptídeos sobrepostos em cadeias pesadas e leves completas. Foi projetado para lidar com pontos problemáticos comuns — como aminoácidos com massas quase idênticas e regiões onde os anticorpos variam mais para o reconhecimento, chamadas regiões determinantes de complementaridade — ao mesmo tempo em que evita lacunas, inserções e trechos com ordem incorreta que podem comprometer a função.
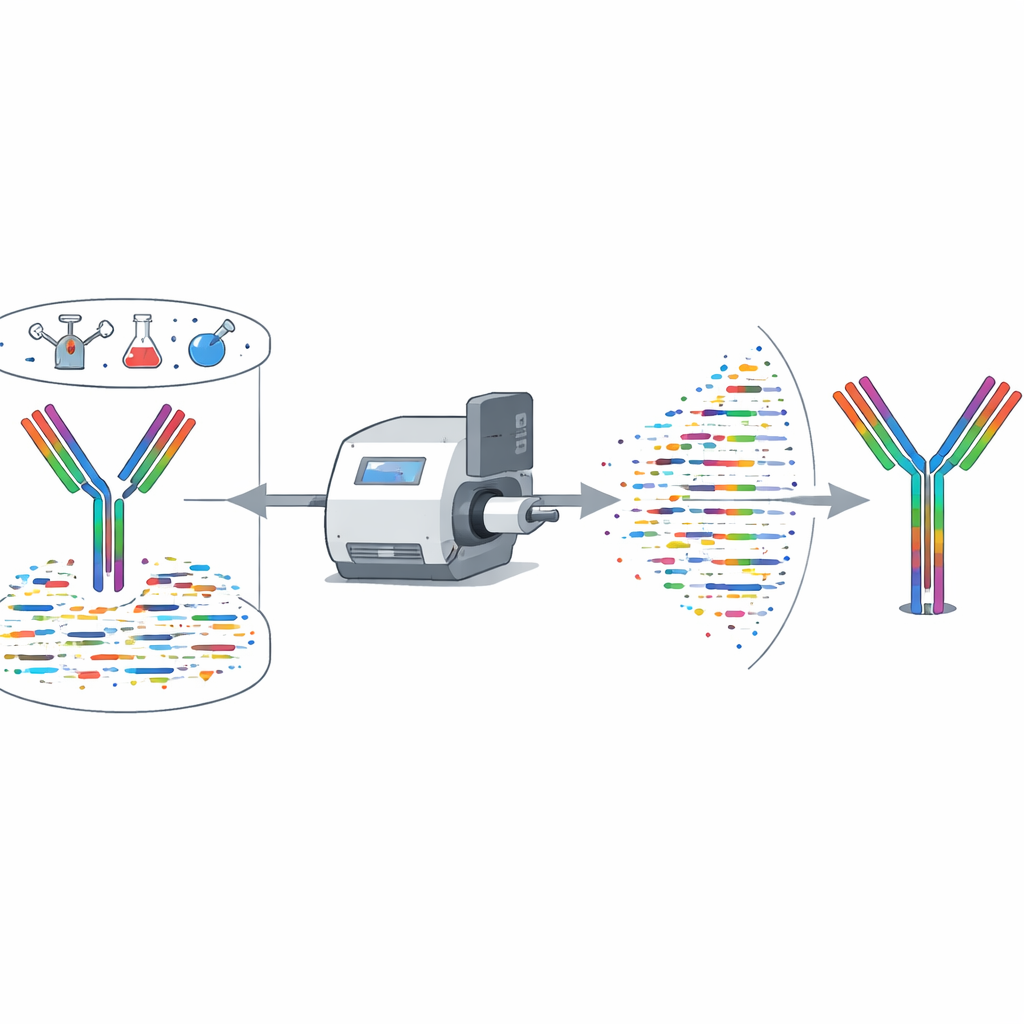
Testando o método
Os autores avaliaram rigorosamente o XA‑Novo em anticorpos com sequências conhecidas de humanos e camundongos, incluindo vários que neutralizam o SARS‑CoV‑2. Em comparação com ferramentas comerciais e algoritmos públicos, o XA‑Novo alcançou consistentemente maior cobertura e precisão de sequência, com reconstrução completa e sem erros nas regiões críticas de ligação. Funcionou de forma confiável mesmo partindo de tão pouco quanto 50 microgramas de anticorpo. A equipe então analisou seis anticorpos terapêuticos cujas sequências não eram publicamente disponíveis. O XA‑Novo decodificou suas cadeias pesadas e leves, as sequências foram clonadas e expressas, e os anticorpos resultantes foram testados em camundongos. Experimentos in vivo mostraram que esses anticorpos reconstruídos eliminaram suas células‑alvo ou macrófagos com a mesma eficácia que as versões comerciais originais, confirmando que as sequências decodificadas eram funcionalmente corretas.
Processando misturas de anticorpos de uma vez
Muitas amostras do mundo real contêm misturas de anticorpos em vez de um único anticorpo puro. O XA‑Novo foi testado com combinações de duas ou três anticorpos neutralizantes da COVID‑19 ao mesmo tempo, tanto humanos quanto de camundongo. O sistema recuperou a sequência de cada componente com pelo menos 99,54% de cobertura precisa, e frequentemente 100%, incluindo os loops de ligação mais variáveis. Esse desempenho supera montadores existentes que normalmente são limitados a anticorpos únicos. Os autores também construíram uma interface web para que pesquisadores possam enviar dados de espectrometria de massas e obter sequências de anticorpos reconstruídas e mapas de cobertura sem hardware especializado ou configuração complexa.
O que isso significa para futuros medicamentos à base de anticorpos
O XA‑Novo demonstra que agora é possível ler sequências completas e altamente precisas de anticorpos diretamente de amostras proteicas, mesmo em misturas, usando quantidades modestas de material e um fluxo de trabalho em grande parte automatizado. Para não especialistas, isso significa que anticorpos promissores descobertos em laboratório ou clínica podem ser revertidos mais rapidamente, reproduzidos de forma confiável e modificados para versões melhores. Ao tornar o sequenciamento de anticorpos mais rápido, escalável e menos dependente de linhagens celulares frágeis, o XA‑Novo pode acelerar estudos básicos de imunologia, ajudar a acompanhar respostas imunes a infecções como a COVID‑19 e acelerar o desenvolvimento e otimização de terapias baseadas em anticorpos.
Citação: Xiong, Y., Jiang, W., Xiao, J. et al. XA-Novo: high-throughput mass spectrometry-based de novo sequencing technology for monoclonal antibodies and antibody mixtures. Nat Commun 17, 3391 (2026). https://doi.org/10.1038/s41467-026-70496-y
Palavras-chave: sequenciamento de anticorpos, espectrometria de massas, anticorpos monoclonais, anticorpos neutralizantes da COVID-19, engenharia de proteínas