Clear Sky Science · it
XA-Novo: tecnologia di de novo sequencing ad alto rendimento basata sulla spettrometria di massa per anticorpi monoclonali e miscele di anticorpi
Perché decodificare gli anticorpi è importante
Gli anticorpi sono piccole proteine a forma di Y che riconoscono virus, batteri e persino cellule tumorali con sorprendente precisione. Per trasformarli in farmaci potenti o strumenti diagnostici, gli scienziati hanno bisogno della loro esatta “ortografia” amminoacidica — la sequenza. Ma leggere quella sequenza è spesso lento, costoso e talvolta impossibile con i metodi basati sul DNA attuali. Questo studio presenta XA-Novo, una nuova tecnologia che legge le sequenze degli anticorpi direttamente dalle proteine stesse, utilizzando la spettrometria di massa e algoritmi intelligenti per svolgere il lavoro più rapidamente, con maggiore accuratezza e anche per miscele complesse di anticorpi.
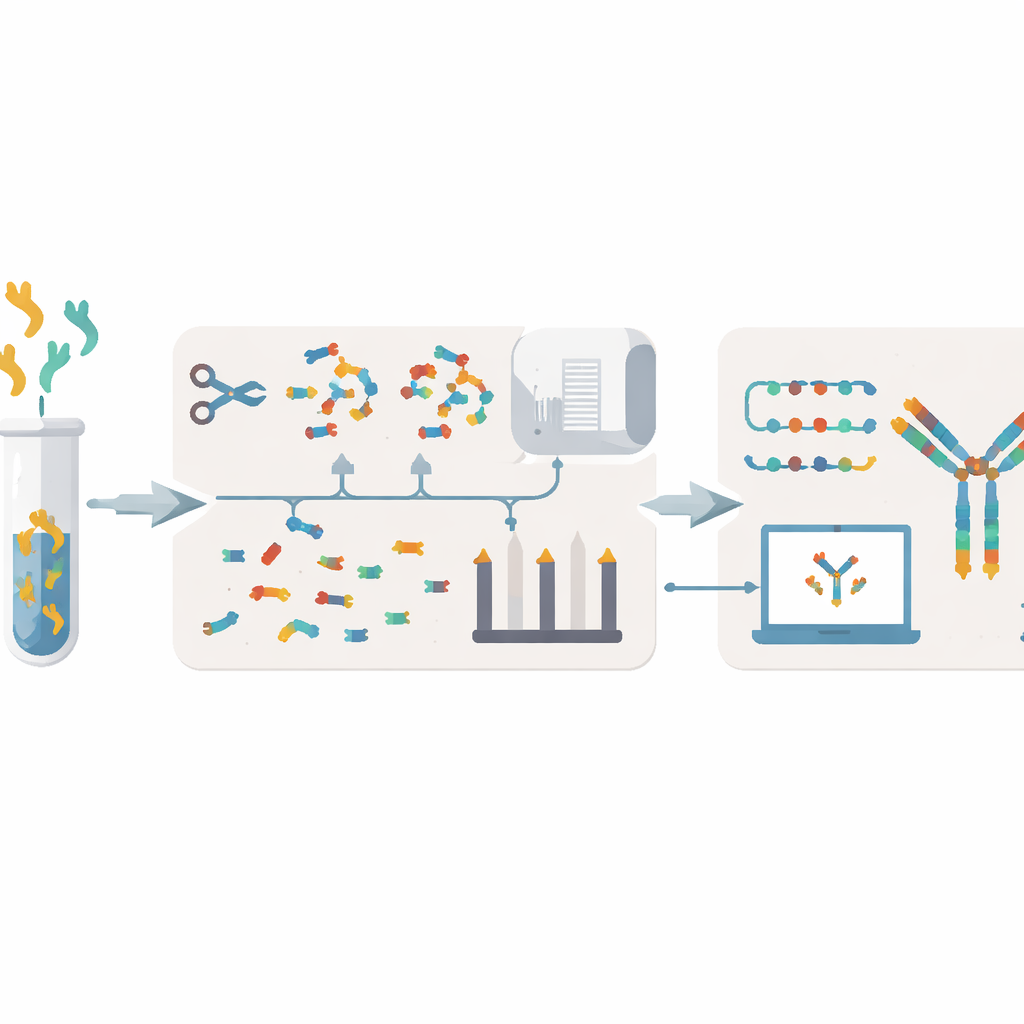
Ostacoli attuali alla lettura delle “ricette” degli anticorpi
I metodi tradizionali per decodificare gli anticorpi di solito partono dalle cellule che li producono. I ricercatori coltivano cellule ibridome o isolano cellule B, estraggono il materiale genetico e poi sequenziano il DNA o l’RNA. Questi approcci possono richiedere settimane o mesi, richiedono cellule vive che possono essere fragili o perdute e talvolta lasciano comunque lacune o errori. Inoltre faticano a dire come gli anticorpi circolanti nel sangue o nel muco si relazionino realmente alla popolazione di cellule B che li ha prodotti. Un’alternativa è lavorare a livello proteico, scomponendo gli anticorpi in piccoli pezzi e analizzandoli con la spettrometria di massa. Tuttavia i metodi di spettrometria esistenti spesso richiedono grandi quantità di campione, hanno bassa produttività e possono assemblare in modo errato le sequenze, specialmente quando sono presenti molteplici anticorpi simili simultaneamente.
Una nuova pipeline che parte dalle proteine
XA-Novo affronta questi problemi combinando chimica migliorata, spettrometria di massa avanzata e apprendimento automatico moderno in un unico flusso di lavoro razionalizzato. Innanzitutto, gli anticorpi vengono delicatamente ma in modo completo frammentati in peptidi sovrapposti usando una strategia di “digestione graduale multi-enzimatica in singola provetta”, in cui cinque enzimi diversi agiscono in modo sfalsato nel tempo. Questo aumenta la diversità e la sovrapposizione dei frammenti senza sprecare campione prezioso. Successivamente questi frammenti vengono analizzati tramite spettrometria di massa ad alta risoluzione in due modalità di frammentazione complementari, generando informazioni spettrali ricche che catturano come ogni peptide si rompe.
Deep learning e assemblaggio intelligente
Una volta raccolti gli spettri, XA-Novo utilizza un modello di deep learning chiamato Casanovo per tradurre i complessi pattern dei picchi di massa in sequenze peptidiche previste, un po’ come un modello linguistico che traduce tra lingue. Queste molte brevi “letture” vengono poi passate a un nuovo assemblatore chiamato Fusion. Fusion usa una strategia di beam search e informazioni da template di anticorpi noti per cucire insieme i peptidi sovrapposti in catene pesanti e leggere complete. È progettato per gestire punti problematici comuni — come amminoacidi con masse quasi identiche e regioni in cui gli anticorpi variano maggiormente per il legame, chiamate regioni determinanti della complementarità — evitando nel contempo gap, inserzioni e tratti disordinati che possono compromettere la funzione.
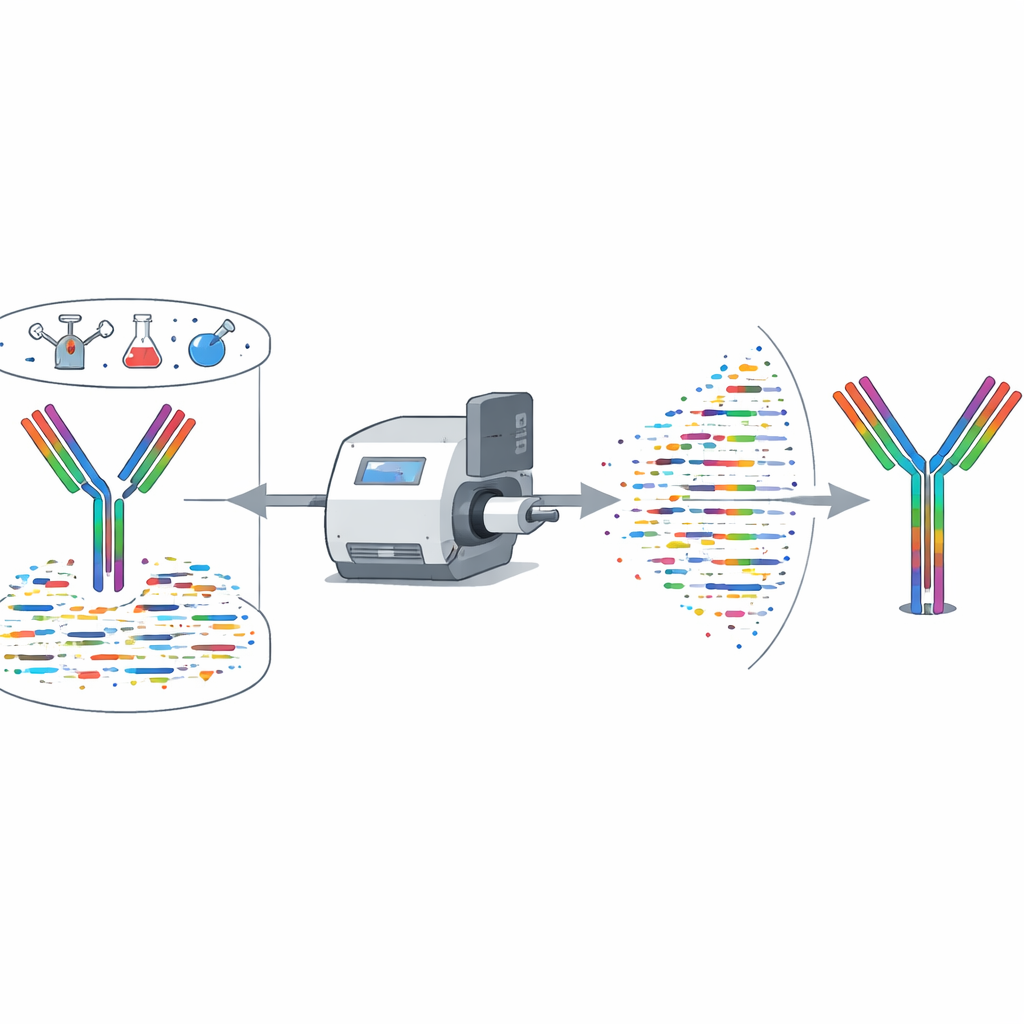
Mettere il metodo alla prova
Gli autori hanno valutato in modo rigoroso XA-Novo su anticorpi con sequenze note di umano e topo, inclusi diversi anticorpi che neutralizzano SARS-CoV-2. Rispetto a strumenti commerciali e algoritmi pubblici, XA-Novo ha ottenuto costantemente maggiore copertura e accuratezza delle sequenze, con ricostruzioni complete e prive di errori nelle regioni critiche di legame. Ha funzionato in modo affidabile anche partendo da appena 50 microgrammi di anticorpo. Il team ha poi affrontato sei anticorpi terapeutici le cui sequenze non erano pubblicamente disponibili. XA-Novo ha decodificato le loro catene pesanti e leggere, le sequenze sono state clonate ed espresse, e gli anticorpi risultanti sono stati testati in topi. Gli esperimenti in vivo hanno mostrato che questi anticorpi ricostruiti depledivano le cellule immunitarie bersaglio o i macrofagi con la stessa efficacia delle versioni commerciali originali, confermando che le sequenze decodificate erano funzionalmente corrette.
Gestire miscele di anticorpi in una volta
Molti campioni reali contengono miscele di anticorpi anziché un singolo anticorpo puro. XA-Novo è stato messo alla prova con blend di due o tre anticorpi neutralizzanti COVID-19 alla volta, sia per anticorpi umani che murini. Il sistema ha recuperato la sequenza di ciascun componente con almeno il 99,54% di copertura accurata, e spesso il 100%, incluse le anse di legame più variabili. Questa prestazione supera gli assemblatori esistenti che sono tipicamente limitati a anticorpi singoli. Gli autori hanno anche creato un’interfaccia web in modo che i ricercatori possano caricare dati di spettrometria di massa e ottenere sequenze ricostruite di anticorpi e mappe di copertura senza hardware specializzato o configurazioni complesse.
Cosa significa per i futuri farmaci a base di anticorpi
XA-Novo dimostra che è ora possibile leggere sequenze anticorpali complete e altamente accurate direttamente da campioni proteici, anche in miscele, usando quantità modeste di materiale e un flusso di lavoro in gran parte automatizzato. Per i non specialisti, questo significa che anticorpi promettenti scoperti in laboratorio o in clinica possono essere ingegnerizzati al contrario più rapidamente, riprodotti in modo affidabile e ottimizzati in versioni migliorate. Rendendo il sequenziamento degli anticorpi più veloce, scalabile e meno dipendente da linee cellulari fragili, XA-Novo potrebbe accelerare gli studi di immunologia di base, aiutare a tracciare le risposte immunitarie a infezioni come il COVID-19 e velocizzare lo sviluppo e l’ottimizzazione di terapie basate su anticorpi.
Citazione: Xiong, Y., Jiang, W., Xiao, J. et al. XA-Novo: high-throughput mass spectrometry-based de novo sequencing technology for monoclonal antibodies and antibody mixtures. Nat Commun 17, 3391 (2026). https://doi.org/10.1038/s41467-026-70496-y
Parole chiave: sequenziamento degli anticorpi, spettrometria di massa, anticorpi monoclonali, anticorpi neutralizzanti COVID-19, ingegneria delle proteine