Clear Sky Science · sv
In-silico identifiering av genetiska varianter kopplade till kronisk lymfatisk leukemi för diagnostiska och terapeutiska tillämpningar
Varför det spelar roll att följa cancer i våra gener
Kronisk lymfatisk leukemi (KLL) är den vanligaste leukemin hos vuxna, men för många patienter förblir sjukdomen obotlig. Familjer till personer med KLL har en markant högre risk, vilket tyder på att ärftliga DNA-förändringar bidrar till sjukdomsutvecklingen. Denna studie ställer en praktisk fråga: kan vi använda storskaliga genetiska data och datoranalys för att peka ut de viktiga svagheterna i vårt DNA som driver KLL — och koppla dem till befintliga eller lovande läkemedel? Svaren skulle kunna förbättra tidig diagnos och leda till mer precisa, mindre slumpmässiga behandlingar.
Genomgång av tusentals genom
Forskarna började med att samla sammanfattande resultat från tre stora genome-wide association-studier, som skannar DNA från många personer med och utan KLL för att hitta små skillnader kopplade till sjukdomsrisk. Genom noggrann rensning och sammanslagning av dessa dataset, alla baserade på samma mänskliga referensgenom, ökade de den statistiska styrkan för att upptäcka subtila genetiska signaler. Med en metaanalysmetod som viktar studier efter precisionen i deras uppskattningar identifierade de 2 357 DNA-positioner, så kallade single nucleotide polymorphisms, som var starkt associerade med KLL. Dessa signaler klustrades i 40 områden i genomet, inklusive 11 regioner som tidigare inte kopplats till sjukdomen.
Från DNA-markörer till nyckelreglerande gener
De flesta riskmarkörerna låg mellan gener eller i icke-kodande delar av gener, där deras effekter inte är uppenbara. För att tolka dem använde teamet bioinformatiska verktyg som förbinder varje markör med närliggande gener eller med gener vars aktivitet i blodceller förändras när markören är närvarande. Denna kartläggning gav 60 gener som ligger i eller nära riskregionerna. Forskarna frågade sedan vilka av dessa gener som upptar centrala positioner i nätverket av protein–protein-kontakter inne i cellerna. En nätverksanalys lyfte fram sju gener — TERT, BCL2, BCL2L11, CFLAR, CASP8, LEF1 och FAS — som nav som kopplar många vägar. Oberoende sjukdomsdatabaser stödde starka länkar mellan dessa gener och KLL, samt andra blodcancerformer och immunrubbningar.
Hur störd celldöd driver leukemi
När teamet granskade vad dessa sju gener gör framträdde ett tydligt tema: de flesta kontrollerar om celler lever eller dör. Flera, inklusive BCL2 och BCL2L11, tillhör en familj som balanserar överlevnadssignaler med självdestruktiva signaler i cellens kraftverk, mitokondrierna. Andra — FAS, CFLAR och CASP8 — styr en parallell "dödsmottagar"-väg vid cellens yta. I KLL lutar denna maskinvara mot överlevnad: pro-överlevnadsproteiner är överaktiva, medan pro-döds-partners är blockerade eller minskade. Den återstående nyckelgenen, LEF1, sitter i en tillväxtväg som hjälper leukemiceller att fortsätta dela sig. När forskarna körde berikningsanalyser var de främsta biologiska temana celldöd, cancerrelaterade vägar och immunsignalering, vilket förstärker idén att ärvda varianter skjuter dessa kontrollsystem mot långlivade, abnorma B-celler.
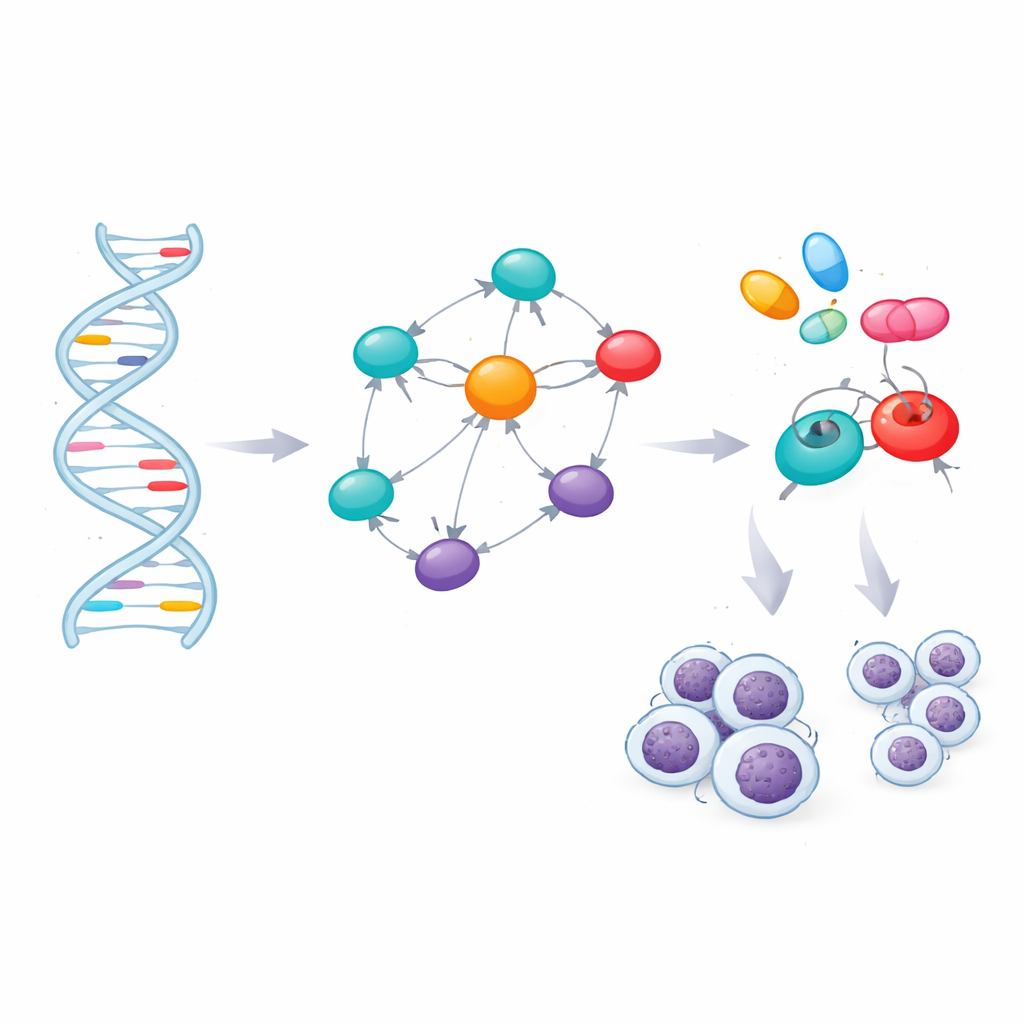
Koppla gener till läkemedel
Att identifiera avgörande gener öppnar dörren för riktad terapi, men bara om dessa gener kan påverkas av läkemedel. Teamet utvärderade de tredimensionella strukturerna hos de sju proteinerna och fann lovande fickor där små molekyler kan binda. De genomsökte sedan ett bibliotek med 166 befintliga eller experimentella föreningar kopplade till KLL eller relaterade tillstånd och använde molekylär dockningssimulering för att se vilka läkemedel som passade tajt in i nyckelproteinerna eller deras huvudregulatorer. Efter att ha rankat dessa virtuella interaktioner filtrerade de toppkandidaterna genom standardregler för "drug-likeness" och genom datorbaserade modeller som förutsäger hur väl en förening absorberas, distribueras, metaboliseras, utsöndras och hur giftig den kan vara. Denna konservativa sållning lämnade fyra starka kandidater: redan godkända cancerläkemedel ibrutinib, selinexor, imatinib och avapritinib.
Vad detta kan betyda för patienter
För personer som lever med KLL förändrar detta arbete ännu inte den dagliga vården, men det hjälper till att sammanföra ärftlig risk, leukemicellernas interna kopplingar och de läkemedel som bäst kan rubba den kopplingen. Två av de framhävda läkemedlen, ibrutinib och selinexor, används redan i KLL och verkar på sätt som stämmer med den genetiska bild som här kartlagts, särskilt genom att återställa balansen mot cancercellsdöd. Studien antyder också att imatinib och avapritinib, som idag används för andra cancerformer, kan förtjäna närmare prövning i KLL. Mer allmänt visar tillvägagångssättet hur gruvdrift i befintliga genetiska data med kraftfulla beräkningsverktyg kan avslöja centrala sjukdomsgeners betydelse och begränsa antalet potentiella terapier, vilket vägleder framtida laboratorieexperiment och kliniska prövningar mot de mest lovande målen.
Citering: Islam, M.S., Mollah, M.H., Ahsan, M.A. et al. In-silico identification of genetic variants associated with chronic lymphocytic leukemia for diagnostic and therapeutic applications. Sci Rep 16, 14545 (2026). https://doi.org/10.1038/s41598-026-45456-7
Nyckelord: kronisk lymfatisk leukemi, genetiska riskvarianter, apoptosvägar, läkemedelsomgöring, riktad cancerterapi