Clear Sky Science · pt
Identificação in silico de variantes genéticas associadas à leucemia linfocítica crônica para aplicações diagnósticas e terapêuticas
Por que rastrear o câncer em nossos genes importa
A leucemia linfocítica crônica (LLC) é a leucemia adulta mais comum, mas continua incurável para muitos pacientes. Familiares de pessoas com LLC apresentam risco marcadamente maior, sugerindo que alterações hereditárias no DNA contribuem para predispor à doença. Este estudo faz uma pergunta prática: podemos usar grandes conjuntos de dados genéticos e análise computacional para identificar os pontos fracos no nosso DNA que impulsionam a LLC — e então relacioná-los a medicamentos existentes ou promissores? As respostas podem melhorar o diagnóstico precoce e apontar tratamentos mais precisos, com menos tentativa e erro.
Analisando milhares de genomas
Os pesquisadores começaram reunindo resultados sumários de três grandes estudos de associação genômica ampla, que examinam o DNA de muitas pessoas com e sem LLC para encontrar pequenas diferenças ligadas ao risco da doença. Ao limpar e mesclar cuidadosamente esses conjuntos de dados, todos alinhados ao mesmo genoma de referência humano, aumentaram o poder estatístico para detectar sinais genéticos sutis. Usando um método de metanálise que pondera estudos pela precisão de suas estimativas, identificaram 2.357 posições no DNA, chamadas polimorfismos de nucleotídeo único, fortemente associadas à LLC. Esses sinais se agruparam em 40 trechos do genoma, incluindo 11 regiões que não haviam sido previamente vinculadas à doença.
De marcadores de DNA a genes de controle-chave
A maioria dos marcadores de risco ocorreu entre genes ou em partes não codificantes, onde seus efeitos não são evidentes. Para interpretá-los, a equipe usou ferramentas de bioinformática que ligam cada marcador a genes próximos ou a genes cuja atividade em células sanguíneas muda quando o marcador está presente. Esse mapeamento produziu 60 genes localizados nas ou nas proximidades das regiões de risco. Os cientistas então investigaram quais desses genes ocupam posições centrais na rede de interações proteína–proteína dentro das células. Uma análise de rede destacou sete genes — TERT, BCL2, BCL2L11, CFLAR, CASP8, LEF1 e FAS — como hubs que conectam muitas vias. Bancos de dados independentes de doenças reforçaram fortes ligações entre esses genes e a LLC, bem como outros cânceres sanguíneos e distúrbios imunológicos.
Como a perturbação da morte celular alimenta a leucemia
Ao examinar as funções desses sete genes, emergiu um tema claro: a maioria controla se as células vivem ou morrem. Vários, incluindo BCL2 e BCL2L11, pertencem a uma família que equilibra sinais de sobrevivência com sinais de autodestruição nas usinas da célula, as mitocôndrias. Outros — FAS, CFLAR e CASP8 — governam uma rota paralela de “receptores de morte” na superfície celular. Na LLC, essa maquinaria se inclina para a sobrevivência: proteínas pró-sobrevivência estão hiperativas, enquanto parceiras pró-morte estão bloqueadas ou reduzidas. O gene-chave restante, LEF1, integra uma via de crescimento que ajuda as células leucêmicas a continuar se dividindo. Quando os pesquisadores realizaram análises de enriquecimento, os principais temas biológicos foram morte celular, vias do câncer e sinalização imune, reforçando a ideia de que variantes hereditárias empurram esses sistemas de controle em direção a células B anormais e de longa duração.
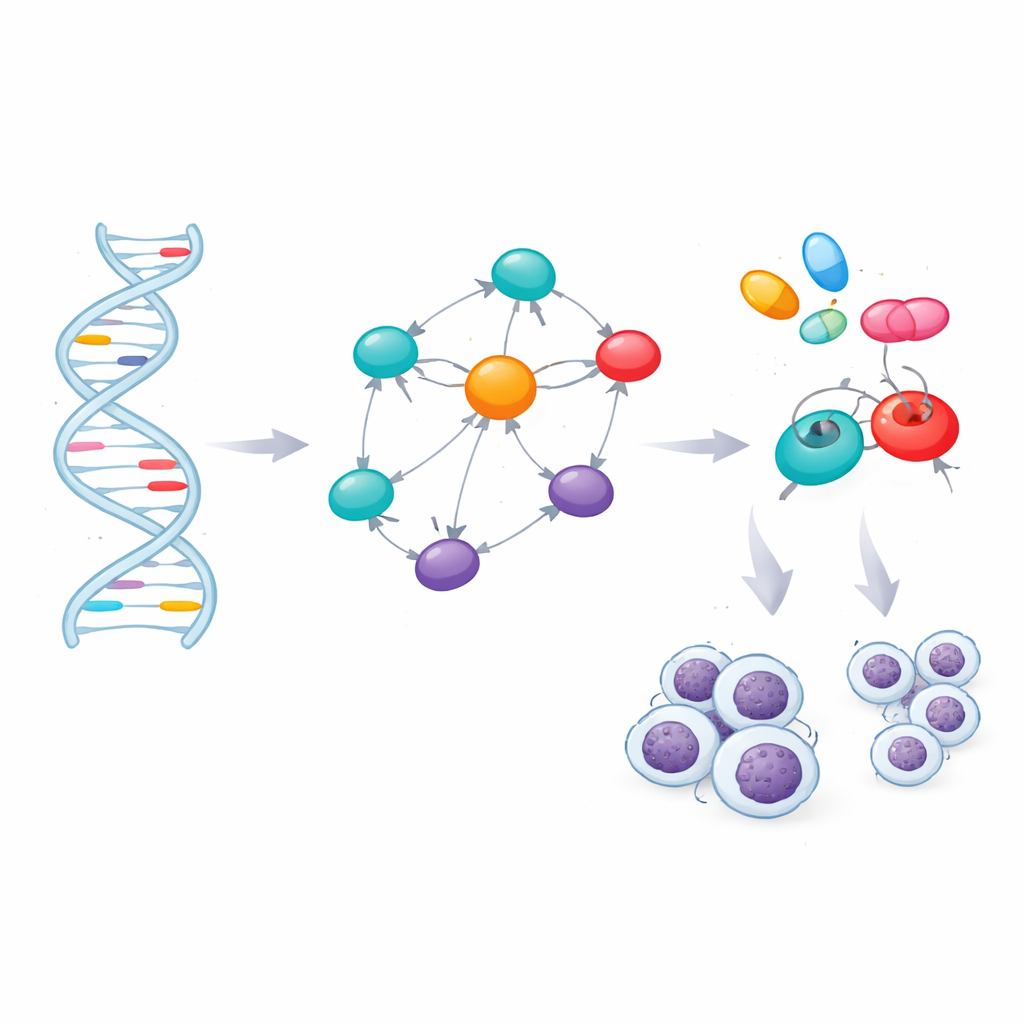
Relacionando genes a medicamentos
Identificar genes cruciais abre a porta para terapias direcionadas, mas somente se esses genes puderem ser modulados por fármacos. A equipe avaliou as estruturas tridimensionais das sete proteínas e encontrou bolsões promissores onde pequenas moléculas poderiam se ligar. Em seguida, vasculharam uma biblioteca de 166 compostos existentes ou experimentais ligados à LLC ou condições relacionadas e usaram simulações de docking molecular para ver quais medicamentos se encaixavam melhor nas proteínas-chave ou em seus principais reguladores. Após classificar essas interações virtuais, filtraram os principais candidatos por regras padrão de “características de fármaco” e por modelos computacionais que predizem quão bem um composto é absorvido, distribuído, metabolizado, excretado e sua potencial toxicidade. Essa triagem conservadora deixou quatro fortes candidatos: os já aprovados medicamentos contra o câncer ibrutinibe, selinexor, imatinibe e avapritinibe.
O que isso pode significar para os pacientes
Para pessoas vivendo com LLC, este trabalho ainda não altera o cuidado diário, mas ajuda a conectar pontos entre o risco hereditário, a fiação interna das células leucêmicas e os medicamentos que podem melhor desorganizar essa fiação. Dois dos fármacos destacados, ibrutinibe e selinexor, já são usados na LLC e atuam de maneiras que se encaixam no panorama genético revelado aqui, especialmente ao restaurar o equilíbrio em favor da morte das células cancerosas. O estudo também sugere que imatinibe e avapritinibe, atualmente usados em outros cânceres, podem merecer testes mais aprofundados na LLC. Em termos mais amplos, a abordagem demonstra como minerar dados genéticos existentes com ferramentas computacionais poderosas pode revelar genes-chave da doença e reduzir o campo de terapias potenciais, orientando experimentos de laboratório futuros e ensaios clínicos para os alvos mais promissores.
Citação: Islam, M.S., Mollah, M.H., Ahsan, M.A. et al. In-silico identification of genetic variants associated with chronic lymphocytic leukemia for diagnostic and therapeutic applications. Sci Rep 16, 14545 (2026). https://doi.org/10.1038/s41598-026-45456-7
Palavras-chave: leucemia linfocítica crônica, variantes genéticas de risco, vias de apoptose, reposicionamento de fármacos, terapia direcionada contra o câncer