Clear Sky Science · fr
Identification in silico de variants génétiques associées à la leucémie lymphoïde chronique pour des applications diagnostiques et thérapeutiques
Pourquoi il est important de surveiller le cancer dans nos gènes
La leucémie lymphoïde chronique (LLC) est la leucémie la plus fréquente chez l’adulte, et pourtant elle reste incurable pour de nombreux patients. Les familles de personnes atteintes de LLC présentent un risque nettement accru, ce qui suggère que des modifications héréditaires de l’ADN contribuent à prédisposer à la maladie. Cette étude pose une question pragmatique : peut-on utiliser des données génétiques à grande échelle et des analyses informatiques pour identifier les points faibles clés de notre génome qui favorisent la LLC — puis les associer à des médicaments existants ou prometteurs ? Les réponses pourraient améliorer le diagnostic précoce et orienter des traitements plus précis, réduisant l’approche par essais-erreurs.
À l’échelle de milliers de génomes
Les chercheurs ont commencé par rassembler les résultats sommaires de trois grandes études d’association pangénomique, qui scrutent l’ADN de nombreuses personnes avec et sans LLC pour repérer de petites différences liées au risque de maladie. En nettoyant et en fusionnant soigneusement ces jeux de données, tous alignés sur la même référence du génome humain, ils ont augmenté la puissance statistique pour détecter des signaux génétiques subtils. En utilisant une méthode de méta-analyse qui pondère les études selon la précision de leurs estimations, ils ont identifié 2 357 positions de l’ADN, appelées polymorphismes nucléotidiques simples, fortement associées à la LLC. Ces signaux se sont regroupés en 40 segments du génome, dont 11 régions qui n’avaient pas été préalablement liées à la maladie.
Des marqueurs d’ADN aux gènes maîtres
La plupart des marqueurs de risque se situaient entre les gènes ou dans des régions non codantes, où leurs effets ne sont pas évidents. Pour les interpréter, l’équipe a utilisé des outils de bioinformatique qui relient chaque marqueur aux gènes voisins ou aux gènes dont l’activité dans les cellules sanguines change en présence de ce marqueur. Ce mappage a produit 60 gènes localisés dans ou à proximité des régions de risque. Les scientifiques ont ensuite évalué lesquels de ces gènes occupent des positions centrales dans le réseau d’interactions protéine–protéine au sein des cellules. Une analyse de réseau a mis en évidence sept gènes — TERT, BCL2, BCL2L11, CFLAR, CASP8, LEF1 et FAS — en tant que hubs reliant de nombreuses voies. Des bases de données indépendantes sur les maladies ont corroboré des liens forts entre ces gènes et la LLC, ainsi que d’autres cancers hématologiques et troubles immunitaires.
Comment la dérégulation de la mort cellulaire alimente la leucémie
Lorsque l’équipe a examiné les fonctions de ces sept gènes, un thème clair est apparu : la plupart contrôlent le destin cellulaire, vie ou mort. Plusieurs d’entre eux, dont BCL2 et BCL2L11, appartiennent à une famille qui équilibre les signaux de survie et les signaux d’autodestruction au niveau des mitochondries, les centrales énergétiques de la cellule. D’autres — FAS, CFLAR et CASP8 — régulent une voie parallèle des « récepteurs de mort » à la surface cellulaire. Dans la LLC, cet appareil penche en faveur de la survie : les protéines pro-survie sont hyperactives, tandis que les partenaires pro-mort sont bloqués ou diminués. Le dernier gène clé, LEF1, intervient dans une voie de croissance qui aide les cellules leucémiques à continuer de se diviser. Les analyses d’enrichissement ont mis en avant comme principaux thèmes biologiques la mort cellulaire, les voies liées au cancer et la signalisation immunitaire, renforçant l’idée que des variants hérités poussent ces systèmes de contrôle vers des lymphocytes B anormalement longévifs.
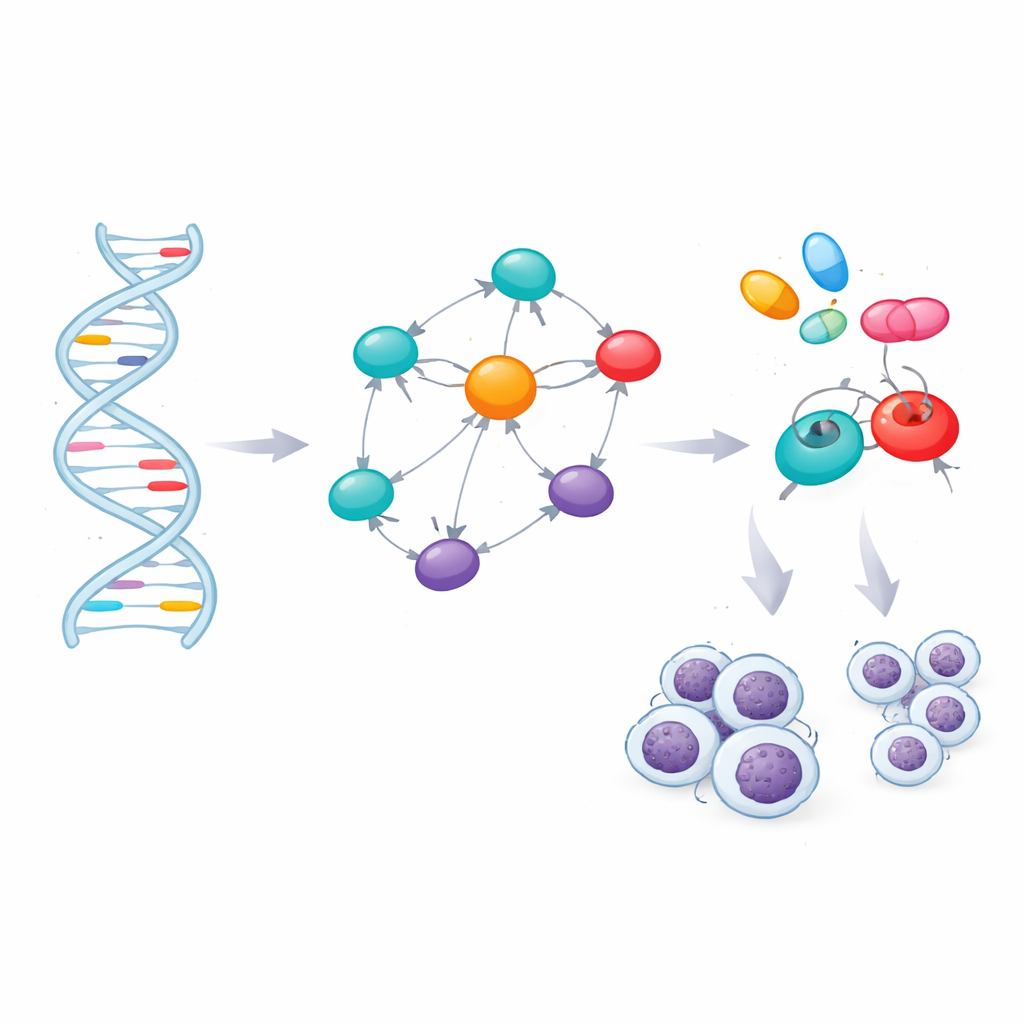
Associer les gènes aux médicaments
Identifier des gènes cruciaux ouvre la voie à une thérapie ciblée, mais seulement si ces gènes peuvent être modulés par des médicaments. L’équipe a évalué les structures tridimensionnelles des sept protéines et a trouvé des poches prometteuses où de petites molécules pourraient se lier. Ils ont ensuite exploré une bibliothèque de 166 composés existants ou expérimentaux liés à la LLC ou à des affections apparentées et ont utilisé des simulations de docking moléculaire pour voir quels médicaments s’inséraient le mieux dans les protéines clés ou leurs principaux régulateurs. Après avoir classé ces interactions virtuelles, ils ont filtré les meilleurs candidats selon des règles standards de « drug-likeness » et via des modèles informatiques prédictifs de l’absorption, de la distribution, du métabolisme, de l’élimination et de la toxicité. Ce criblage conservateur a retenu quatre candidats solides : les médicaments anticancéreux déjà approuvés ibrutinib, selinexor, imatinib et avapritinib.
Ce que cela pourrait signifier pour les patients
Pour les personnes vivant avec la LLC, ce travail ne change pas encore la prise en charge quotidienne, mais il aide à relier le risque héréditaire, l’architecture interne des cellules leucémiques et les médicaments susceptibles de perturber au mieux cette architecture. Deux des médicaments mis en avant, ibrutinib et selinexor, sont déjà utilisés en LLC et agissent d’une manière cohérente avec le tableau génétique révélé ici, notamment en réorientant l’équilibre vers la mort des cellules cancéreuses. L’étude suggère aussi que l’imatinib et l’avapritinib, actuellement employés pour d’autres cancers, mériteraient d’être testés plus attentivement en LLC. Plus généralement, l’approche montre comment l’exploitation de données génétiques existantes par des outils computationnels puissants peut dévoiler des gènes clés de la maladie et réduire le champ des thérapies potentielles, orientant les expériences de laboratoire et les essais cliniques futurs vers les cibles les plus prometteuses.
Citation: Islam, M.S., Mollah, M.H., Ahsan, M.A. et al. In-silico identification of genetic variants associated with chronic lymphocytic leukemia for diagnostic and therapeutic applications. Sci Rep 16, 14545 (2026). https://doi.org/10.1038/s41598-026-45456-7
Mots-clés: leucémie lymphoïde chronique, variants de risque génétique, voies d'apoptose, repositionnement de médicaments, thérapie ciblée du cancer