Clear Sky Science · it
Identificazione in silico di varianti genetiche associate alla leucemia linfatica cronica per applicazioni diagnostiche e terapeutiche
Perché è importante tracciare il cancro nei nostri geni
La leucemia linfatica cronica (LLC) è la leucemia adulta più comune, ma rimane incurabile per molti pazienti. Le famiglie di persone con LLC presentano un rischio nettamente più alto, suggerendo che modifiche ereditarie del DNA contribuiscano a predisporre alla malattia. Questo studio pone una domanda pratica: possiamo usare dati genetici su larga scala e analisi al computer per individuare i punti deboli nel nostro DNA che guidano la LLC e poi abbinarli a farmaci esistenti o promettenti? Le risposte potrebbero migliorare la diagnosi precoce e indirizzare terapie più precise, riducendo il ricorso al metodo per tentativi.
Analizzando migliaia di genomi
I ricercatori hanno iniziato raccogliendo i risultati di sintesi di tre grandi studi di associazione genome-wide, che esaminano il DNA di molte persone con e senza LLC per trovare piccole differenze legate al rischio di malattia. Pulendo e unendo con attenzione questi dataset, tutti allineati allo stesso genoma di riferimento umano, hanno aumentato la potenza statistica per rilevare segnali genetici deboli. Usando un metodo di meta-analisi che pesa gli studi in base alla precisione delle stime, hanno identificato 2.357 posizioni del DNA, dette polimorfismi a singolo nucleotide, fortemente associate alla LLC. Questi segnali si sono raggruppati in 40 regioni del genoma, incluse 11 aree non precedentemente correlate alla malattia.
Dai marcatori del DNA ai geni di controllo chiave
La maggior parte dei marcatori di rischio ricade tra i geni o nelle parti non codificanti dei geni, dove i loro effetti non sono evidenti. Per interpretarli, il gruppo ha impiegato strumenti bioinformatici che collegano ogni marcatore ai geni vicini o ai geni la cui attività nelle cellule del sangue cambia quando quel marcatore è presente. Questa mappatura ha prodotto 60 geni situati dentro o vicino alle regioni di rischio. Gli scienziati hanno poi verificato quali di questi geni occupano posizioni centrali nella rete di interazioni proteina–proteina all'interno delle cellule. L'analisi di rete ha evidenziato sette geni—TERT, BCL2, BCL2L11, CFLAR, CASP8, LEF1 e FAS—come hub che connettono numerose vie. Banche dati indipendenti sulle malattie hanno confermato forti legami tra questi geni e la LLC, oltre ad altre neoplasie ematiche e a disturbi immunitari.
Come la disfunzione della morte cellulare alimenta la leucemia
Esaminando le funzioni di questi sette geni è emerso un tema chiaro: la maggior parte regola la vita o la morte cellulare. Diversi, tra cui BCL2 e BCL2L11, appartengono a una famiglia che bilancia i segnali di sopravvivenza con i segnali di autodistruzione nei mitocondri, le centrali della cellula. Altri—FAS, CFLAR e CASP8—governano una via parallela del «recettore della morte» sulla superficie cellulare. Nella LLC, questo apparato è sbilanciato a favore della sopravvivenza: le proteine pro-sopravvivenza sono iperattive, mentre i partner pro-morte sono bloccati o ridotti. Il gene chiave rimanente, LEF1, è inserito in una via di crescita che aiuta le cellule leucemiche a continuare a dividersi. Le analisi di arricchimento hanno mostrato che i temi biologici principali sono la morte cellulare, le vie oncologiche e il segnalamento immunitario, rafforzando l'idea che varianti ereditarie spingano questi sistemi di controllo verso linfociti B anomali e a vita prolungata.
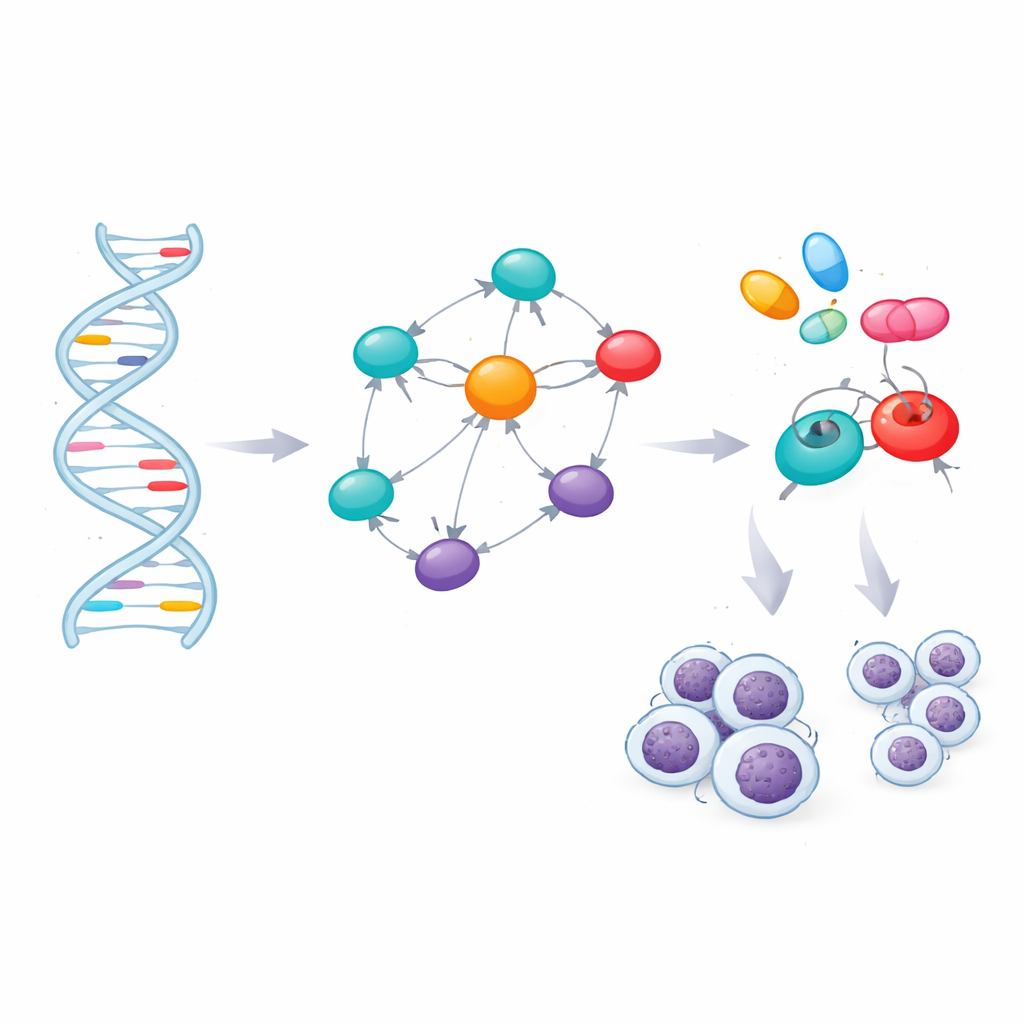
Abbinare i geni ai farmaci
Identificare i geni cruciale apre la strada alla terapia mirata, ma solo se quei geni possono essere influenzati farmacologicamente. Il team ha valutato le strutture tridimensionali delle sette proteine e ha individuato siti promettenti dove piccole molecole potrebbero legarsi. Ha quindi scandagliato una libreria di 166 composti esistenti o sperimentali collegati alla LLC o a condizioni affini e ha usato simulazioni di docking molecolare per vedere quali farmaci si adattavano meglio alle proteine chiave o ai loro principali regolatori. Dopo aver classificato queste interazioni virtuali, hanno filtrato i migliori candidati con regole standard di “drug-likeness” e con modelli computazionali che predicono assorbimento, distribuzione, metabolismo, escrezione e potenziale tossicità. Questo screening conservativo ha lasciato quattro forti contendenti: i farmaci oncologici già approvati ibrutinib, selinexor, imatinib e avapritinib.
Cosa può significare per i pazienti
Per le persone con LLC, questo lavoro non cambia ancora la cura quotidiana, ma aiuta a collegare il rischio ereditario, il cablaggio interno delle cellule leucemiche e i farmaci che potrebbero meglio interrompere tale cablaggio. Due dei farmaci evidenziati, ibrutinib e selinexor, sono già impiegati nella LLC e agiscono in modi coerenti con il quadro genetico emerso qui, in particolare riportando l'equilibrio verso la morte delle cellule tumorali. Lo studio suggerisce anche che imatinib e avapritinib, attualmente usati per altri tumori, meritano ulteriori test nella LLC. Più in generale, l'approccio dimostra come l'estrazione di dati genetici esistenti con potenti strumenti computazionali possa rivelare geni chiave della malattia e restringere il campo di terapie potenziali, guidando esperimenti di laboratorio e trial clinici futuri verso i bersagli più promettenti.
Citazione: Islam, M.S., Mollah, M.H., Ahsan, M.A. et al. In-silico identification of genetic variants associated with chronic lymphocytic leukemia for diagnostic and therapeutic applications. Sci Rep 16, 14545 (2026). https://doi.org/10.1038/s41598-026-45456-7
Parole chiave: leucemia linfatica cronica, varianti genetiche di rischio, vie dell'apoptosi, riproposta di farmaci, terapia mirata del cancro