Clear Sky Science · sv
3d-OT: ett djupinriktat, geometri-medvetet ramverk för anpassning av heterogena snitt i rumslig multi-omik
Att se vävnader i tre dimensioner
Biologer kan alltmer inte bara mäta vilka molekyler som är aktiva i en cell, utan också exakt var cellen sitter i en vävnad. Dessa nya ”rumsliga” kartor lovar klarare insikter i hur hjärnor är kopplade, hur tumörer sprider sig och hur embryon bygger organ. Ändå fångar de flesta experiment fortfarande bara tunna snitt, där varje snitt använder olika mätmetoder och upplösningar. I denna artikel presenteras 3d-OT, en beräkningsmetod som syr ihop dessa snitt till sammanhängande 3D-vyer samtidigt som den tar tillvara den rika molekylära informationen i varje snitt.
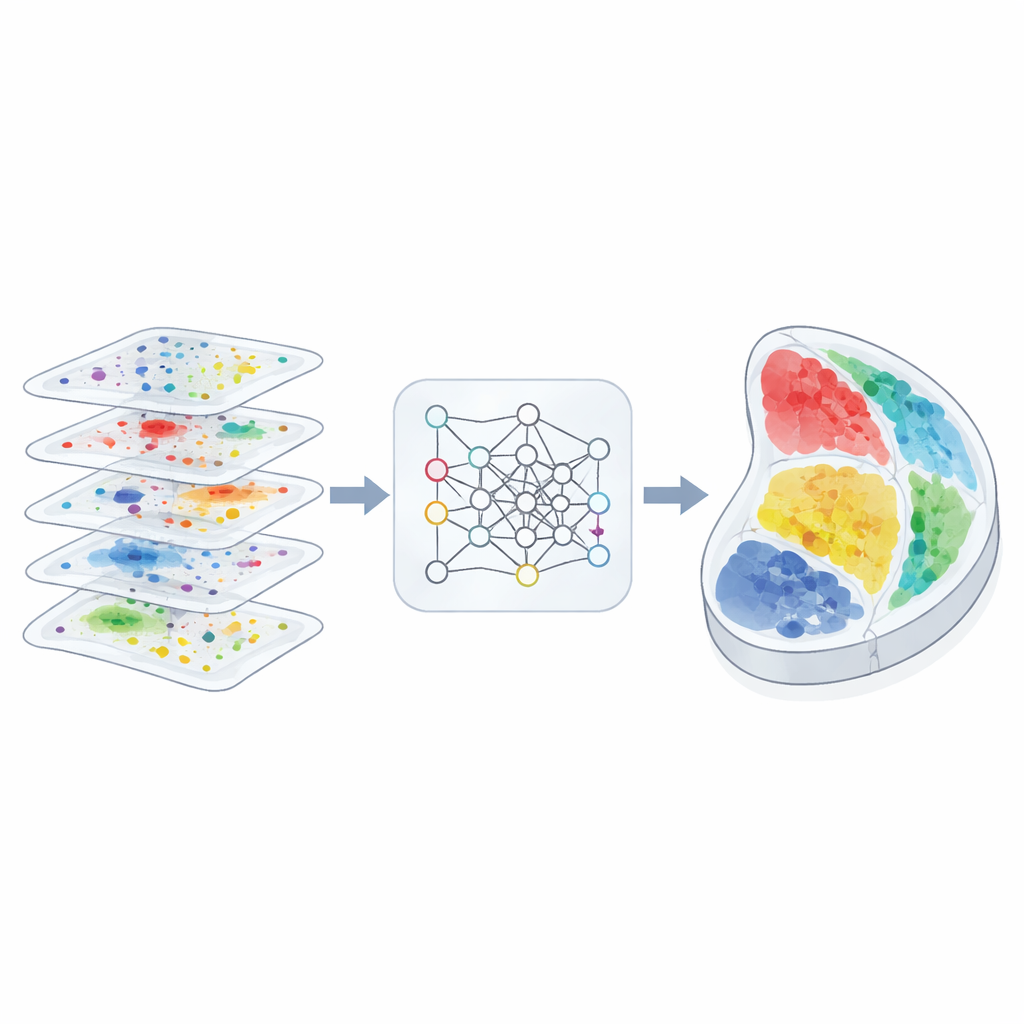
Varför det spelar roll att kartlägga rummet
Traditionell genetik och genomik berättar vilka molekyler celler innehåller, men inte var dessa celler finns. Rumsliga tekniker ändrar på det genom att samtidigt registrera både den molekylära profilen för varje liten punkt i en vävnad och dess fysiska koordinater. Olika metoder betonar olika molekylära lager: vissa profilerar RNA, andra proteiner, andra de kemiska märkningarna på DNA. Varje lager avslöjar en annan aspekt av vävnadsorganisationen. Utmaningen är att forskare ofta sitter med flera, delvis överlappande snitt mätta med olika verktyg. Att alignera dessa heterogena snitt i ett konsekvent 3D-utrymme, utan att förlora fin anatomisk detalj, har varit ett stort olöst problem.
En geometri-medveten syn på vävnader
Författarna utformade 3d-OT för att behandla varje vävnadssnitt som ett ”punktmoln”, en samling punkter i det fysiska rummet där varje punkt bär multi-omik-mätningar. Istället för att i första hand förlita sig på ett rutnät eller graf för att beskriva grannskap, använder 3d-OT en neuralt nätverksarkitektur kallad PointNet++ som ursprungligen skapades för 3D-objektsigenkänning. Detta nätverk matar upprepade gånger varje punkt inte bara med sina molekylära signaler utan också med dess exakta koordinater, vilket låter modellen lära sig subtila geometriska mönster som lager i cortex eller böjda organsgränser. För snitt med mer än ett molekylärt lager blandar en fusionsmodul modaliteterna till en gemensam representation samtidigt som varje lags särskilda bidrag bevaras.
Att alignera snitt med mjuka matchningar
Den andra kärnan i 3d-OT är en aligneringsmodul baserad på ”optimal transport”, ett matematiskt ramverk för att matcha två fördelningar samtidigt som deras övergripande form bevaras. Istället för att tvinga fram en styv en-till-en-parning mellan punkter i två snitt beräknar metoden mjuka korrespondenser: varje punkt i ett källa-snitt kan delvis matcha flera kandidater i ett mål-snitt. En rekonstruktionsförlust baserad på chamfer-avstånd belönar aligneringar som får de rekonstruerade positionerna att likna de verkliga målpositionerna. Ytterligare jämnhets- och ”noll-divergens”-begränsningar uppmuntrar flödet av punkter mellan snitt att följa realistiska, kontinuerliga vävnadsdeformationer, såsom böjning, töjning eller tillväxt, istället för osannolika hopp eller vridningar.
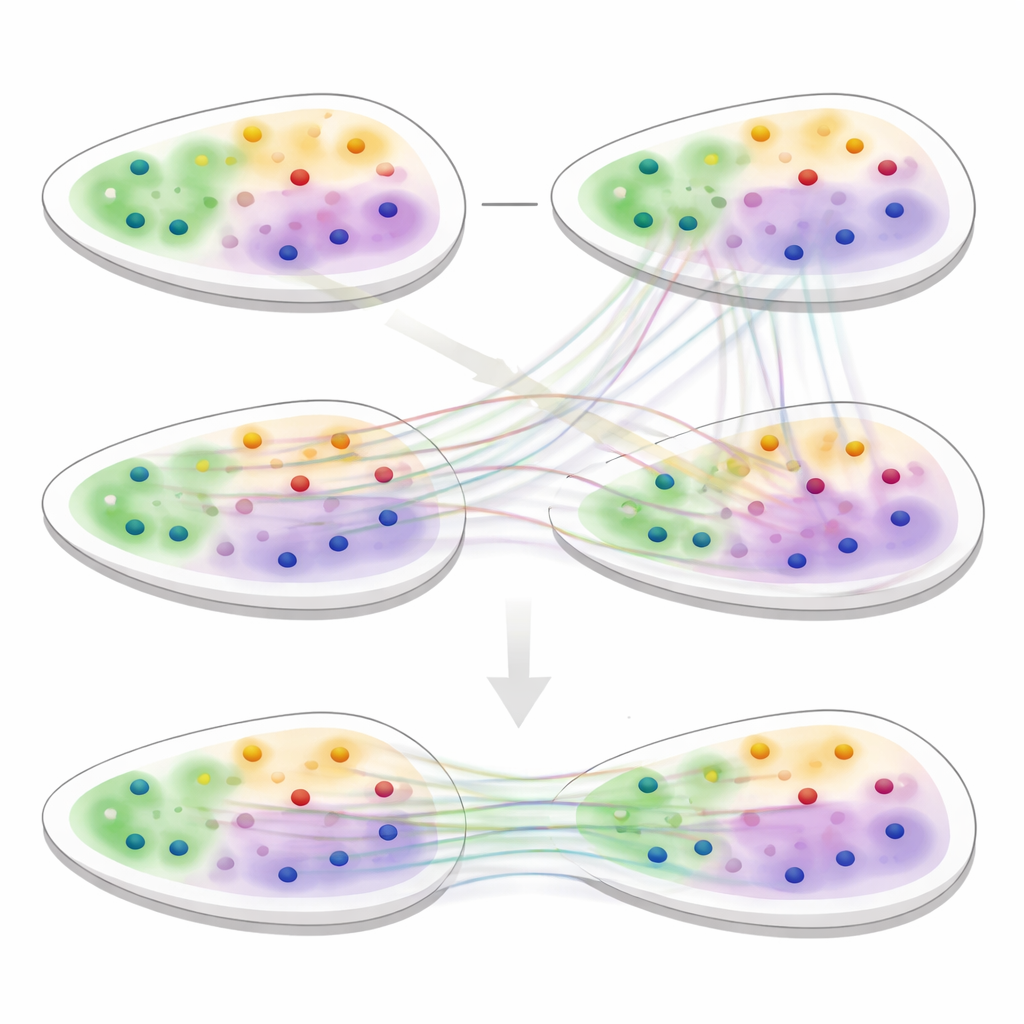
Avslöjar dold vävnadsstruktur
För att testa 3d-OT jämförde teamet det med ledande verktyg för rumslig analys på en rad dataset, inklusive mänsklig hjärna, bröstcancer, lymfknuta och flera musorgan. I uppgifter med clustering på enskilda snitt återfann 3d-OT mer exakt kända lager i mänsklig och muscortex och särskilde cancerregioner bättre än konkurrerande metoder. I multi-omik-data från mushjärnan som kombinerade RNA med kromatinmärken separerade det två sublager inom det djupaste cortexlagret som ofta framträder som ett enda band, och tydliggjorde markörgener för dessa fina regioner. Över flera tekniker och upplösningar, inklusive utmanande hjärt- och neuralgälvävnader, gav 3d-OT jämnare och mer anatomiskt trogna aligneringar än befintliga metoder.
Följa organ över tiden
Kanske den mest slående demonstrationen kom från att rekonstruera musens embryonala utveckling. Med rumsliga data från flera embryonala dagar alignerade 3d-OT snitt över tid för att bygga 3D-”filmer” av organens tillväxt. Metoden fångade till exempel hur hjärtat ändrar form från kompakt till en ringliknande struktur och tillbaka, och hur levern expanderar stadigt. Den kopplade också tidiga prekursorregioner till senare organ, och följde korrekt urogenitala åsen in i njure och äggstock, och dermomyotomet in i muskel och bindväv. Dessa banor överensstämde med känd utvecklingsbiologi samtidigt som de föreslog ytterligare differentieringsvägar för vidare studier.
Vad detta betyder för framtidens biologi
Enkelt uttryckt omvandlar 3d-OT spridda, flerskiktade ögonblicksbilder av vävnader till konsekventa, högupplösta 3D-kartor som respekterar både molekylär identitet och fysisk form. Genom att uttryckligen koda geometri och tillåta flexibla, mjuka matchningar mellan snitt överträffar det tidigare verktyg när det gäller att identifiera fina vävnadsregioner och alignera data från olika teknologier och tidpunkter. Allteftersom rumsliga multi-omik-dataset växer kommer metoder som 3d-OT att hjälpa forskare att gå från platta bilder till dynamiska 3D-atlaser över organ i hälsa, sjukdom och utveckling.
Citering: Dai, B., Yi, L., Wang, P. et al. 3d-OT: a deep geometry-aware framework for heterogeneous slices alignment of spatial multi-omics. Nat Methods 23, 760–771 (2026). https://doi.org/10.1038/s41592-026-03034-9
Nyckelord: rumslig omik, integration av multi-omik, 3D-återuppbyggnad av vävnad, embryonal utveckling, beräkningsbiologi