Clear Sky Science · pl
3d-OT: głęboka, świadoma geometrii ramka do wyrównywania heterogenicznych przekrojów przestrzennych multi-omików
Widzieć tkanki w trzech wymiarach
Naukowcy coraz częściej potrafią zmierzyć nie tylko, które cząsteczki są aktywne w komórce, ale też dokładnie, gdzie ta komórka znajduje się w obrębie tkanki. Nowe „przestrzenne” mapy obiecują jaśniejsze spojrzenie na to, jak są połączone sieci mózgowe, jak rozprzestrzeniają się nowotwory i jak zarodki budują narządy. Jednak w większości eksperymentów nadal pozyskuje się jedynie cienkie przekroje, z których każdy powstaje przy użyciu różnych typów pomiarów i w różnych rozdzielczościach. W artykule przedstawiono 3d-OT, metodę obliczeniową, która spaja te przekroje w spójne widoki 3D, wykorzystując przy tym bogate informacje molekularne zawarte w każdym przekroju.
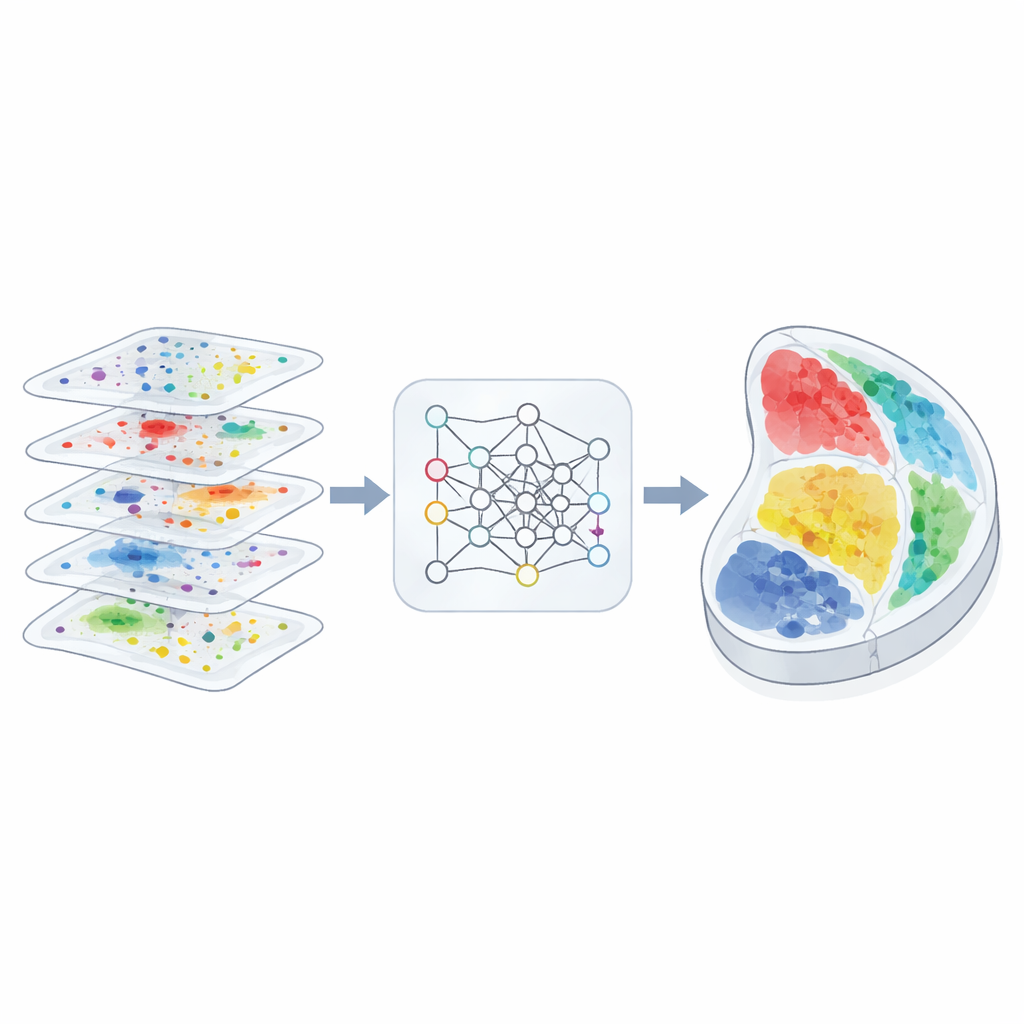
Dlaczego mapowanie przestrzeni ma znaczenie
Tradycyjna genetyka i genomika mówią, jakie cząsteczki zawierają komórki, ale nie informują, gdzie te komórki się znajdują. Technologie przestrzenne to zmieniają, rejestrując zarówno profil molekularny każdego małego punktu w tkance, jak i jego współrzędne fizyczne. Różne metody kładą nacisk na różne warstwy molekularne: niektóre profilują RNA, inne białka, jeszcze inne chemiczne modyfikacje DNA. Każda warstwa odsłania inną stronę organizacji tkanki. Problem polega na tym, że badacze często kończą z kilkoma częściowo nakładającymi się przekrojami tkanki mierzonymi różnymi narzędziami. Wyrównanie tych heterogenicznych przekrojów w spójną przestrzeń 3D, bez utraty drobnych detali anatomicznych, było dotąd dużym nierozwiązanym wyzwaniem.
Widok tkanek uwzględniający geometrię
Autorzy zaprojektowali 3d-OT tak, aby traktował każdy przekrój tkanki jako „chmurę punktów” — zbiór miejsc w przestrzeni fizycznej, z których każde niesie pomiary multi-omikowe. Zamiast polegać głównie na siatce czy grafie opisującym relacje sąsiedztwa, 3d-OT wykorzystuje architekturę sieci neuronowej PointNet++, pierwotnie stworzoną do rozpoznawania obiektów 3D. Sieć ta wielokrotnie podaje każdemu punktowi nie tylko sygnały molekularne, lecz także jego dokładne współrzędne, pozwalając modelowi uczyć się subtelnych wzorców geometrycznych, takich jak warstwowa struktura kory czy zakrzywione granice narządów. Dla przekrojów z więcej niż jedną warstwą molekularną moduł fuzji łączy modalności w wspólną reprezentację, zachowując jednocześnie wyróżniający wkład każdej warstwy.
Wyrównywanie przekrojów z miękkimi dopasowaniami
Drugim filarem 3d-OT jest moduł wyrównywania oparty na „transporcie optymalnym”, matematycznym ramieniu do dopasowywania dwóch rozkładów przy zachowaniu ich ogólnego kształtu. Zamiast wymuszać sztywne parowanie jeden-do-jednego między punktami w dwóch przekrojach, metoda oblicza miękkie korespondencje: każdy punkt w przekroju źródłowym może częściowo odpowiadać kilku kandydatom w przekroju docelowym. Funkcja straty rekonstrukcji oparta na odległości Chamfera nagradza wyrównania, które sprawiają, że zrekonstruowane pozycje jak najbliżej przypominają rzeczywiste pozycje docelowe. Dodatkowe ograniczenia na płynność i „zero-dywergencję” zachęcają przepływ punktów między przekrojami, aby odzwierciedlał realistyczne, ciągłe odkształcenia tkanki, takie jak zginanie, rozciąganie czy wzrost, zamiast nieprawdopodobnych skoków czy skrętów.
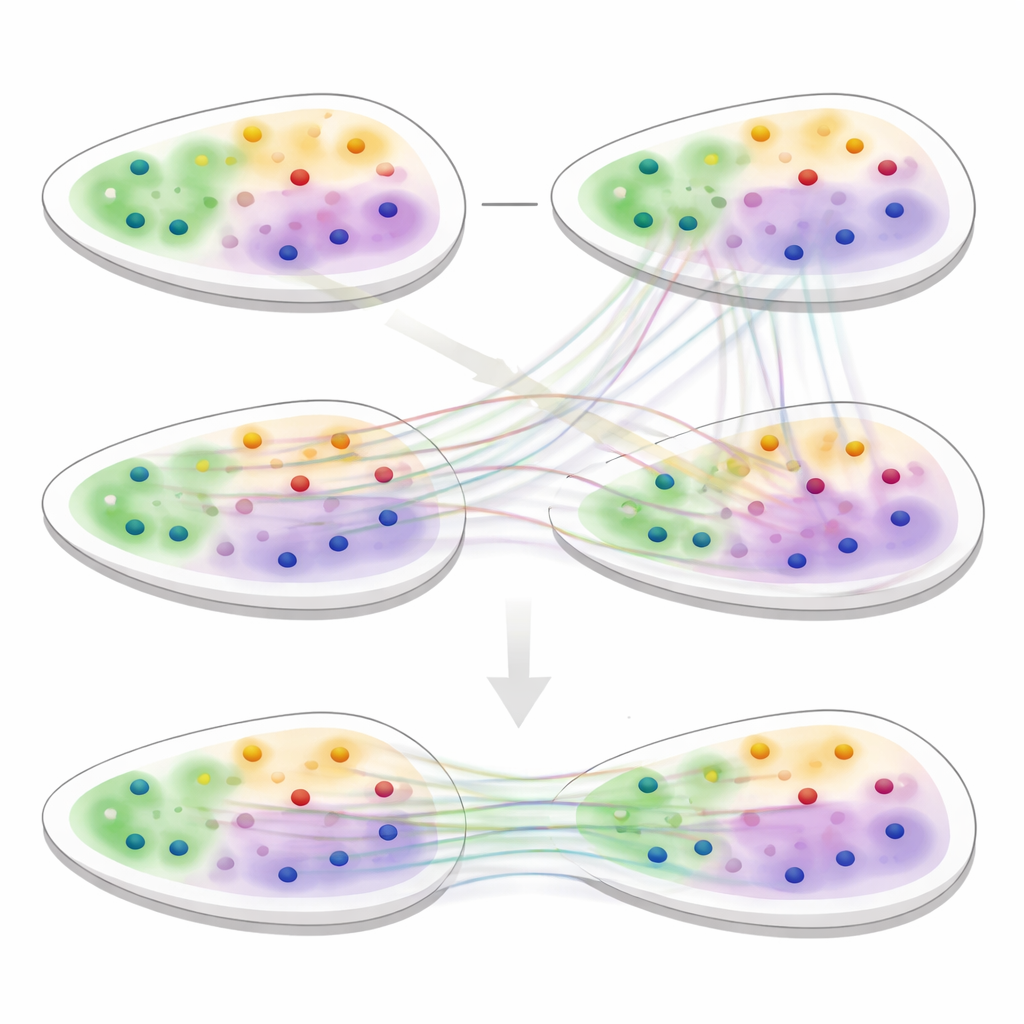
Odkrywanie ukrytej struktury tkanek
Aby przetestować 3d-OT, zespół porównał je z wiodącymi narzędziami analizy przestrzennej na różnych zestawach danych, w tym tętnów ludzkiego mózgu, raka piersi, węzła chłonnego i kilku narządów mysich. W zadaniach klastrowania pojedynczych przekrojów 3d-OT dokładniej odtworzyło znane warstwy kory ludzkiej i mysiej oraz lepiej rozróżniło obszary nowotworowe niż konkurencyjne metody. W danych multi-omicznych mózgu myszy, łączących RNA z oznaczeniami chromatyny, metoda rozdzieliła dwie podwarstwy w najgłębszej warstwie korowej, które często pojawiają się jako pojedynczy pas, i uwypukliła geny markerowe dla tych drobnych regionów. W różnych technologiach i rozdzielczościach, włącznie z wymagającymi tkankami serca i grzebienia nerwowego, 3d-OT dostarczyło gładszych i bardziej anatomicznie wiernych wyrównań niż istniejące metody.
Śledzenie narządów w czasie
Być może najbardziej efektowna demonstracja pochodziła z rekonstrukcji rozwoju zarodka myszy. Wykorzystując dane przestrzenne z kilku dni embrionalnych, 3d-OT wyrównało przekroje w czasie, budując trójwymiarowe „filmy” wzrostu narządów. Metoda uchwyciła na przykład, jak serce zmienia się z zwartej formy w strukturę przypominającą pierścień i z powrotem, oraz jak wątroba rozszerza się stopniowo. Połączyła też wczesne regiony prekursorowe z późniejszymi narządami, poprawnie śledząc grzbiet moczowo-płciowy do nerki i jajnika oraz dermomiotom do mięśnia i tkanki łącznej. Te trajektorie zgadzały się z znaną biologią rozwojową, a jednocześnie sugerowały dodatkowe ścieżki różnicowania warte dalszych badań.
Co to oznacza dla przyszłej biologii
W prostych słowach, 3d-OT przekształca rozproszone, wielowarstwowe migawki tkanek w spójne, wysokorozdzielcze mapy 3D, które szanują zarówno tożsamość molekularną, jak i kształt fizyczny. Dzięki jawnemu kodowaniu geometrii i pozwoleniu na elastyczne, miękkie dopasowania między przekrojami przewyższa starsze narzędzia w identyfikacji drobnych regionów tkanki i wyrównywaniu danych z różnych technologii i punktów czasowych. W miarę jak zestawy danych spatial multi-omics będą się rozwijać, metody takie jak 3d-OT pomogą badaczom przejść od płaskich obrazów do dynamicznych atlasów 3D narządów w zdrowiu, chorobie i rozwoju.
Cytowanie: Dai, B., Yi, L., Wang, P. et al. 3d-OT: a deep geometry-aware framework for heterogeneous slices alignment of spatial multi-omics. Nat Methods 23, 760–771 (2026). https://doi.org/10.1038/s41592-026-03034-9
Słowa kluczowe: spatial omics, integracja multi-omików, rekonstrukcja 3D tkanek, rozwój zarodkowy, biologia obliczeniowa