Clear Sky Science · pt
3d-OT: uma estrutura profunda consciente da geometria para alinhamento de fatias heterogêneas em multi-ômicas espaciais
Ver Tecidos em Três Dimensões
Os biólogos estão cada vez mais aptos a medir não apenas quais moléculas estão ativas em uma célula, mas também exatamente onde essa célula se localiza dentro de um tecido. Esses novos mapas “espaciais” prometem visões mais claras de como cérebros são conectados, como tumores se espalham e como embriões constroem órgãos. Ainda assim, a maioria dos experimentos captura apenas fatias finas, cada uma usando diferentes tipos de mensuração e resoluções. Este artigo apresenta o 3d-OT, um método computacional que costura essas fatias em vistas 3D coerentes, aproveitando ao máximo as ricas informações moleculares de cada fatia.
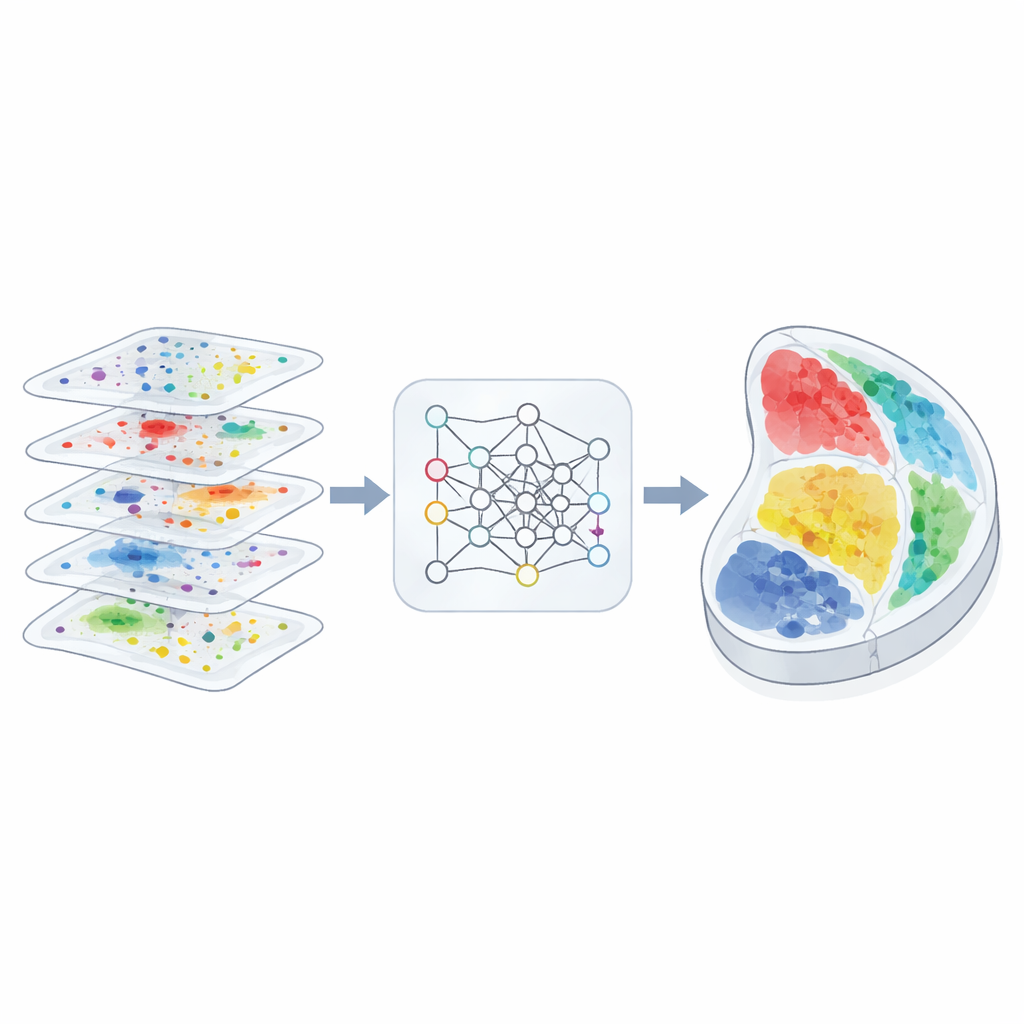
Por que Mapear o Espaço Importa
A genética e a genômica tradicionais dizem quais moléculas as células contêm, mas não onde essas células vivem. As tecnologias espaciais mudam isso ao registrar tanto o perfil molecular de cada pequeno ponto em um tecido quanto suas coordenadas físicas. Métodos diferentes enfatizam camadas moleculares distintas: alguns perfis medem RNA, outros proteínas, outros as marcas químicas no DNA. Cada camada revela um aspecto diferente da organização do tecido. O desafio é que os pesquisadores frequentemente acabam com múltiplas fatias parcialmente sobrepostas do tecido medidas com ferramentas diferentes. Alinhar essas fatias heterogêneas em um espaço 3D consistente, sem perder detalhes anatômicos finos, tem sido um grande problema não solucionado.
Uma Visão dos Tecidos Sensível à Geometria
Os autores projetaram o 3d-OT para tratar cada fatia de tecido como uma “nuvem de pontos”, uma nuvem de pontos no espaço físico, cada um portando medições multi-ômicas. Em vez de se apoiar principalmente em uma grade ou grafo para descrever relações de vizinhança, o 3d-OT usa uma arquitetura de rede neural chamada PointNet++, originalmente criada para reconhecimento de objetos 3D. Essa rede alimenta repetidamente cada ponto não apenas com seus sinais moleculares, mas também com suas coordenadas exatas, permitindo que o modelo aprenda padrões geométricos sutis, como estruturas corticais em camadas ou limites de órgãos curvos. Para fatias com mais de uma camada molecular, um módulo de fusão combina as modalidades em uma representação compartilhada ao mesmo tempo em que preserva a contribuição distintiva de cada camada.
Alinhando Fatias com Correspondências Suaves
O segundo núcleo do 3d-OT é um módulo de alinhamento baseado em “transporte ótimo”, um arcabouço matemático para combinar duas distribuições preservando sua forma geral. Em vez de forçar um pareamento rígido um-para-um entre pontos em duas fatias, o método computa correspondências suaves: cada ponto em uma fatia de origem pode corresponder parcialmente a vários candidatos em uma fatia alvo. Uma perda de reconstrução baseada na distância de Chamfer recompensa alinhamentos que fazem as posições reconstruídas se assemelharem às posições reais do alvo. Restrições adicionais de suavidade e de “divergência zero” encorajam o fluxo de pontos entre fatias a seguir deformações teciduais realistas e contínuas, como dobramento, estiramento ou crescimento, em vez de saltos ou torções implausíveis.
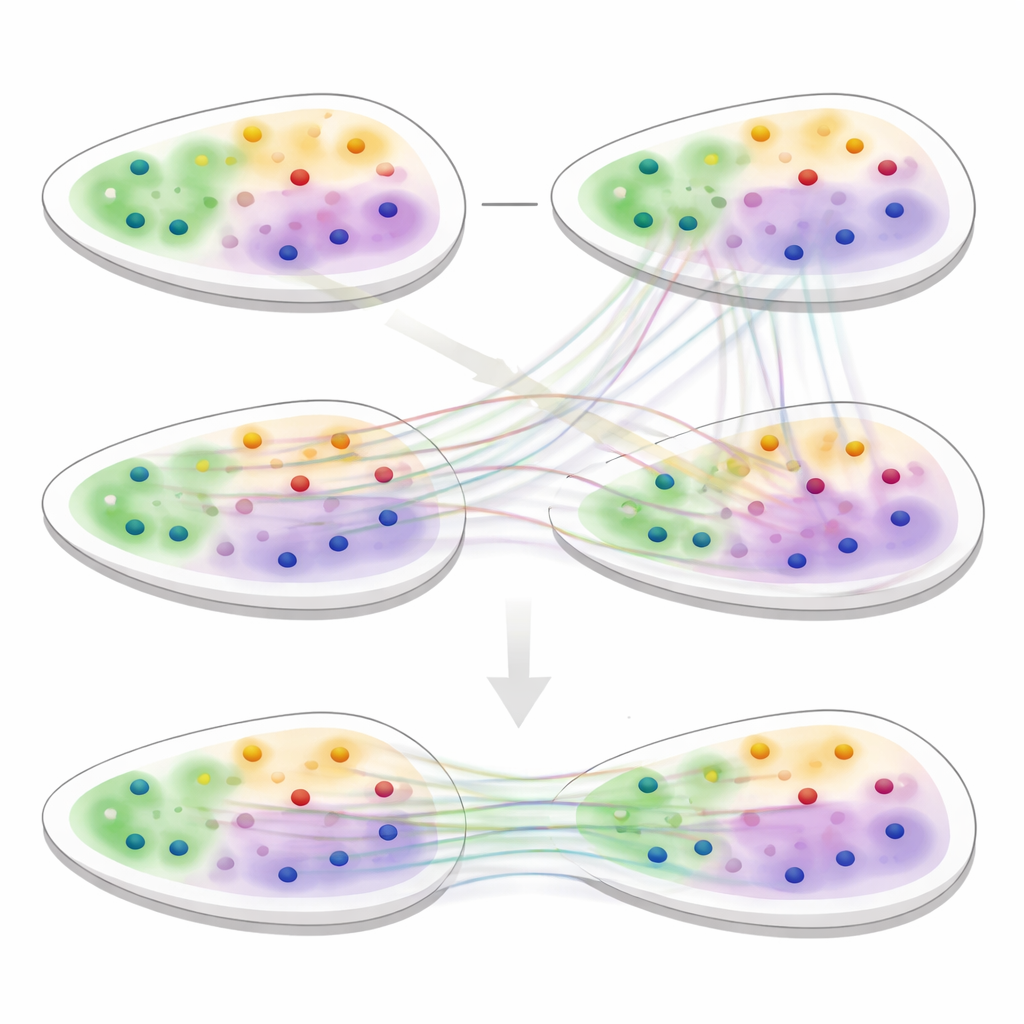
Revelando Estruturas Tissulares Ocultas
Para testar o 3d-OT, a equipe o comparou com as principais ferramentas de análise espacial em uma variedade de conjuntos de dados, incluindo cérebro humano, câncer de mama, linfonodo e múltiplos órgãos de camundongo. Em tarefas de clusterização de fatia única, o 3d-OT recuperou com mais precisão camadas conhecidas do córtex humano e de camundongo e distinguiu melhor regiões tumorais do que métodos concorrentes. Em dados multi-ômicos do cérebro de camundongo que combinaram RNA com marcas de cromatina, separou duas subcamadas dentro da camada cortical mais profunda que frequentemente aparecem como uma única faixa, e destacou genes marcadores para essas regiões finas. Através de múltiplas tecnologias e resoluções, incluindo tecidos desafiadores como coração e crista neural, o 3d-OT forneceu alinhamentos mais suaves e anatomicamente fiéis do que métodos de alinhamento existentes.
Seguindo Órgãos ao Longo do Tempo
Talvez a demonstração mais impressionante tenha vindo da reconstrução do desenvolvimento embrionário de camundongo. Usando dados espaciais de vários dias embrionários, o 3d-OT alinhou fatias ao longo do tempo para construir “filmes” 3D do crescimento de órgãos. Capturou, por exemplo, como o coração muda de uma forma compacta para uma estrutura em anel e volta, e como o fígado se expande de forma contínua. O método também vinculou regiões precursoras iniciais a órgãos posteriores, traçando corretamente a crista urogenital até rim e ovário, e o dermomiótomo até músculo e tecido conjuntivo. Essas trajetórias corresponderam ao conhecimento do desenvolvimento biológico, ao mesmo tempo que sugeriram caminhos adicionais de diferenciação para estudo posterior.
O que Isso Significa para a Biologia Futura
Em termos simples, o 3d-OT transforma instantâneos dispersos e em múltiplas camadas de tecidos em mapas 3D consistentes e de alta resolução que respeitam tanto a identidade molecular quanto a forma física. Ao codificar explicitamente a geometria e permitir correspondências flexíveis e suaves entre fatias, ele supera ferramentas anteriores na identificação de regiões teciduais finas e no alinhamento de dados de diferentes tecnologias e pontos temporais. À medida que os conjuntos de dados de multi-ômicas espaciais crescem, métodos como o 3d-OT ajudarão os pesquisadores a avançar de imagens planas para atlas 3D dinâmicos de órgãos em saúde, doença e desenvolvimento.
Citação: Dai, B., Yi, L., Wang, P. et al. 3d-OT: a deep geometry-aware framework for heterogeneous slices alignment of spatial multi-omics. Nat Methods 23, 760–771 (2026). https://doi.org/10.1038/s41592-026-03034-9
Palavras-chave: ômicas espaciais, integração multi-ômicas, reconstrução 3D de tecido, desenvolvimento embrionário, biologia computacional