Clear Sky Science · ja
3d-OT: 空間型マルチオミクスの異種スライス整列のための深層ジオメトリ認識フレームワーク
組織を三次元で見る
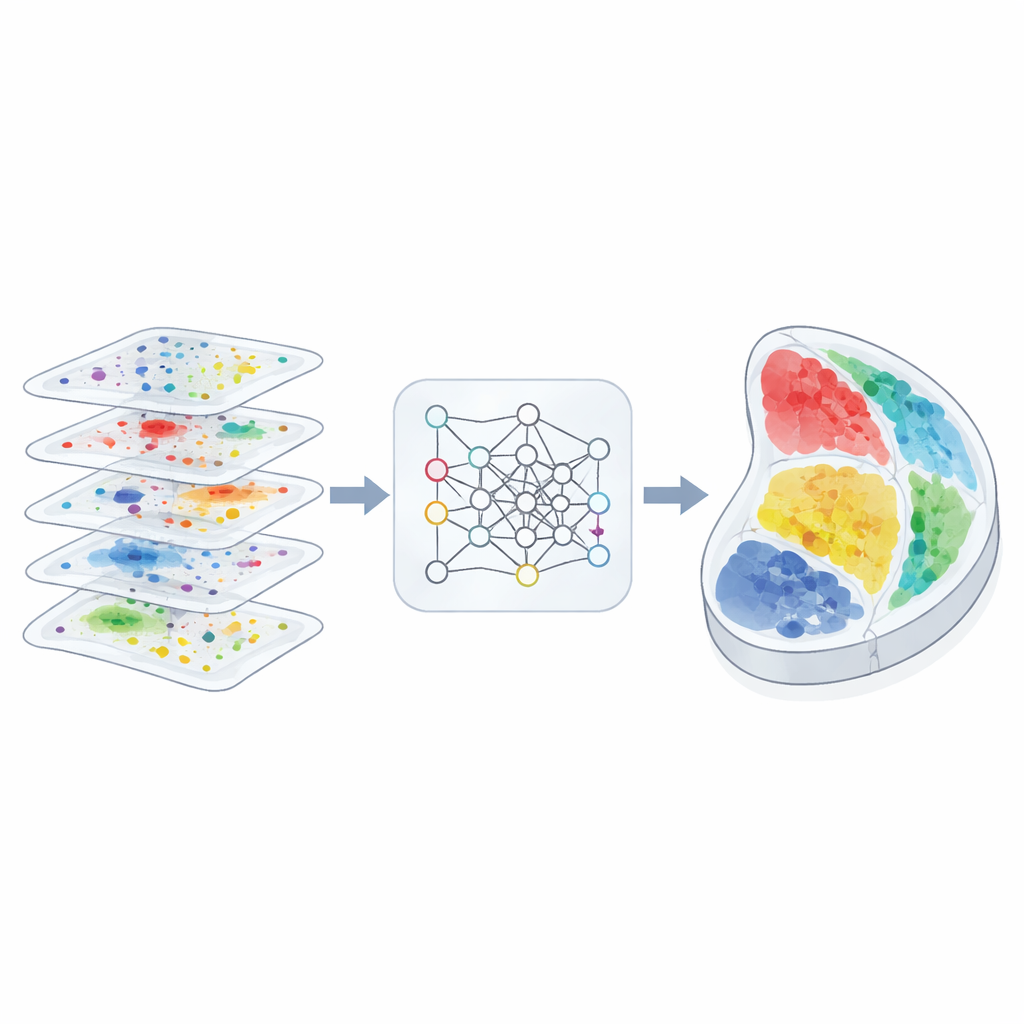
生物学者は、細胞内でどの分子が活性化しているかを測るだけでなく、その細胞が組織内のどこに存在するかを正確に測定できるようになってきました。こうした新しい「空間的」マップは、脳の配線、腫瘍の浸潤、胚が臓器を作る過程をより明瞭に示す可能性があります。しかし多くの実験は依然として薄いスライスを取得するにとどまり、それぞれが異なる測定タイプや解像度を用いています。本論文は3d-OTを提示し、各スライスに含まれる豊富な分子情報を最大限に活用しつつ、それらのスライスを一貫した3Dビューに継ぎ合わせる計算手法を示します。
空間マッピングが重要な理由
従来の遺伝学やゲノミクスは、細胞がどのような分子を持つかを教えてくれますが、それらの細胞がどこにいるかは示しません。空間技術は、組織内の各小さなスポットの分子プロファイルとその物理座標の両方を記録することでこれを変えます。手法ごとに強調される分子層は異なり、RNAをプロファイリングするもの、タンパク質を測るもの、DNA上の化学的修飾を捉えるものなどがあります。それぞれの層は組織構造の異なる側面を明らかにします。問題は、研究者がしばしば異なるツールで測定された複数の、部分的に重なるスライスを抱えることになる点です。細かい解剖学的詳細を失うことなく、それら異種スライスを一貫した3D空間に整列させることは、長らく未解決の主要な課題でした。
ジオメトリを意識した組織の見方
著者らは3d-OTを、各組織スライスを物理空間上のスポットの「点群」と見なすよう設計しました。各スポットはマルチオミクスの測定値を携えています。近傍関係を記述するために主にグリッドやグラフに依存するのではなく、3d-OTはもともと3D物体認識のために作られたニューラルネットワークアーキテクチャPointNet++を用います。このネットワークは各スポットに分子信号だけでなくその正確な座標も繰り返し入力し、層状の皮質構造や湾曲した臓器境界といった微妙なジオメトリパターンを学習できるようにします。複数の分子層を持つスライスに対しては、フュージョンモジュールが各モダリティの特徴的貢献を保ちながらそれらを共有表現へと融合します。
ソフトマッチでスライスを整列する
3d-OTのもう一つの中核は「最適輸送」に基づく整列モジュールです。これは二つの分布をその全体形状を保ちながら対応付ける数学的枠組みです。二つのスライスのスポット間で硬直した一対一対応を強制する代わりに、この手法はソフトな対応関係を計算します:ソーススライスの各スポットがターゲットスライスの複数の候補と部分的にマッチすることを許容します。チャムファー距離に基づく再構成損失は、再構築された位置が実際のターゲット位置によく似ている整列を評価します。さらに平滑性および「ゼロ発散」制約により、スライス間のスポットの流れが現実的で連続した組織変形(曲がり、伸展、成長など)に沿うよう促し、不自然な飛びやねじれを抑えます。
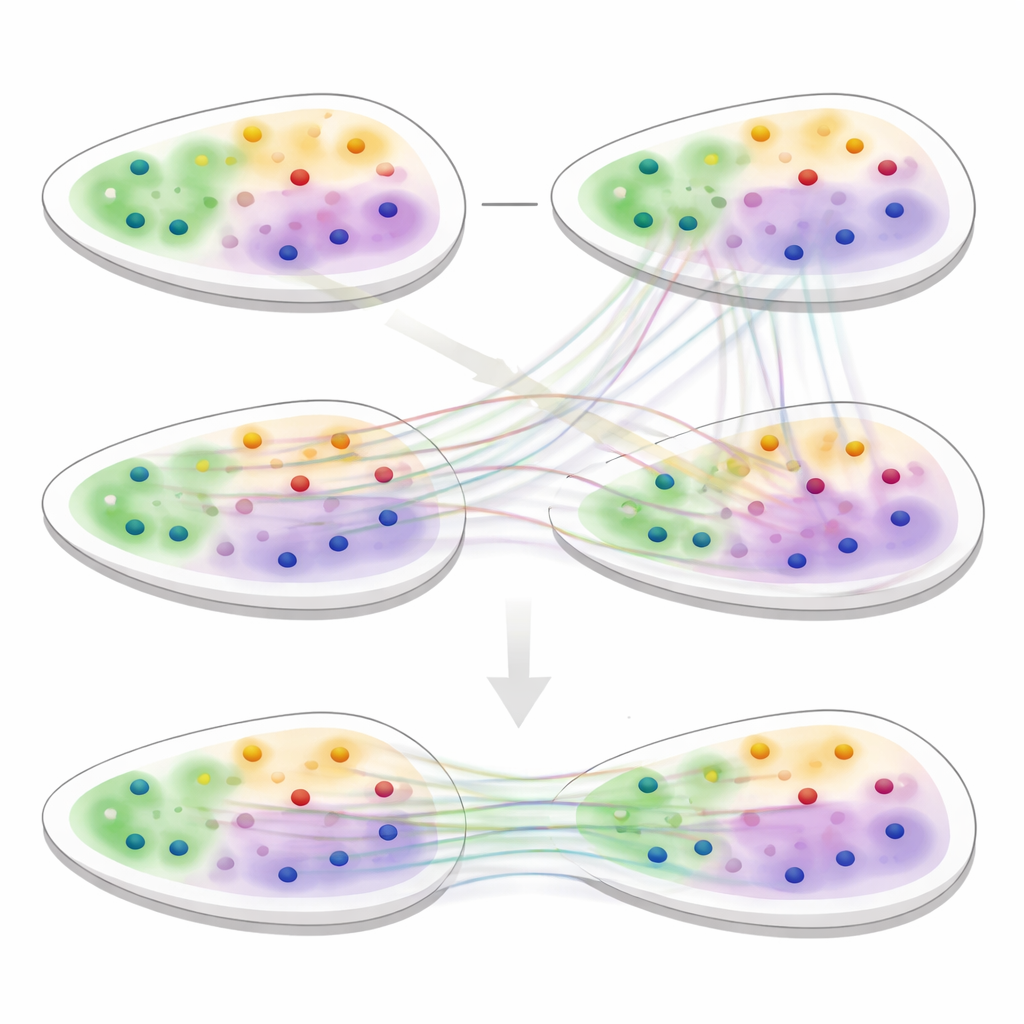
隠れた組織構造の顕在化
3d-OTを検証するために、チームはヒト脳、乳がん、リンパ節、複数のマウス臓器を含むさまざまなデータセットで主要な空間解析ツールと比較しました。単一スライスのクラスタリング課題では、3d-OTはヒトおよびマウス皮質の既知の層をより正確に再現し、競合手法よりも腫瘍領域をより良く識別しました。RNAとクロマチンマークを組み合わせたマルチオミクスのマウス脳データでは、しばしば単一の帯状に見える最深部皮質層内の二つのサブレイヤーを分離し、これらの細かい領域のマーカー遺伝子を強調しました。複数の技術と解像度にまたがり、心臓や神経堤のような難しい組織を含め、3d-OTは既存の整列法よりも滑らかで解剖学的に忠実な整列を提供しました。
時間を通して臓器を追う
最も印象的なデモンストレーションは、マウス胚の発生を再構築した事例から得られました。複数の胚日からの空間データを用いて、3d-OTは時間を越えてスライスを整列し、臓器成長の3D「ムービー」を構築しました。例えば心臓が緻密な形状からリング状の構造へと変化し再び戻る様子や、肝臓が安定して拡大する過程を捉えました。また、初期の前駆領域を後の臓器に結びつけ、尿生殖稜が腎臓や卵巣へ、皮筋板(dermomyotome)が筋肉や結合組織へと正しくトレースされる経路を示しました。これらの軌跡は既知の発生生物学と一致すると同時に、さらなる研究のための追加的な分化経路を示唆しました。
将来の生物学にとっての意味
簡潔に言えば、3d-OTは散在する多層の組織スナップショットを、分子的同一性と物理的形状の両方を尊重する一貫した高解像度3Dマップに変換します。ジオメトリを明示的に符号化し、スライス間で柔軟なソフトマッチを可能にすることで、異なる技術や時間点からのデータを整列し、微細な組織領域を識別する点で従来の手法を上回ります。空間マルチオミクスのデータセットが増大するにつれて、3d-OTのような手法は研究者が平面的な画像から、健康・疾患・発生における臓器の動的な3Dアトラスへと進むのを助けるでしょう。
引用: Dai, B., Yi, L., Wang, P. et al. 3d-OT: a deep geometry-aware framework for heterogeneous slices alignment of spatial multi-omics. Nat Methods 23, 760–771 (2026). https://doi.org/10.1038/s41592-026-03034-9
キーワード: 空間オミクス, マルチオミクス統合, 組織の3D再構築, 胚発生, 計算生物学