Clear Sky Science · fr
3d-OT : un cadre profond conscient de la géométrie pour l’alignement de coupes hétérogènes en multi-omique spatiale
Voir les tissus en trois dimensions
Les biologistes peuvent de plus en plus mesurer non seulement quelles molécules sont actives dans une cellule, mais aussi l’emplacement exact de cette cellule au sein d’un tissu. Ces nouvelles cartes « spatiales » promettent une meilleure compréhension de la connectivité cérébrale, de la propagation des tumeurs et de la façon dont les embryons construisent les organes. Pourtant, la plupart des expériences ne capturent encore que des coupes fines, chacune utilisant des types de mesures et des résolutions différentes. Cet article présente 3d-OT, une méthode computationnelle qui assemble ces coupes en vues 3D cohérentes, tout en exploitant au mieux l’information moléculaire riche contenue dans chaque tranche.
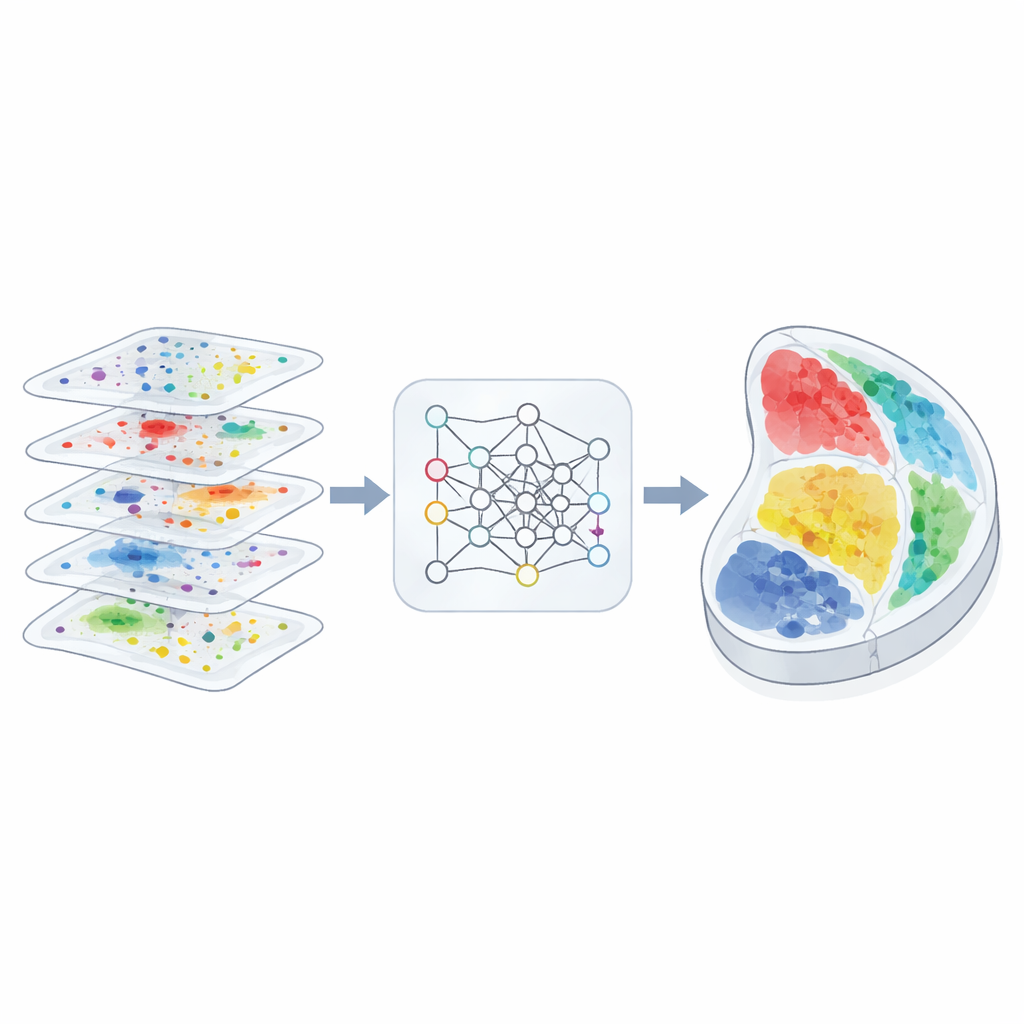
Pourquoi cartographier l’espace est important
La génétique et la génomique traditionnelles nous indiquent quelles molécules contiennent les cellules, mais pas où ces cellules se situent. Les technologies spatiales changent la donne en enregistrant à la fois le profil moléculaire de chaque micro-zone d’un tissu et ses coordonnées physiques. Différentes méthodes mettent en avant différentes couches moléculaires : certaines profilent l’ARN, d’autres les protéines, d’autres encore les marques chimiques sur l’ADN. Chaque couche révèle un aspect distinct de l’organisation tissulaire. Le défi vient du fait que les chercheurs se retrouvent souvent avec plusieurs coupes partielles et chevauchantes, mesurées avec des outils différents. Aligner ces coupes hétérogènes dans un espace 3D cohérent, sans perdre le détail anatomique fin, a été un problème majeur non résolu.
Une vision des tissus consciente de la géométrie
Les auteurs ont conçu 3d-OT pour traiter chaque coupe comme un « nuage de points », un ensemble de spots dans l’espace physique portant des mesures multi-omiques. Plutôt que de s’appuyer principalement sur une grille ou un graphe pour décrire les relations de voisinage, 3d-OT utilise une architecture de réseau neuronal appelée PointNet++, développée à l’origine pour la reconnaissance d’objets 3D. Ce réseau alimente à plusieurs reprises chaque spot non seulement avec ses signaux moléculaires mais aussi avec ses coordonnées exactes, permettant au modèle d’apprendre des motifs géométriques subtils tels que des structures corticales en couches ou des frontières d’organes courbées. Pour les coupes comportant plus d’une couche moléculaire, un module de fusion combine les modalités en une représentation partagée tout en préservant la contribution distinctive de chaque couche.
Aligner les coupes avec des correspondances souples
Le deuxième pilier de 3d-OT est un module d’alignement basé sur le « transport optimal », un cadre mathématique pour appairer deux distributions tout en préservant leur forme globale. Plutôt que d’imposer un appariement rigide un-à-un entre les spots de deux coupes, la méthode calcule des correspondances souples : chaque spot d’une coupe source peut s’apparier partiellement à plusieurs candidats d’une coupe cible. Une perte de reconstruction fondée sur la distance de Chamfer récompense les alignements qui font que les positions reconstruites ressemblent étroitement aux positions réelles de la cible. Des contraintes supplémentaires de lissage et de « divergence nulle » encouragent le flux de spots entre les coupes à suivre des déformations tissulaires réalistes et continues, telles que le pliage, l’étirement ou la croissance, plutôt que des sauts ou torsions improbables.
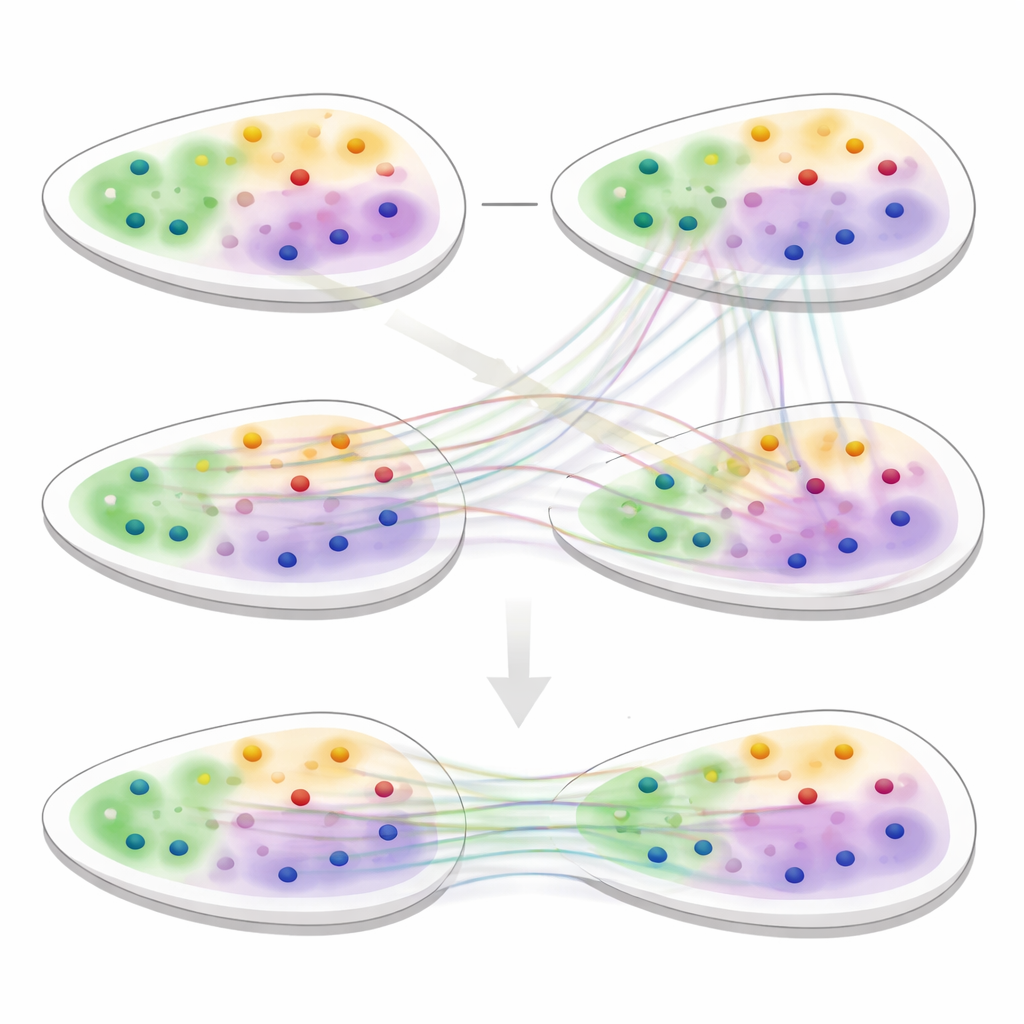
Révéler la structure tissulaire cachée
Pour évaluer 3d-OT, l’équipe l’a comparé aux principaux outils d’analyse spatiale sur une variété de jeux de données, incluant cerveau humain, cancer du sein, ganglion lymphatique et plusieurs organes de souris. Dans des tâches de clustering sur une seule coupe, 3d-OT a récupéré avec plus de précision les couches connues du cortex humain et murin et a mieux distingué les régions cancéreuses que les méthodes concurrentes. Dans des données multi-omiques du cerveau de souris combinant ARN et marques chromatiniennes, il a séparé deux sous-couches à l’intérieur de la couche corticale la plus profonde qui apparaissent souvent comme une seule bande, et a mis en évidence des gènes marqueurs pour ces régions fines. À travers plusieurs technologies et résolutions, y compris des tissus difficiles comme le cœur et la crête neurale, 3d-OT a fourni des alignements plus lisses et plus fidèles anatomiquement que les méthodes d’alignement existantes.
Suivre les organes au fil du temps
La démonstration la plus frappante provenait peut-être de la reconstruction du développement embryonnaire chez la souris. En utilisant des données spatiales de plusieurs jours embryonnaires, 3d-OT a aligné des coupes au fil du temps pour construire des « films » 3D de la croissance des organes. Il a capturé, par exemple, comment le cœur passe d’une forme compacte à une structure en anneau puis revient, et comment le foie s’étend de façon continue. La méthode a aussi relié des régions précurseures précoces à des organes ultérieurs, retraçant correctement la crête urogénitale vers rein et ovaire, et le dermomyotome vers muscle et tissu conjonctif. Ces trajectoires correspondaient à la biologie du développement connue, tout en suggérant des voies de différenciation supplémentaires à explorer.
Ce que cela signifie pour la biologie future
En termes simples, 3d-OT transforme des instantanés dispersés et multi-couches de tissus en cartes 3D cohérentes et haute résolution qui respectent à la fois l’identité moléculaire et la forme physique. En encodant explicitement la géométrie et en permettant un appariement flexible et souple entre les coupes, il surpasse les outils antérieurs pour identifier des régions tissulaires fines et aligner des données issues de technologies et de moments différents. À mesure que les jeux de données de multi-omique spatiale s’étendront, des méthodes comme 3d-OT aideront les chercheurs à passer d’images planes à des atlas 3D dynamiques des organes en santé, en maladie et en développement.
Citation: Dai, B., Yi, L., Wang, P. et al. 3d-OT: a deep geometry-aware framework for heterogeneous slices alignment of spatial multi-omics. Nat Methods 23, 760–771 (2026). https://doi.org/10.1038/s41592-026-03034-9
Mots-clés: omique spatiale, intégration multi-omique, reconstruction tissulaire 3D, développement embryonnaire, biologie computationnelle