Clear Sky Science · sv
Kontextmedveten design av syntetiska promotorer med neurala nätverk möjliggör omkoppling av eukaryota transkriptionsnätverk
Lära celler nya trick
Modern bioteknik vilar ofta på en enkel fråga: kan vi tala om för en cell exakt när en gen ska slås på eller av? Den här artikeln utforskar ett nytt sätt att göra just det i bakjäst, genom att använda artificiell intelligens för att omforma små DNA-brytare kallade promotorer. Genom att lära sig hur dessa naturliga brytare är uppbyggda visar författarna att datorer kan föreslå precisa ändringar som låter forskare koppla in nya kontrollknappar i cellens genetiska kretsar.
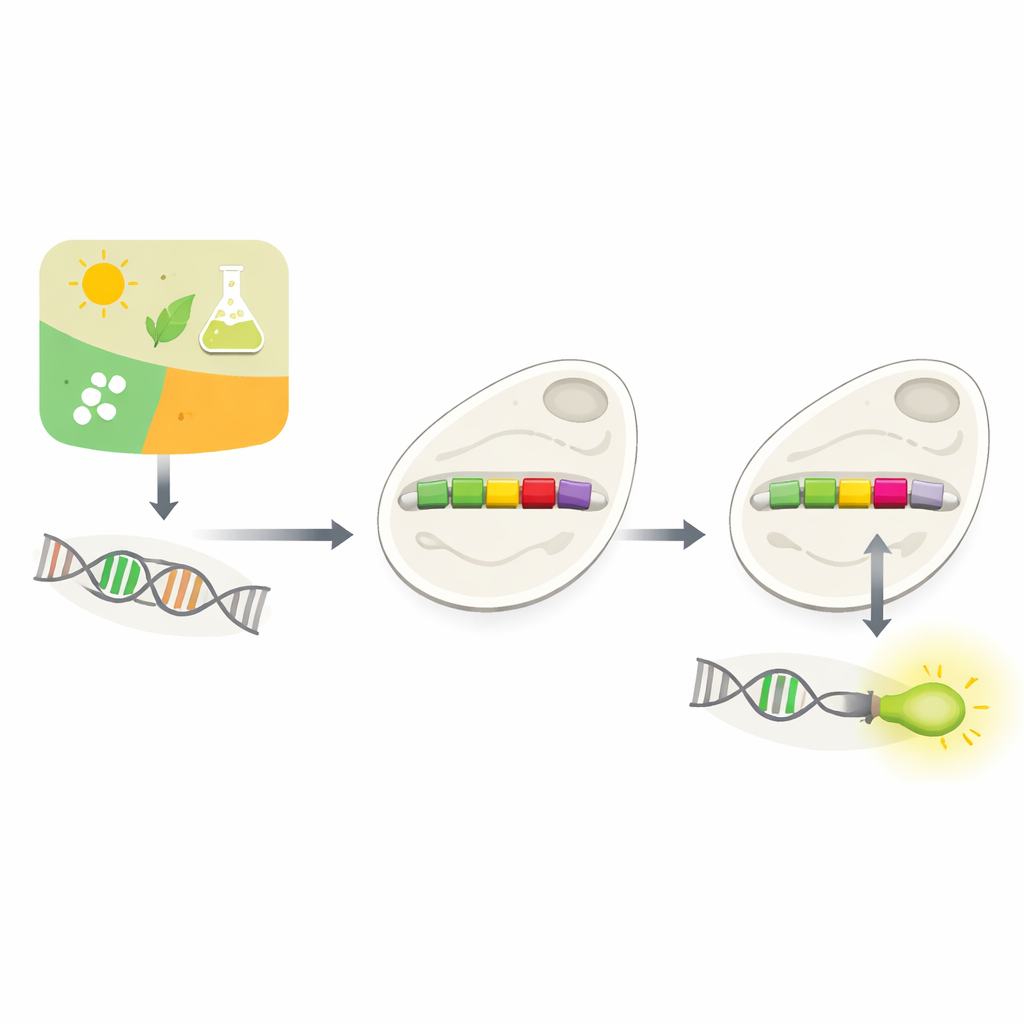
Hur celler bestämmer vilka gener de ska använda
Varje cell måste ständigt bestämma vilka gener som ska användas och när. Mycket av detta beslutsfattande sker vid promotorer, korta DNA-sträckor som ligger precis före gener. Promotorer fungerar som dimmerknappar och svarar på signaler från omgivningen eller från cellens inre. Biologer har länge försökt bygga anpassade promotorer för att kunna styra gener fritt — till exempel för att få jäst att producera värdefulla kemikalier eller att känna av toxiner. Men naturliga promotorer är komplicerade och kontextberoende, och att bara lägga in nya kontrollelement i dem bryter ofta deras funktion. Experimentell testning av många möjliga designer är långsam och dyr.
Låta neurala nätverk läsa DNA-logik
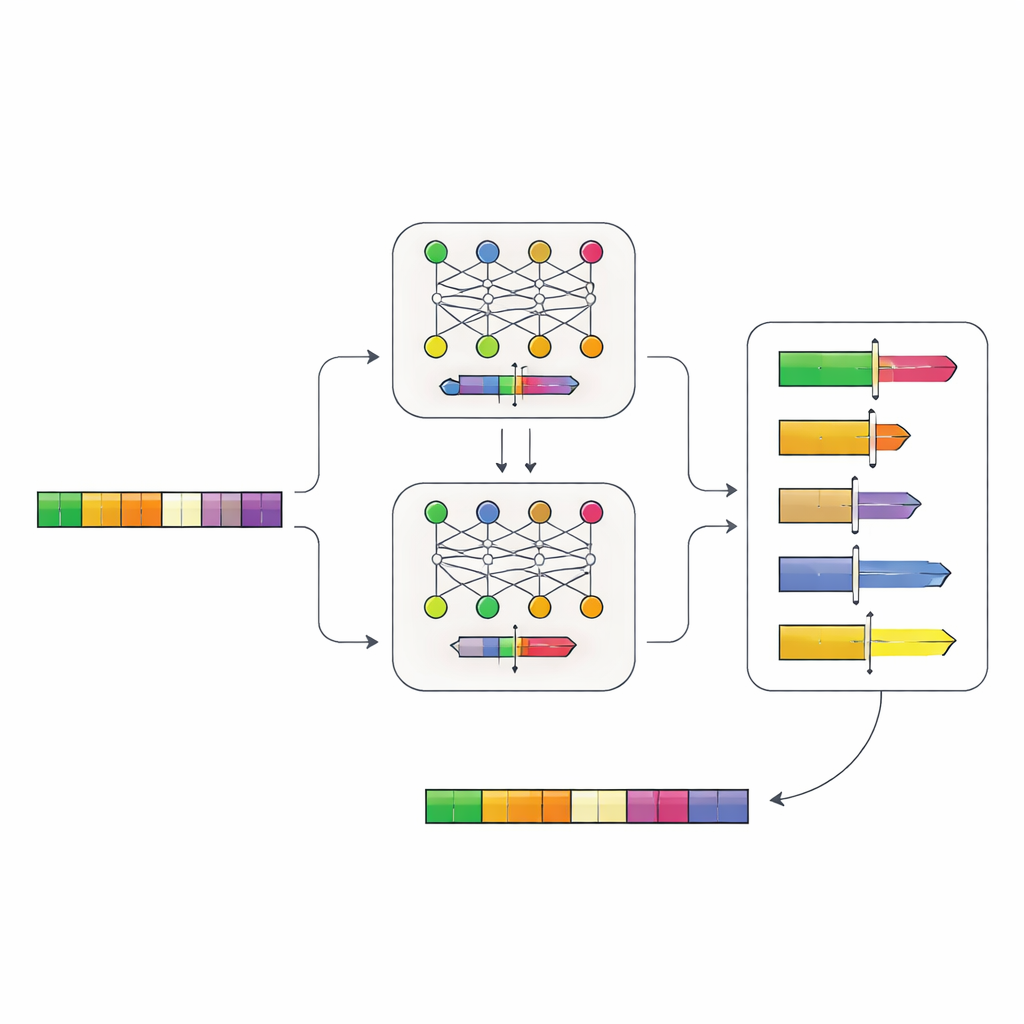
Författarna byggde ett tvåstegs system med neurala nätverk som lär sig promotorernas ”grammatik” direkt från DNA. Först samlade de in promotorsekvenser från mer än 100 000 gener i jästsläktingar och tränade en modell, kallad Place-Back, att känna igen var en kort DNA-segment ursprungligen kom ifrån efter att det hade skrikits om och delvis ersatts. Eftersom modellen måste återfinna rätt plats utifrån kontexten ensam, lärde den sig subtila mönster om vilka regioner i en promotor som kan ändras utan att störa dess kärnfunktion. En andra modell, Determiner, granskade sedan Place-Backs förutsägelser och bestämde både var ett nytt kontrollelement borde sitta och hur stor region av DNA som borde skrivas om.
Designa växlingsbara promotorer in silico
Med detta system i handen ställde teamet en praktisk fråga: var kunde de sätta in ett välkänt bindningsställe för TetR-repressorproteinet i verkliga jästpromotorer, så att gener kunde stängas av på kommando? De testade virtuellt alla 6 011 promotorer i jästgenomet och producerade en rangordnad lista med tusentals kandidater där det nya elementet borde ”passa” utan att störa viktiga funktioner, som själva startregionen där transkriptionen börjar. Modellerna föredrog ofta platser nära dessa kärnregioner men utan att orsaka direkt skada, vilket tyder på att de hade lärt sig biologiskt meningsfulla begränsningar.
Sätta AI-designade brytare på prov
För att se om datorns förslag fungerade i levande celler valde forskarna fyra naturliga jästpromotorer med olika styrkor och redigerade var och en exakt enligt rekommendation, genom att infoga TetR-bindningsstället på den förutsagda platsen. De kopplade dessa promotorer till en stark luciferasrapportör och introducerade TetR på en separat DNA-bit, så att det nya systemet inte skulle störa jästens egna regleringssystem. I närvaro av TetR visade tre av de fyra konstruktionerna stark repression, och en uppnådde nästan fullständig avstängning — ungefär 98 % minskning i aktivitet — utan ytterligare justeringar. Alternativa insättningsställen som inte föreslogs av modellen skadade ofta promotorn eller förstörde dess förmåga att svara, vilket understryker att placeringen spelar roll och att det neurala nätverket identifierade specifika ”sweet spots”.
Omkoppling av jästens inbyggda beslutsfattande
Teamet använde sedan samma angreppssätt för att ändra jästens egna regleringsnätverk, snarare än att lägga till ett artificiellt system. De redigerade promotorn för PCF11, en gen som är nödvändig för överlevnad, för att infoga ett bindningsställe för Mig1, en naturlig repressor som blir aktiv i närvaro av glukos. I tester uppträdde den omdesignade promotorn som avsett: när glukos fanns närvarande sjönk PCF11-aktiviteten med mer än hälften; när glukos saknades var aktiviteten något högre än normalt. Efter att ha bytt in denna syntetiska promotor i jästgenomet växte cellerna nästan normalt vid låg sockerhalt men nådde en lägre maximal täthet vid hög sockerhalt, vilket visar att den essentiella genen nu villkorligt begränsats av den nya kopplingen.
Vad detta betyder för framtida genetisk design
Enkelt uttryckt visar detta arbete att neurala nätverk kan lära sig tillräckligt mycket om genregleringens ”språk” för att föreslå smarta, kontextmedvetna ändringar i DNA-brytare. Utan att behöva experimentella mätningar som träningsetiketter pekar modellerna ut platser där nya kontrollelement säkert kan infogas så att gener blir responsiva för valda signaler. De framgångsrika testerna i jäst, inklusive omkopplingen av en essentiell gens reglering, antyder en väg mot skalbar, prediktiv design av regulatoriskt DNA i många organismer. Detta kan påskynda skapandet av skräddarsydda genetiska program för medicin, jordbruk och industriell bioteknik, samtidigt som det avslöjar nya regler för hur celler naturligt organiserar sina egna beslutskretsar.
Citering: Kuhajda, L., Honzik, T., Svec, J. et al. Context-aware synthetic promoter design using neural networks enables rewiring of eukaryotic transcriptional networks. npj Syst Biol Appl 12, 65 (2026). https://doi.org/10.1038/s41540-026-00684-5
Nyckelord: syntetisk biologi, genreglering, neurala nätverk, promotorengineering, jäst