Clear Sky Science · pl
Projektowanie syntetycznych promotorów świadomych kontekstu z użyciem sieci neuronowych umożliwia przerejestrowanie eukariotycznych sieci transkrypcyjnych
Nauczanie komórek nowych umiejętności
Współczesna biotechnologia często sprowadza się do prostego pytania: czy możemy dokładnie powiedzieć komórce, kiedy włączyć lub wyłączyć dany gen? W artykule opisano nową metodę osiągnięcia tego w piekarniczych drożdżach, wykorzystując sztuczną inteligencję do przeprojektowania malutkich przełączników DNA zwanych promotorami. Ucząc się, jak te naturalne przełączniki są zbudowane, autorzy pokazują, że komputery mogą proponować precyzyjne edycje, które pozwalają naukowcom podłączyć nowe pokrętła sterujące do genetycznego układu komórki.
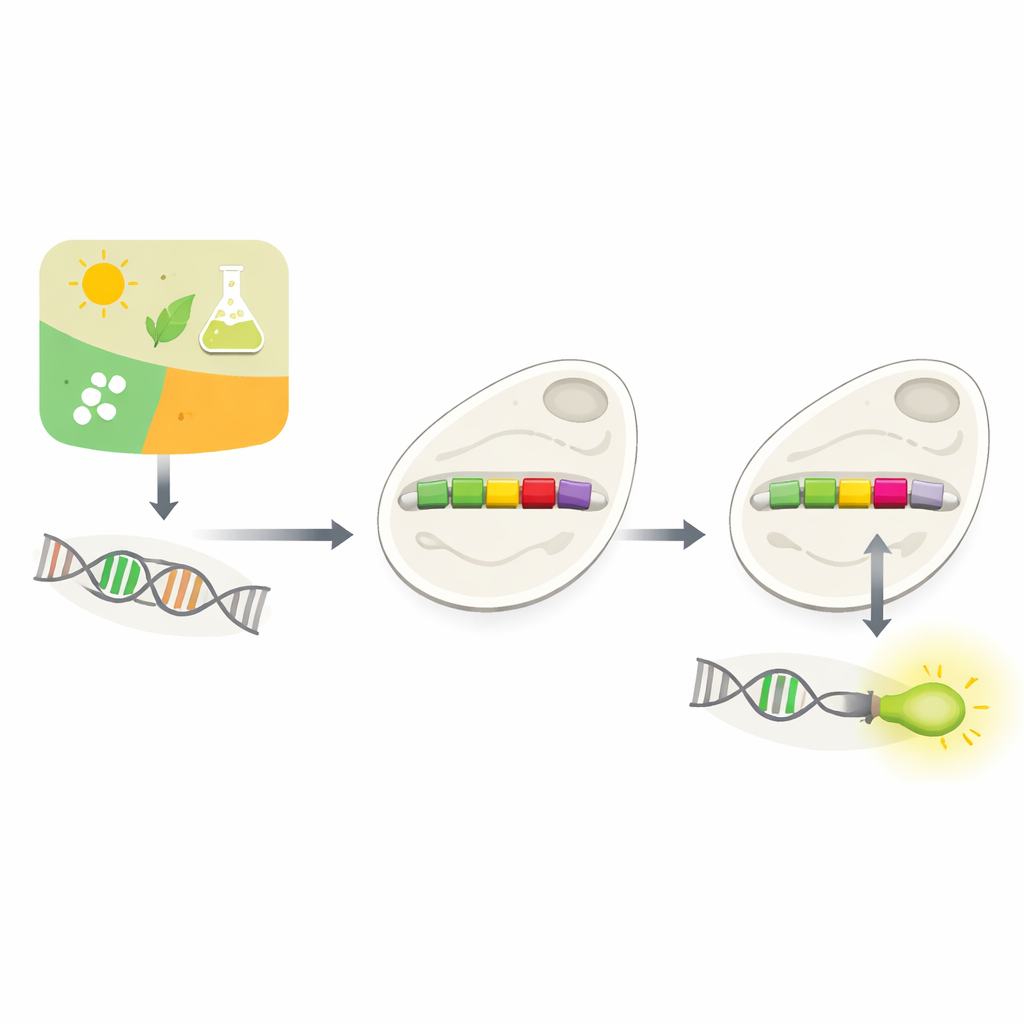
Jak komórki decydują, których genów używać
Każda komórka musi nieustannie decydować, których genów użyć i kiedy. Duża część tego procesu podejmowania decyzji odbywa się w promotorach — krótkich odcinkach DNA znajdujących się tuż przed genami. Promotory działają jak ściemniacze, reagując na sygnały z otoczenia lub z wnętrza komórki. Biolodzy od dawna próbują tworzyć niestandardowe promotory, aby móc kontrolować geny wedle potrzeby — na przykład by drożdże produkowały cenne chemikalia lub wykrywały toksyny. Jednak naturalne promotory są skomplikowane i zależne od kontekstu, a proste wstawianie nowych elementów regulacyjnych często zaburza ich funkcję. Eksperymentalne testowanie wielu możliwych projektów jest wolne i kosztowne.
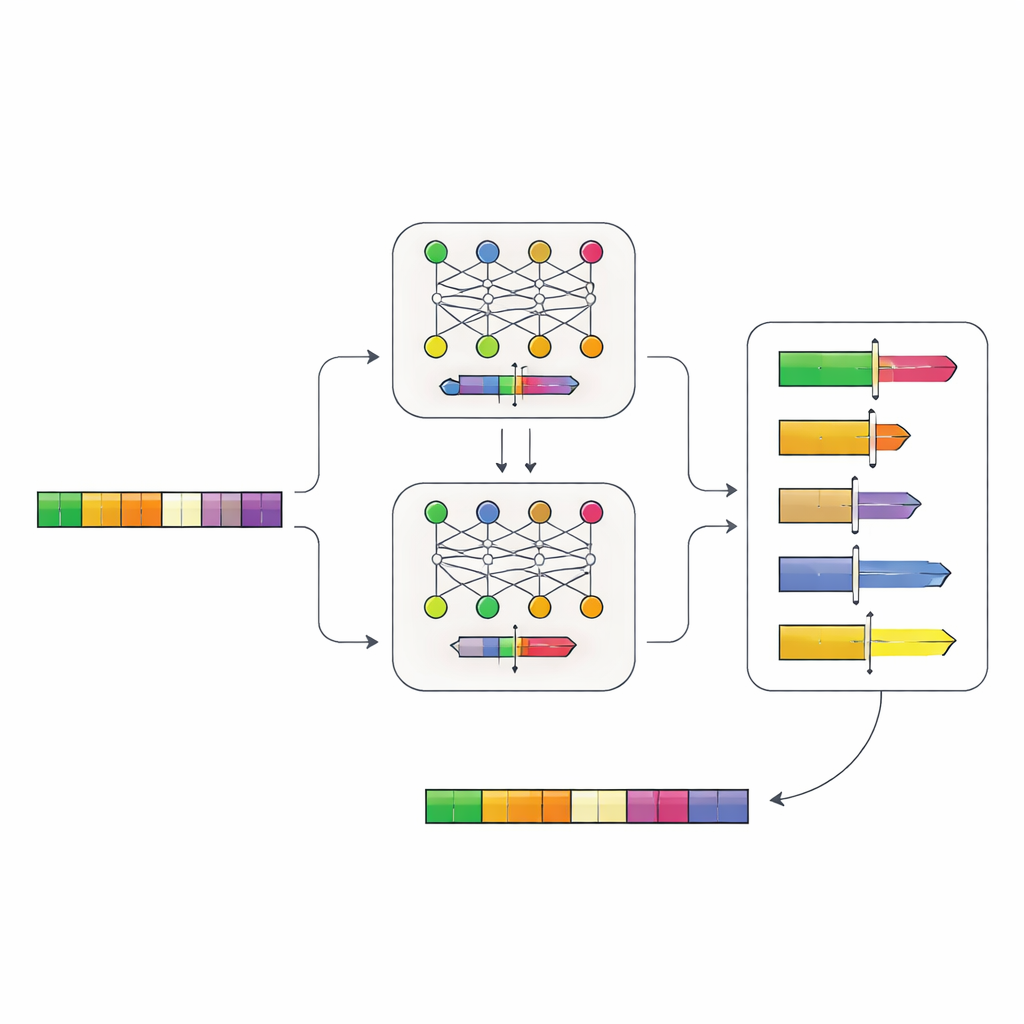
Pozwalając sieciom neuronowym czytać logikę DNA
Autorzy zbudowali dwustopniowy system sieci neuronowych, który uczy się „gramatyki” promotorów bezpośrednio z DNA. Najpierw zebrali sekwencje promotorów z ponad 100 000 genów u krewnych drożdży i wytrenowali model o nazwie Place-Back, aby rozpoznawał, skąd pochodził krótki fragment DNA po jego przetasowaniu i częściowej zamianie. Ponieważ model musiał odtworzyć właściwe miejsce wyłącznie na podstawie kontekstu, nauczył się subtelnych wzorców, które regiony promotora można zmieniać bez zakłócania jego podstawowej funkcji. Drugi model, Determiner, analizował następnie prognozy Place-Back i decydował zarówno, gdzie należy umieścić nowy element regulacyjny, jak i jak duży fragment DNA powinien zostać przepisany.
Projektowanie przełączalnych promotorów in silico
Wyposażony w ten system zespół postawił praktyczne pytanie: gdzie można wstawić dobrze znane miejsce wiązania dla represora TetR do rzeczywistych promotorów drożdży, tak aby geny dało się wyłączać na zawołanie? Wirtualnie przetestowali wszystkie 6 011 promotorów w genomie drożdży i wygenerowali uszeregowaną listę tysięcy kandydatów, w których nowy element powinien „pasować” bez naruszenia istotnych cech, takich jak podstawowy region startowy, gdzie zaczyna się transkrypcja. Modele często faworyzowały miejsca blisko tych regionów jądrowych, jednocześnie unikając bezpośrednich uszkodzeń, co sugeruje, że nauczyły się biologicznie istotnych ograniczeń.
Sprawdzanie w praktyce przełączników zaprojektowanych przez AI
Aby sprawdzić, czy sugestie komputera działają w żywych komórkach, badacze wybrali cztery rodzime promotory drożdżowe o różnej sile i edytowali każdy dokładnie zgodnie z zaleceniami, wstawiając miejsce wiązania TetR w przewidzianym miejscu. Podłączyli te promotory do jasnego raportera lucyferazy i wprowadzili TetR na oddzielnym kawałku DNA, aby nowy system nie zakłócał własnej regulacji drożdży. W obecności TetR trzy z czterech projektów wykazały silne tłumienie, a jeden osiągnął niemal całkowite wyciszenie — około 98% redukcji aktywności — bez dalszego strojenia. Alternatywne miejsca wstawienia, niezasugerowane przez model, często uszkadzały promotor lub niszczyły jego zdolność do reagowania, co podkreśla znaczenie miejsca wstawienia i że sieć neuronowa identyfikowała specyficzne „słodkie punkty”.
Przeregulowanie natywnego systemu decyzyjnego drożdży
Następnie zespół użył tej samej metody, aby zmienić własną sieć regulacyjną drożdży, zamiast stosować sztuczny dodatek. Zedytowali promotor PCF11, genu niezbędnego do przeżycia, aby wstawić miejsce wiązania dla Mig1, naturalnego represora aktywnego w obecności glukozy. W testach przeprojektowany promotor zachowywał się zgodnie z założeniem: w obecności glukozy aktywność PCF11 spadła o ponad połowę; przy braku glukozy aktywność była nieco wyższa niż normalnie. Po podmianie tego syntetycznego promotora w genomie drożdży komórki rosły niemal normalnie przy niskiej zawartości cukru, ale osiągały niższą maksymalną gęstość przy wysokiej zawartości cukru, co pokazuje, że gen niezbędny został teraz warunkowo ograniczony przez nowe połączenie.
Co to oznacza dla przyszłego projektowania genetycznego
Mówiąc prosto, praca ta pokazuje, że sieci neuronowe mogą nauczyć się wystarczająco dużo o „języku” kontroli genów, aby proponować sprytne, świadome kontekstu edycje przełączników DNA. Bez konieczności używania pomiarów eksperymentalnych jako etykiet treningowych modele wskazują miejsca, w które można bezpiecznie wstawiać nowe elementy sterujące, tak aby geny stawały się reagujące na wybrane sygnały. Udane testy w drożdżach, w tym przerejestrowanie kontroli genu niezbędnego, sugerują drogę ku skalowalnemu, predykcyjnemu projektowaniu DNA regulatorowego w wielu organizmach. Może to przyspieszyć tworzenie szytych na miarę programów genetycznych dla medycyny, rolnictwa i biotechnologii przemysłowej, a także ujawnić nowe reguły dotyczące tego, jak komórki naturalnie organizują własne układy decyzyjne.
Cytowanie: Kuhajda, L., Honzik, T., Svec, J. et al. Context-aware synthetic promoter design using neural networks enables rewiring of eukaryotic transcriptional networks. npj Syst Biol Appl 12, 65 (2026). https://doi.org/10.1038/s41540-026-00684-5
Słowa kluczowe: biologia syntetyczna, regulacja genów, sieci neuronowe, inżynieria promotorów, drożdże