Clear Sky Science · ru
scDecorr: обучение представлений на основе декорреляции признаков позволяет самообучающейся выравнивать множественные эксперименты по одиночным клеткам
Почему важно объединять данные одиночных клеток
Современная биология умеет считывать активность тысяч генов в отдельных клетках, обнаруживая редкие типы клеток и тонкие состояния при заболеваниях. Но такие эксперименты по одиночным клеткам часто выполняют в разных лабораториях, на разных приборах и по разным протоколам, поэтому их результаты трудно объединять. В статье предлагается scDecorr — новый вычислительный метод, который автоматически согласует такие разнородные наборы данных, так что похожие клетки оказываются рядом, даже если они были измерены очень разными способами. Это облегчает создание богатых атласов клеток и повторное использование данных между исследованиями.
Много наборов данных — один общий язык
Секвенирование РНК в одиночных клетках показывает, какие гены включены в каждой клетке. В теории это позволяет сравнивать клетки между органами, пациентами или состояниями болезни. На практике технические особенности — так называемые эффекты партии — могут заглушить истинные биологические различия. Клетки одного типа могут выглядеть по-разному лишь потому, что их обработали в другой день или на другой технологии. scDecorr решает эту проблему, обучая компактное численное «представление» для каждой клетки, в котором похожие по поведению клетки располагаются рядом, а различающиеся — дальше друг от друга. Важная особенность — метод не требует маркированных экспертами меток типов клеток, что делает его пригодным для больших и шумных наборов данных.
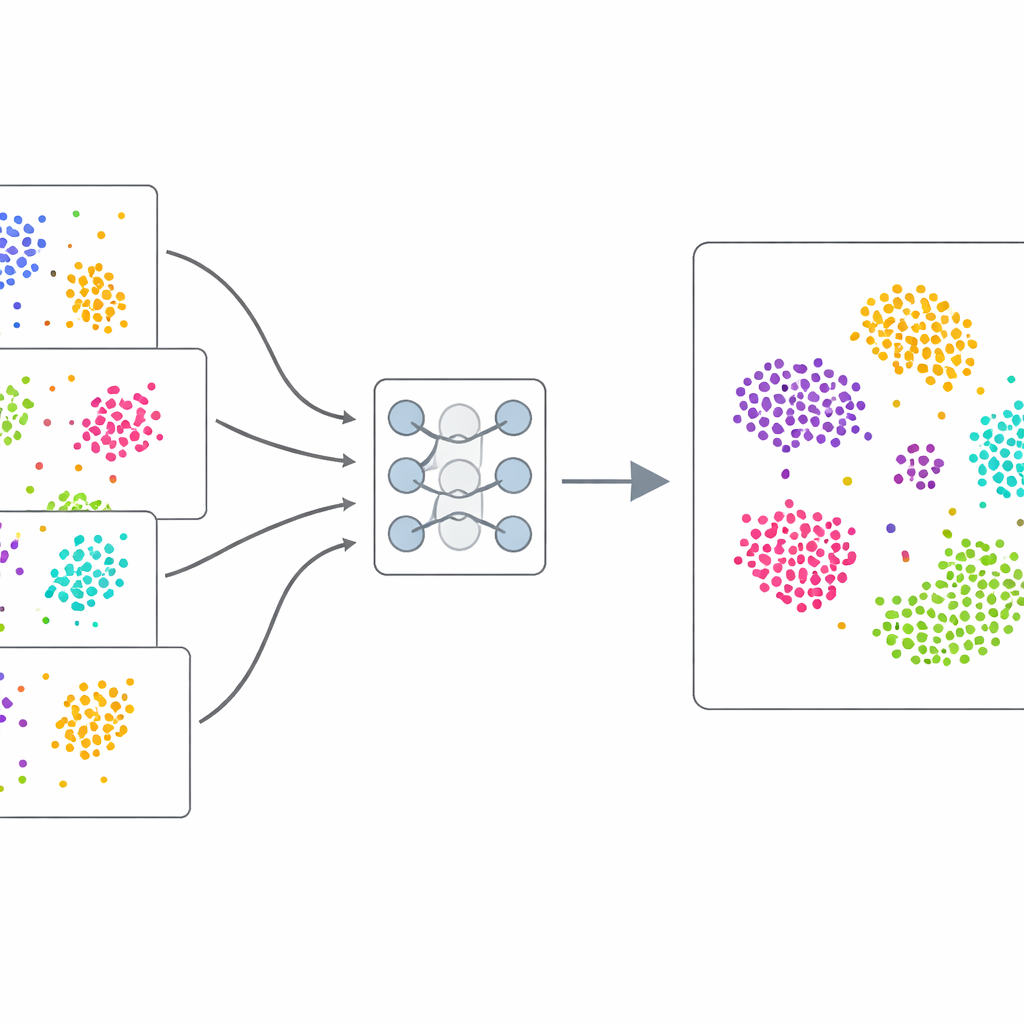
Обучение на самих данных
Вместо опоры на вручную размеченные примеры scDecorr использует самообучение: сами данные дают обучение. Для каждой клетки метод создаёт две слегка искажённые копии её профиля экспрессии генов, например случайно опуская или перемешивая некоторые значения. Близнецовая нейронная сеть обрабатывает обе версии и обучается выдавать очень похожие внутренние свёртки для двух представлений одной и той же клетки, но различающиеся свёртки для разных клеток. Одновременно scDecorr поощряет каждую компоненту этих свёрток нести уникальную информацию, чтобы ни одна из характеристик просто не дублировала другую. Этот шаг «декорреляции» помогает предотвратить свёртывание модели на нескольких доминирующих шаблонах и вместо этого захватить широкий спектр биологических сигналов.
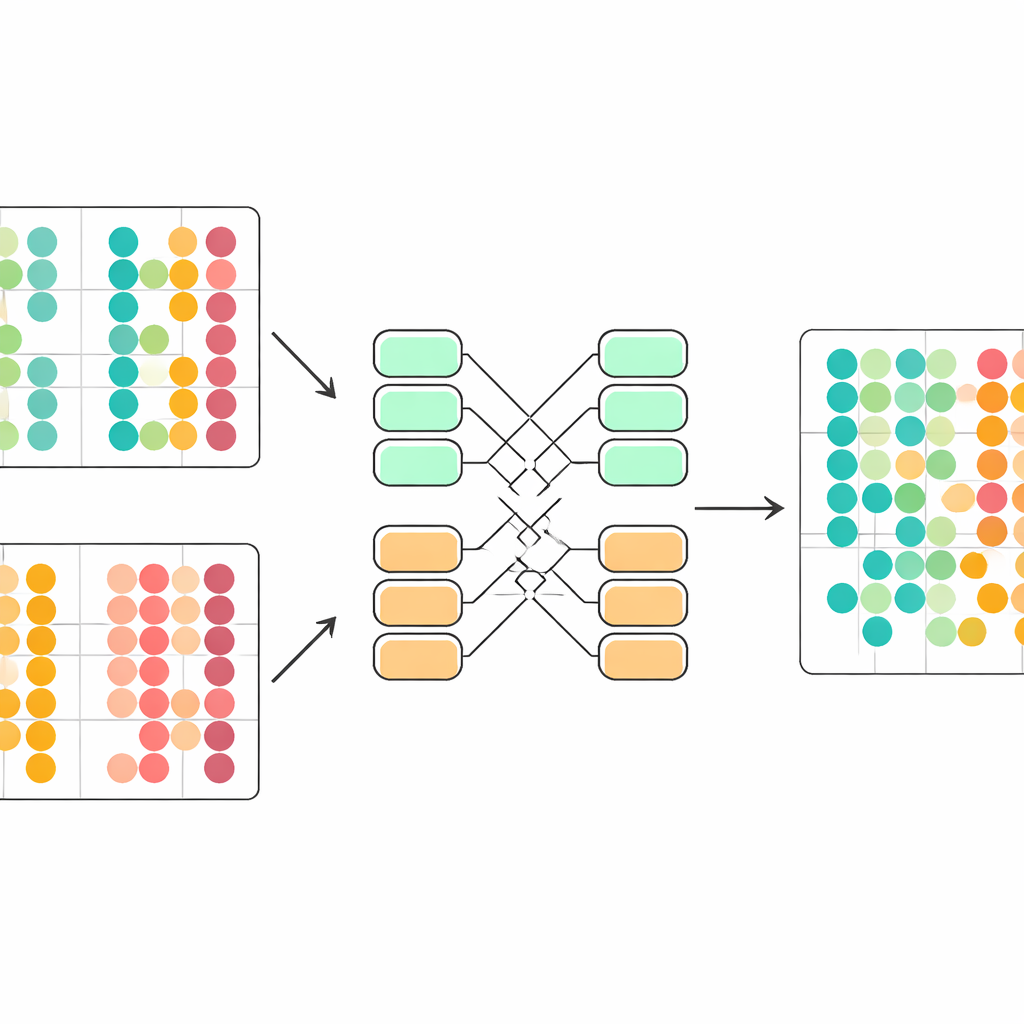
Ненавязчивая коррекция технических различий
Ключевая проблема в том, что клетки из разных исследований подчиняются немного разным статистическим законам. При наивном смешивании модель может принять технические различия за биологию. scDecorr решает это идеей из адаптации доменов. Все партии используют один и тот же энкодер, но у каждой партии свои слои нормализации, которые масштабируют признаки так, чтобы внутри этой партии каждое измерение имело стандартное распределение. Цель декорреляции затем применяется отдельно внутри каждой партии, при этом все партии проходят через тот же энкодер. Это мягко побуждает энкодер выдавать представления, имеющие общую структуру между экспериментами, так что похожие типы клеток из разных источников естественно выравниваются в изученном пространстве без явных шагов сопоставления.
Лучше существующих инструментов на реальных данных
Авторы тщательно тестируют scDecorr на пяти требовательных коллекциях данных по одиночным клеткам, охватывающих ткани человека и мыши, иммунные клетки из разных органов и несколько технологий секвенирования. Они сравнивают метод с несколькими широко используемыми инструментами интеграции, а также с простыми подходами типа главных компонент. В задаче за задачей scDecorr лучше сохраняет истинные биологические группировки клеток — по стандартным метрикам кластеризации — при этом достаточно смешивая партии, чтобы убрать очевидное техническое разделение. Он особенно хорошо избегает чрезмерной коррекции, когда разные типы клеток ошибочно сливаются в результате удаления эффектов партии, и, как правило, сохраняет чёткие границы для редких или специфичных для партии типов клеток, которые другие методы размывают или теряют.
Надёжная передача меток клеток
Кроме слияния наборов данных, scDecorr тестируют на задаче переноса меток: использование аннотированного референсного набора для присвоения меток типов клеток новому, немаркированному набору. С помощью простых классификаторов или кластеризации в пространстве scDecorr метод надежно восстанавливает известные типы клеток между разными химиями, платформами и исследованиями. Он часто превосходит или сравним с лучшими существующими инструментами по точности классификации, при этом более последовательно сохраняя внутреннюю структуру типов клеток в каждом наборе. Это поведение сохраняется даже когда только часть типов клеток разделяют наборы данных или когда партии сильно несбалансированы, хотя авторы отмечают, что экстремально несопоставимые настройки остаются трудной задачей для всех методов.
Что это значит для будущих атласов клеток
Проще говоря, scDecorr предлагает способ заставить разнородные эксперименты по одиночным клеткам «говорить на одном языке» без грубой коррекции, стирающей важные различия. Обучая богатые низкоразмерные резюме, устойчивые к шуму, но чувствительные к подлинному биологическому разнообразию, метод упрощает создание объединённых карт клеток по тканям, технологиям и исследованиям, а также повторное использование доступных данных для аннотирования новых экспериментов. Хотя есть простор для дальнейших улучшений — особенно для очень несбалансированных наборов — scDecorr даёт мощную и более осторожную альтернативу классической коррекции партии, помогая учёным яснее увидеть настоящей клеточный ландшафт с меньшими техническими искажениями.
Цитирование: Sanyal, R., Xu, Y., Kim, H. et al. scDecorr: feature decorrelation based representation learning enables self-supervised alignment of multiple single-cell experiments. Sci Rep 16, 13782 (2026). https://doi.org/10.1038/s41598-026-50586-z
Ключевые слова: секвенирование РНК на уровне одной клетки, интеграция данных, самообучение, коррекция эффектов партии, атлас клеток