Clear Sky Science · es
scDecorr: el aprendizaje de representaciones basado en la decorrelación de características permite la alineación auto-supervisada de múltiples experimentos de una sola célula
Por qué importa unir datos de célula única
La biología moderna ya puede leer la actividad de miles de genes en células individuales, revelando tipos celulares raros y estados de enfermedad sutiles. Pero estos experimentos de célula única a menudo se realizan en laboratorios distintos, con máquinas y protocolos diferentes, lo que dificulta combinar sus resultados. El artículo presenta scDecorr, un nuevo método computacional que alinea automáticamente conjuntos de datos tan diversos para que células similares queden juntas, incluso si se midieron de maneras muy distintas. Esto facilita a los investigadores construir atlas celulares ricos y reutilizar datos entre estudios.
Muchos conjuntos de datos, un lenguaje común
La secuenciación de ARN de célula única mide qué genes están activados en cada célula. En principio, esto permite comparar células entre órganos, pacientes o enfermedades. En la práctica, peculiaridades técnicas—conocidas como efectos de lote—pueden ahogar las verdaderas diferencias biológicas. Células del mismo tipo pueden parecer distintas solo porque se procesaron en otro día o con otra tecnología. scDecorr aborda esto aprendiendo un “perfil” numérico compacto para cada célula, en el que las células que actúan de forma similar quedan cerca y las disímiles se mantienen separadas. De forma crucial, lo hace sin necesitar etiquetas de tipo celular proporcionadas por expertos, lo que lo hace adecuado para conjuntos de datos grandes y desordenados.
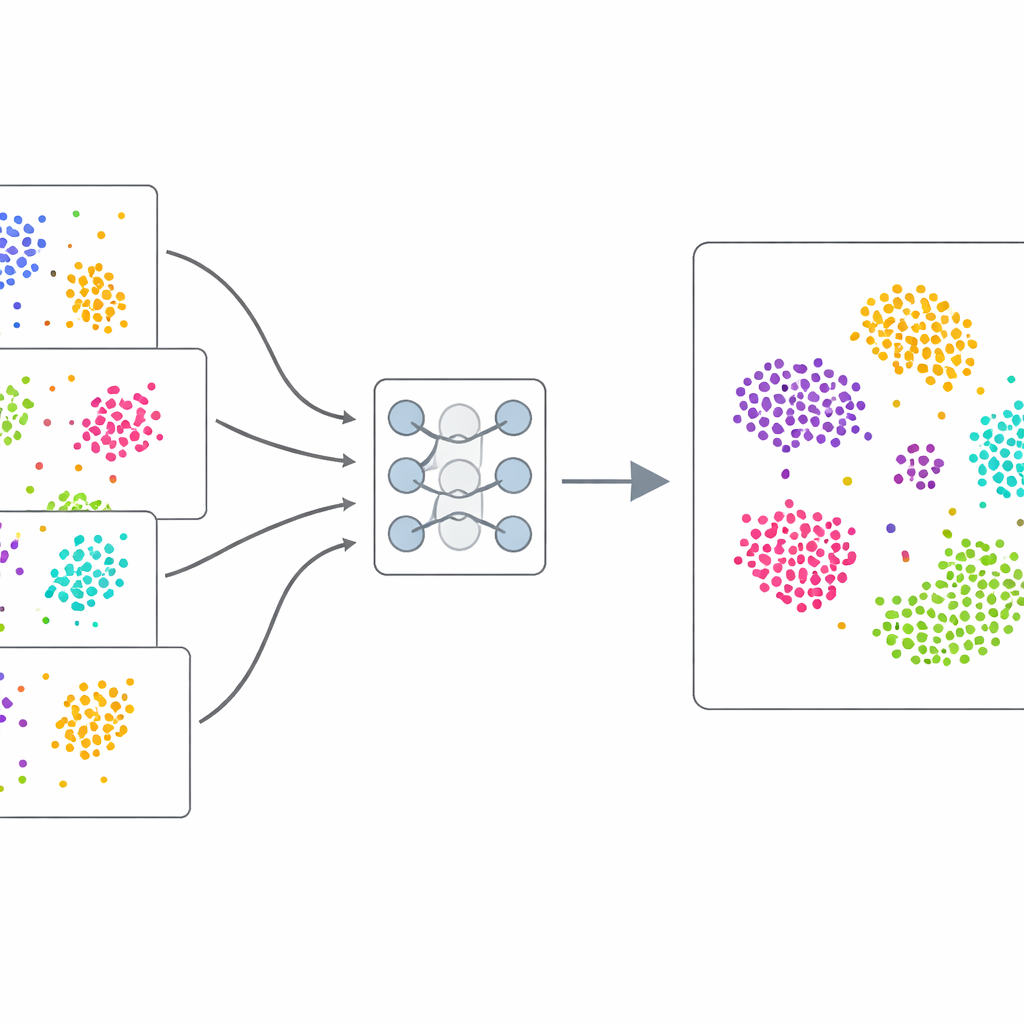
Aprender a partir de los propios datos
En lugar de confiar en ejemplos etiquetados manualmente, scDecorr usa aprendizaje auto-supervisado: los datos proporcionan su propia señal de entrenamiento. Para cada célula, el método crea dos copias ligeramente distorsionadas de su patrón de expresión génica, por ejemplo eliminando o barajando aleatoriamente algunos valores. Una red neuronal gemela procesa ambas versiones y se entrena para producir resúmenes internos muy similares para las dos vistas de la misma célula, pero resúmenes distintos para células diferentes. Al mismo tiempo, scDecorr fomenta que cada componente de esos resúmenes transporte información única, de modo que ninguna característica simplemente duplique a otra. Este paso de "decorrelación" ayuda a evitar que el modelo colapse en unos pocos patrones dominantes y, en su lugar, capture una amplia gama de señales biológicas.
Corrigiendo silenciosamente las diferencias técnicas
Un desafío central es que las células de distintos estudios siguen reglas estadísticas ligeramente diferentes. Si se mezclan de forma ingenua, el modelo puede interpretar erróneamente diferencias técnicas como biológicas. scDecorr afronta esto con una idea tomada de la adaptación entre dominios. Todos los lotes comparten la misma red codificadora, pero cada lote tiene sus propias capas de normalización que reescalan las características para que, dentro de ese lote, cada dimensión tenga una forma estándar. El objetivo de decorrelación se aplica entonces por separado dentro de cada lote, aunque todos los lotes deben pasar por el mismo codificador. Esto empuja suavemente al codificador a producir representaciones que siguen una estructura compartida entre experimentos, de modo que tipos celulares similares de distintas fuentes se alineen naturalmente en el espacio aprendido sin ningún paso explícito de emparejamiento.
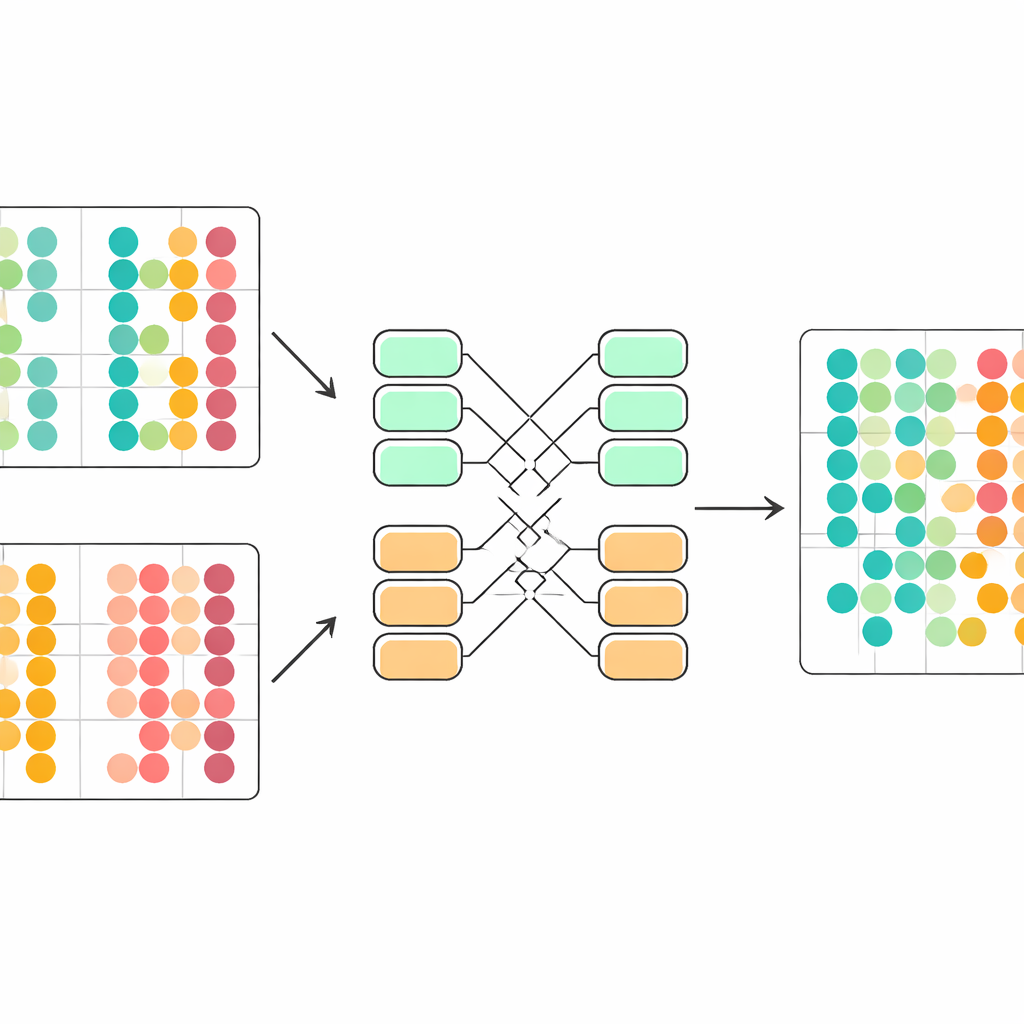
Superando herramientas consolidadas en conjuntos de datos reales
Los autores prueban rigurosamente scDecorr en cinco colecciones exigentes de datos de célula única, abarcando tejidos humanos y de ratón, células inmunitarias de distintos órganos y múltiples tecnologías de secuenciación. Lo comparan con varias herramientas de integración ampliamente usadas, así como con enfoques simples como el análisis de componentes principales. Tarea tras tarea, scDecorr preserva mejor las agrupaciones biológicas reales de las células—medidas por puntuaciones estándar de clúster—al tiempo que mezcla los lotes lo suficiente para eliminar la separación técnica evidente. Es especialmente eficaz evitando la sobrecorrección, donde distintos tipos celulares se fusionan erróneamente en nombre de la eliminación del lote, y tiende a mantener límites claros para tipos celulares raros o específicos de un lote que otros métodos difuminan o pierden.
Transferencia fiable de etiquetas celulares
Más allá de fusionar conjuntos de datos, scDecorr se prueba en transferencia de etiquetas: usar un conjunto de referencia anotado para asignar etiquetas de tipo celular a uno nuevo y no etiquetado. Usando clasificadores simples o agrupamiento en el espacio de scDecorr, el método recupera de forma fiable tipos celulares conocidos a través de distintas químicas, plataformas y estudios. A menudo supera o iguala a las mejores herramientas existentes en precisión de clasificación, a la vez que preserva de forma más consistente la estructura interna de tipos celulares dentro de cada conjunto. Este rendimiento se mantiene incluso cuando solo algunos tipos celulares se comparten entre conjuntos de datos o cuando los lotes están muy desbalanceados, aunque los autores señalan que escenarios extremadamente desajustados siguen siendo desafiantes para todos los métodos.
Qué significa esto para futuros atlas celulares
En términos sencillos, scDecorr ofrece una forma de permitir que experimentos diversos de célula única "hablen el mismo idioma" sin correcciones bruscas que borren diferencias importantes. Al aprender resúmenes ricos y de baja dimensión que son robustos al ruido pero sensibles a la diversidad biológica genuina, facilita construir mapas combinados de células entre tejidos, tecnologías y estudios, y reutilizar datos existentes para anotar nuevos experimentos. Aunque hay margen para refinamientos futuros—especialmente para conjuntos de datos muy desbalanceados—scDecorr proporciona una alternativa potente y más prudente a la corrección de lote, ayudando a los científicos a ver el paisaje celular real con menos distorsiones técnicas.
Cita: Sanyal, R., Xu, Y., Kim, H. et al. scDecorr: feature decorrelation based representation learning enables self-supervised alignment of multiple single-cell experiments. Sci Rep 16, 13782 (2026). https://doi.org/10.1038/s41598-026-50586-z
Palabras clave: secuenciación de ARN de célula única, integración de datos, aprendizaje auto-supervisado, corrección de efectos de lote, atlas celular