Clear Sky Science · nl
KDM3A katalyseert de oxidatie van acetyl-lysine tot hydroxyacetyl-lysine op histon H3K9
Hoe cellen genen bijstellen met kleine chemische schakelaars
Elke cel in je lichaam draagt hetzelfde DNA, maar hartcellen, hersencellen en huidcellen gedragen zich heel verschillend. Een reden is dat cellen hun DNA-verpakkende eiwitten, histonen genoemd, versieren met kleine chemische labels die als schakelaars fungeren om genen aan of uit te zetten. Dit artikel onthult een verrassend nieuw soort schakel op een sleutelplaats van een histon en laat zien dat deze direct door zuurstof wordt aangestuurd, waarmee het lezen van genen wordt verbonden met hoe cellen de lucht die ze inademen waarnemen.
Een nieuwe wending aan een goed bekend histonlabel
Histonen zijn spoelen waar DNA omheen gewikkeld zit. Cellen hechten chemische groepen zoals acetyl- of methylgroepen aan specifieke plekken op histonen om DNA losser of strakker te maken, wat beïnvloedt welke genen actief zijn. Een beroemd knooppunt is lysine 9 op histon H3 (H3K9), waar acetylatie meestal genactiviteit bevordert, terwijl bepaalde methylmerken samenhangen met genstillegging. Enzymen die histonacetyltransferases heten voegen acetylgroepen toe, en deacetylases verwijderen ze; andere enzymen voegen methylgroepen toe of wissen ze. Tot nu toe werd gedacht dat deze veranderingen “redox-neutraal” waren — ze hingen niet expliciet af van zuurstof. 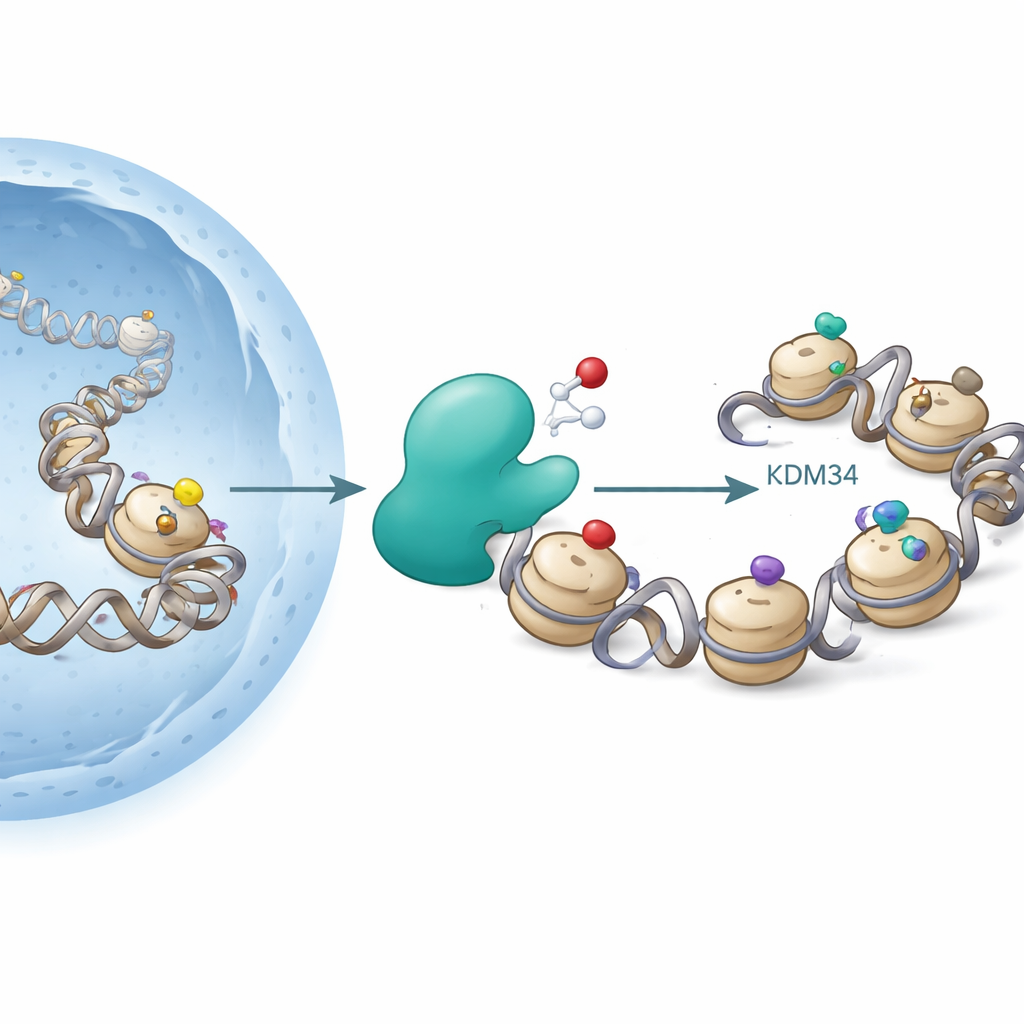
Een zuurstofgekoppeld histonmerk ontdekken
De auteurs richtten zich op KDM3A, een enzym dat al bekend stond om het verwijderen van methylgroepen van H3K9. KDM3A behoort tot een familie van zuurstofafhankelijke enzymen die ijzer en een kleine cofactor (2-oxoglutaraat) nodig hebben om te werken, vergelijkbaar met enzymen die lage zuurstof (hypoxie) in weefsels waarnemen. Toen de onderzoekers verschillende gemodificeerde histonfragmenten screeneden als mogelijke KDM3A-doelen, bevestigden ze dat KDM3A efficiënt bepaalde methylmerken op H3K9 verwijderde. Onverwacht ontdekten ze ook dat gezuiverd KDM3A de acetylgroep op H3K9 kon oxideren, waarbij deze werd omgezet in een nieuwe vorm die hydroxyacetyl-lysine wordt genoemd. Deze verandering komt overeen met het toevoegen van een zuurstofatoom aan de acetylgroep, en verdere experimenten toonden aan dat het enzym onder bepaalde omstandigheden zelfs verder kan oxideren, wat wijst op een route naar meer exotische chemieën.
Aantonen dat het nieuwe merkteken in cellen bestaat
Het vinden van een nieuw chemisch product in een reageerbuis is slechts de eerste stap; het team moest ook aantonen dat hydroxyacetyl-lysine voorkomt op histonen in levende cellen. Ze ontwikkelden een speciaal antilichaam dat H3K9 met de hydroxyacetylgroep herkent maar niet de standaard acetylvorm. Met dit hulpmiddel toonden ze aan dat toevoeging van gezuiverd KDM3A aan geïsoleerde histonen het signaal voor het nieuwe merkteken verhoogde, terwijl bekende methylmerken op H3K9 afnamen, zoals verwacht van KDM3A’s dubbele activiteit. Overexpressie van KDM3A in menselijke cellen leverde vergelijkbare effecten op: methylmerken daalden en het hydroxyacetylsignaal steeg op bulk-histonen en op enkelcelniveau. Massaspectrometrie, een zeer gevoelige techniek om moleculen te wegen, bevestigde onafhankelijk dat het precieze H3K9-peptide met hydroxyacetyl-lysine aanwezig is in cellen wanneer KDM3A actief is.
Waar het nieuwe merkteken op het genoom zit
Om te zien waar dit merkteken langs het DNA verschijnt, voerden de onderzoekers ChIP-seq uit, een methode voor genoomwijde mapping. Ze vonden dat H3K9-hydroxyacetylatie clustert rond genstartplaatsen, vooral bij genen die al sterk tot expressie komen. Het patroon volgt nauwkeurig dat van klassieke “actieve” merken zoals H3K9-acetylatie en H3K4-trimethylatie, wat suggereert dat het nieuwe label ook tot het instrumentarium van actieve chromatine behoort. Behandeling van cellen met een histondeacetylaseremmer, een type medicijn dat al in kankertherapie wordt gebruikt, verhoogde zowel de standaardacetylatie als het nieuwe hydroxyacetylmerk, waarschijnlijk door de beschikbaarheid van substraat voor KDM3A te vergroten en de verwijdering van deze acylgroepen te vertragen. 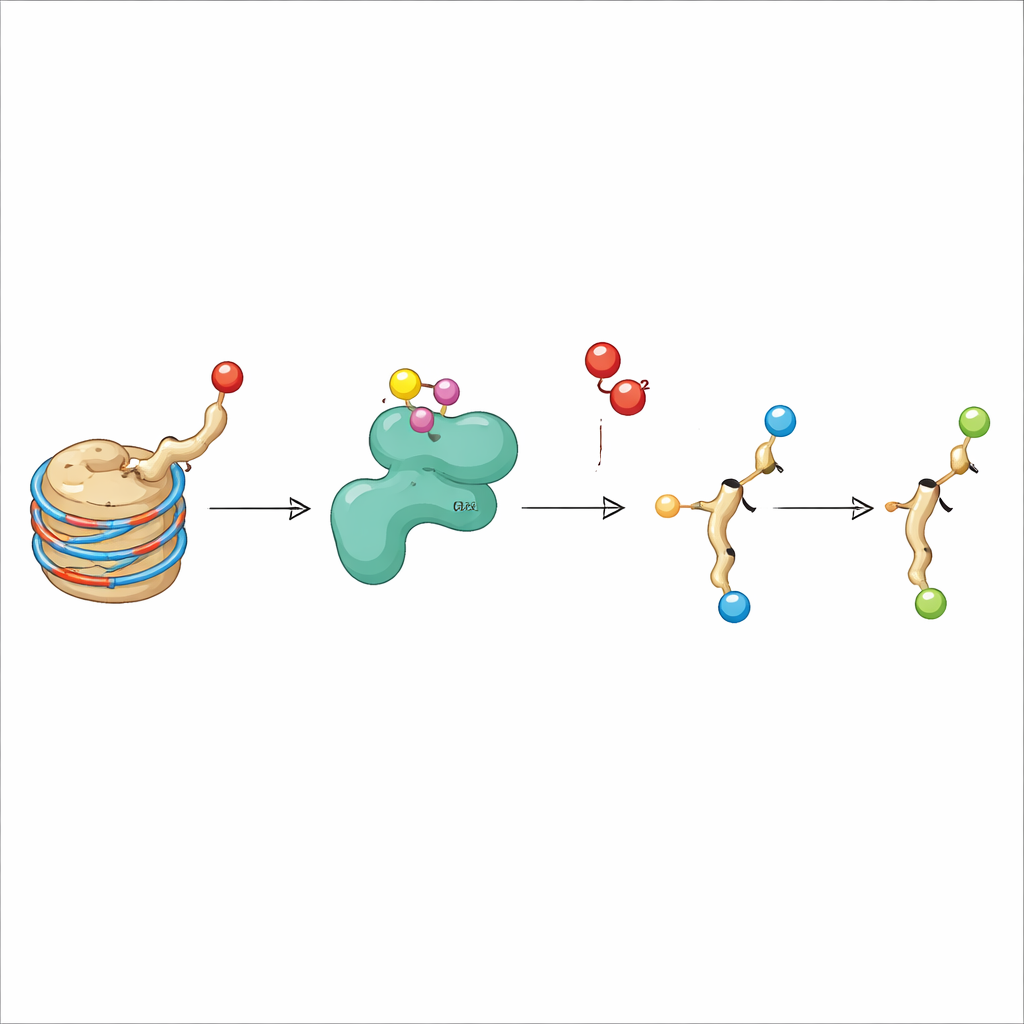
Hoe andere eiwitten het nieuwe label lezen en verwerken
De studie testte ook hoe bestaande chromatine-"lezers" en "wissers" op het nieuwe merkteken reageren. Een lezerdomain van het AF9-eiwit, dat normaal acetyl- en crotonylmerken herkent, bond aan de hydroxyacetylversie met slechts licht verminderde affiniteit, wat impliceert dat bekende lezers deze modificatie kunnen waarnemen. Twee deacetylase-enzymen, SIRT1 en HDAC8, verwerkten hydroxyacetyl-lysine verschillend: SIRT1 was veel minder efficiënt in het verwijderen van het nieuwe label dan van de standaardacetylgroep, terwijl HDAC8 weinig voorkeur toonde. Deze verschillen suggereren dat hydroxyacetylatie subtiel kan veranderen hoe lang een merkteken blijft zitten en welke enzymen ermee in wisselwerking treden, waardoor het chromatine fijnmazig wordt bijgesteld.
Waarom deze zuurstofafhankelijke schakel ertoe doet
Samengevat onthult het werk H3K9-hydroxyacetylatie als een eerder onbekend histonmerk geproduceerd door KDM3A, en waarschijnlijk onder bepaalde omstandigheden ook door het nauwe verwante KDM3B. Omdat KDM3A zelf wordt geactiveerd door lage zuurstof via het hypoxie-induceerbare factorpad, creëert dit een directe chemische koppeling tussen zuurstofniveaus en histonacetylatiestaten. Simpel gezegd kan het enzym zowel onderdrukkende methylmerken verwijderen als activerende acetylmerken omzetten in een licht andere zuurstofhoudende vorm op dezelfde histonplaats, wat genprogramma’s kan herschikken tijdens stress, ontwikkeling of kanker. De ontdekking verruimt ons beeld van wat "demethylase"-enzymen kunnen doen en opent de deur naar het verkennen van vergelijkbare hydroxyacetyl-merken op andere eiwitten, evenals hun rollen in gezondheid en ziekte.
Bronvermelding: Belle, R., Bukowski, JP., Schiller, R. et al. KDM3A catalyses the oxidation of acetyl-lysine to hydroxyacetyl-lysine on histone H3K9. Nat. Chem. 18, 823–834 (2026). https://doi.org/10.1038/s41557-026-02112-x
Trefwoorden: histonmodificatie, epigenetica, zuurstofsensing, KDM3A-enzym, genregulatie