Clear Sky Science · es
Evaluación crítica de modelos de predicción de respuesta a fármacos con DrEval
Por qué importan pruebas de fármacos más inteligentes en cáncer
Cuando los médicos eligen fármacos para el cáncer, con frecuencia se basan en categorías amplias como el tipo de tumor y un puñado de marcadores genéticos. En la última década, los científicos han comenzado a probar cientos de fármacos en cientos de líneas celulares de cáncer cultivadas en laboratorio, midiendo asimismo los genes y otras características moleculares de cada línea. Muchos modelos informáticos afirman predecir qué fármacos funcionarán a partir de estos datos. Este artículo examina críticamente esas afirmaciones y presenta DrEval, una nueva caja de herramientas de evaluación que comprueba qué tan bien rinden realmente estos modelos en situaciones que se parecen a las decisiones médicas reales. 
Cómo intentan los ordenadores adivinar el éxito de un fármaco
Los modelos de predicción de respuesta a fármacos aprenden a partir de proyectos de cribado de gran escala en los que las líneas celulares de cáncer se exponen a muchos fármacos a diferentes dosis y se mide su supervivencia. Los investigadores ofrecen a cada modelo perfiles moleculares detallados de las líneas celulares y diversas descripciones de los fármacos, y luego le piden que prediga medidas resumen estándar de cuánto ralentiza cada fármaco el crecimiento celular. Algunos enfoques entrenan un modelo por fármaco, mientras que otros entrenan un único modelo para muchos fármacos con la esperanza de que pueda incluso estimar respuestas para medicamentos nuevos. En los artículos, estos métodos a menudo reportan cifras de precisión impresionantes, lo que sugiere que el tratamiento personalizado del cáncer podría estar al alcance.
Trampas ocultas en las evaluaciones actuales
Los autores muestran que estos resultados optimistas a menudo provienen de cómo se dividen y puntúan los datos, no de un conocimiento genuino sobre la biología del cáncer. Si la misma línea celular o fármaco aparece tanto en los conjuntos de entrenamiento como en los de prueba, el modelo puede simplemente memorizar el comportamiento típico en lugar de aprender patrones más profundos. Dado que diferentes fármacos actúan en rangos de dosis muy distintos, un modelo que solo memoriza la respuesta media por fármaco ya puede explicar gran parte de la variación de los datos. Esto crea una ilusión estadística en la que la precisión global parece alta, aunque el modelo no distinga qué líneas celulares son más o menos sensibles a un fármaco determinado.
Qué hace DrEval de forma diferente
DrEval es un marco de evaluación abierto que estandariza cómo se prueban los modelos de respuesta a fármacos. Proporciona conjuntos de datos armonizados, limpieza cuidadosa de los datos y varios escenarios de prueba realistas que reflejan objetivos comunes: predecir respuestas para nuevos pacientes (nuevas líneas celulares), para nuevos tipos de cáncer (nuevos tejidos) o para fármacos completamente nuevos. También incluye métodos de referencia simples, como un predictor que usa solo los efectos medios de cada fármaco y línea celular, y modelos basados en árboles que son mucho más fáciles de entrenar que las redes neuronales profundas. DrEval ejecuta todos los modelos bajo el mismo esquema de validación cruzada y ajuste, y luego informa resultados con métricas que eliminan la influencia engañosa de los efectos medios de fármaco y línea celular. 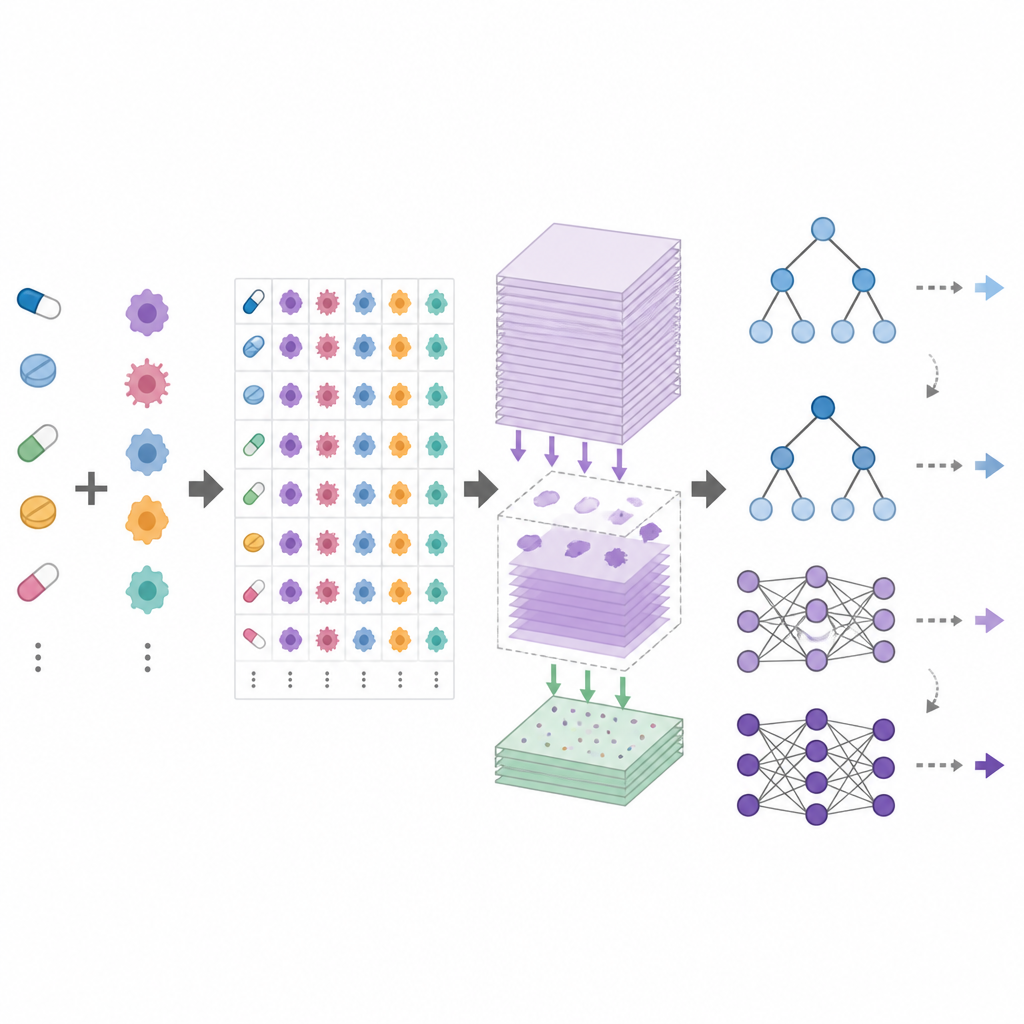
Qué revelan las pruebas sobre los modelos actuales
Cuando los autores evaluaron una amplia gama de modelos modernos con DrEval, hallaron que muchos apenas superaban al predictor ingenuo que solo usa el comportamiento medio de fármaco y línea celular. En los escenarios más relevantes para los pacientes, donde los modelos deben tratar con líneas celulares que nunca han visto antes, los ensamblajes afinados basados en árboles, como los bosques aleatorios, rindieron tan bien o mejor que redes profundas complejas. Todos los métodos fallaron al intentar predecir el efecto de fármacos que no formaban parte de sus datos de entrenamiento, y el rendimiento cayó drásticamente al pasar de un estudio de cribado a otro o de líneas celulares a muestras más realistas de pacientes. Experimentos de “ablación” cuidadosos mostraron que la mayor parte de la señal útil proviene de mediciones básicas de actividad génica, mientras que capas de datos adicionales y codificaciones sofisticadas de fármacos a menudo añaden poco.
Por qué esto importa para el futuro tratamiento del cáncer
El mensaje principal del estudio es que la predicción fiable de la respuesta a fármacos en cáncer sigue siendo un problema sin resolver. Muchos éxitos anteriores se vieron inflados por evaluaciones sesgadas en lugar de por verdadero poder predictivo. Al hacer visibles estos problemas y proporcionar un banco de pruebas compartido y reproducible, DrEval ayuda al campo a centrarse en métodos que realmente aprendan cómo responden los cánceres al tratamiento en lugar de explotar atajos en los datos. Para los pacientes, esto significa que los modelos informáticos todavía no están listos para guiar decisiones rutinarias sobre fármacos, pero el camino hacia herramientas fiables está más claro: mejores datos, pruebas más estrictas y comparaciones justas entre modelos simples y complejos.
Cita: Bernett, J., Iversen, P., Picciani, M. et al. Critical evaluation of drug response prediction models with DrEval. Nat Commun 17, 4238 (2026). https://doi.org/10.1038/s41467-026-72903-w
Palabras clave: predicción de respuesta a fármacos, líneas celulares de cáncer, aprendizaje automático, evaluación comparativa, evaluación de modelos