Clear Sky Science · zh
一种用于多态布朗轨迹的轻量级数据驱动分割方法
观察分子漫游
在活细胞内,无数分子不断碰撞、结合与解离,它们的运动蕴含着生命过程的线索。现代显微镜能够追踪单个分子的运动轨迹,但将这些错综复杂的路径转换为关于分子扩散速率或结合时刻的清晰结论却出乎意料地困难。本文介绍了一种简单、快速的方法,将此类运动分解为不同的运动“状态”,从而让生物学家更容易解读单分子影像所传达的信息。
为何追踪分子很棘手
单粒子追踪技术记录单个分子随时间变化的位置,构成反映其探索周围环境方式的轨迹。在许多真实系统中,分子的运动并非仅有一种模式:它可能在某段时间内自由漫游,随后在结合到受体或被聚集体束缚时变慢。因此轨迹是若干运动模式的混合,每种模式有其特征速率。现有分析工具理论上可以分离这些模式,但广泛使用的基于隐马尔可夫模型或深度学习的方法通常计算量大、需要专家调参,或像“黑箱”一样其决策难以解释。
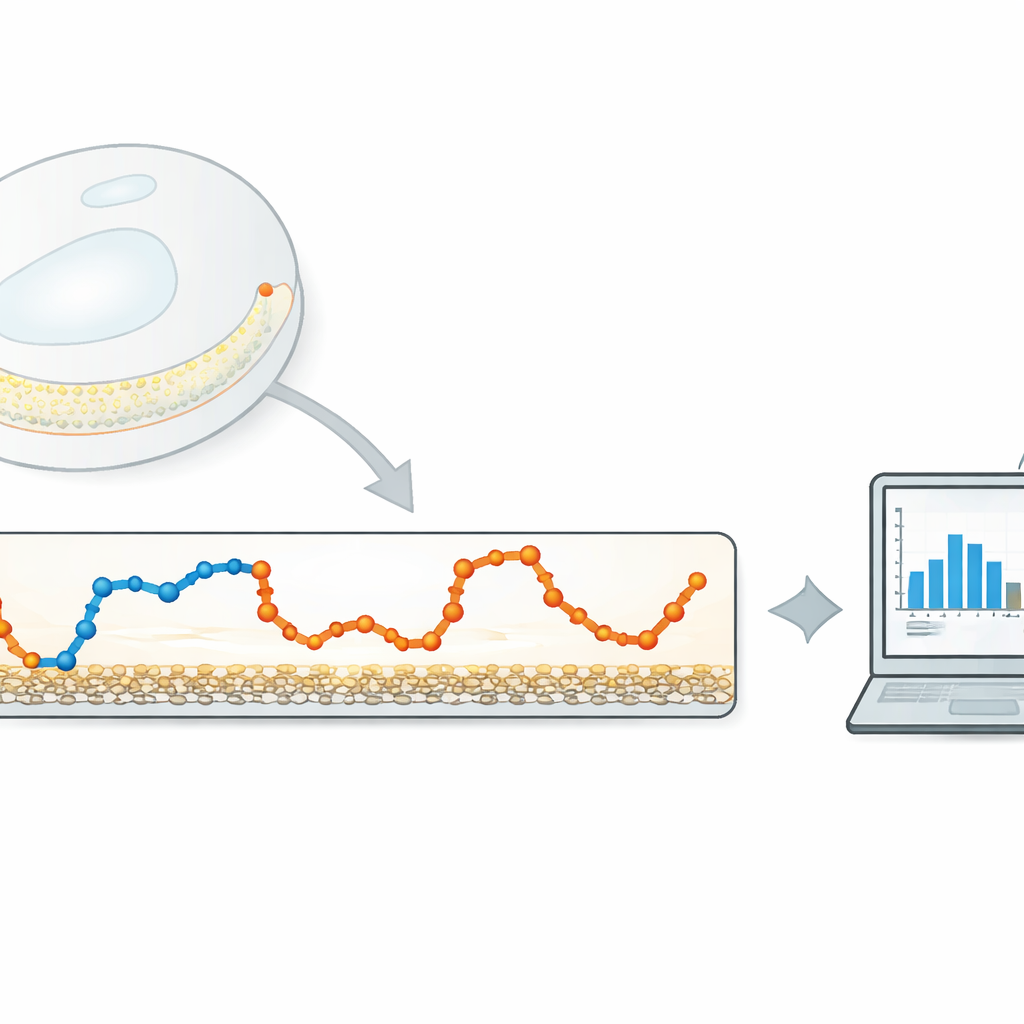
相对于复杂算法的精简替代
作者提出了一种轻量级的数据驱动方法,聚焦于一个非常简单的量:粒子在连续相机帧之间移动的距离。首先,从追踪到的轨迹中计算逐步位移时间序列。然后对该序列施加一维高斯滤波——一种滑动的、平滑加权平均。滤波宽度决定了相邻步长被平均的强度:滤波太窄,噪声无法充分去除;滤波太宽,不同运动状态间的转换会被模糊掉。关键思想是自动调整该宽度,使得来自每个运动状态的滤后步长尽可能少地重叠。
让数据自行分类
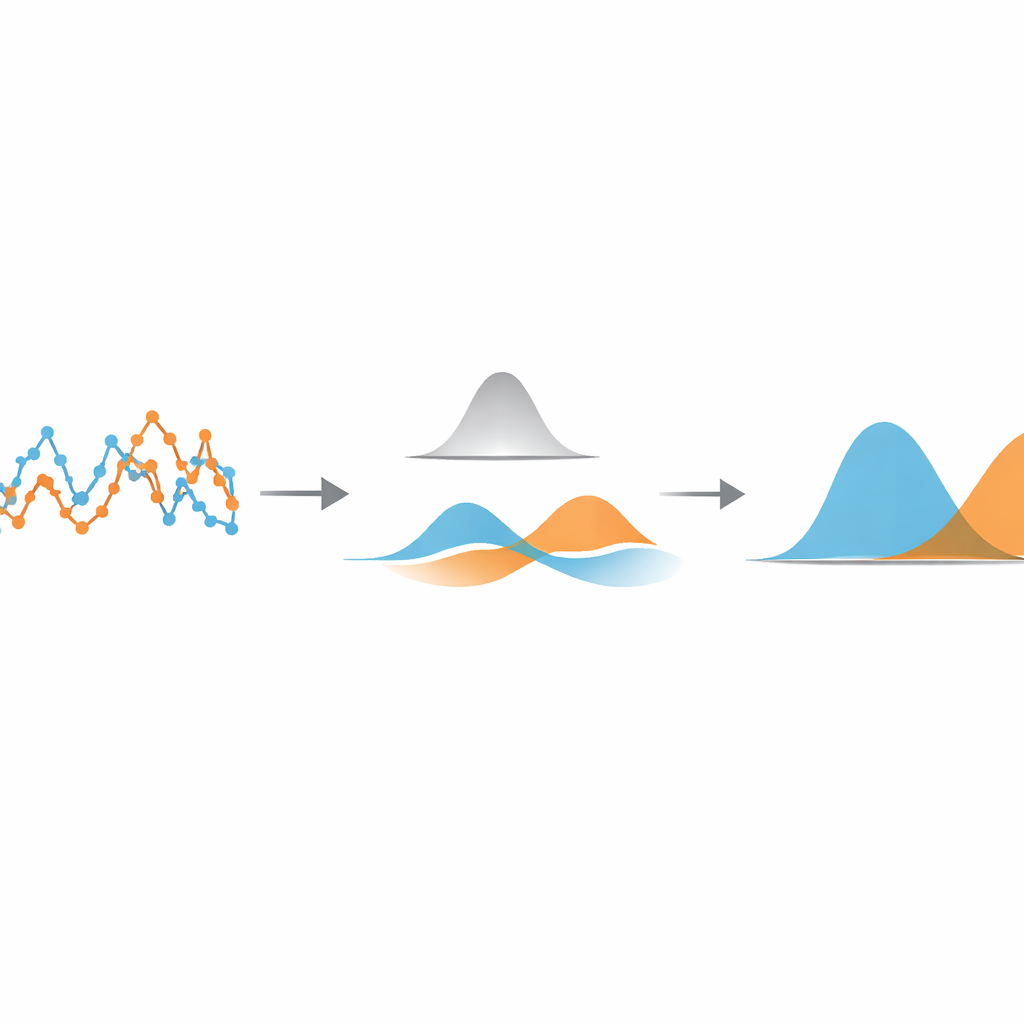
为找到最佳点,方法将滤波后的位移视为来自若干简单钟形曲线的混合体。使用一种标准统计工具——高斯混合模型,对滤波数据拟合两条这样的曲线并计算它们的重叠度。通过扫描不同的滤波宽度并选择使重叠最小的那个,算法将不同运动状态在数据允许范围内区分得尽可能清楚。一旦找到该最优设置,每个位移就被分配到最有可能产生它的钟形曲线所属状态,从而把原始轨迹有效地切分为快与慢的片段。重要的是,这种分割发生在尝试估计扩散系数或状态寿命等物理参数之前,因此后续可以用熟悉且验证过的公式来测量这些参数。
用模拟与真实分子进行测试
研究者在计算机生成的轨迹上对其方法进行了严格测试,这些轨迹中的粒子在已知属性的两种扩散速度间切换。他们改变两种速度的差异、粒子在每个状态停留的时间、位置测量的噪声水平以及相机引入的模糊量。在广泛的现实条件下——当快慢两态的差异至少约为四倍且每个状态持续多于数个相机帧时——该算法对时间点的正确标注率超过90%。关键是,当将该方法应用到在支持膜中扩散的荧光标记蛋白的实验数据时,它也表现出鲁棒性,揭示了两类明显分离的群体:一类可动,另一类几乎不动。
从干净的片段到生物学洞见
一旦轨迹被分段,团队表明即便在存在显著测量噪声或运动模糊的情况下,扩散系数仍能较准确地恢复。估计分子在每个状态中典型停留时间则更具挑战,需要更长的轨迹,但在合适条件下仍能得到合理的寿命估计。总体信息是:一种相对简单、透明的程序——在时间上滤波步长并拟合两条钟形曲线——可以在普通计算机上快速运行,其性能可与更复杂的方法相媲美。对于实验人员而言,这意味着他们可以实时处理单粒子数据、即时调整成像条件,并更清晰地理解分子在拥挤的细胞环境中如何结合、解离与移动。
引用: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
关键词: 单粒子追踪, 分子扩散, 轨迹分割, 布朗运动, 膜蛋白