Clear Sky Science · it
Un metodo leggero e guidato dai dati per la segmentazione di traiettorie browniane multi-stato
Osservare le molecole che vagano
All'interno delle cellule vive, innumerevoli molecole sono costantemente in movimento, legandosi e sganciandosi, e il loro moto contiene indizi sul funzionamento della vita. I microscopi moderni possono seguire singole molecole mentre si muovono, ma trasformare questi percorsi intrecciati in storie chiare su quanto velocemente una molecola diffonde o quando si lega a un partner è sorprendentemente difficile. Questo articolo introduce un modo semplice e veloce per suddividere tale movimento in distinti «stati» di moto, rendendo più facile per i biologi interpretare ciò che i filmati di singole molecole cercano di raccontare.
Perché seguire le molecole è complicato
Le tecniche di single-particle tracking registrano le posizioni di singole molecole nel tempo, costruendo una traiettoria che riflette come esplorano l'ambiente. In molti sistemi reali, una molecola non si muove in un solo modo: può vagare liberamente per un periodo e poi rallentare quando si lega a un recettore o rimane intrappolata in un grappolo. Ciò significa che la traiettoria è una mescolanza di diversi modi di moto, ciascuno con una velocità caratteristica. Gli strumenti di analisi esistenti possono, in linea di principio, separare queste modalità, ma i metodi ampiamente usati basati su modelli di Markov nascosti o apprendimento profondo sono spesso computazionalmente pesanti, richiedono tarature esperte o funzionano come «scatole nere» le cui decisioni sono difficili da interpretare.
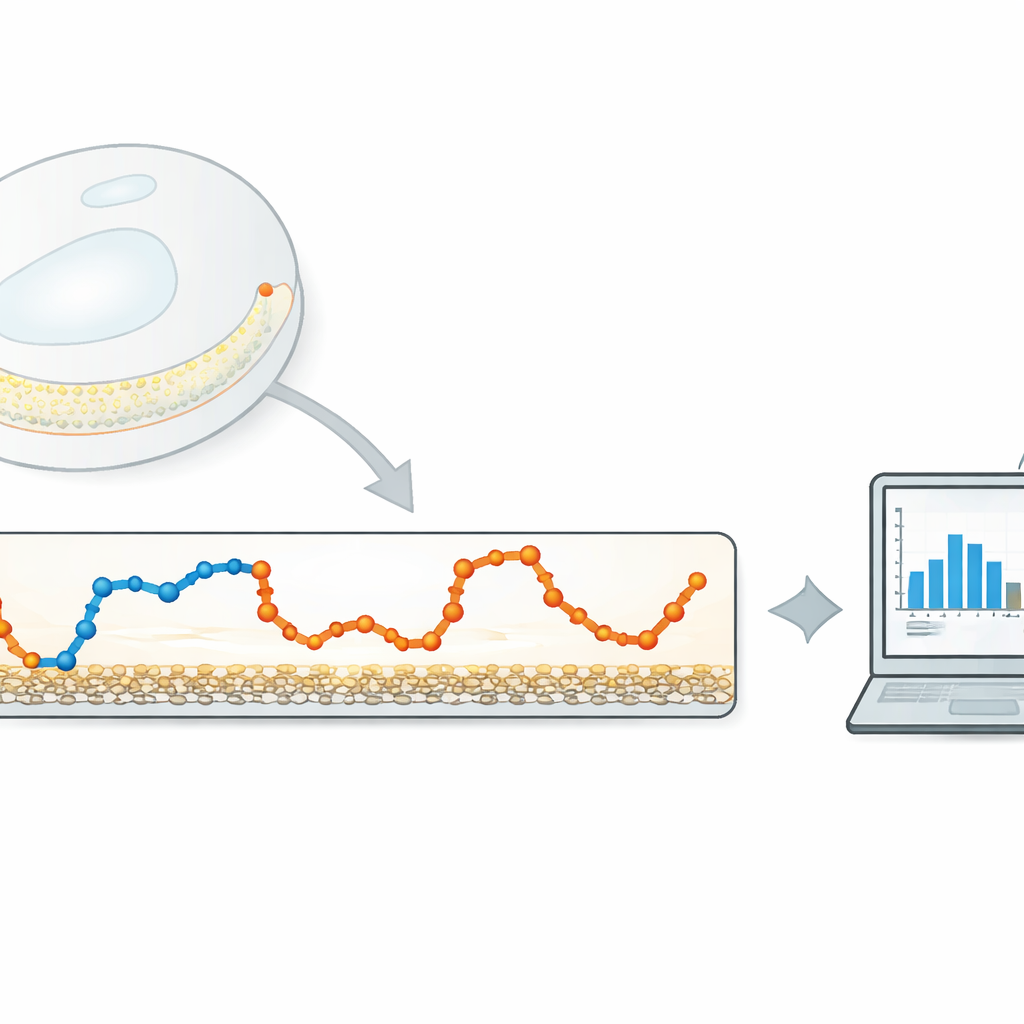
Un'alternativa snella agli algoritmi pesanti
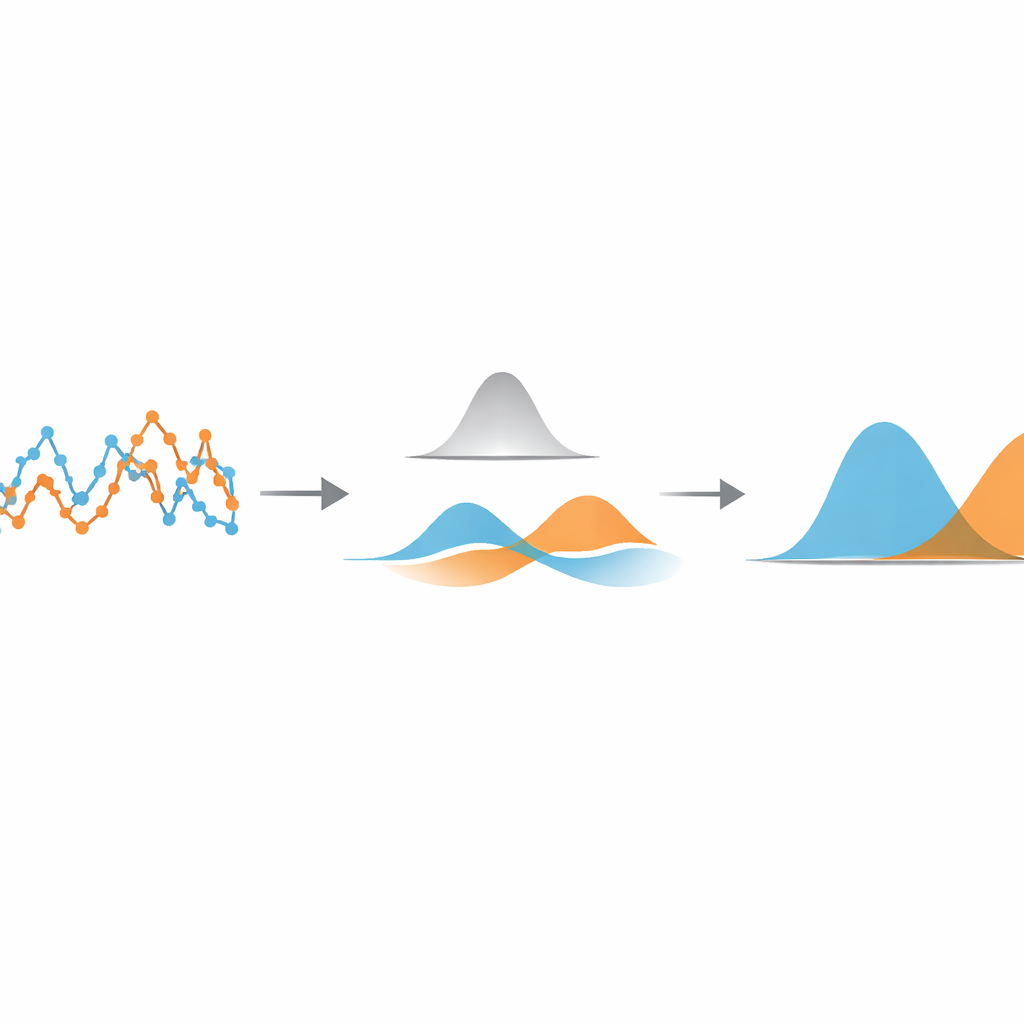
Gli autori propongono un metodo leggero e guidato dai dati che si concentra su una quantità molto semplice: quanto si sposta la particella tra fotogrammi consecutivi della videocamera. Innanzitutto calcolano questa serie temporale di spostamenti passo dopo passo a partire da una traiettoria tracciata. Poi applicano a questa serie un filtro gaussiano monodimensionale — un tipo di media mobile con pesi smussati — Il cui intervallo controlla quanto gli spostamenti vicini vengano mediati tra loro. Se il filtro è troppo stretto, viene rimosso poco rumore; se è troppo largo, le transizioni tra diversi stati di movimento vengono annacquate. L'idea chiave è regolare automaticamente questa larghezza in modo che gli spostamenti filtrati di ciascuno stato di movimento si sovrappongano il meno possibile.
Lasciare che siano i dati a ordinarsi
Per trovare quel punto ottimale, il metodo considera gli spostamenti filtrati come provenienti da una miscela di semplici curve a campana. Usando uno strumento statistico standard chiamato modello di miscela gaussiana, adatta due di queste curve ai dati filtrati e calcola quanto si sovrappongono. Scansionando diverse larghezze del filtro e scegliendo quella che minimizza questa sovrapposizione, l'algoritmo rende gli stati di movimento tanto distinti quanto consentono i dati. Una volta trovato questo settaggio ottimale, ogni spostamento viene assegnato allo stato a cui probabilmente appartiene in base alla curva a campana, segmentando così la traiettoria originale in tratti veloci e lenti. È importante notare che questa segmentazione avviene prima di qualsiasi tentativo di stimare parametri fisici come coefficienti di diffusione o tempi di vita degli stati, in modo che questi possano essere misurati successivamente con formule familiari e ben collaudate.
Test con simulazioni e molecole reali
I ricercatori hanno messo alla prova il loro metodo su traiettorie generate al computer in cui una particella passa tra due velocità di diffusione con proprietà note. Hanno variato quanto le due velocità differissero, quanto a lungo la particella restasse in ciascuno stato, quanto fosse rumorosa la misura di posizione e quanta sfocatura introducesse la fotocamera. In un'ampia gamma di condizioni realistiche — ogni volta che gli stati veloce e lento differivano di almeno un fattore di circa quattro e ciascuno stato durava più di alcuni fotogrammi della videocamera — l'algoritmo identificava correttamente oltre il 90 percento dei punti temporali. In modo cruciale, il metodo si è dimostrato robusto anche applicato a dati sperimentali di proteine fluorescentemente marcate che diffondono su una membrana supportata, dove ha rivelato due popolazioni chiaramente separate: una mobile e una quasi immobile.
Dai segmenti puliti all'intuizione biologica
Una volta segmentate le traiettorie, il gruppo ha dimostrato che i coefficienti di diffusione possono essere recuperati con buona accuratezza, anche in presenza di rumore significativo nelle misurazioni o di motion blur. Stimare quanto tempo le molecole rimangono tipicamente in ciascuno stato è risultato più impegnativo e ha richiesto traiettorie più lunghe, ma ha comunque fornito tempi di vita ragionevoli in condizioni adeguate. Il messaggio complessivo è che una procedura relativamente semplice e trasparente — filtrare gli spostamenti nel tempo e adattare una coppia di curve a campana — può competere con approcci più complessi pur operando rapidamente su computer comuni. Per gli sperimentatori, questo significa poter processare i dati di singole particelle in tempo reale, mettere a punto le condizioni di imaging sul momento e ottenere immagini più nitide di come le molecole si leghino, si separino e si muovano in ambienti cellulari affollati.
Citazione: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
Parole chiave: tracciamento di singole particelle, diffusione molecolare, segmentazione di traiettorie, moto Browniano, proteine di membrana