Clear Sky Science · pl
Lekka, oparta na danych metoda segmentacji dla trajektorii Browna o wielu stanach
Obserwowanie wędrówek cząsteczek
W komórkach żywych niezliczone cząsteczki nieustannie się zderzają, wiążą i odłączają — ich ruch kryje wskazówki dotyczące mechanizmów życia. Nowoczesne mikroskopy potrafią śledzić pojedyncze cząsteczki w ruchu, jednak przekształcenie tych poplątanych ścieżek w klarowne historie o tym, jak szybko cząsteczka dyfunduje lub kiedy się wiąże, okazuje się zaskakująco trudne. W artykule przedstawiono prosty, szybki sposób podziału takiego ruchu na odrębne „stany” ruchu, co ułatwia biologom odczytywanie, co pokazują filmy pojedynczych cząsteczek.
Dlaczego śledzenie cząsteczek jest trudne
Techniki śledzenia pojedynczych cząstek rejestrują pozycje poszczególnych cząsteczek w czasie, budując trajektorię, która odzwierciedla sposób, w jaki eksplorują otoczenie. W wielu rzeczywistych układach cząsteczka nie porusza się w tylko jeden sposób: może przez pewien czas swobodnie krążyć, a potem zwolnić, gdy zwiąże się z receptorem lub zostanie uwięziona w skupisku. Oznacza to, że trajektoria jest mieszanką kilku trybów ruchu, z których każdy ma charakterystyczną prędkość. Istniejące narzędzia analityczne w zasadzie potrafią rozdzielić te tryby, ale powszechnie stosowane metody oparte na ukrytych modelach Markowa lub uczeniu głębokim często są obciążające obliczeniowo, wymagają eksperckiej regulacji parametrów lub działają jako „czarne skrzynki”, których decyzje trudno interpretować.
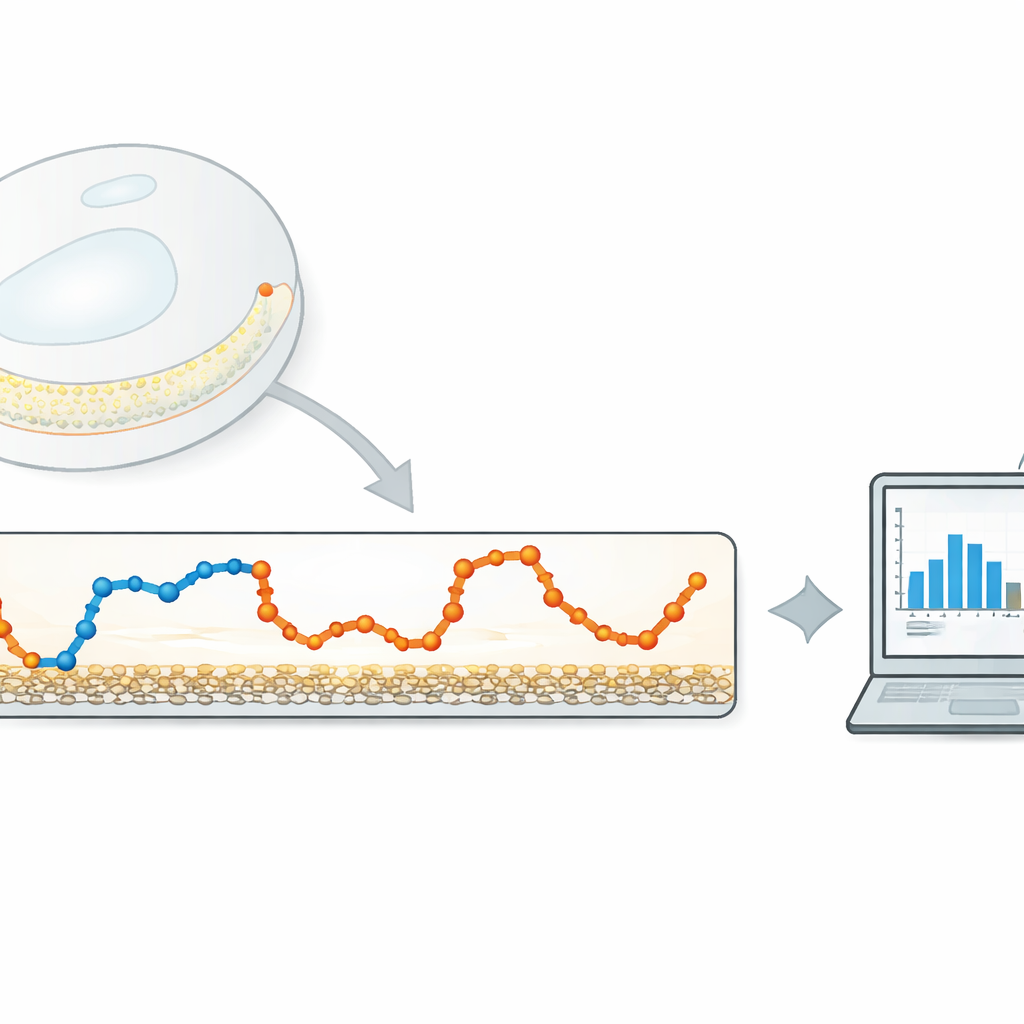
Smukła alternatywa dla „ciężkich” algorytmów
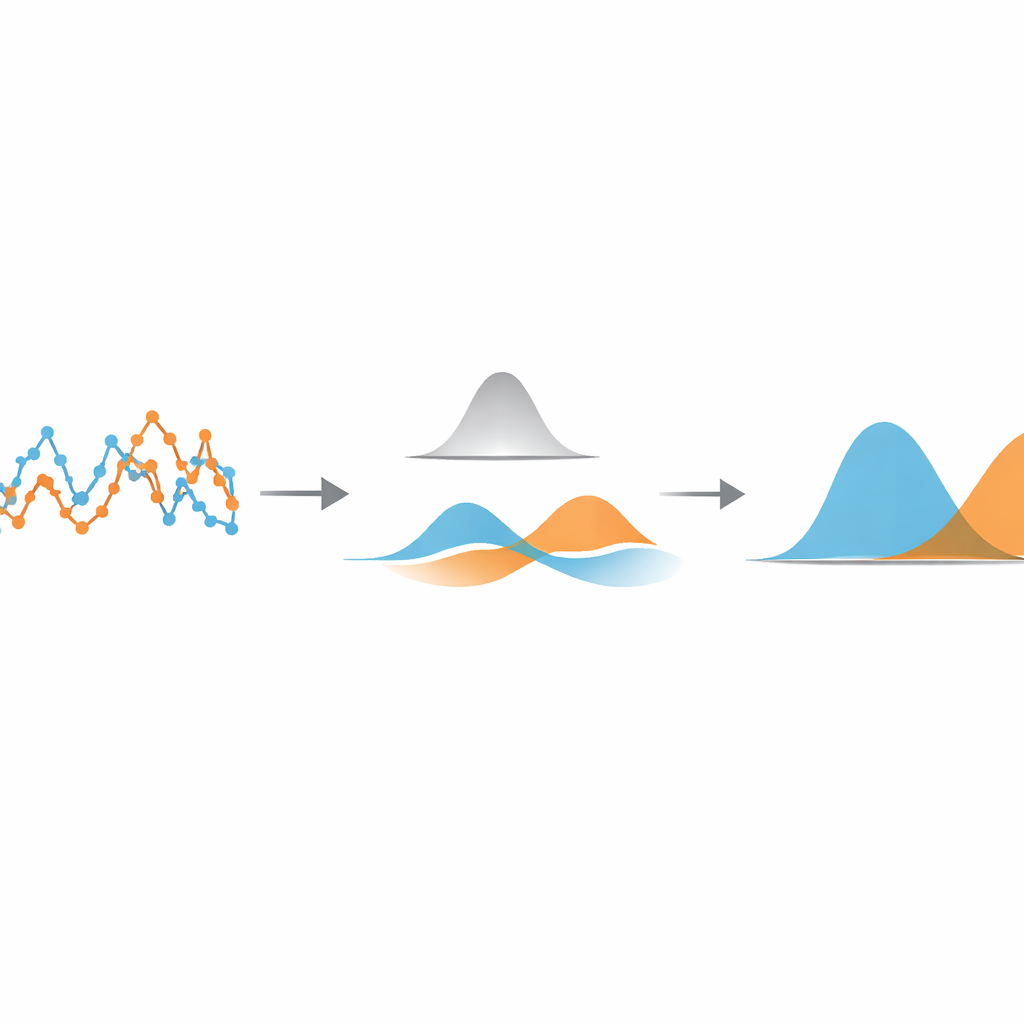
Autorzy proponują lekką, opartą na danych metodę skupioną na bardzo prostej wielkości: jak daleko porusza się cząstka między kolejnymi klatkami kamery. Najpierw obliczają czasowy szereg przemieszczeń krok po kroku z zaśledzonej trajektorii. Następnie stosują jednowymiarowy filtr Gaussowski — rodzaj przesuwanej, płynnie ważonej średniej — do tego szeregu. Szerokość filtra kontroluje, jak silnie są uśredniane sąsiednie kroki. Jeśli filtr jest zbyt wąski, usuwa niewiele szumu; jeśli zbyt szeroki, przejścia między różnymi stanami ruchu ulegają rozmyciu. Kluczowy pomysł polega na automatycznym dostrojeniu tej szerokości tak, by filtrowane kroki z każdego stanu ruchu zachodziły na siebie jak najmniej.
Pozwolić danym, by same się uporządkowały
Aby znaleźć tę optymalną wartość, metoda traktuje filtrowane przemieszczenia jako pochodzące z mieszanki prostych dzwonowych krzywych. Z użyciem standardowego narzędzia statystycznego, zwanego modelem mieszanki Gaussowskiej, dopasowuje dwie takie krzywe do filtrowanych danych i oblicza, jak bardzo się pokrywają. Przeszukując różne szerokości filtra i wybierając tę, która minimalizuje to pokrywanie, algorytm sprawia, że różne stany ruchu są tak odrębne, jak pozwalają na to dane. Po znalezieniu tego optymalnego ustawienia każde przemieszczenie jest przypisywane do stanu, do którego dzwonowa krzywa je najprawdopodobniej zalicza, efektywnie segmentując pierwotną trajektorię na odcinki szybkie i wolne. Co ważne, segmentacja ta odbywa się zanim podejmie się próbę oszacowania parametrów fizycznych, takich jak współczynniki dyfuzji czy czasy życia stanów, które można potem mierzyć znanymi, sprawdzonymi wzorami.
Testy na symulacjach i rzeczywistych cząsteczkach
Badacze sprawdzili metodę w trudnych warunkach na trajektoriach wygenerowanych komputerowo, gdzie cząstka przełącza się między dwoma prędkościami dyfuzji o znanych właściwościach. Zmieniali, jak bardzo różniły się obie prędkości, jak długo cząstka pozostawała w każdym stanie, jak szumne były pomiary pozycji i jak duże rozmycie wprowadzała kamera. W szerokim zakresie realistycznych warunków — zawsze gdy stany szybki i wolny różniły się co najmniej około czterokrotnie i każdy stan trwał dłużej niż kilka klatek — algorytm poprawnie oznaczał ponad 90 procent punktów czasowych. Co kluczowe, metoda okazała się również odporna przy zastosowaniu do danych eksperymentalnych z fluorescencyjnie znakowanymi białkami dyfundującymi w wspieranej błonie, gdzie ujawniła dwie wyraźnie oddzielone populacje: jedną mobilną i jedną niemal nieruchomą.
Od czystych segmentów do biologicznego wglądu
Po segmentacji trajektorii zespół wykazał, że współczynniki dyfuzji można odtworzyć z dobrą dokładnością, nawet w obecności znacznego szumu pomiarowego czy rozmycia ruchu. Szacowanie typowego czasu przebywania cząsteczek w każdym stanie było bardziej wymagające i wymagało dłuższych trajektorii, ale w odpowiednich warunkach nadal dawało rozsądne czasy życia. Ogólne przesłanie jest takie, że stosunkowo prosta, przejrzysta procedura — filtrowanie kroków w czasie i dopasowanie pary dzwonowych krzywych — może dorównywać bardziej złożonym podejściom, działając przy tym szybko na zwykłych komputerach. Dla eksperymentatorów oznacza to możliwość przetwarzania danych pojedynczych cząstek w czasie rzeczywistym, dostrajania warunków obrazowania na bieżąco i uzyskiwania jaśniejszych obrazów tego, jak cząsteczki wiążą się, odłączają i poruszają w zatłoczonych środowiskach komórkowych.
Cytowanie: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
Słowa kluczowe: śledzenie pojedynczych cząstek, dyfuzja molekularna, segmentacja trajektorii, ruch Browna, białka błonowe