Clear Sky Science · sv
En lättviktig, datadriven segmenteringsmetod för flerstats Brownska banor
Att följa molekylernas vandringar
Inuti levande celler trängs ett otal molekyler ständigt, binder och släpper, och deras rörelser bär på ledtrådar om hur livet fungerar. Moderna mikroskop kan följa enskilda molekyler när de rör sig, men att omvandla dessa intrasslade banor till tydliga berättelser om hur snabbt en molekyl diffunderar eller när den binder en partner är överraskande svårt. Denna artikel presenterar ett enkelt, snabbt sätt att dela upp sådan rörelse i distinkta rörelsestater, vilket gör det lättare för biologer att tolka vad filmer av enskilda molekyler försöker berätta.
Varför det är knepigt att spåra molekyler
Single-particle tracking-tekniker registrerar positionerna för individuella molekyler över tid och bygger upp en bana som speglar hur de utforskar sin omgivning. I många verkliga system rör sig en molekyl inte på bara ett sätt: den kan irra fritt ett tag och sedan sakta ner när den binder en receptor eller blir fångad i ett kluster. Det gör att banan är en blandning av flera rörelsemönster, var och en med sin karakteristiska hastighet. Befintliga analystekniker kan i princip separera dessa lägen, men vanliga metoder baserade på dolda Markov-modeller eller djupinlärning är ofta beräkningsmässigt tunga, kräver expertinställning eller fungerar som ”svarta lådor” vars beslut är svåra att tolka.
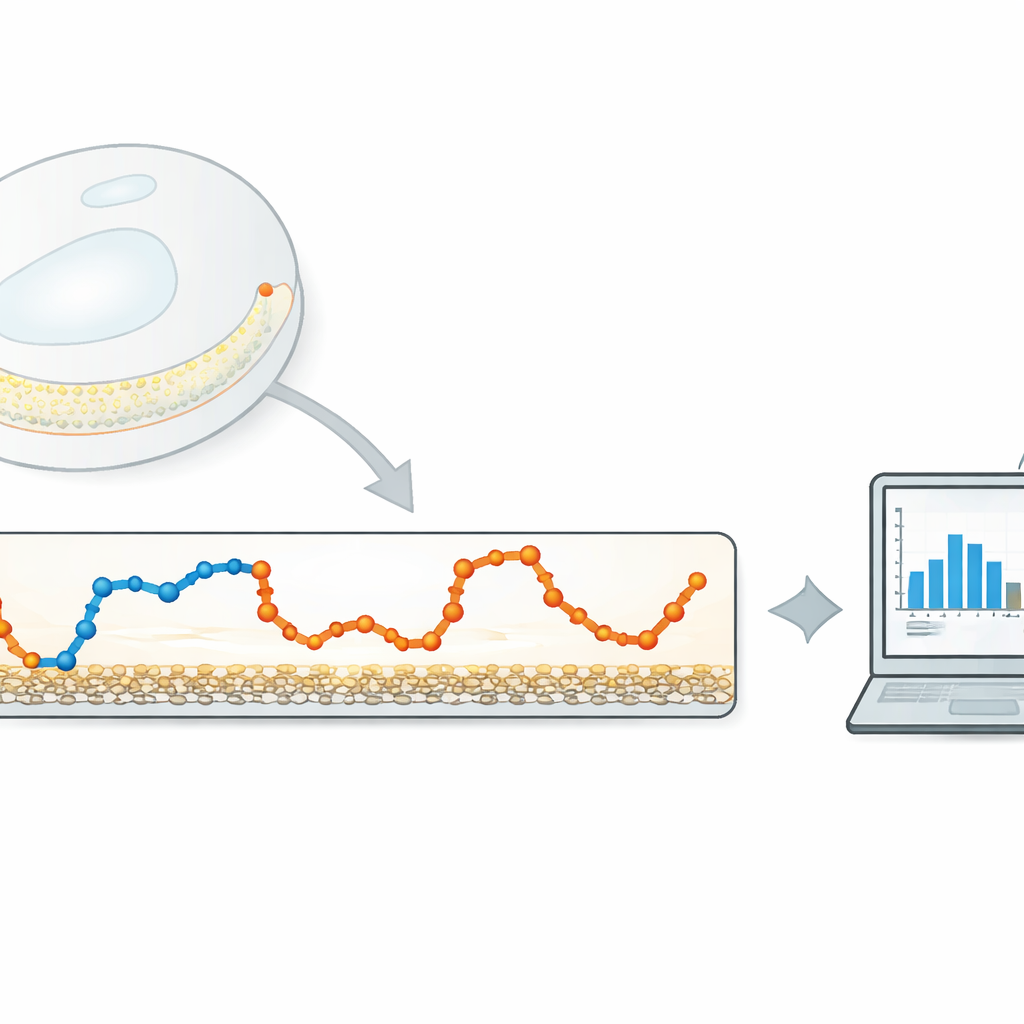
En slankare alternativ till tunga algoritmer
Författarna föreslår en lättviktig, datadriven metod som fokuserar på en mycket enkel storhet: hur långt partikeln rör sig mellan på varandra följande kameraramar. Först beräknar de denna steg-för-steg-förskjutningsserie från en spårad bana. Därefter tillämpar de ett endimensionellt Gaussiskt filter—en typ av glidande, mjukt viktat medelvärde—på serien. Filterbredden styr hur kraftigt närliggande steg jämnas ut. Om filtret är för smalt avlägsnas lite brus; om det är för brett suddas övergångar mellan olika rörelsestater ut. Nyckelidén är att automatiskt ställa in denna bredd så att de filtrerade stegen från varje rörelsestata överlappar så lite som möjligt.
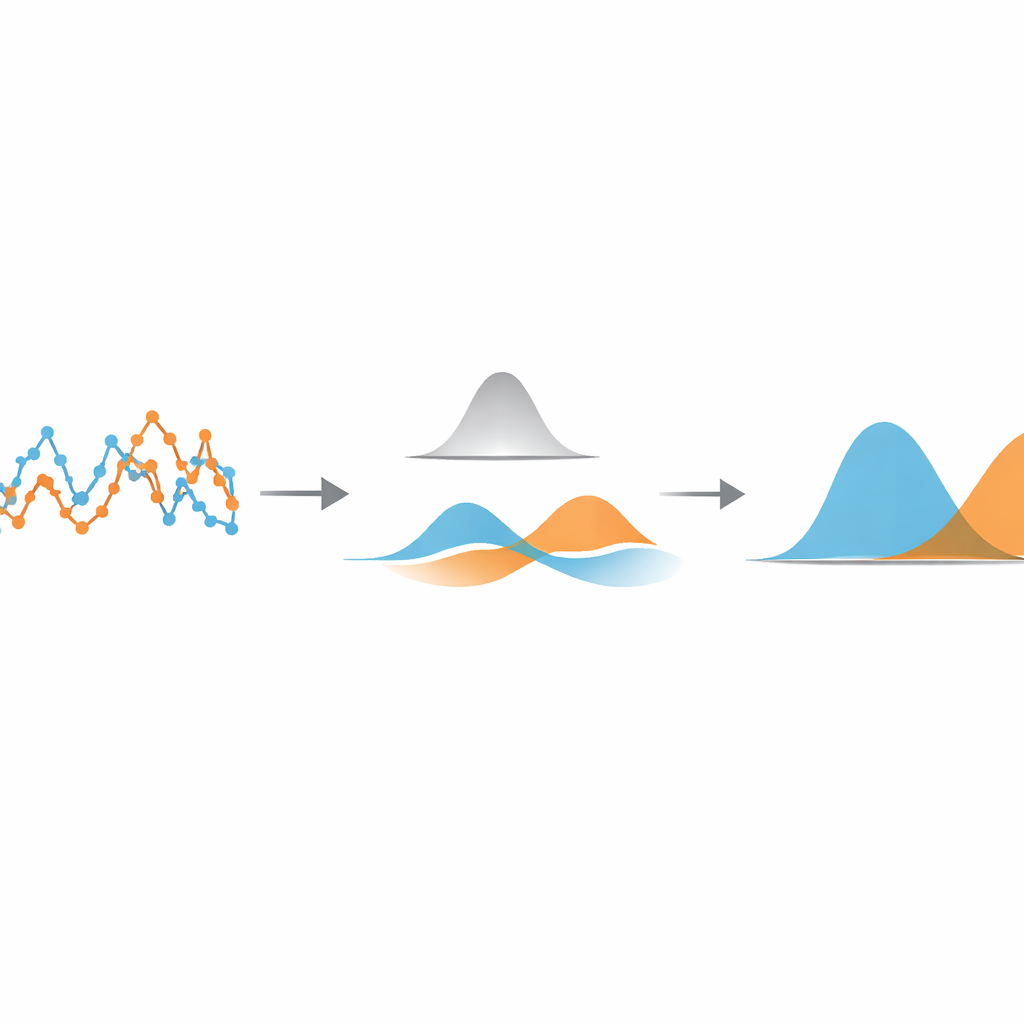
Låta data sortera sig själv
För att hitta den optimala inställningen behandlar metoden de filtrerade förskjutningarna som hämtade från en blandning av enkla klockformade kurvor. Med ett standardstatistiskt verktyg kallat en Gaussisk blandningsmodell anpassar den två sådana kurvor till de filtrerade data och beräknar hur mycket de överlappar. Genom att skanna över olika filterbredder och välja den som minimerar denna överlappning gör algoritmen de olika rörelsestaterna så distinkta som data tillåter. När denna optimala inställning hittats tilldelas varje förskjutning den stat vars klockform den mest sannolikt tillhör, vilket effektivt segmenterar den ursprungliga banan i snabba och långsamma partier. Viktigt är att denna segmentering sker innan man försöker uppskatta fysikaliska parametrar som diffusionskoefficienter eller statslivslängder, så att dessa senare kan mätas med välkända, väletablerade formler.
Testning med simuleringar och verkliga molekyler
Forskarna utsatte sin metod för stresstest på datorgenererade banor där en partikel byter mellan två diffusionshastigheter med kända egenskaper. De varierade hur olika de två hastigheterna var, hur länge partikeln stannade i varje tillstånd, hur brusiga positionsmätningarna var och hur mycket oskärpa kameran introducerade. Över ett brett spektrum av realistiska förhållanden—när de snabba och långsamma staterna skiljde sig åt med åtminstone ungefär en faktor fyra och varje tillstånd varade mer än några kameraramar—klassificerade algoritmen rätt för mer än 90 procent av tidpunkterna. Avgörande visade sig metoden också vara robust när den tillämpades på experimentella data från fluorescensmärkta proteiner som diffunderar i ett understött membran, där den avslöjade två tydligt separerade populationer: en rörlig och en nästan orörlig.
Från rena segment till biologisk insikt
När banorna hade segmenterats visade teamet att diffusionskoefficienter kunde återfinnas med god noggrannhet, även i närvaro av betydande mätbrus eller rörelseoskärpa. Att uppskatta hur länge molekyler typiskt stannade i varje tillstånd var mer krävande och fordrade längre banor, men gav ändå rimliga livslängder under lämpliga förhållanden. Budskapet är att ett relativt enkelt, genomskinligt förfarande—filtrering av steg i tiden och passning av ett par klockformade kurvor—kan mäta sig med mer komplexa angreppssätt samtidigt som det körs snabbt på vanliga datorer. För experimentutförare innebär detta att de kan bearbeta single-particle-data i realtid, justera sina bildförhållanden direkt och få klarare bilder av hur molekyler binder, släpper och rör sig i trånga cellulära miljöer.
Citering: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
Nyckelord: single-particle tracking, molekylär diffusion, bana-segmentering, Brownsk rörelse, membranproteiner