Clear Sky Science · fr
Une méthode légère, fondée sur les données, pour segmenter des trajectoires browniens à états multiples
Observer les molécules errer
À l’intérieur des cellules vivantes, d’innombrables molécules s’agitent constamment, se lient et se délient, et leurs mouvements renferment des indices sur le fonctionnement du vivant. Les microscopes modernes peuvent suivre des molécules individuelles au fil du temps, mais transformer ces trajectoires emmêlées en récits clairs sur la vitesse de diffusion d’une molécule ou le moment où elle se lie à un partenaire est étonnamment difficile. Cet article présente une façon simple et rapide de découper un tel mouvement en « états » distincts, ce qui facilite la lecture par les biologistes de ce que racontent les films de molécules uniques.
Pourquoi suivre les molécules est délicat
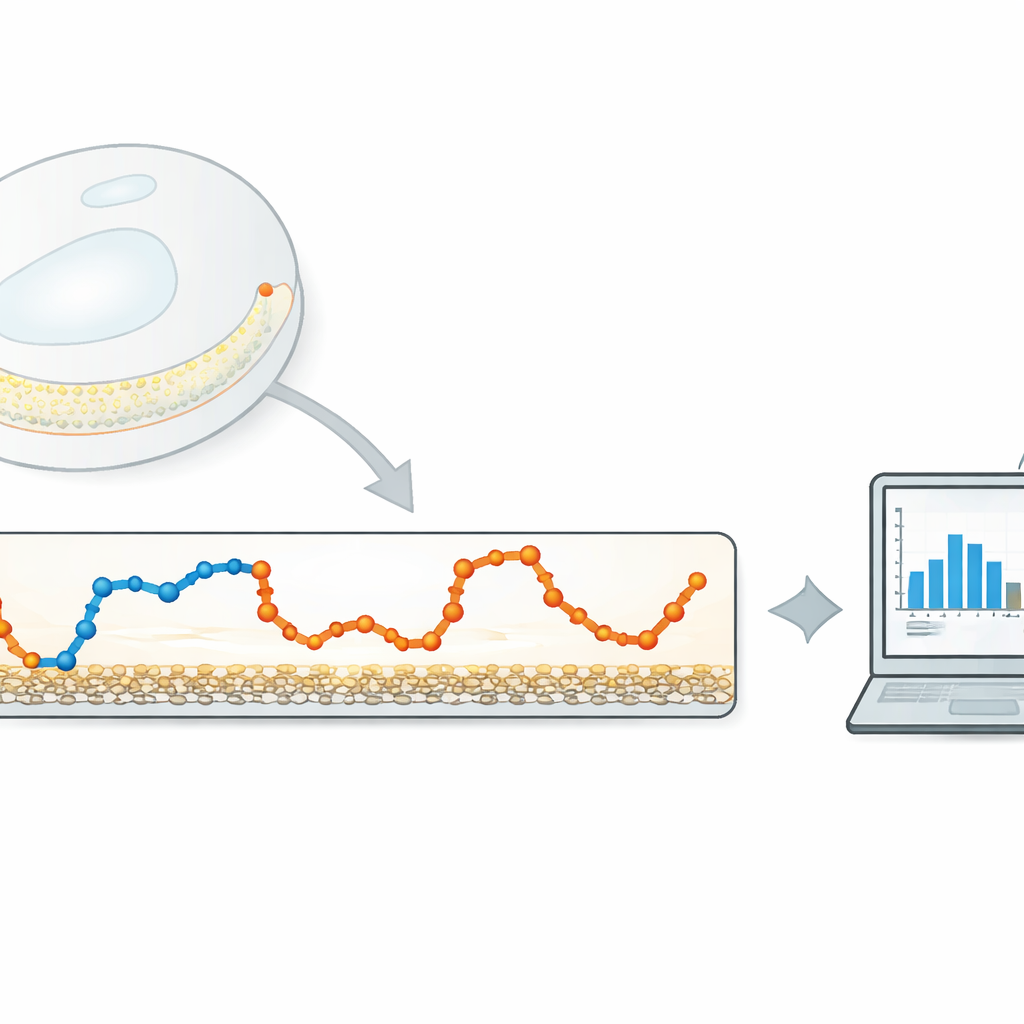
Les techniques de suivi de particules uniques enregistrent les positions de molécules individuelles au cours du temps, construisant une trajectoire qui reflète la façon dont elles explorent leur environnement. Dans de nombreux systèmes réels, une molécule ne se déplace pas d’une seule manière : elle peut vagabonder librement pendant un temps puis ralentir lorsqu’elle se lie à un récepteur ou se retrouve piégée dans un agrégat. La trajectoire est donc un mélange de plusieurs modes de mouvement, chacun avec sa vitesse caractéristique. Les outils d’analyse existants peuvent, en principe, séparer ces modes, mais les méthodes largement utilisées, basées sur les modèles de Markov cachés ou l’apprentissage profond, sont souvent coûteuses en calcul, nécessitent des réglages experts, ou fonctionnent comme des « boîtes noires » dont les décisions sont difficiles à interpréter.
Une alternative légère aux algorithmes lourds
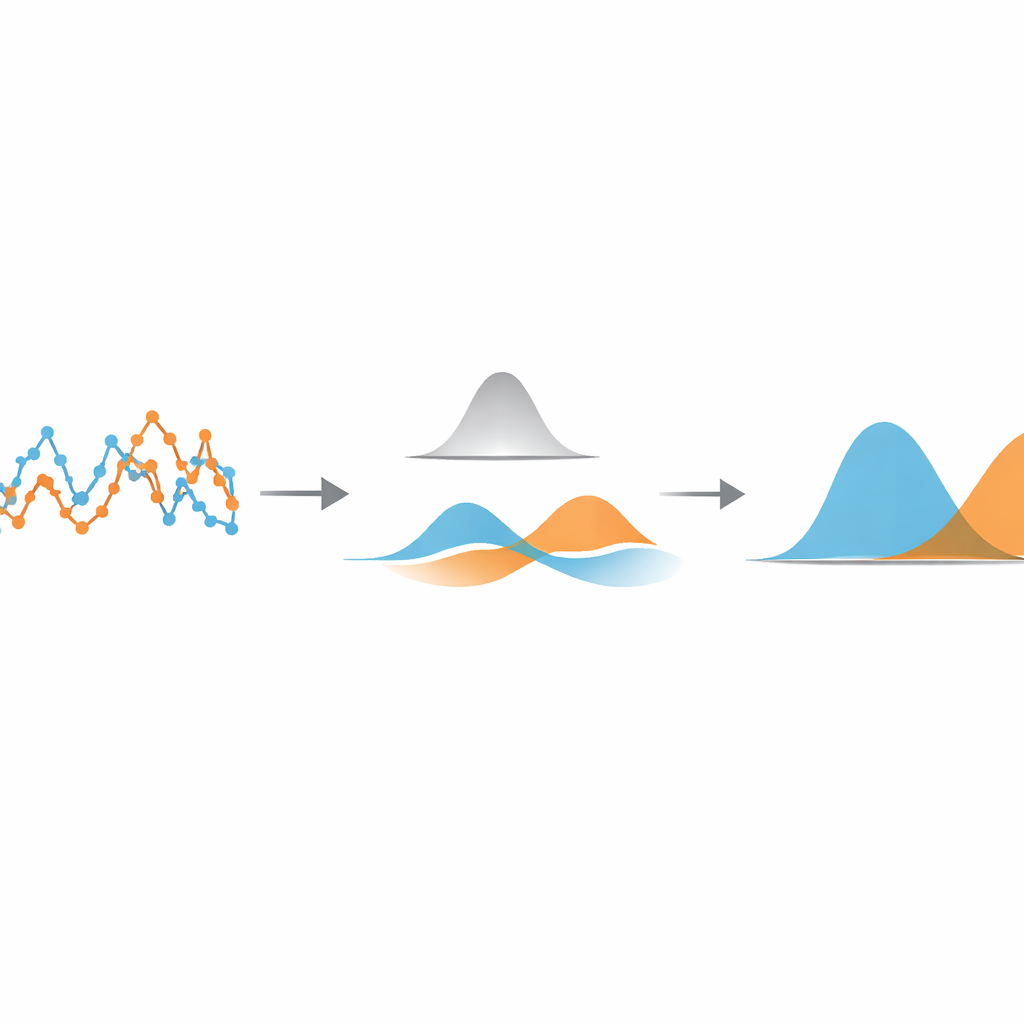
Les auteurs proposent une méthode légère, guidée par les données, qui se concentre sur une quantité très simple : la distance parcourue par la particule entre deux images consécutives. Ils calculent d’abord cette série temporelle de déplacements pas à pas à partir d’une trajectoire suivie. Ils appliquent ensuite un filtre gaussien unidimensionnel — un type de moyenne glissante à pondération douce — à cette série. La largeur du filtre contrôle l’intensité de lissage des pas voisins. Si le filtre est trop étroit, peu de bruit est éliminé ; s’il est trop large, les transitions entre les différents états de mouvement sont estompées. L’idée clé est d’ajuster automatiquement cette largeur afin que les pas filtrés issus de chaque état de mouvement se chevauchent le moins possible.
Laisser les données se classer elles‑mêmes
Pour trouver ce point optimal, la méthode considère les déplacements filtrés comme provenant d’un mélange de simples courbes en cloche. En utilisant un outil statistique standard appelé modèle de mélange gaussien, elle ajuste deux telles courbes aux données filtrées et calcule leur recouvrement. En balayant différentes largeurs de filtre et en choisissant celle qui minimise ce recouvrement, l’algorithme rend les états de mouvement aussi distincts que les données le permettent. Une fois ce réglage optimal trouvé, chaque déplacement est attribué à l’état dont la courbe en cloche a la probabilité la plus élevée, segmentant ainsi la trajectoire originale en phases rapides et lentes. Il est important de noter que cette segmentation intervient avant toute tentative d’estimer des paramètres physiques comme les coefficients de diffusion ou les durées d’état, qui peuvent ensuite être évalués avec des formules familières et éprouvées.
Tests par simulation et sur de vraies molécules
Les chercheurs ont mis leur méthode à l’épreuve sur des trajectoires générées par ordinateur où une particule bascule entre deux vitesses de diffusion aux propriétés connues. Ils ont fait varier le contraste entre les deux vitesses, la durée de séjour dans chaque état, le bruit des mesures de position et le flou introduit par la caméra. Sur une large gamme de conditions réalistes — chaque fois que les états rapide et lent différaient d’au moins un facteur d’environ quatre et que chaque état durait plus que quelques images — l’algorithme a correctement étiqueté plus de 90 % des instants. De manière cruciale, la méthode s’est aussi montrée robuste lorsqu’elle a été appliquée à des données expérimentales de protéines marquées par fluorescence diffusant dans une membrane supportée, révélant deux populations clairement séparées : une mobile et une quasi immobile.
Des segments propres vers des insights biologiques
Une fois les trajectoires segmentées, l’équipe a montré que les coefficients de diffusion pouvaient être récupérés avec une bonne précision, même en présence d’un bruit de mesure substantiel ou de flou de mouvement. L’estimation des durées typiques de séjour dans chaque état était plus exigeante et nécessitait des trajectoires plus longues, mais fournissait néanmoins des durées raisonnables dans des conditions appropriées. Le message général est qu’une procédure relativement simple et transparente — lisser les pas dans le temps et ajuster une paire de courbes en cloche — peut rivaliser avec des approches plus complexes tout en s’exécutant rapidement sur des ordinateurs ordinaires. Pour les expérimentateurs, cela signifie qu’ils peuvent traiter les données de particules uniques en temps réel, ajuster leurs conditions d’imagerie sur le vif et obtenir des images plus claires de la façon dont les molécules se lient, se délient et se déplacent dans des environnements cellulaires encombrés.
Citation: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
Mots-clés: suivi de particules uniques, diffusion moléculaire, segmentation de trajectoire, mouvement brownien, protéines membranaires