Clear Sky Science · es
Un método de segmentación ligero y basado en datos para trayectorias brownianas con varios estados
Observando cómo vagan las moléculas
Dentro de las células vivas, innumerables moléculas se agitan, se unen y se separan constantemente, y su movimiento contiene pistas sobre cómo funciona la vida. Los microscopios modernos pueden seguir moléculas individuales mientras se desplazan, pero convertir esos caminos en historias claras sobre la velocidad de difusión de una molécula o sobre cuándo se une a una pareja es sorprendentemente difícil. Este artículo presenta una manera simple y rápida de dividir ese movimiento en “estados” de desplazamiento distintos, lo que facilita a los biólogos leer lo que las películas de moléculas individuales tratan de contarnos.
Por qué es difícil rastrear moléculas
Las técnicas de seguimiento de partículas individuales registran las posiciones de moléculas concretas a lo largo del tiempo, construyendo una trayectoria que refleja cómo exploran su entorno. En muchos sistemas reales, una molécula no se mueve de una sola forma: puede vagar libremente durante un tiempo y luego ralentizarse cuando se une a un receptor o queda atrapada en un agregado. Eso significa que la trayectoria es una mezcla de varios modos de movimiento, cada uno con su propia velocidad característica. Las herramientas de análisis existentes, en principio, pueden separar esos modos, pero los métodos ampliamente usados basados en modelos ocultos de Markov o en aprendizaje profundo suelen ser computacionalmente costosos, requieren ajustes expertos o actúan como “cajas negras” cuyas decisiones son difíciles de interpretar.
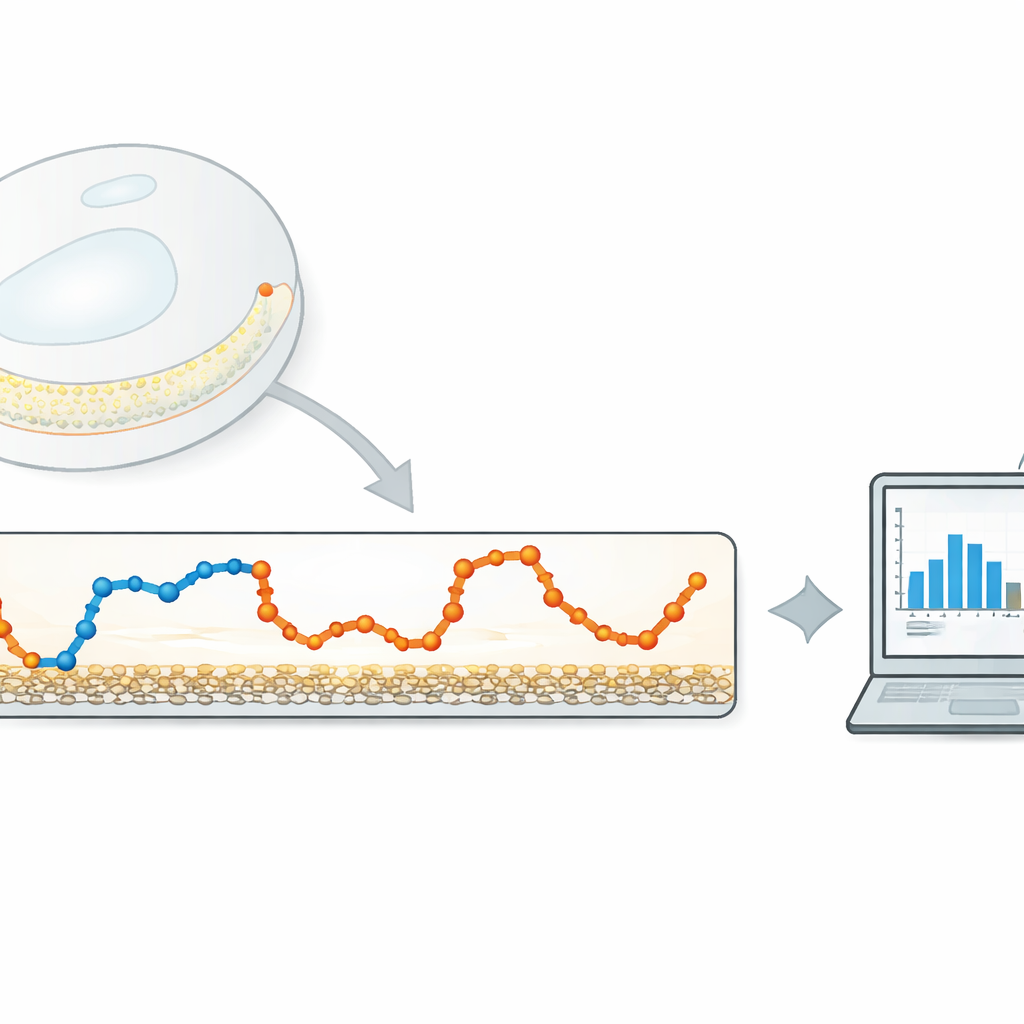
Una alternativa ligera a los algoritmos pesados
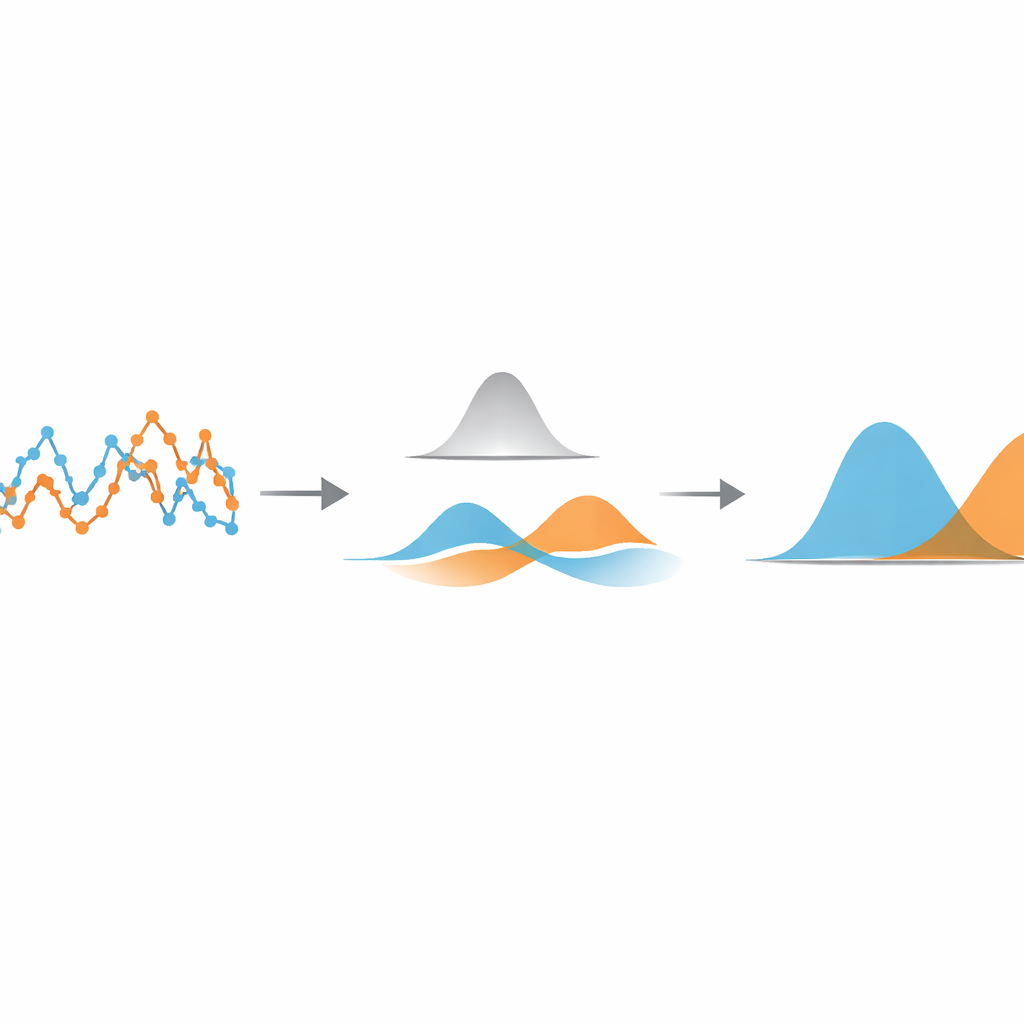
Los autores proponen un método ligero y basado en datos que se centra en una cantidad muy simple: cuánto se desplaza la partícula entre fotogramas consecutivos de la cámara. Primero calculan esta serie temporal de desplazamientos paso a paso a partir de una trayectoria rastreada. Luego aplican un filtro gaussiano unidimensional—un tipo de promedio deslizante con ponderación suave—a esta serie. La anchura del filtro controla con qué intensidad se promedian entre sí los pasos cercanos. Si el filtro es demasiado estrecho, se elimina poco ruido; si es demasiado ancho, las transiciones entre diferentes estados de movimiento se diluyen. La idea clave es ajustar automáticamente esa anchura de modo que los pasos filtrados de cada estado de movimiento se solapen lo menos posible.
Dejar que los datos se ordenen por sí mismos
Para encontrar ese punto óptimo, el método trata los desplazamientos filtrados como procedentes de una mezcla de curvas en forma de campana simples. Utilizando una herramienta estadística estándar llamada modelo de mezcla gaussiana, ajusta dos de esas curvas a los datos filtrados y calcula cuánto se solapan. Al barrer distintas anchuras de filtro y escoger la que minimiza ese solapamiento, el algoritmo hace que los distintos estados de movimiento sean lo más distintos que permitan los datos. Una vez hallada esa configuración óptima, cada desplazamiento se asigna al estado cuya campana lo representa con mayor probabilidad, segmentando así la trayectoria original en tramos rápidos y lentos. Es importante que esta segmentación ocurra antes de intentar estimar parámetros físicos como coeficientes de difusión o tiempos de permanencia en los estados, de modo que esos parámetros puedan medirse después con fórmulas conocidas y bien probadas.
Pruebas con simulaciones y moléculas reales
Los investigadores sometieron su método a pruebas exigentes usando trayectorias generadas por ordenador en las que una partícula alterna entre dos velocidades de difusión con propiedades conocidas. Variaron cuánto diferían las dos velocidades, cuánto tiempo permanecía la partícula en cada estado, el ruido en las mediciones de posición y cuánto desenfoque introducía la cámara. En un amplio rango de condiciones realistas—siempre que los estados rápido y lento difirieran al menos por un factor de aproximadamente cuatro y cada estado durara más que varios fotogramas de la cámara—el algoritmo etiquetó correctamente más del 90 % de los instantes. De forma crucial, el método también mostró robustez al aplicarlo a datos experimentales de proteínas marcadas con fluorescencia difundiendo en una membrana soportada, donde reveló dos poblaciones claramente separadas: una móvil y otra casi inmóvil.
De segmentos limpios a conocimiento biológico
Una vez segmentadas las trayectorias, el equipo demostró que los coeficientes de difusión podían recuperarse con buena precisión, incluso en presencia de ruido de medición considerable o desenfoque por movimiento. Estimar cuánto tiempo permanecen típicamente las moléculas en cada estado fue más exigente y requirió trayectorias más largas, pero aun así arrojó tiempos de permanencia razonables en condiciones adecuadas. El mensaje global es que un procedimiento relativamente simple y transparente—filtrar pasos en el tiempo y ajustar un par de curvas en forma de campana—puede competir con enfoques más complejos a la vez que se ejecuta con rapidez en ordenadores comunes. Para los experimentadores, esto significa que pueden procesar datos de partículas individuales al instante, ajustar sus condiciones de imagen en tiempo real y obtener imágenes más claras de cómo las moléculas se unen, se separan y se desplazan en entornos celulares densamente poblados.
Cita: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
Palabras clave: seguimiento de partículas individuales, difusión molecular, segmentación de trayectorias, movimiento browniano, proteínas de membrana