Clear Sky Science · pt
Um método leve e orientado por dados para segmentação de trajetórias Brownianas multiestado
Observando Moléculas Vaguearem
No interior de células vivas, incontáveis moléculas estão constantemente se chocando, ligando e desligando, e seu movimento guarda pistas sobre como a vida funciona. Microscópios modernos conseguem seguir moléculas individuais enquanto elas se movem, mas transformar esses caminhos emaranhados em relatos claros sobre quão rápido uma molécula difunde ou quando ela se liga a um parceiro é surpreendentemente difícil. Este artigo apresenta uma forma simples e rápida de decompor tal movimento em “estados” distintos, facilitando para biólogos a leitura do que os filmes de moléculas singulares estão tentando nos dizer.
Por Que Rastrear Moléculas É Complicado
Técnicas de rastreamento de partícula única registram as posições de moléculas individuais ao longo do tempo, construindo uma trajetória que reflete como elas exploram o ambiente. Em muitos sistemas reais, uma molécula não se move de apenas uma maneira: ela pode vagar livremente por um período e então desacelerar ao se ligar a um receptor ou ficar presa em um aglomerado. Isso significa que a trajetória é uma mistura de vários modos de movimento, cada um com sua velocidade característica. Ferramentas de análise existentes podem, em princípio, separar esses modos, mas métodos amplamente usados baseados em modelos ocultos de Markov ou em aprendizado profundo costumam ser computacionalmente pesados, requerer ajuste por especialistas ou atuar como “caixas-pretas” cujas decisões são difíceis de interpretar.
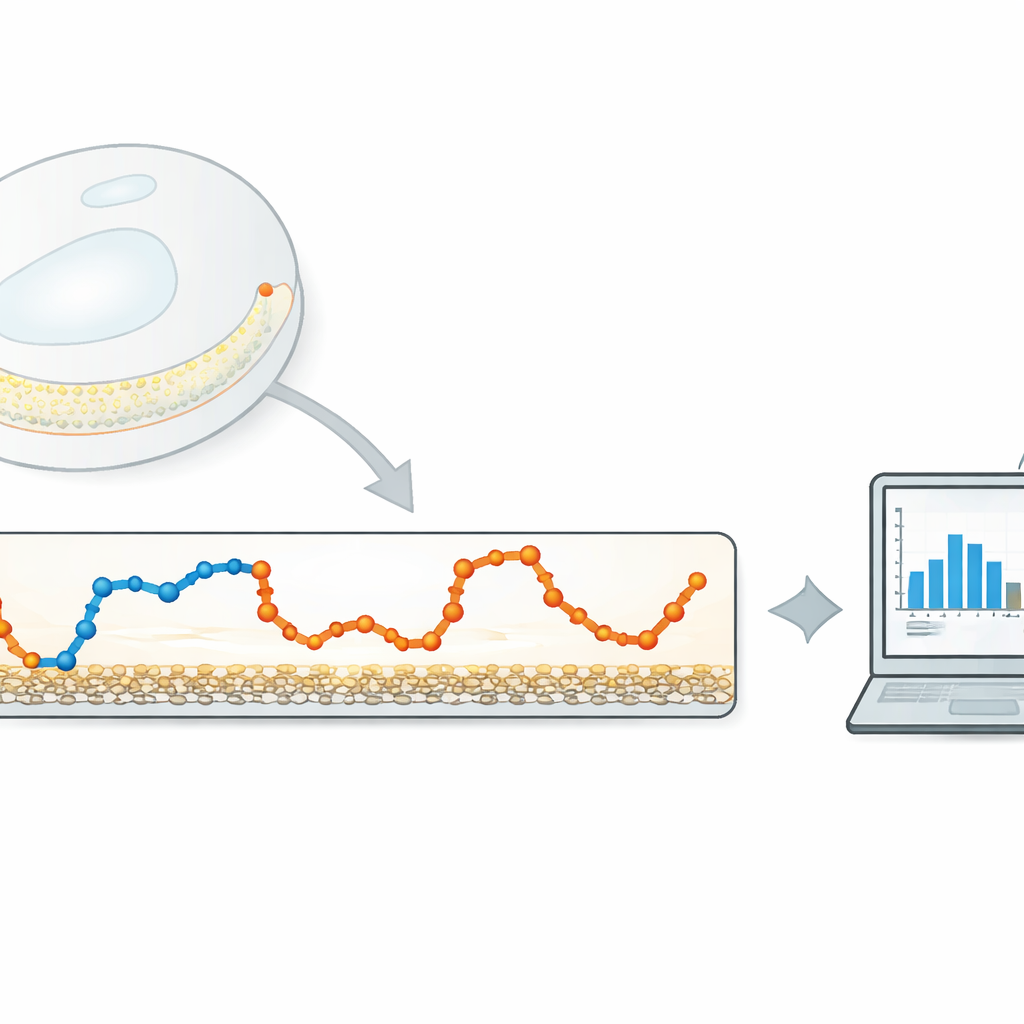
Uma Alternativa Enxuta a Algoritmos Pesados
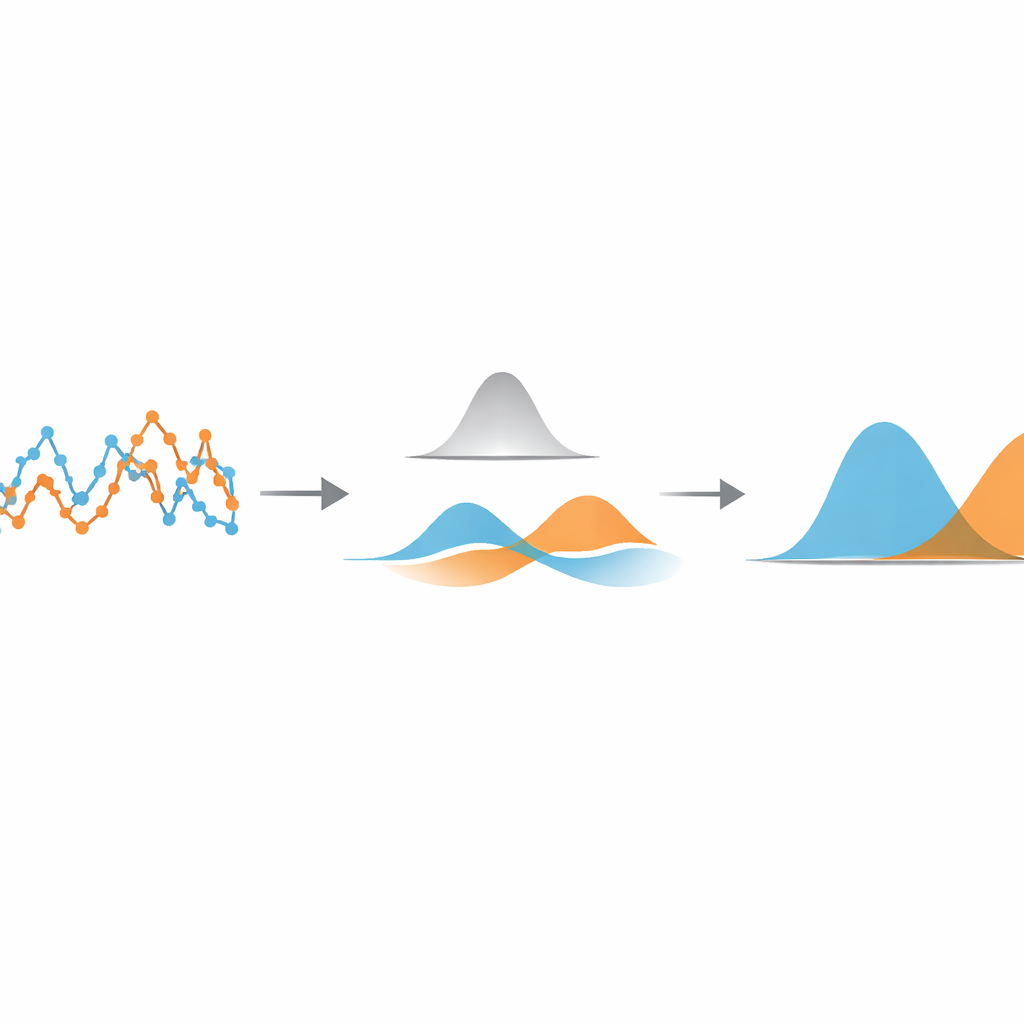
Os autores propõem um método leve e orientado por dados que foca em uma quantidade muito simples: o quanto a partícula se desloca entre quadros consecutivos da câmera. Primeiro, eles calculam essa série temporal de deslocamentos passo a passo a partir de uma trajetória rastreada. Em seguida aplicam um filtro gaussiano unidimensional—um tipo de média deslizante com pesos suaves—a essa série. A largura do filtro controla o quanto passos próximos são combinados. Se o filtro for muito estreito, pouco ruído é removido; se for muito largo, as transições entre diferentes estados de movimento são atenuadas. A ideia-chave é ajustar automaticamente essa largura para que os passos filtrados de cada estado de movimento se sobreponham o mínimo possível.
Deixando os Dados Separem Sozinhos
Para encontrar esse ponto ideal, o método trata os deslocamentos filtrados como vindos de uma mistura de curvas em forma de sino simples. Usando uma ferramenta estatística padrão chamada modelo de mistura gaussiana, ele ajusta duas dessas curvas aos dados filtrados e calcula quanto elas se sobrepõem. Varrendo diferentes larguras de filtro e escolhendo aquela que minimiza essa sobreposição, o algoritmo torna os diferentes estados de movimento tão distintos quanto os dados permitem. Uma vez encontrado esse ajuste ótimo, cada deslocamento é atribuído ao estado cuja curva em sino tem maior probabilidade de tê-lo gerado, segmentando efetivamente a trajetória original em trechos rápidos e lentos. É importante que essa segmentação aconteça antes de qualquer tentativa de estimar parâmetros físicos como coeficientes de difusão ou tempos de permanência dos estados, de modo que estes possam ser medidos depois com fórmulas familiares e bem testadas.
Testando com Simulações e Moléculas Reais
Os pesquisadores testaram rigorosamente seu método em trajetórias geradas por computador nas quais uma partícula alterna entre duas velocidades de difusão com propriedades conhecidas. Eles variaram o quão diferentes eram as duas velocidades, quanto tempo a partícula permanecia em cada estado, quão ruidosas eram as medidas de posição e quanto desfoque a câmera introduzia. Em uma ampla gama de condições realistas—sempre que os estados rápido e lento diferiam por pelo menos cerca de um fator quatro e cada estado durava mais do que várias imagens de câmera—o algoritmo rotulou corretamente mais de 90% dos pontos temporais. Crucialmente, o método também se mostrou robusto quando aplicado a dados experimentais de proteínas marcadas fluorescentemente difundindo em uma membrana apoiada, onde revelou duas populações claramente separadas: uma móvel e outra quase imóvel.
De Segmentos Limpos a Insight Biológico
Uma vez segmentadas as trajetórias, a equipe mostrou que os coeficientes de difusão podiam ser recuperados com boa precisão, mesmo na presença de ruído substancial nas medições ou desfoque de movimento. Estimar quanto tempo as moléculas tipicamente permaneciam em cada estado foi mais exigente e requereu trajetórias mais longas, mas ainda assim forneceu tempos de permanência razoáveis sob condições adequadas. A mensagem geral é que um procedimento relativamente simples e transparente—filtrar passos no tempo e ajustar um par de curvas em sino—pode rivalizar com abordagens mais complexas enquanto roda rapidamente em computadores comuns. Para experimentadores, isso significa que eles podem processar dados de partícula única em tempo real, ajustar suas condições de imagem imediatamente e obter quadros mais claros de como moléculas se ligam, desligam e se movem em ambientes celulares lotados.
Citação: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
Palavras-chave: rastreamento de partícula única, difusão molecular, segmentação de trajetória, movimento browniano, proteínas de membrana