Clear Sky Science · nl
Een lichtgewicht, datagedreven segmentatiemethode voor multi‑state Brownse trajecten
Moleculen zien zwerven
In levende cellen bewegen talloze moleculen continu: ze botsen, binden en lossen weer op, en hun bewegingen geven aanwijzingen over hoe leven functioneert. Moderne microscopen kunnen enkelvoudige moleculen volgen terwijl ze zich verplaatsen, maar die verwarde paden omzetten in duidelijke verhalen over hoe snel een molecuul diffundeert of wanneer het aan een partner bindt, blijkt verrassend lastig. Dit artikel introduceert een eenvoudige, snelle manier om zulke bewegingen op te delen in onderscheidende “toestanden” van beweging, waardoor biologen beter kunnen aflezen wat single‑molecule opnames proberen te vertellen.
Waarom moleculen volgen lastig is
Single‑particle tracking technieken registreren de positie van individuele moleculen in de tijd en bouwen daarmee een traject op dat weergeeft hoe ze hun omgeving verkennen. In veel reële systemen beweegt een molecuul zich niet op slechts één manier: het kan een tijd vrij rondzwerven en vervolgens vertragen wanneer het aan een receptor bindt of in een cluster vastloopt. Dat betekent dat het traject een mengsel is van meerdere bewegingsmodi, elk met een kenmerkende snelheid. Bestaande analysetools kunnen deze modi in principe scheiden, maar veelgebruikte methoden op basis van verborgen Markov‑modellen of deep learning zijn vaak rekenkundig zwaar, vereisen deskundige afstemming of functioneren als “black boxes” waarvan de beslissingen moeilijk te interpreteren zijn.
Een slanke tegenhanger van zware algoritmen
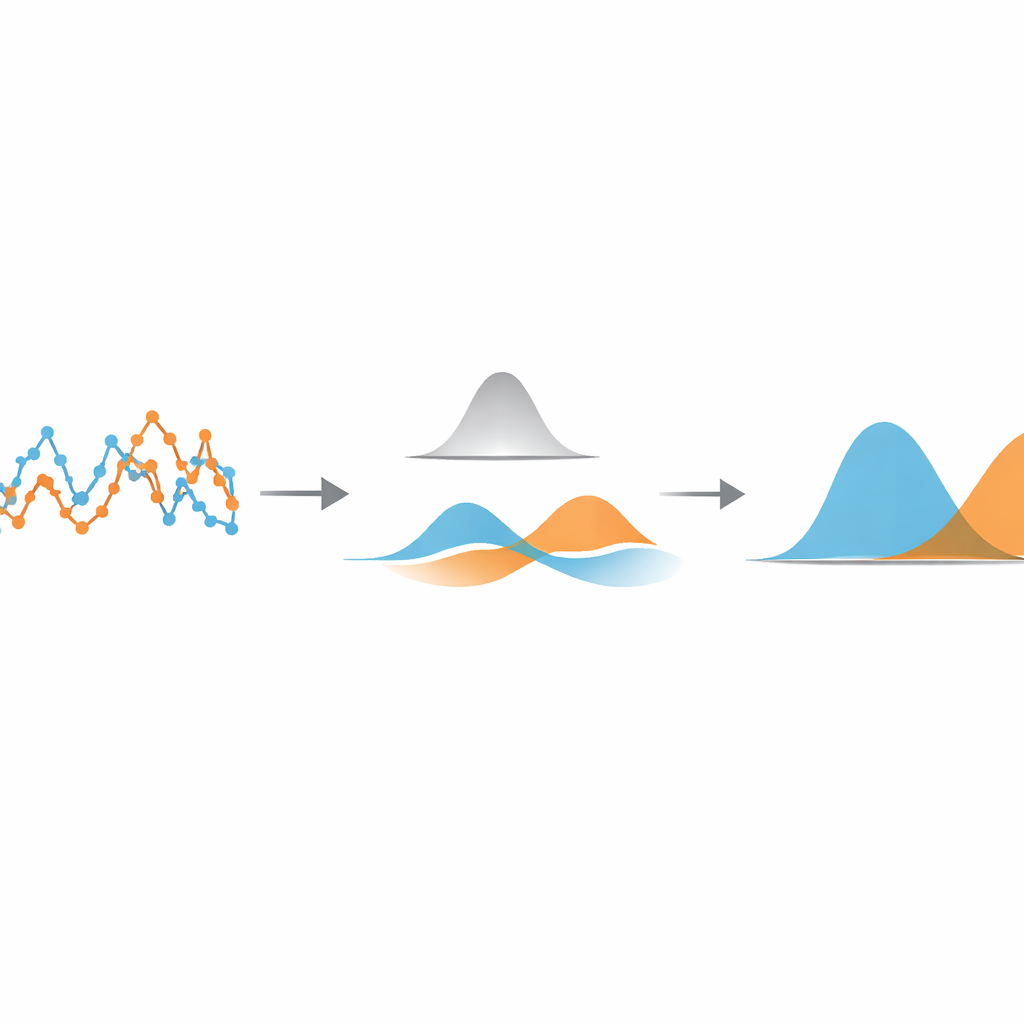
De auteurs stellen een lichtgewicht, datagedreven methode voor die zich richt op een zeer eenvoudige grootheid: hoe ver het deeltje beweegt tussen opeenvolgende cameraframes. Eerst berekenen ze deze stap‑voor‑stap verplaatsingsreeks uit een gevolgd traject. Vervolgens passen ze een eendimensionale Gaussiaanse filter toe—een type schuivend, soepel gewogen gemiddelde—op deze reeks. De filterbreedte bepaalt hoe sterk nabije stappen elkaar beïnvloeden. Als de filter te smal is, wordt weinig ruis verwijderd; is hij te breed, dan vervagen de overgangen tussen verschillende bewegingsstaten. Het sleutelidee is deze breedte automatisch af te stemmen zodat de gefilterde stappen van elke bewegingsstaat zo min mogelijk overlappen.
Het laten opdelen door de data zelf
Om dat goede punt te vinden, behandelt de methode de gefilterde verplaatsingen als afkomstig van een mengsel van eenvoudige klokvormige verdelingen. Met een standaard statistisch hulpmiddel, een Gaussian mixture model, passen ze twee zulke curves op de gefilterde data en berekenen ze hoeveel overlap er is. Door verschillende filterbreedtes te doorlopen en de breedte te kiezen die deze overlap minimaliseert, maakt het algoritme de bewegingsstaten zo onderscheidend als de data toestaan. Zodra deze optimale instelling is gevonden, wordt elke verplaatsing toegewezen aan de staat waartoe de bijbehorende klokvormige verdeling het meest waarschijnlijk behoort, waarmee het oorspronkelijke traject effectief wordt gesegmenteerd in snelle en langzame stukken. Belangrijk is dat deze segmentatie plaatsvindt voordat men fysieke parameters als diffusiecoëfficiënten of staatlevensduren probeert te schatten, zodat die later met bekende, goed geteste formules gemeten kunnen worden.
Getest met simulaties en echte moleculen
De onderzoekers hebben hun methode zwaar getest op computersimulaties waarbij een deeltje wisselt tussen twee diffusiemijngedragingen met bekende eigenschappen. Ze varieerden hoe verschillend de twee snelheden waren, hoe lang het deeltje in elke toestand verbleef, hoe ruisig de positiemetingen waren en hoeveel vervaging de camera introduceerde. Over een breed scala aan realistische omstandigheden—wanneer de snelle en langzame staten minstens ongeveer een factor vier verschilden en elke staat langer dan enkele cameraframes duurde—labelde het algoritme meer dan 90 procent van de tijdstippen correct. Cruciaal is dat de methode ook robuust bleek bij toepassing op experimentele data van fluorescent gelabelde eiwitten die in een ondersteund membraan diffundeerden, waar het twee duidelijk gescheiden populaties onthulde: één mobiel en één vrijwel immobiel.
Van schone segmenten naar biologische inzichten
Zodra de trajecten waren gesegmenteerd, toonden de onderzoekers aan dat diffusiecoëfficiënten met goede nauwkeurigheid teruggewonnen konden worden, zelfs bij aanzienlijke meetruis of bewegingsonscherpte. Het schatten van hoe lang moleculen typisch in elke staat verbleven, vergde meer en langere trajecten, maar leverde onder geschikte omstandigheden nog steeds redelijke levensduren op. De algemene boodschap is dat een relatief eenvoudige, transparante procedure—stappen in de tijd filteren en een paar klokvormige curves passen—het kan opnemen tegen complexere benaderingen terwijl hij snel draait op gewone computers. Voor experimenteerders betekent dit dat ze single‑particle data direct kunnen verwerken, hun beeldcondities in real time kunnen bijsturen en helderdere beelden krijgen van hoe moleculen binden, ontbinden en bewegen in dichtbevolkte cellulaire omgevingen.
Bronvermelding: El Korde, I., Lewis, J.M., Clarkson, E. et al. A light-weight, data-driven segmentation method for multi-state Brownian trajectories. npj Biol. Phys. Mech. 3, 6 (2026). https://doi.org/10.1038/s44341-026-00037-7
Trefwoorden: single-particle tracking, moleculaire diffusie, trajectsegmentatie, Brownse beweging, membraaneiwitten