Clear Sky Science · zh
基于深度学习的多重 FUCCI 采集中生物图像分析
观察细胞的日常生活
每个活细胞持续不断地在生长、复制 DNA 和分裂等阶段间循环。生物学家现在有荧光工具可以让这些细胞周期阶段以不同颜色发光,从而实时观察这一过程的展开。但当同时记录过多信号时,图像变得嘈杂且难以解读——即使对计算机也是如此。本文介绍了一种基于深度学习的方法,能够清理这些复杂的时序影像、追踪单个细胞,并判读每个细胞所处的周期阶段,为癌症研究、干细胞研究和药物测试提供了新能力。
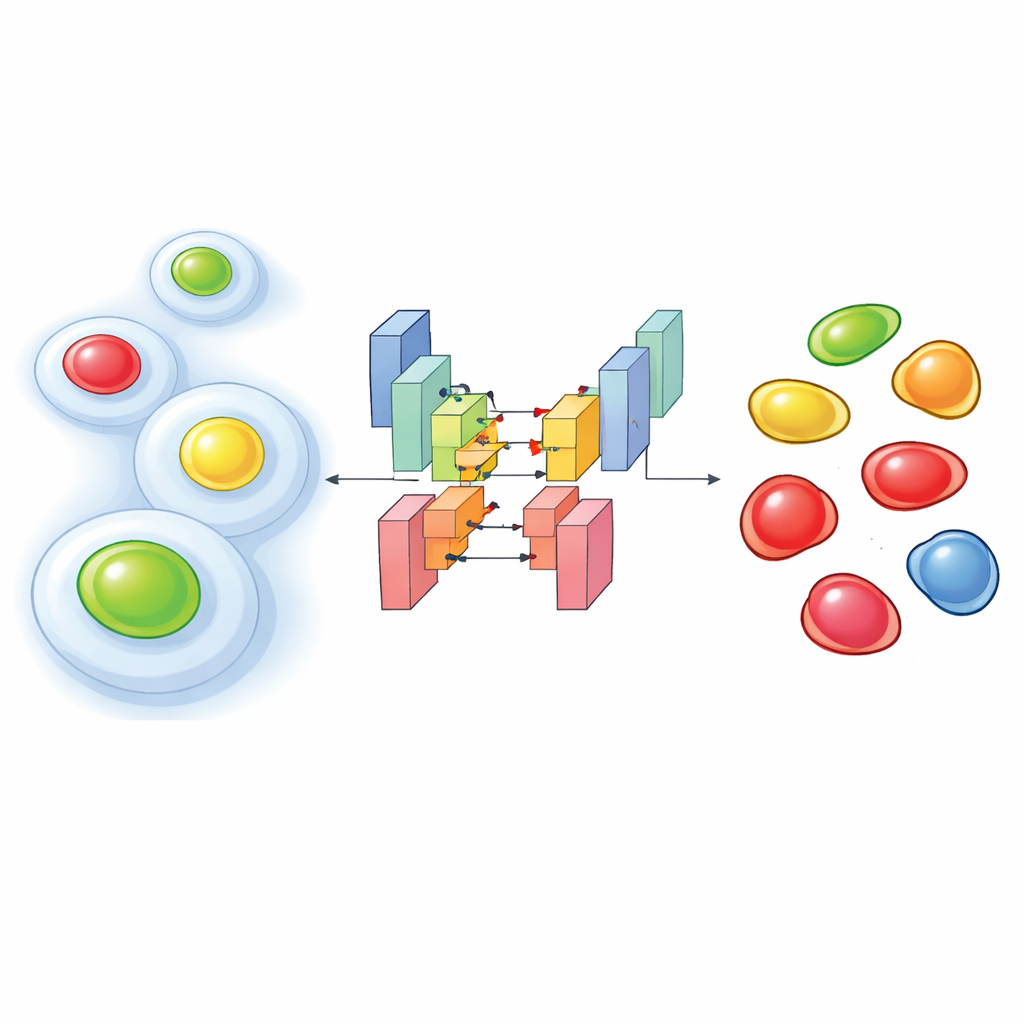
活细胞内的发光计时器
为了观察细胞如何经过生命周期,研究者常用一种称为 FUCCI 的分子工具,它使细胞核在早期阶段以一种颜色发光、在晚期以另一种颜色发光,中间则呈现混合颜色。更新的实验更进一步:将 FUCCI 与额外的荧光标记一起记录,这些标记突显细胞的内在支架或其他结构。这种“多重标记”有助于将细胞的结构行为与其处于生命周期的位置关联起来。缺点是,为避免损伤活细胞,科学家必须以较弱的光照观察,这会产生暗淡且噪声大的图像,并导致颜色相互渗漏。在这些条件下,常规图像分析软件经常无法正确识别每个细胞核或分配正确的细胞周期阶段。
教算法穿透噪声去“看见”
作者通过在两个人源细胞系的数千张精心注释的图像上训练定制深度学习网络来解决这个问题。他们的方法将多通道输入送入基于 StarDist 架构的分割模型,该架构善于勾勒出单个细胞核的轮廓。他们测试了三种输入设置:仅使用胞质标记(一个带荧光的结构蛋白)、仅使用两种 FUCCI 色彩,以及结合所有三种。尽管条件嘈杂,两通道和三通道版本在识别细胞核方面都达到了很高的准确率,明显优于在弱信号下表现不佳的流行预训练工具。令人惊讶的是,即便只用胞质标记的模型也常能推断出细胞核的位置,因为周围的支架在细胞核处留下了一个典型的“空洞”。
从彩色斑点到细胞周期标签
找到细胞核只是其中一半工作;研究者还需要知道每个细胞核处于哪个细胞周期阶段。传统上,这是通过对 FUCCI 颜色设定强度阈值来完成的,这种简单方法很容易被其他通道的渗漏所误导。团队扩展了他们的网络,使其不仅勾勒每个细胞核,还根据颜色模式将其标注为属于若干细胞周期阶段之一。将该方法与经典的强度阈值法比较时,深度学习分类器在噪声数据中尤其更准确。它甚至可以推广到另一个实验室的 FUCCI 变体:作者只需重新映射哪些颜色组合对应哪些阶段,无需重新训练即可适用。
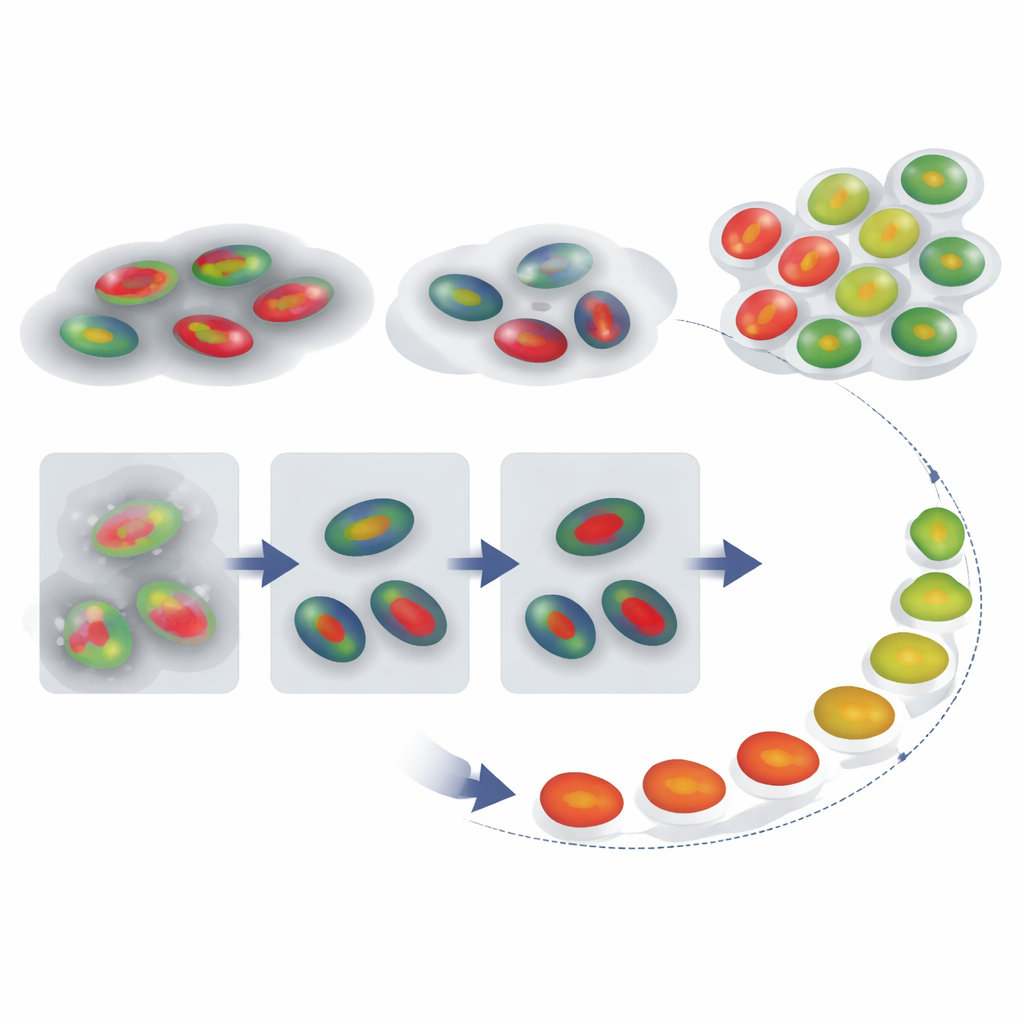
重建细胞的时间旅程
在获得可靠的细胞核轮廓和阶段标签后,作者接着探讨是否能够重建单个细胞随时间经过周期的轨迹,即便记录并不包含完整的从一次分裂到下一次分裂的序列。他们追踪单个细胞的 FUCCI 信号,并使用一种称为动态时间规整(dynamic time warping)的技术,将每条强度曲线与典型周期的参考模式进行比较,该技术灵活地拉伸或压缩时间轴以找到最佳匹配。由此为每个细胞给出一个“细胞周期百分比”,作为伪时间——估计其前进的程度。同样重要的是,匹配所需的时间拉伸量可以作为警示:那些必须被大幅扭曲才能与参考匹配的细胞,可能表现异常,例如长时间滞留在某一阶段。
为何这对健康与疾病很重要
通过将多重荧光成像与定制的深度学习工具相结合,这项工作提供了一条端到端的流程:它能分割暗淡且嘈杂的图像,为每个细胞核标注细胞周期阶段,追踪细胞随时间的变化,并标记偏离标准模式的细胞。对非专家而言,关键信息是研究者现在可以在更温和的成像条件下、更可靠且更少人工干预地追踪数千个活细胞,从而保护细胞健康。这为更精确地研究癌症药物如何阻断细胞分裂、干细胞如何决定命运,以及组织中的机械力如何影响细胞何时选择分裂或暂停,打开了大门。
引用: Zimmermann, J., Pezzotti, M., Torchia, E. et al. Bioimage analysis for multiplexed FUCCI acquisitions powered by deep learning. npj Imaging 4, 27 (2026). https://doi.org/10.1038/s44303-026-00159-6
关键词: 细胞周期成像, 深度学习显微镜, FUCCI 传感器, 细胞追踪, 生物图像分析