Clear Sky Science · tr
CAMEX ile tek hücre RNA-sekans verilerinin çoklu tür entegrasyonu, hizalanması ve anotasyonu
Bu araştırma neden önemli
Her hayvan vücudu zengin bir hücre tipi kadrosundan oluşur, fakat bu hücrelerin türler arasında nasıl karşılaştırıldığı veya evrim boyunca nasıl değiştiği konusunda hâlâ net bir haritamız yok. Bu çalışma, farklı hayvanlardan elde edilmiş tek hücre gen etkinliği verilerini ortak bir resim halinde birleştiren CAMEX adlı hesaplamalı bir aracı tanıtıyor. Genel okuyucu için bu heyecan verici çünkü hangi hücre tiplerinin gerçekten evrensel olduğunu, hangilerinin insanlara özgü olduğunu ve beyin, karaciğer ya da testis gibi organların evrimsel süreçte nasıl şekillendiğini yanıtlamaya bizi daha da yaklaştırıyor.
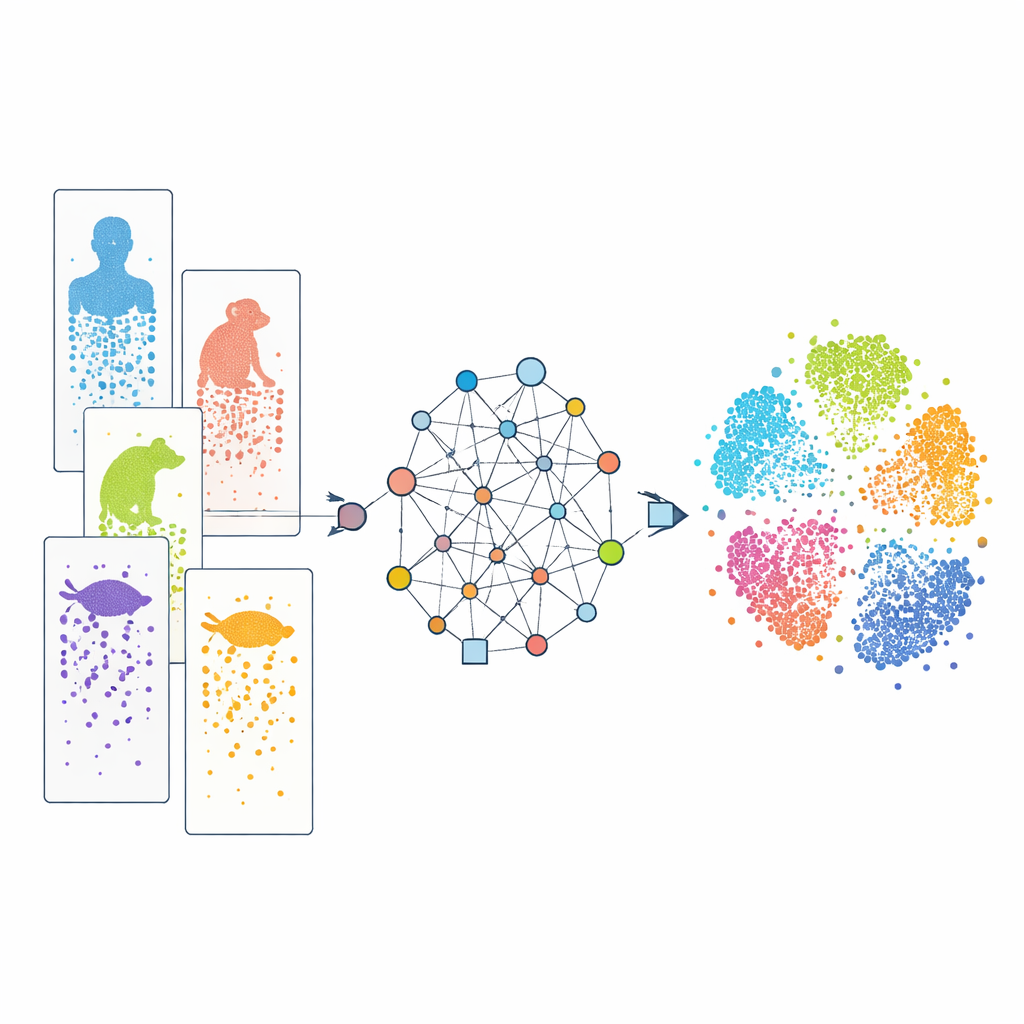
Hücreleri tek tek incelemek
Günümüz tek hücre RNA dizilemesi, bilim insanlarının tek bir deneyde binlerce ila milyonlarca bireysel hücrede hangi genlerin aktif olduğunu okumalarını sağlıyor. Bu desenleri karşılaştırarak araştırmacılar hücreleri tiplere ayırabiliyor ve gelişim süreçlerini izleyebiliyor. İnsan, maymun, fare, balık, sürüngen ve daha fazlası için birçok böyle veri seti artık mevcut. Ancak her çalışma genellikle farklı deneysel teknolojiler kullanıyor ve türler gen setleri bakımından farklılık gösteriyor. Buna ek olarak genlerle ilgili bilgilerimiz düzensiz: iyi çalışılmış laboratuvar hayvanları, nadir türlere göre çok daha iyi anotasyonlara sahip. Bu farklılıklar “parti etkileri” ve eksik sözlükler gibi davranarak benzer hücreleri türler arasında hizalamayı ve hangi özelliklerin gerçekten paylaşılan hangilerinin türe özgü olduğunu görmeyi zorlaştırıyor.
Türleri bağlamak için graf tabanlı bir yaklaşım
CAMEX, tüm verileri hem hücreleri hem de genleri içeren tek büyük bir ağa dönüştürerek bu engellerle başa çıkıyor. Bu ağda hücreler ifade ettikleri genlere, en benzer komşu hücrelerine bağlanıyor ve genler, tek eşleşme yerine çoktan-çoka olabilen evrimsel ilişkilere dayanarak türler arasında bağlanabiliyor. Heterojen bir graf sinir ağı türü olan özel bir makine öğrenmesi modeli, bu bağlantılar boyunca bilgi aktarır ve paylaşılan düşük boyutlu bir uzayda her hücre ve gen için sıkıştırılmış bir “gömü” (embedding) öğrenir. Veri entegrasyonu için model, ağ yapısını ve orijinal gen etkinliği desenlerini hücre tipleri önceden söylenmeden yeniden oluşturacak şekilde eğitiliyor. Hücre anotasyonu için aynı kodlayıcı, referans bir türden daha az çalışılmış türlere bilinen etiketleri aktarabilen dikkat (attention)-tabanlı bir sınıflandırıcıya besleniyor.
Paylaşılan hücre tiplerini ve gelişimi ortaya koymak
Yazarlar, CAMEX’in zorlu, gerçek dünya veri setleriyle karşılaştığında popüler araçlar dizisinden daha iyi performans gösterdiğini gösteriyor. Dört türe kadar ve birden fazla deneysel platformu kapsayan karaciğer, yumurtalık ve pankreas verilerinde CAMEX, yapay parti farklılıklarını ortadan kaldırmak ile hücre tipleri arasındaki gerçek biyolojik ayrımları korumak olmak üzere iki karşıt hedefi en iyi dengelemiş. Hepatositler ve immün hücreler gibi yaygın hücre popülasyonlarını doğru şekilde hizaladı ve önemlisi, diğer yöntemlerin bulanıklaştırma eğiliminde olduğu nadir hücre tiplerini korudu. Dramatik bir teste, CAMEX primatlardan ornitorinkuza ve tavuklara kadar 11 türün testis verilerini entegre etti. Germ hücrelerinin sperme olgunlaştığı sürekli yolu geri kazandı ve türler daha uzaklaştıkça performansı korumak için çoktan-çoka gen ilişkilerini kullanmanın kritik olduğunu gösterdi. Model ayrıca yedi tür arasında organ gelişim aşamalarını başarılı biçimde hizalayarak klasifik Carnegie gelişim aşamaları fikrini, aslında ilk tanımlandıkları küçük model organizma setinin ötesine genişletti.
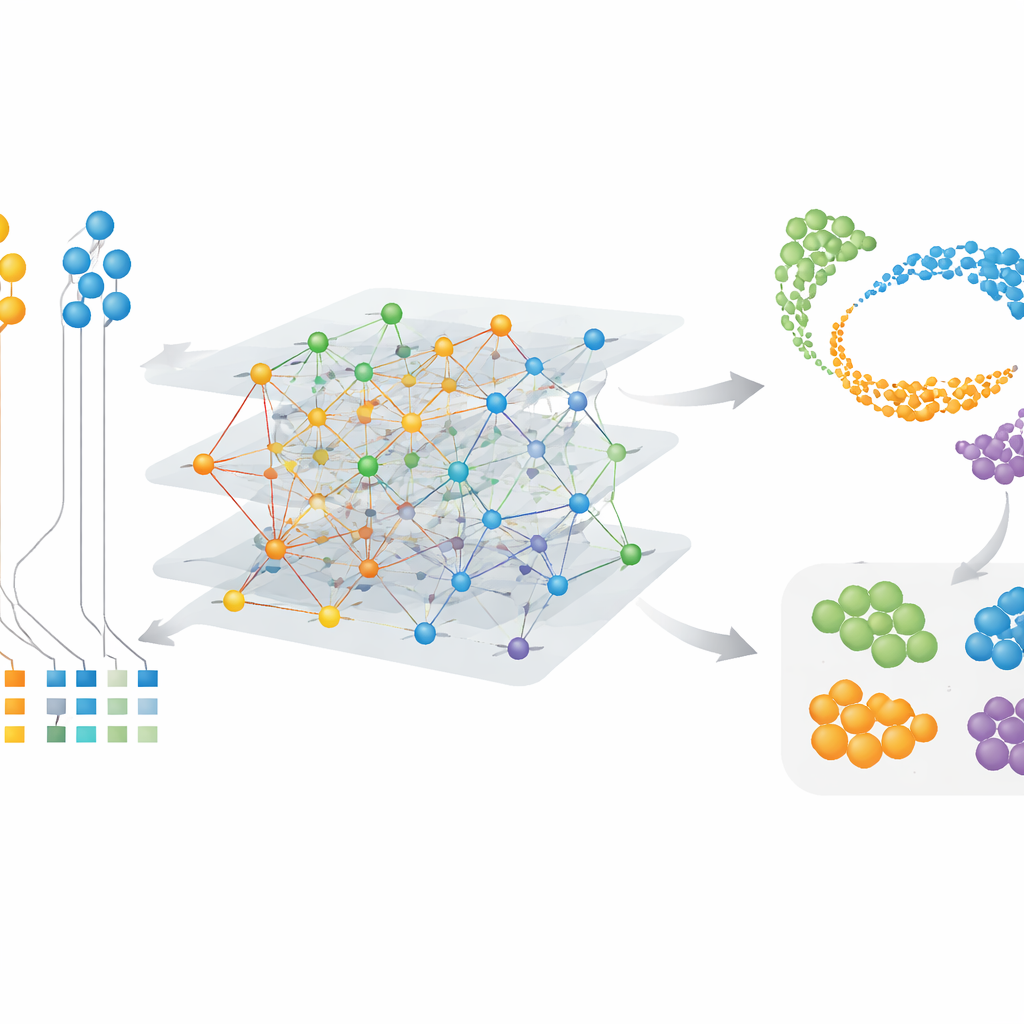
Türe özgü hücreleri ve gen modüllerini bulmak
CAMEX hem hücreler hem de genler için gömüler öğrendiği için yalnızca paylaşılan özellikleri değil, özel özellikleri de vurgulayabiliyor. İnsan, fare, kertenkele ve kaplumbağa içeren beyin veri setlerinde CAMEX verileri entegre etti ve insan etiketleri bir rehber olarak verildiğinde diğer türlerdeki hücre tiplerini, kaplumbağadaki beyin perisitleri gibi küçük alt grupları bile doğru şekilde anotladı. Yöntemi primat dorsolateral prefrontal korteksinin ayrıntılı bir haritasına uyguladıklarında, yazarlar yalnızca insanlara özgü veya şempanzelerle paylaşılan belirli mikroglia alt tiplerini izole edebildiler. Gen gömülerini kümeleyerek ayrıca ana işlevlerle ilişkilendirilmiş gen grupları buldular: örneğin testiste somatik destek hücrelerinde aktif modüller ve sperm üreten mayozla ilgili modüller. Bu sonuçlar hem korunmuş programlara hem de türlere özgü ince ayarlara işaret ediyor.
Daha geniş çerçeve için ne anlama geliyor
Basitçe söylemek gerekirse, CAMEX yaşam ağacı boyunca tek hücre verileri için güçlü yeni bir “çeviri motoru”. Farklı hayvanlardan hücrelerin esasen aynı işi ne zaman yaptığını, ne zaman farklılaştığını ve gelişim zaman çizelgelerinin türler arasında nasıl karşılaştırıldığını görmeyi kolaylaştırıyor. Yöntemin hâlâ sınırlamaları var—mevcut homoloji haritalarına dayanmak ve graf tabanlı modelleri yorumlamanın genel zorlukları gibi—ancak zaten önceki olanaklardan daha zengin evrimsel karşılaştırmaları mümkün kılıyor. Zamanla CAMEX gibi araçlar gerçek bir hücre tipi yaşam ağacı inşa etmeye, organ gelişimi modellerimizi keskinleştirmeye ve hem insanlarda hem de hayvan modellerinde hastalıkla ilişkili hücre tipleri ve ilaç hedefleri arayışını yönlendirmeye yardımcı olabilir.
Atıf: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Anahtar kelimeler: tek hücre RNA dizilemesi, türler arası entegrasyon, graf sinir ağları, hücre tipi evrimi, karşılaştırmalı genomik