Clear Sky Science · sv
Integration, alligning och annotering av encells RNA-sekvenseringsdata över flera arter med CAMEX
Varför denna forskning är viktig
Varje djurkropp är uppbyggd av ett rikt spektrum av celltyper, men vi saknar fortfarande en tydlig karta över hur dessa celler jämförs mellan arter eller förändras över evolutionen. Denna studie presenterar CAMEX, ett beräkningsverktyg som syr ihop enkells genaktivitetsdata från många olika djur till en gemensam bild. För en allmän läsare är detta spännande eftersom det för oss närmare svar på frågor som vilka celltyper som verkligen är universella, vilka som är unika för människor, och hur organ som hjärnan, levern och testiklarna formades över evolutionär tid.
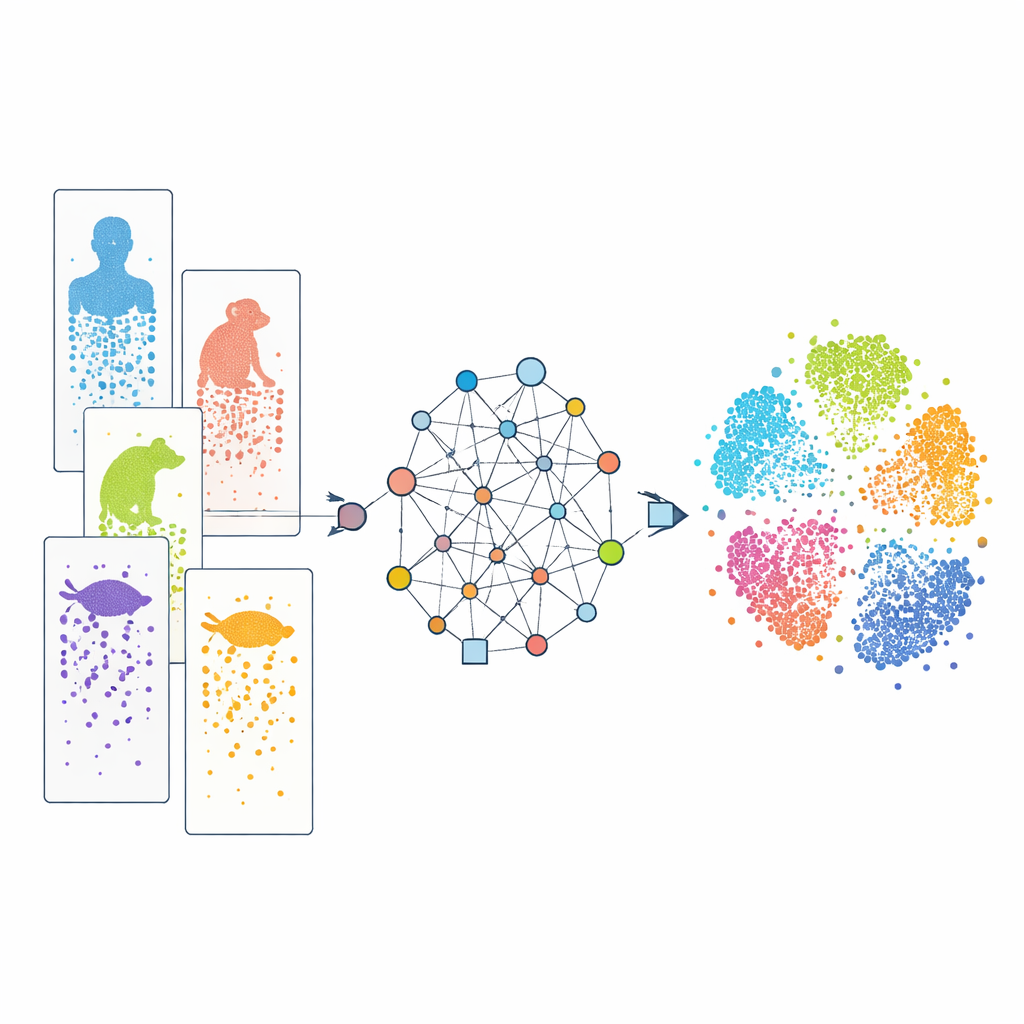
Att betrakta celler en och en
Modern enkells RNA-sekvensering gör det möjligt för forskare att läsa av vilka gener som är aktiva i tusentals till miljontals individuella celler i ett enda experiment. Genom att jämföra dessa mönster kan forskare sortera celler i typer och följa hur de utvecklas. Många sådana datamängder finns nu för människor, apor, möss, fiskar, reptiler och fler. Men varje studie använder ofta olika experimentella teknologier, och arter skiljer sig åt i sina genuppsättningar. Utöver det är vår kunskap om gener ojämnt fördelad: väldokumenterade laboratoriedjur är mycket bättre annoterade än obskyra arter. Dessa skillnader fungerar som ”batch-effekter” och ofullständiga ordböcker, vilket gör det svårt att rada upp liknande celler över arter och att avgöra vilka egenskaper som verkligen är delade kontra artspecifika.
En grafbaserad metod för att koppla ihop arter
CAMEX tar sig an dessa hinder genom att omvandla all data till ett enda stort nätverk som inkluderar både celler och gener. I detta nätverk kopplas celler till de gener de uttrycker, till sina mest liknande närliggande celler, och gener länkas över arter om de bedöms vara evolutionärt besläktade, även när relationen är många-till-många snarare än en enkel en-till-en-matchning. En specialiserad typ av maskininlärningsmodell, ett heterogent grafneuronalt nätverk, förmedlar sedan information längs dessa förbindelser och lär sig en kompakt ”inbäddning” för varje cell och gen i ett gemensamt lågdimensionellt rum. För dataintegration tränas modellen att rekonstruera både nätverksstrukturen och de ursprungliga genaktivitetsmönstren utan att någonsin få celltyperna angivna i förväg. För cellannotering matas samma encoder in i en uppmärksamhetsbaserad klassificerare som kan överföra kända etiketter från en referensart till mindre studerade arter.
Avslöja delade celltyper och utveckling
Författarna visar att CAMEX överträffar en rad populära verktyg när det utmanas med krävande, verkliga datamängder. I lever-, äggstocks- och pankreasdata som spänner över upp till fyra arter och flera experimentplattformar balanserade CAMEX bäst två konkurrerande mål: att ta bort konstgjorda batchskillnader samtidigt som verkliga biologiska skiljelinjer mellan celltyper bevarades. Det justerade korrekt vanliga cellpopulationer som hepatocyter och immunceller, och—viktigt—bevarade sällsynta celltyper som andra metoder tenderade att sudda ut. I ett dramatiskt test integrerade CAMEX testisdata från 11 arter, från primater till näbbdjur och kyckling. Det återfann den kontinuerliga vägen där germinalceller mognar till spermier och visade att användningen av många-till-många genrelationer är avgörande för att behålla prestanda när arter blir mer avlägsna. Modellen anpassade sig också framgångsrikt till organutvecklingsstadier över sju arter, vilket utvidgar idén om de klassiska Carnegie-utvecklingsstadierna bortom den lilla uppsättning modellorganismer för vilka de ursprungligen definierades.
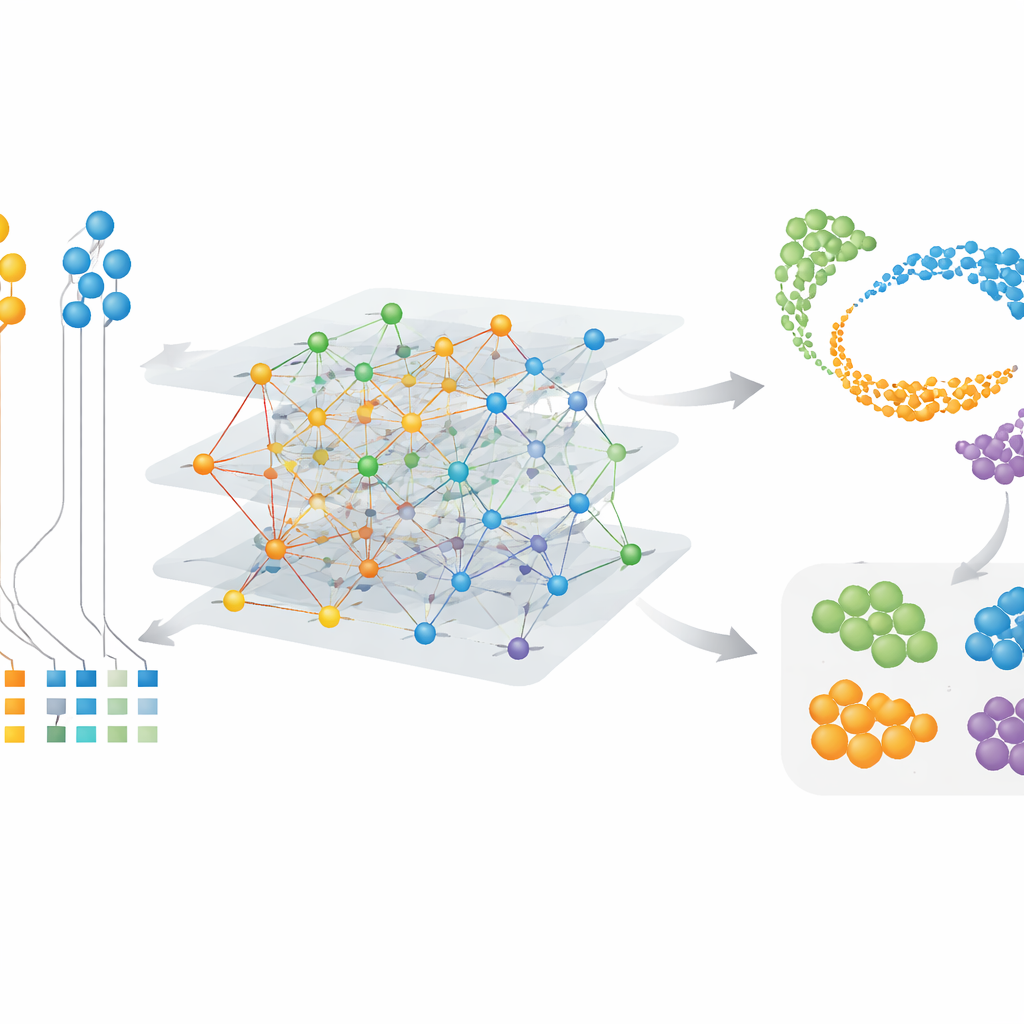
Hitta artspecifika celler och genmoduler
Eftersom CAMEX lär sig inbäddningar för både celler och gener kan det framhäva särskilda egenskaper istället för bara delade. I hjärndata som inkluderade människa, mus, ödla och sköldpadda integrerade CAMEX datan och, när det gavs mänskliga etiketter som vägledning, annoterade korrekt celltyper i de andra arterna, även små undergrupper som hjärnans pericyter hos sköldpadda. När metoden tillämpades på en detaljerad karta av primatens dorsolaterala prefrontala cortex kunde författarna isolera specifika undertyper av mikroglia—hjärnans immunceller—som endast finns hos människor eller delas med schimpanser. Genom att klustra geninbäddningarna fann de också grupper av gener kopplade till centrala funktioner: till exempel moduler aktiva i somatiska stödjeceller i testis, och andra bundna till meios, den celldelningsprocess som producerar spermier. Dessa resultat pekar på både bevarade program och artspecifika finjusteringar i cellbeteende.
Vad detta betyder för det större perspektivet
I klara ordalag är CAMEX en kraftfull ny ”översättningsmotor” för enkellssdata över livets träd. Den hjälper forskare att se när celler från olika djur i grunden utför samma uppgift, när de har avvikit, och hur utvecklingstidslinjer jämförs mellan arter. Även om metoden fortfarande har begränsningar—såsom beroendet av befintliga homologi-kartor och de generella utmaningarna med att tolka grafbaserade modeller—möjliggör den redan rikare evolutionära jämförelser än tidigare. Med tiden kan verktyg som CAMEX bidra till att bygga ett verkligt celltypers livets träd, skärpa våra modeller för organutveckling och vägleda sökandet efter sjukdomsrelevanta celltyper och läkemedelsmål både hos människor och i djurmodeller.
Citering: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Nyckelord: encells RNA-sekvensering, tvärartintegration, grafneuronala nätverk, celltypsevolution, jämförande genomik