Clear Sky Science · es
Integración, alineamiento y anotación de datos de RNA-seq unicelular entre múltiples especies con CAMEX
Por qué importa esta investigación
El cuerpo de todo animal se construye a partir de una rica variedad de tipos celulares, y aun así carecemos de un mapa claro sobre cómo se comparan estas células entre especies o cómo cambian a lo largo de la evolución. Este estudio presenta CAMEX, una herramienta computacional que ensambla datos de actividad génica a nivel unicelular de distintos animales en una imagen compartida. Para un lector no especializado, esto resulta emocionante porque nos acerca a responder preguntas como qué tipos celulares son realmente universales, cuáles son únicos en humanos y cómo órganos como el cerebro, el hígado y los testículos se formaron a lo largo del tiempo evolutivo.
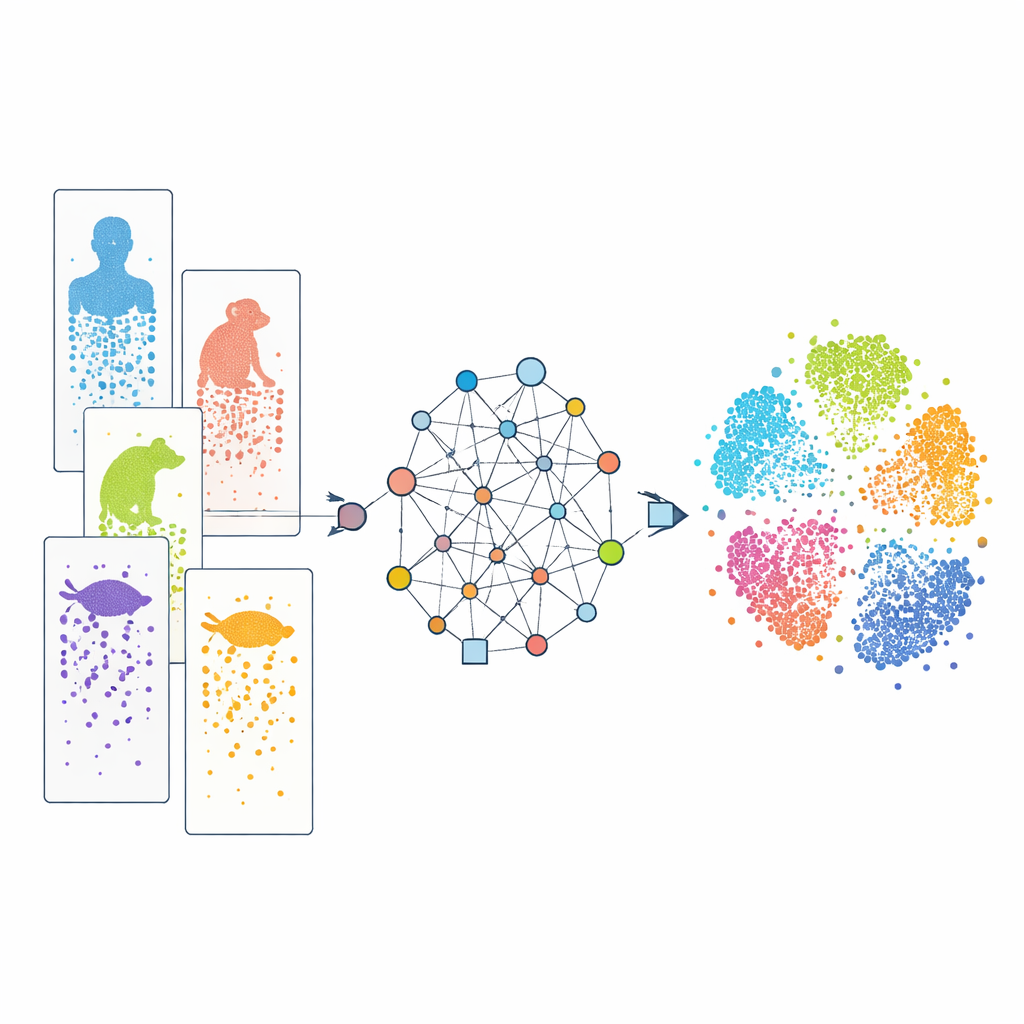
Observando las células una por una
La secuenciación de ARN unicelular moderna permite a los científicos leer qué genes están activos en miles o millones de células individuales en un solo experimento. Al comparar estos patrones, los investigadores pueden clasificar las células en tipos y rastrear cómo se desarrollan. Ahora existen muchos conjuntos de datos para humanos, monos, ratones, peces, reptiles y más. Sin embargo, cada estudio suele emplear diferentes tecnologías experimentales, y las especies varían en sus repertorios génicos. Además, nuestro conocimiento sobre los genes es desigual: los animales de laboratorio bien estudiados están mucho mejor anotados que especies poco conocidas. Estas diferencias actúan como “efectos de lote” y diccionarios incompletos, lo que dificulta alinear células similares entre especies y distinguir qué características son realmente compartidas frente a específicas de cada especie.
Una forma basada en grafos de conectar especies
CAMEX aborda estos obstáculos convirtiendo todos los datos en una única gran red que incluye tanto células como genes. En esta red, las células se conectan con los genes que expresan, con sus células vecinas más similares, y los genes se enlazan entre especies si se considera que están relacionados evolutivamente, incluso cuando la relación es muchos-a-muchos en lugar de una coincidencia uno-a-uno. Un tipo especializado de modelo de aprendizaje automático, una red neuronal de grafos heterogénea, transmite información a lo largo de estas conexiones y aprende una “incrustación” compacta para cada célula y gen en un espacio compartido de baja dimensión. Para la integración de datos, el modelo se entrena para reconstruir tanto la estructura de la red como los patrones originales de actividad génica sin que se le indiquen previamente los tipos celulares. Para la anotación celular, el mismo codificador alimenta un clasificador basado en atención que puede transferir etiquetas conocidas de una especie de referencia a otras menos estudiadas.
Revelando tipos celulares y desarrollo compartidos
Los autores muestran que CAMEX supera a una batería de herramientas populares cuando se le desafía con conjuntos de datos exigentes y del mundo real. En datos de hígado, ovario y páncreas que abarcan hasta cuatro especies y múltiples plataformas experimentales, CAMEX equilibró mejor dos objetivos en competencia: eliminar diferencias artificiales de lote manteniendo las verdaderas distinciones biológicas entre tipos celulares. Alineó con precisión poblaciones celulares comunes como hepatocitos y células inmunes y, lo que es importante, preservó tipos celulares raros que otros métodos tendían a difuminar. En una prueba llamativa, CAMEX integró datos de testículo de 11 especies, desde primates hasta ornitorrinco y gallina. Recuperó la trayectoria continua por la que las células germinales maduran hasta convertirse en espermatozoides y mostró que el uso de relaciones génicas muchos-a-muchos es crucial para mantener el rendimiento a medida que las especies se vuelven más distantes. El modelo también alineó con éxito etapas del desarrollo de órganos en siete especies, extendiendo la idea de las clásicas etapas de Carnegie más allá del pequeño conjunto de organismos modelo para los que se definieron originalmente.
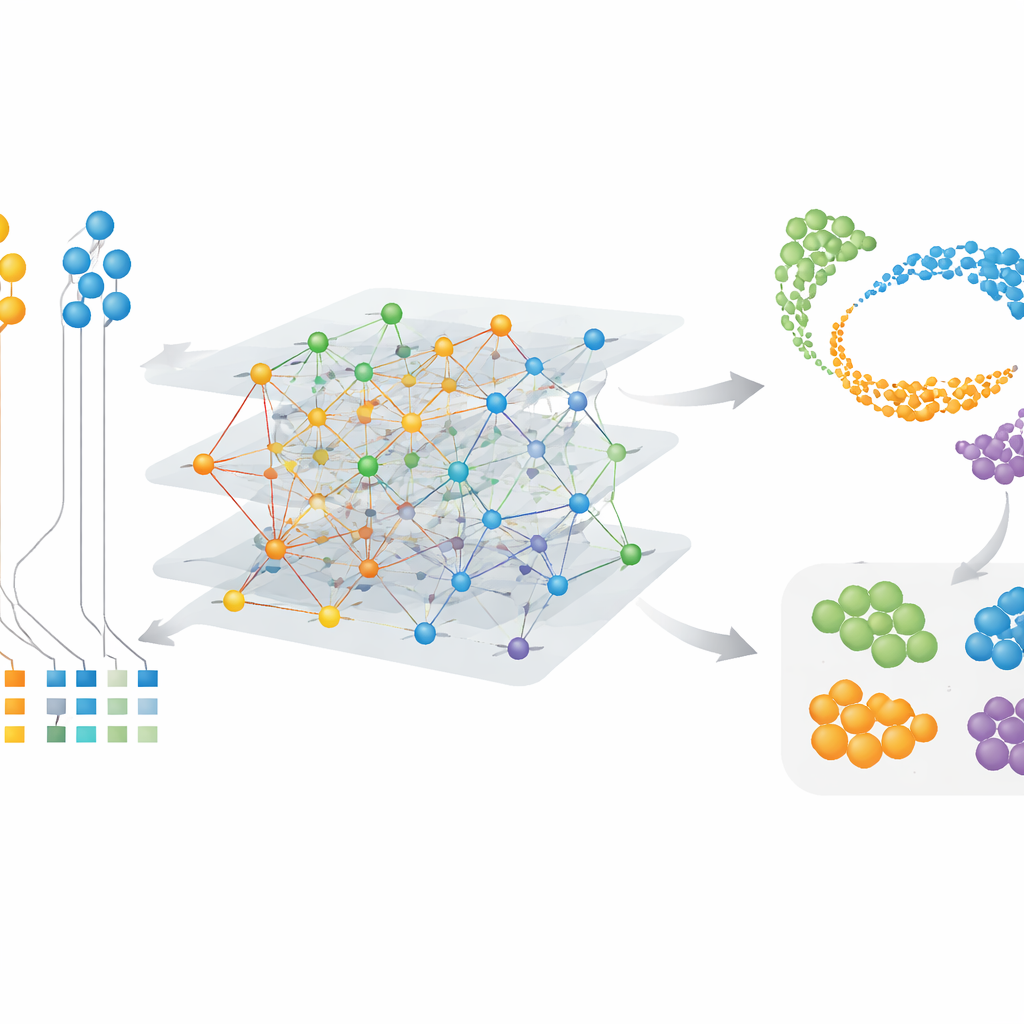
Encontrar células y módulos génicos específicos de cada especie
Puesto que CAMEX aprende incrustaciones tanto para células como para genes, puede destacar características especiales además de las compartidas. En conjuntos de datos cerebrales que incluían humano, ratón, lagarto y tortuga, CAMEX integró los datos y, al usar etiquetas humanas como guía, anotó con precisión tipos celulares en las otras especies, incluso subgrupos pequeños como pericitos cerebrales en tortuga. Aplicando el método a un mapa detallado de la corteza prefrontal dorsolateral de primates, los autores pudieron aislar subtipos específicos de microglía—células inmunes del cerebro—que están presentes solo en humanos o compartidos con chimpancés. Al agrupar las incrustaciones génicas, también encontraron conjuntos de genes vinculados a funciones clave: por ejemplo, módulos activos en células de soporte somático en el testículo y otros ligados a la meiosis, el proceso de división celular que produce espermatozoides. Estos resultados apuntan tanto a programas conservados como a ajustes específicos de especie en el comportamiento celular.
Qué significa esto para el panorama general
En términos sencillos, CAMEX es un potente nuevo “motor de traducción” para datos unicelulares a lo largo del árbol de la vida. Ayuda a los científicos a ver cuándo células de diferentes animales realizan esencialmente la misma función, cuándo han divergido y cómo se comparan las líneas temporales del desarrollo entre especies. Si bien el método aún tiene limitaciones—como depender de mapas de homología existentes y los desafíos generales de interpretar modelos basados en grafos—ya permite comparaciones evolutivas más ricas de lo que era posible antes. Con el tiempo, herramientas como CAMEX podrían ayudar a construir un auténtico árbol de la vida de los tipos celulares, afinar nuestros modelos del desarrollo de órganos y guiar la búsqueda de tipos celulares relevantes para enfermedades y dianas farmacológicas tanto en humanos como en modelos animales.
Cita: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Palabras clave: secuenciación de ARN unicelular, integración entre especies, redes neuronales basadas en grafos, evolución de tipos celulares, genómica comparativa