Clear Sky Science · fr
Intégration, alignement et annotation multi-espèces des données d’ARN-seq unicellulaire avec CAMEX
Pourquoi cette recherche est importante
Chaque organisme animal est construit à partir d’un riche ensemble de types cellulaires, et pourtant nous ne disposons toujours pas d’une cartographie claire de la façon dont ces cellules se comparent entre espèces ni de leur évolution. Cette étude présente CAMEX, un outil computationnel qui assemble des données d’activité génique unicellulaire provenant de nombreux animaux en une représentation commune. Pour un lecteur non spécialisé, c’est enthousiasmant car cela nous rapproche de réponses à des questions telles que quels types cellulaires sont véritablement universels, lesquels sont propres à l’humain, et comment des organes comme le cerveau, le foie ou les testicules se sont formés au cours de l’évolution.
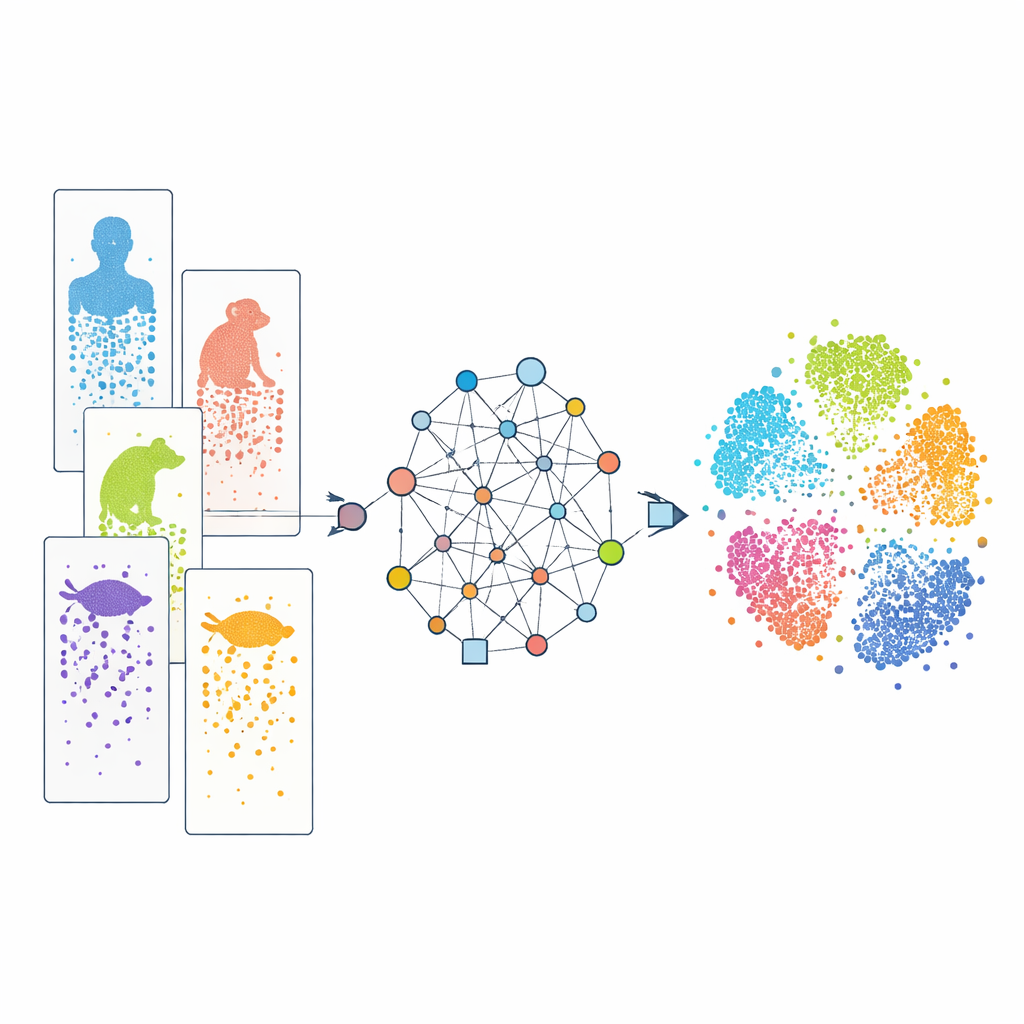
Examiner les cellules une par une
Le séquençage d’ARN unicellulaire moderne permet aux scientifiques de lire quels gènes sont actifs dans des milliers à des millions de cellules individuelles au cours d’une seule expérience. En comparant ces profils, les chercheurs peuvent classer les cellules par type et suivre leur développement. De nombreux jeux de données existent désormais pour l’humain, le singe, la souris, le poisson, le reptile, et d’autres. Cependant, chaque étude utilise souvent des technologies expérimentales différentes et les espèces diffèrent par leurs ensembles de gènes. De plus, notre connaissance des gènes est inégale : les animaux de laboratoire bien étudiés sont beaucoup mieux annotés que des espèces peu connues. Ces différences agissent comme des « effets de lot » et des dictionnaires incomplets, rendant difficile l’alignement de cellules similaires entre espèces et la distinction entre caractéristiques réellement partagées et spécificités d’une espèce.
Une approche par graphe pour relier les espèces
CAMEX contourne ces obstacles en transformant l’ensemble des données en un grand réseau unique qui inclut à la fois les cellules et les gènes. Dans ce réseau, les cellules sont reliées aux gènes qu’elles expriment, à leurs voisines cellulaires les plus similaires, et les gènes sont liés entre espèces lorsqu’ils sont considérés comme apparentés évolutivement, même quand la relation est many-to-many plutôt qu’un simple appariement un-à-un. Un type spécialisé de modèle d’apprentissage automatique, un réseau de neurones graphe hétérogène, transmet ensuite l’information le long de ces connexions et apprend une « représentation » compacte pour chaque cellule et chaque gène dans un espace partagé de basse dimension. Pour l’intégration des données, le modèle est entraîné à reconstruire à la fois la structure du réseau et les profils d’activité génique originaux sans jamais recevoir au préalable les types cellulaires. Pour l’annotation des cellules, le même encodeur alimente un classifieur basé sur l’attention capable de transférer des étiquettes connues d’une espèce de référence vers des espèces moins étudiées.
Révéler des types cellulaires et des développements partagés
Les auteurs montrent que CAMEX surpasse un ensemble d’outils populaires lorsqu’il est confronté à des jeux de données exigeants et représentatifs du monde réel. Sur des données de foie, d’ovaire et de pancréas couvrant jusqu’à quatre espèces et plusieurs plateformes expérimentales, CAMEX a le mieux concilié deux objectifs concurrents : supprimer les différences artificielles de lot tout en préservant les distinctions biologiques réelles entre types cellulaires. Il a aligné avec précision des populations cellulaires communes telles que les hépatocytes et les cellules immunitaires et, fait important, a préservé des types cellulaires rares que d’autres méthodes avaient tendance à estomper. Dans un test spectaculaire, CAMEX a intégré des données de testicule de 11 espèces, des primates à l’ornithorynque et au poulet. Il a retrouvé le parcours continu par lequel les cellules germinales mûrissent en spermatozoïdes et montré que l’utilisation de relations géniques many-to-many est cruciale pour maintenir les performances à mesure que les espèces s’éloignent. Le modèle a aussi aligné avec succès des stades de développement d’organes sur sept espèces, étendant l’idée classique des stades de Carnegie au-delà du petit ensemble d’organismes modèles pour lesquels ils avaient été définis à l’origine.
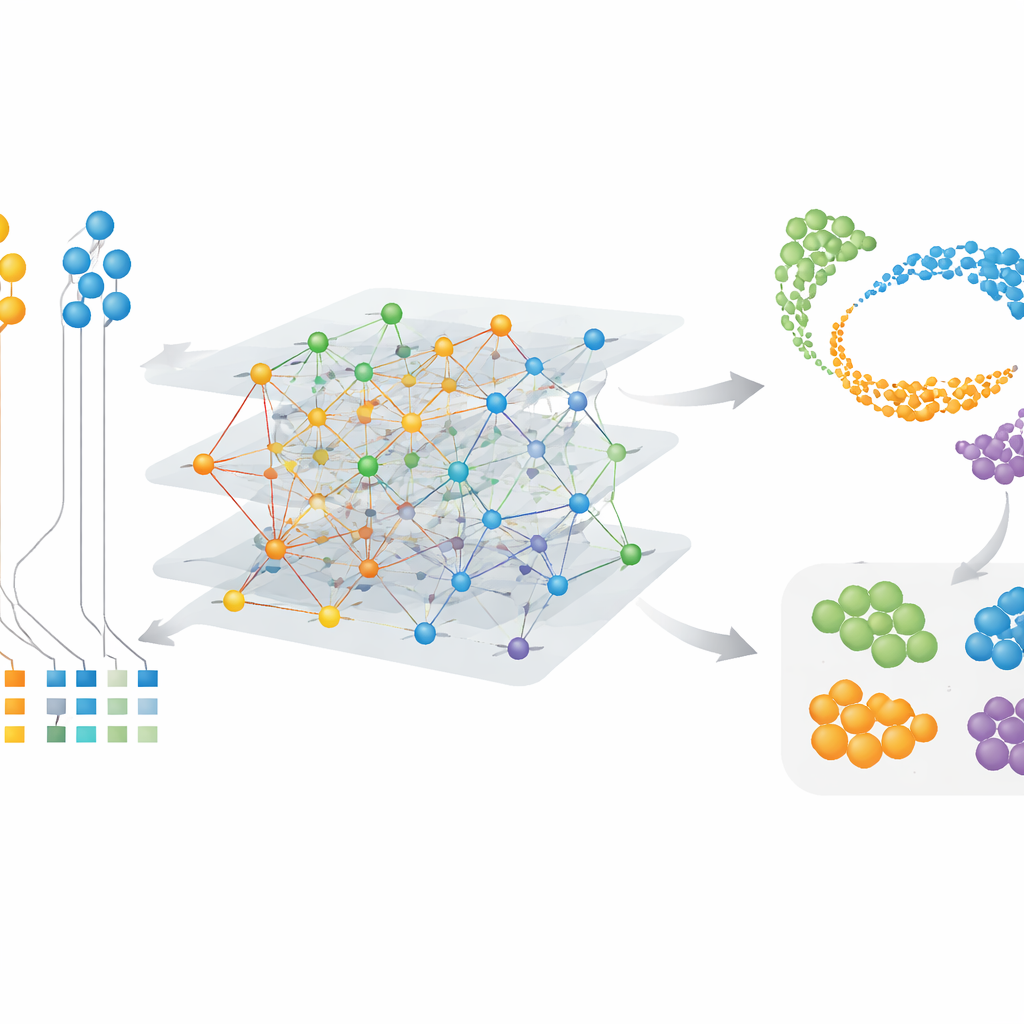
Identifier des cellules et modules géniques spécifiques à une espèce
Parce que CAMEX apprend des représentations à la fois pour les cellules et pour les gènes, il peut mettre en évidence des caractéristiques particulières et pas seulement les traits partagés. Dans des jeux de données cérébraux incluant l’humain, la souris, le lézard et la tortue, CAMEX a intégré les données et, guidé par des annotations humaines, a annoté avec précision les types cellulaires des autres espèces, y compris de petits sous-groupes comme les péricytes cérébraux chez la tortue. Appliquée à une carte détaillée du cortex préfrontal dorsolatéral des primates, la méthode a permis d’isoler des sous-types spécifiques de microglies — cellules immunitaires du cerveau — présents uniquement chez l’humain ou partagés avec le chimpanzé. En clusterisant les représentations des gènes, les auteurs ont aussi identifié des groupes de gènes liés à des fonctions clés : par exemple des modules actifs dans les cellules de soutien somatique du testicule, et d’autres liés à la méiose, le processus de division cellulaire qui produit les spermatozoïdes. Ces résultats indiquent à la fois des programmes conservés et des ajustements spécifiques aux espèces dans le comportement cellulaire.
Ce que cela signifie pour la perspective générale
En termes simples, CAMEX est un nouveau « moteur de traduction » puissant pour les données unicellulaires à travers l’arbre de la vie. Il aide les scientifiques à déterminer quand des cellules d’animaux différents remplissent essentiellement la même fonction, quand elles ont divergé, et comment les chronologies du développement se comparent entre espèces. Bien que la méthode ait encore des limites — comme sa dépendance aux cartes d’homologie existantes et les défis généraux d’interprétation des modèles basés sur des graphes — elle permet déjà des comparaisons évolutives plus riches qu’auparavant. Avec le temps, des outils comme CAMEX pourraient contribuer à construire un véritable arbre de vie des types cellulaires, affiner nos modèles du développement des organes et orienter la recherche de types cellulaires et de cibles médicamenteuses pertinents pour les maladies chez l’homme et chez les modèles animaux.
Citation: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Mots-clés: séquençage d’ARN unicellulaire, intégration inter-espèces, réseaux de neurones graphe, évolution des types cellulaires, génomique comparative