Clear Sky Science · de
Multi-Spezies-Integration, Ausrichtung und Annotation von Einzelzell-RNA-seq-Daten mit CAMEX
Warum diese Forschung wichtig ist
Jeder tierische Körper besteht aus einer Vielzahl unterschiedlicher Zelltypen, und dennoch fehlt uns noch eine klare Landkarte dafür, wie diese Zellen zwischen Arten vergleichbar sind oder sich im Lauf der Evolution verändert haben. Diese Studie stellt CAMEX vor, ein rechnerisches Werkzeug, das Einzelzell-Genaktivitätsdaten vieler verschiedener Tiere zu einem gemeinsamen Bild zusammenfügt. Für Leser ohne Fachhintergrund ist das spannend, weil es uns näher daran bringt, Fragen zu beantworten wie: Welche Zelltypen sind wirklich universell, welche sind für den Menschen einzigartig, und wie haben sich Organe wie Gehirn, Leber und Hoden im Verlauf der Evolution geformt?
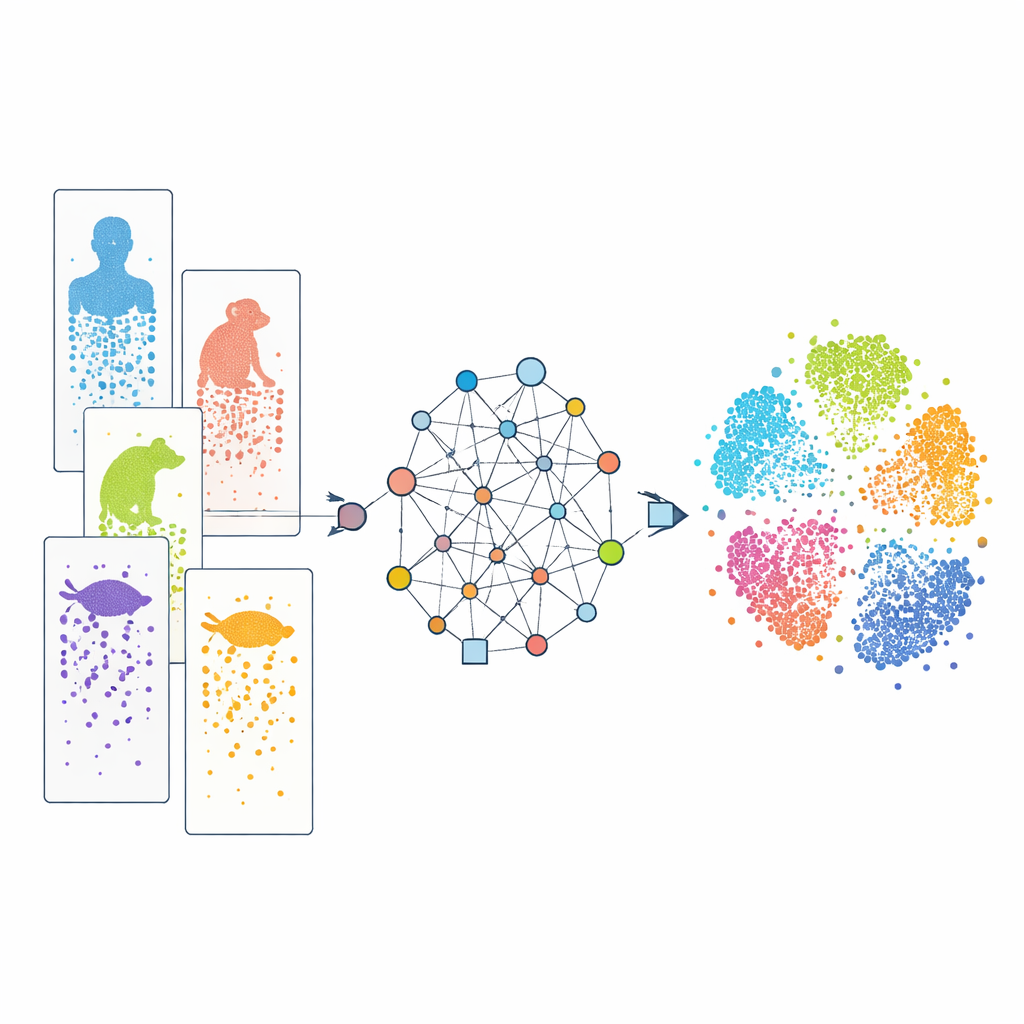
Zellen einzeln betrachten
Moderne Einzelzell-RNA-Sequenzierung erlaubt es Wissenschaftlern, in Tausenden bis Millionen einzelner Zellen eines Experiments nachzulesen, welche Gene aktiv sind. Durch den Vergleich dieser Muster können Forschende Zellen in Typen einordnen und ihre Entwicklung verfolgen. Viele solcher Datensätze existieren inzwischen für Menschen, Affen, Mäuse, Fische, Reptilien und mehr. Allerdings verwendeten die Studien häufig unterschiedliche experimentelle Technologien, und die Arten unterscheiden sich in ihren Genmengen. Hinzu kommt, dass unser Wissen über Gene ungleich verteilt ist: gut untersuchte Labortiere sind wesentlich besser annotiert als wenig bekannte Arten. Diese Unterschiede wirken wie „Batch-Effekte“ und unvollständige Wörterbücher, was das Abgleichen ähnlicher Zellen über Arten hinweg erschwert und es schwierig macht zu erkennen, welche Merkmale wirklich geteilt oder artspezifisch sind.
Ein graphbasierter Weg, Arten zu verknüpfen
CAMEX begegnet diesen Herausforderungen, indem es alle Daten in ein einziges großes Netzwerk überführt, das sowohl Zellen als auch Gene umfasst. In diesem Netzwerk sind Zellen mit den Genen verbunden, die sie exprimieren, mit ihren ähnlichsten Nachbarzellen, und Gene werden über Arten hinweg verknüpft, wenn sie evolutionär verwandt erscheinen — auch wenn diese Beziehungen viele-zu-viele statt eins-zu-eins sind. Ein spezialisierter Maschineller-Lern-Ansatz, ein heterogener graphneurales Netzwerk, leitet dann Informationen entlang dieser Verbindungen weiter und lernt eine kompakte „Einbettung“ (Embedding) für jede Zelle und jedes Gen in einem gemeinsamen, niedrigdimensionalen Raum. Für die Datenintegration wird das Modell so trainiert, dass es sowohl die Netzwerkstruktur als auch die ursprünglichen Genaktivitätsmuster rekonstruiert, ohne dass ihm die Zelltypen im Voraus genannt werden. Für die Zellannotation speist derselbe Encoder ein auf Aufmerksamkeit basierendes Klassifikationsmodell, das bekannte Labels von einer Referenzart auf weniger gut untersuchte Arten übertragen kann.
Gemeinsame Zelltypen und Entwicklung aufdecken
Die Autoren zeigen, dass CAMEX eine Reihe populärer Werkzeuge übertrifft, wenn es mit anspruchsvollen, realen Datensätzen konfrontiert wird. In Leber-, Eierstock- und Pankreasdaten, die bis zu vier Arten und mehrere experimentelle Plattformen umfassen, fand CAMEX die beste Balance zwischen zwei konkurrierenden Zielen: künstliche Batch-Unterschiede zu entfernen und gleichzeitig echte biologische Unterschiede zwischen Zelltypen zu bewahren. Es richtete häufige Zellpopulationen wie Hepatozyten und Immunzellen akkurat aus und erhielt, wichtig, auch seltene Zelltypen, die andere Methoden oft verwischen. In einem eindrücklichen Test integrierte CAMEX Hodendaten aus 11 Arten, von Primaten bis Schnabeltier und Huhn. Es rekonstruierte den kontinuierlichen Pfad, auf dem Keimzellen zu Spermien reifen, und zeigte, dass die Modellierung viele-zu-viele-Genbeziehungen entscheidend ist, um die Leistung zu erhalten, wenn die Arten weiter auseinander liegen. Das Modell richtete außerdem Organentwicklungsstadien über sieben Arten aus und erweiterte damit die Idee der klassischen Carnegie-Entwicklungsstadien über die kleine Gruppe von Modellorganismen hinaus, für die sie ursprünglich definiert wurden.
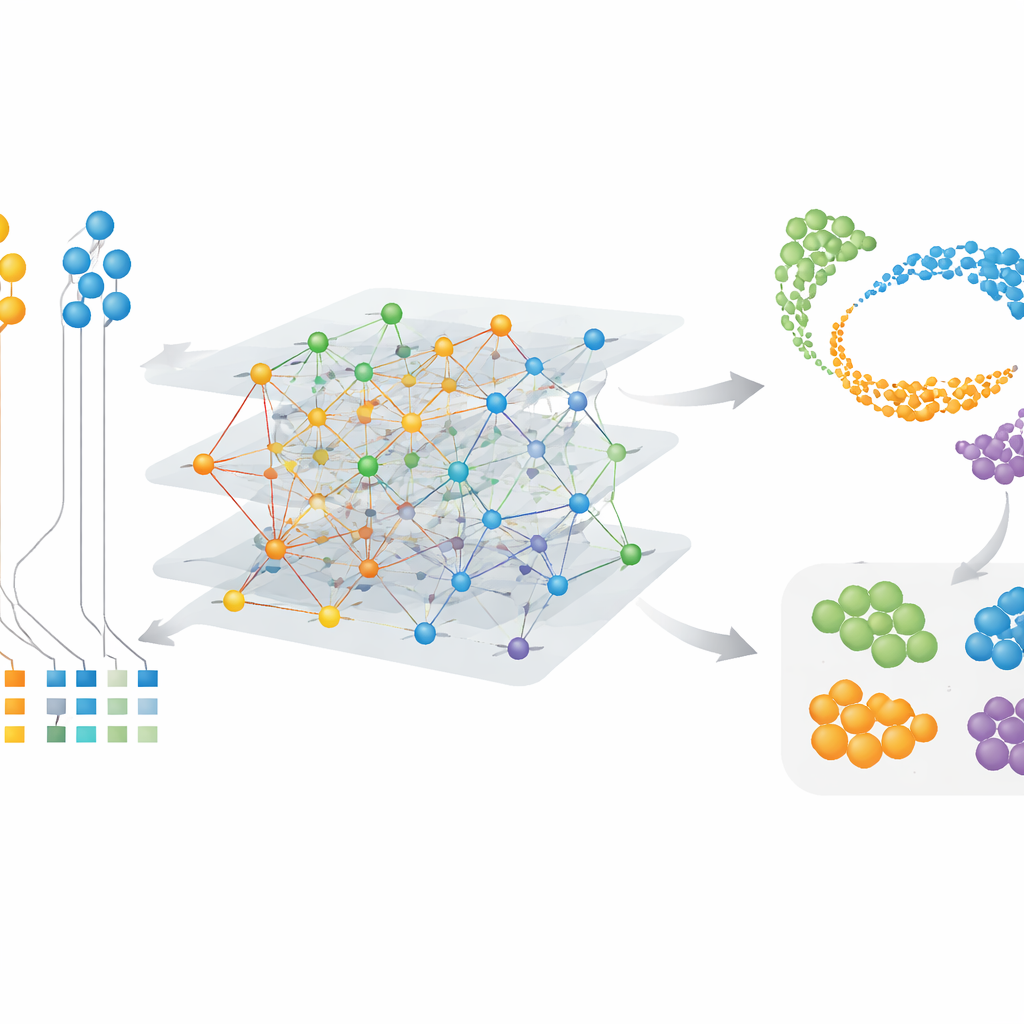
Artspezifische Zellen und Genmodule finden
Weil CAMEX Einbettungen sowohl für Zellen als auch für Gene lernt, kann es besondere Merkmale hervorheben und nicht nur gemeinsame. In Gehirndatensätzen, die Mensch, Maus, Eidechse und Schildkröte einschlossen, integrierte CAMEX die Daten und annotierte unter Anleitung menschlicher Labels Zelltypen in den anderen Arten akkurat, sogar kleine Untergruppen wie Gehirn-Perizyten in der Schildkröte. Bei Anwendung der Methode auf eine detaillierte Karte des dorsolateralen präfrontalen Kortex von Primaten konnten die Autoren spezifische Microglia-Subtypen isolieren — Immunzellen des Gehirns —, die nur beim Menschen oder gemeinsam mit Schimpansen vorkommen. Durch Clustering der Gen-Embeddings fanden sie außerdem Gencluster, die mit Schlüsselaufgaben verknüpft sind: etwa Module, die in somatischen Stütz-Zellen im Hoden aktiv sind, und andere, die mit der Meiose verbunden sind, dem Zellteilungsprozess, der Spermien erzeugt. Diese Ergebnisse deuten sowohl auf konservierte Programme als auch auf artspezifische Feinabstimmungen im Zellverhalten hin.
Was das für das größere Bild bedeutet
Einfach gesagt ist CAMEX eine leistungsfähige neue „Übersetzungsmaschine“ für Einzelzelldaten über den Stammbaum des Lebens hinweg. Sie hilft Forschenden zu erkennen, wann Zellen verschiedener Tiere im Wesentlichen die gleiche Funktion ausüben, wann sie sich auseinanderentwickelt haben und wie Entwicklungszeitlinien zwischen Arten vergleichbar sind. Während die Methode noch Einschränkungen hat — etwa die Abhängigkeit von bestehenden Homologiekarten und die allgemeinen Herausforderungen bei der Interpretation graphbasierter Modelle — ermöglicht sie bereits jetzt reichhaltigere evolutionäre Vergleiche als zuvor. Im Laufe der Zeit könnten Werkzeuge wie CAMEX dazu beitragen, einen echten Zelltyp-Stammbaum des Lebens zu erstellen, unsere Modelle der Organentwicklung zu schärfen und die Suche nach krankheitsrelevanten Zelltypen und Wirkstoffzielen sowohl beim Menschen als auch in Tiermodellen zu leiten.
Zitation: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Schlüsselwörter: Einzelzell-RNA-Sequenzierung, Artübergreifende Integration, Graphneurale Netzwerke, Zellentwicklung und Evolution, vergleichende Genomik