Clear Sky Science · nl
Integratie, uitlijning en annotatie van single-cell RNA-seq data over meerdere soorten met CAMEX
Waarom dit onderzoek ertoe doet
Ieder dierenlichaam bestaat uit een rijke verzameling celtypen, maar we hebben nog geen duidelijk overzicht van hoe deze cellen tussen soorten vergelijkbaar zijn of hoe ze tijdens de evolutie veranderen. Deze studie introduceert CAMEX, een computationeel hulpmiddel dat single-cell-genactiviteitsdata van veel verschillende dieren samenvoegt tot een gedeeld beeld. Voor een algemene lezer is dit bijzonder omdat het ons dichter bij antwoorden brengt op vragen zoals welke celtypen werkelijk universeel zijn, welke uniek voor de mens zijn, en hoe organen zoals hersenen, lever en testis zich over evolutionaire tijd hebben gevormd.
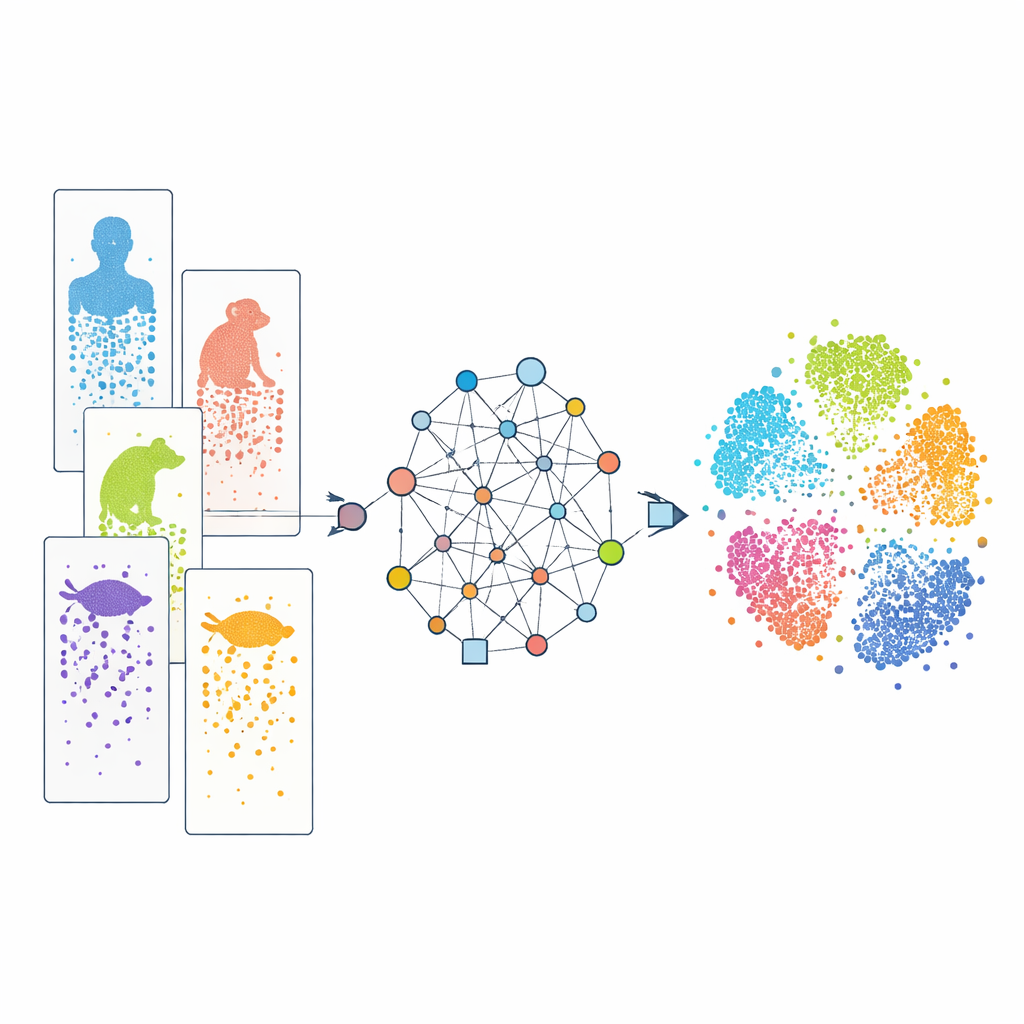
Cellen één voor één bekijken
Moderne single-cell RNA-sequencing stelt onderzoekers in staat om af te lezen welke genen actief zijn in duizenden tot miljoenen individuele cellen in één experiment. Door deze patronen te vergelijken, kunnen onderzoekers cellen indelen in typen en volgen hoe ze zich ontwikkelen. Veel van dergelijke datasets bestaan inmiddels voor mensen, apen, muizen, vissen, reptielen en meer. Elk onderzoek gebruikt echter vaak andere experimentele technologieën, en soorten verschillen in hun genenpakketten. Bovendien is onze kennis van genen ongelijk verdeeld: goed bestudeerde laboratoriumdieren zijn veel beter geannoteerd dan obscure soorten. Deze verschillen werken als ‘batch-effecten’ en onvolledige woordenboeken, waardoor het lastig is om vergelijkbare cellen over soorten heen op één lijn te krijgen en vast te stellen welke kenmerken echt gedeeld of juist soort-specifiek zijn.
Een grafgebaseerde manier om soorten te verbinden
CAMEX pakt deze obstakels aan door alle data om te zetten in één groot netwerk dat zowel cellen als genen bevat. In dit netwerk verbinden cellen zich met de genen die ze tot expressie brengen, met hun meest vergelijkbare naburige cellen, en genen worden over soorten heen gekoppeld als ze evolutionair gerelateerd worden geacht, zelfs wanneer die relatie veel-op-veel is in plaats van één-op-één. Een gespecialiseerd type machine learning-model, een heterogeen graf-neuraal netwerk, geeft vervolgens informatie door langs deze verbindingen en leert een compacte “embedding” voor elke cel en elk gen in een gedeelde laag-dimensionale ruimte. Voor data-integratie wordt het model getraind om zowel de netwerkstructuur als de oorspronkelijke genactiviteitspatronen te reconstrueren zonder vooraf celtypen te krijgen. Voor celannotatie voedt dezelfde encoder een op aandacht gebaseerde classifier die bekende labels van een referentiesoort naar minder bestudeerde soorten kan overdragen.
Gedeelde celtypen en ontwikkeling blootleggen
De auteurs tonen aan dat CAMEX beter presteert dan een reeks populaire tools wanneer het wordt uitgedaagd met veeleisende, realistische datasets. In lever-, eierstok- en alvleesklierdata die tot vier soorten en meerdere experimentele platformen beslaan, vond CAMEX de beste balans tussen twee concurrerende doelen: het verwijderen van kunstmatige batchverschillen terwijl ware biologische verschillen tussen celtypen behouden blijven. Het zette veelvoorkomende celpopulaties zoals hepatocyten en immuuncellen nauwkeurig op één lijn en, belangrijker, behield zeldzame celtypen die andere methoden vaak vervaagden. In een indrukwekkende test integreerde CAMEX testisdata uit 11 soorten, van primaten tot vogelbekdier en kip. Het herstelde het continue pad waarmee kiemcellen rijpen tot zaadcellen en liet zien dat het gebruik van veel-op-veel genrelaties cruciaal is om prestaties te behouden naarmate soorten verder uit elkaar liggen. Het model bracht ook met succes orgaanontwikkelingsstadia op één lijn over zeven soorten, waarmee het idee van klassieke Carnegie-ontwikkelingsstadia uitbreidt voorbij de kleine set modelorganismen waarvoor ze oorspronkelijk waren gedefinieerd.
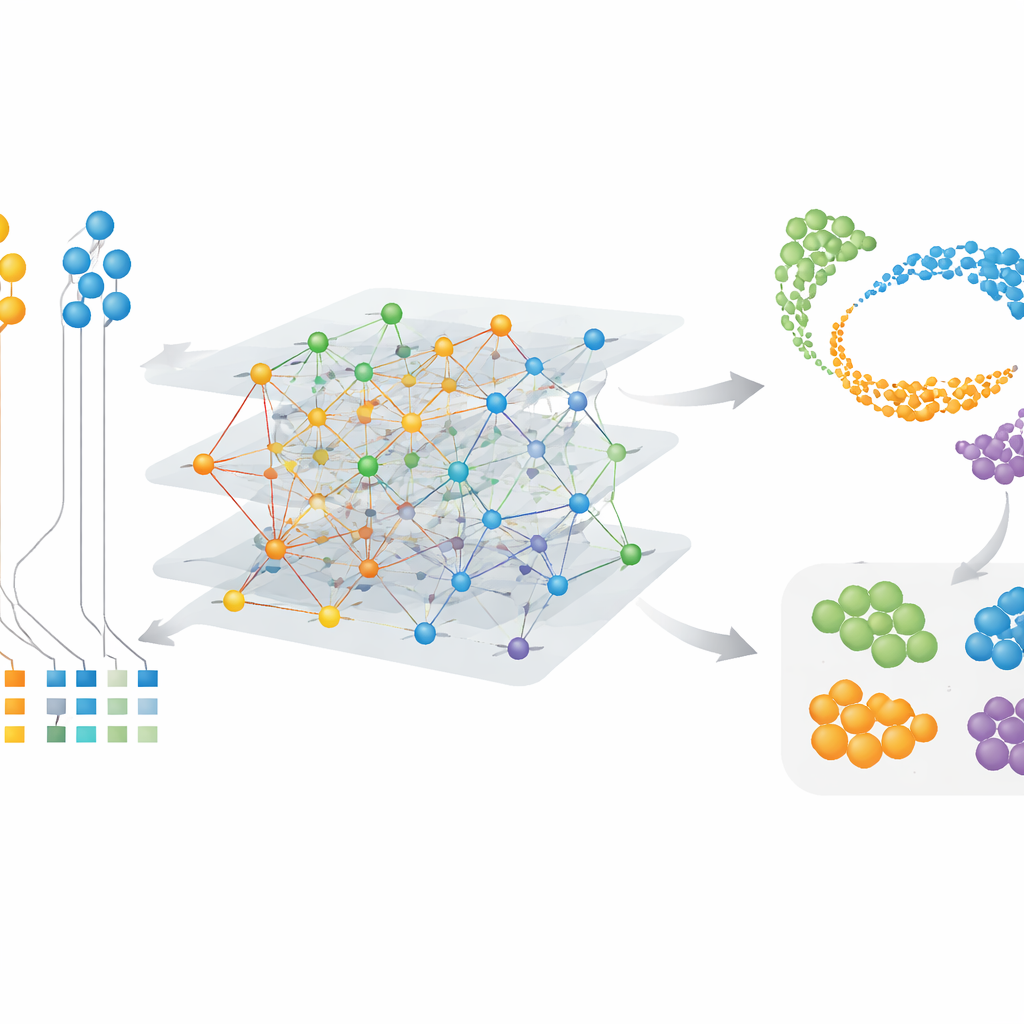
Soortspecifieke cellen en genmodules vinden
Omdat CAMEX embeddings leert voor zowel cellen als genen, kan het bijzondere kenmerken benadrukken in plaats van alleen gedeelde. In hersendatasets met mens, muis, hagedis en schildpad integreerde CAMEX de data en annoteerde het, wanneer menselijke labels als gids werden gebruikt, celtypen nauwkeurig in de andere soorten, zelfs kleine subgroepen zoals hersenpericyten bij schildpad. Toegepast op een gedetailleerde kaart van de primaten dorsolaterale prefrontale cortex konden de auteurs specifieke subtypes van microglia—immuuncellen in de hersenen—isoleren die alleen bij mensen voorkomen of gedeeld worden met chimpansees. Door de gen-embeddings te clusteren vonden ze ook groepen genen die aan sleutelprocessen gekoppeld zijn: bijvoorbeeld modules actief in somatische ondersteunende cellen in de testis, en andere verbonden aan meiose, het celdelingsproces dat spermatozoa produceert. Deze resultaten wijzen op zowel bewaarde programma’s als soortspecifieke aanpassingen in celgedrag.
Wat dit betekent voor het grotere geheel
Simpel gezegd is CAMEX een krachtig nieuw “vertalingsmechanisme” voor single-cell-data over de levensboom. Het helpt wetenschappers te zien wanneer cellen van verschillende dieren in wezen dezelfde taak uitvoeren, wanneer ze zijn gedivergeerd, en hoe ontwikkelingstijdlijnen tussen soorten te vergelijken zijn. Hoewel de methode nog beperkingen heeft—zoals de afhankelijkheid van bestaande homologiemaps en de algemene uitdagingen bij het interpreteren van grafgebaseerde modellen—maakt het al rijkere evolutionaire vergelijkingen mogelijk dan voorheen. In de loop van de tijd zouden tools als CAMEX kunnen bijdragen aan het opbouwen van een echte celtype-boom des levens, onze modellen van orgaanontwikkeling aanscherpen en de zoektocht naar ziekte-relevante celtypen en medicijndoelen in zowel mensen als diermodellen sturen.
Bronvermelding: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Trefwoorden: single-cell RNA-sequencing, integratie tussen soorten, graf-neurale netwerken, celtype-evolutie, vergelijkende genomica