Clear Sky Science · pt
Integração, alinhamento e anotação multiespécies de dados de RNA-seq de célula única com CAMEX
Por que esta pesquisa importa
Todo corpo animal é composto por um elenco variado de tipos celulares, mas ainda não disponhamos de um mapa claro de como essas células se comparam entre espécies ou mudam ao longo da evolução. Este estudo apresenta o CAMEX, uma ferramenta computacional que costura dados de atividade gênica em células únicas de muitos animais diferentes em uma imagem compartilhada. Para o leitor leigo, isso é empolgante porque nos aproxima de responder perguntas como quais tipos celulares são verdadeiramente universais, quais são exclusivos dos humanos e como órgãos como cérebro, fígado e testículos se formaram ao longo do tempo evolutivo.
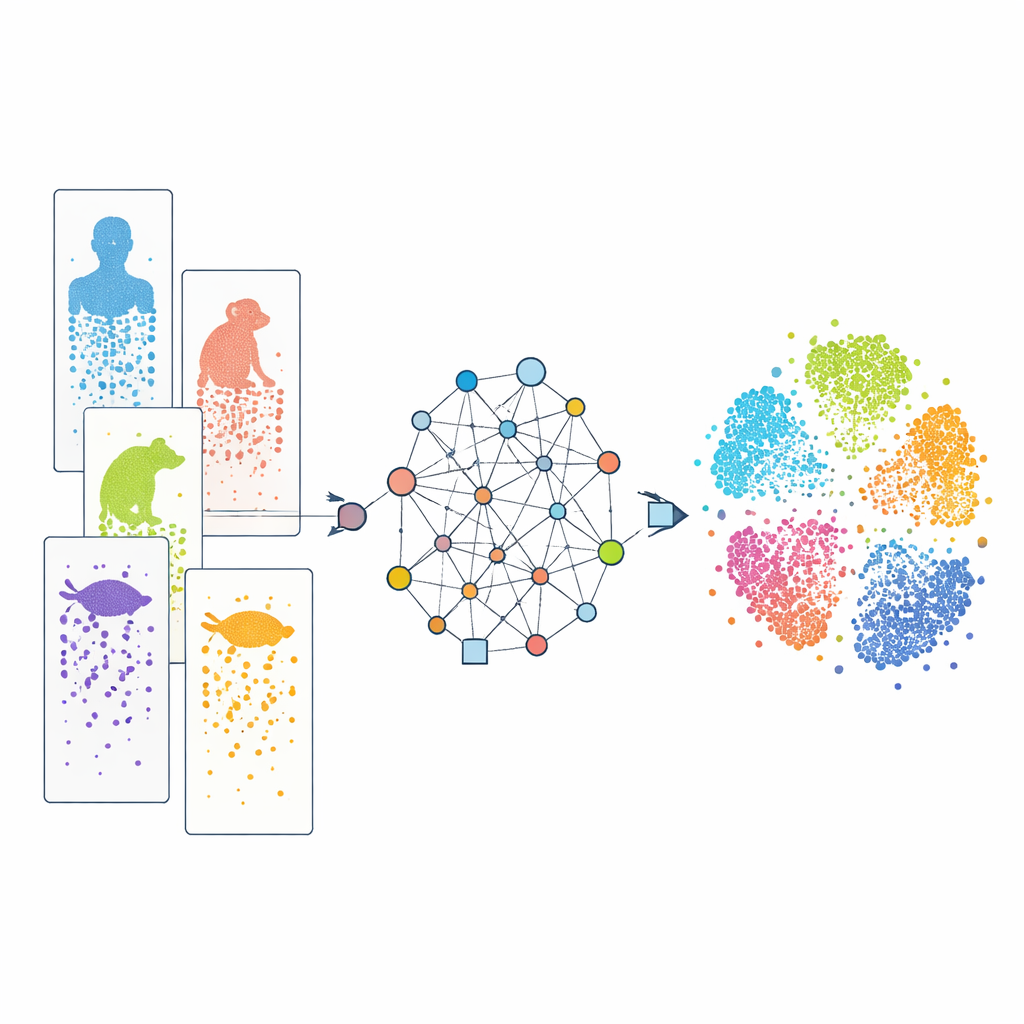
Observando as células uma a uma
O sequenciamento moderno de RNA de célula única permite aos cientistas ler quais genes estão ativos em milhares a milhões de células individuais em um único experimento. Comparando esses padrões, os pesquisadores podem classificar células em tipos e rastrear como elas se desenvolvem. Muitos desses conjuntos de dados agora existem para humanos, macacos, camundongos, peixes, répteis e outros. No entanto, cada estudo frequentemente usa tecnologias experimentais diferentes, e as espécies variam em seus conjuntos de genes. Além disso, nosso conhecimento sobre genes é desigual: animais de laboratório bem estudados são muito melhor anotados do que espécies obscuras. Essas diferenças atuam como “efeitos de lote” e dicionários incompletos, tornando difícil alinhar células semelhantes entre espécies e ver quais características são realmente compartilhadas versus específicas de uma espécie.
Uma abordagem baseada em grafos para conectar espécies
O CAMEX enfrenta esses obstáculos transformando todos os dados em uma única rede grande que inclui tanto células quanto genes. Nessa rede, células se conectam aos genes que expressam, às suas células vizinhas mais semelhantes, e genes são ligados entre espécies se forem considerados relacionados por evolução, mesmo quando a relação é muitos-para-muitos em vez de um simples correspondência um-para-um. Um tipo especializado de modelo de aprendizado de máquina, uma rede neural em grafo heterogênea, então propaga informação ao longo dessas conexões e aprende uma “embedding” compacta para cada célula e gene em um espaço compartilhado de baixa dimensionalidade. Para integração de dados, o modelo é treinado para reconstruir tanto a estrutura da rede quanto os padrões originais de atividade gênica sem nunca ser informado sobre os tipos celulares antecipadamente. Para anotação celular, o mesmo codificador alimenta um classificador baseado em atenção que pode transferir rótulos conhecidos de uma espécie de referência para espécies menos estudadas.
Revelando tipos celulares e desenvolvimento compartilhados
Os autores mostram que o CAMEX supera um conjunto de ferramentas populares quando desafiado com conjuntos de dados reais e exigentes. Em dados de fígado, ovário e pâncreas abrangendo até quatro espécies e múltiplas plataformas experimentais, o CAMEX equilibrou melhor dois objetivos concorrentes: remover diferenças artificiais de lote enquanto mantém distinções biológicas reais entre tipos celulares. Alinhou com precisão populações celulares comuns como hepatócitos e células imunes e, o que é importante, preservou tipos celulares raros que outros métodos tendiam a borrar. Em um teste dramático, o CAMEX integrou dados de testículo de 11 espécies, de primatas a ornitorrinco e galinha. Recuperou o caminho contínuo pelo qual as células germinativas amadurecem em espermatozoides e mostrou que usar relações gênicas muitos-para-muitos é crucial para manter o desempenho conforme as espécies se tornam mais distantes. O modelo também alinhou com sucesso estágios de desenvolvimento de órgãos em sete espécies, estendendo a ideia dos clássicos estágios desenvolvimentais de Carnegie além do pequeno conjunto de organismos modelo para os quais eles foram originalmente definidos.
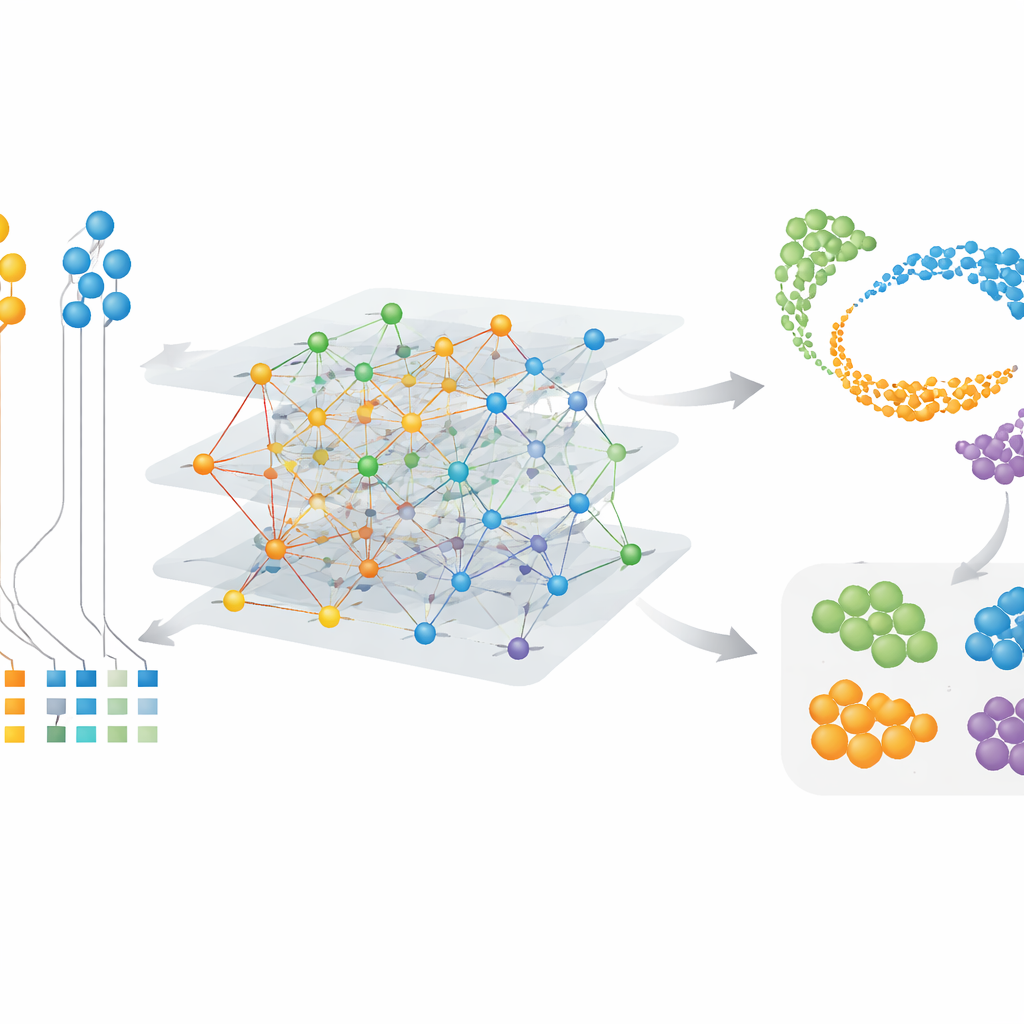
Encontrando células e módulos gênicos específicos de espécies
Como o CAMEX aprende embeddings tanto para células quanto para genes, ele pode destacar características especiais em vez de apenas as compartilhadas. Em conjuntos de dados cerebrais que incluíam humano, camundongo, lagarto e tartaruga, o CAMEX integrou os dados e, quando orientado por rótulos humanos, anotou com precisão tipos celulares nas outras espécies, mesmo subgrupos pequenos como pericitos cerebrais na tartaruga. Aplicando o método a um mapa detalhado do córtex pré-frontal dorsolateral de primatas, os autores conseguiram isolar subtipos específicos de microglia — células imunes do cérebro — que estão presentes apenas em humanos ou compartilhadas com chimpanzés. Ao agrupar as embeddings gênicas, também encontraram grupos de genes ligados a funções chave: por exemplo, módulos ativos em células de suporte somáticas no testículo e outros associados à meiose, o processo de divisão celular que produz espermatozoides. Esses resultados apontam tanto para programas conservados quanto para ajustes específicos de espécie no comportamento celular.
O que isso significa para o panorama maior
Em termos simples, o CAMEX é um poderoso novo “motor de tradução” para dados de célula única ao longo da árvore da vida. Ele ajuda cientistas a ver quando células de diferentes animais estão fazendo essencialmente o mesmo trabalho, quando divergiram e como as linhas do tempo do desenvolvimento se comparam entre espécies. Embora o método ainda tenha limitações — como depender de mapas de homologia existentes e os desafios gerais de interpretar modelos baseados em grafos — ele já possibilita comparações evolutivas mais ricas do que eram antes. Com o tempo, ferramentas como o CAMEX poderão ajudar a construir uma verdadeira árvore da vida de tipos celulares, afinar nossos modelos de desenvolvimento de órgãos e orientar a busca por tipos celulares e alvos terapêuticos relevantes para doenças em humanos e em modelos animais.
Citação: Guo, ZH., Huang, DS. & Zhang, S. Multi-species integration, alignment and annotation of single-cell RNA-seq data with CAMEX. Nat Commun 17, 3017 (2026). https://doi.org/10.1038/s41467-026-69696-3
Palavras-chave: sequenciamento de RNA de célula única, integração entre espécies, redes neurais em grafos, evolução de tipos celulares, genômica comparativa